Clear Sky Science · pt
Plataforma de triagem virtual orientada por IA identifica novos candidatos a inibidores de NSUN2 para terapia direcionada contra o câncer: uma abordagem computacional de descoberta de fármacos
Novas maneiras de superar cânceres resistentes
Muitos cânceres se tornam letais não apenas porque surgem, mas porque aprendem a escapar dos nossos melhores medicamentos. Este estudo explora uma abordagem promissora para desligar um ajudante chave do crescimento tumoral, usando inteligência artificial para vasculhar mais de cem milhões de potenciais remédios em computador antes de qualquer mistura em um tubo de ensaio real.
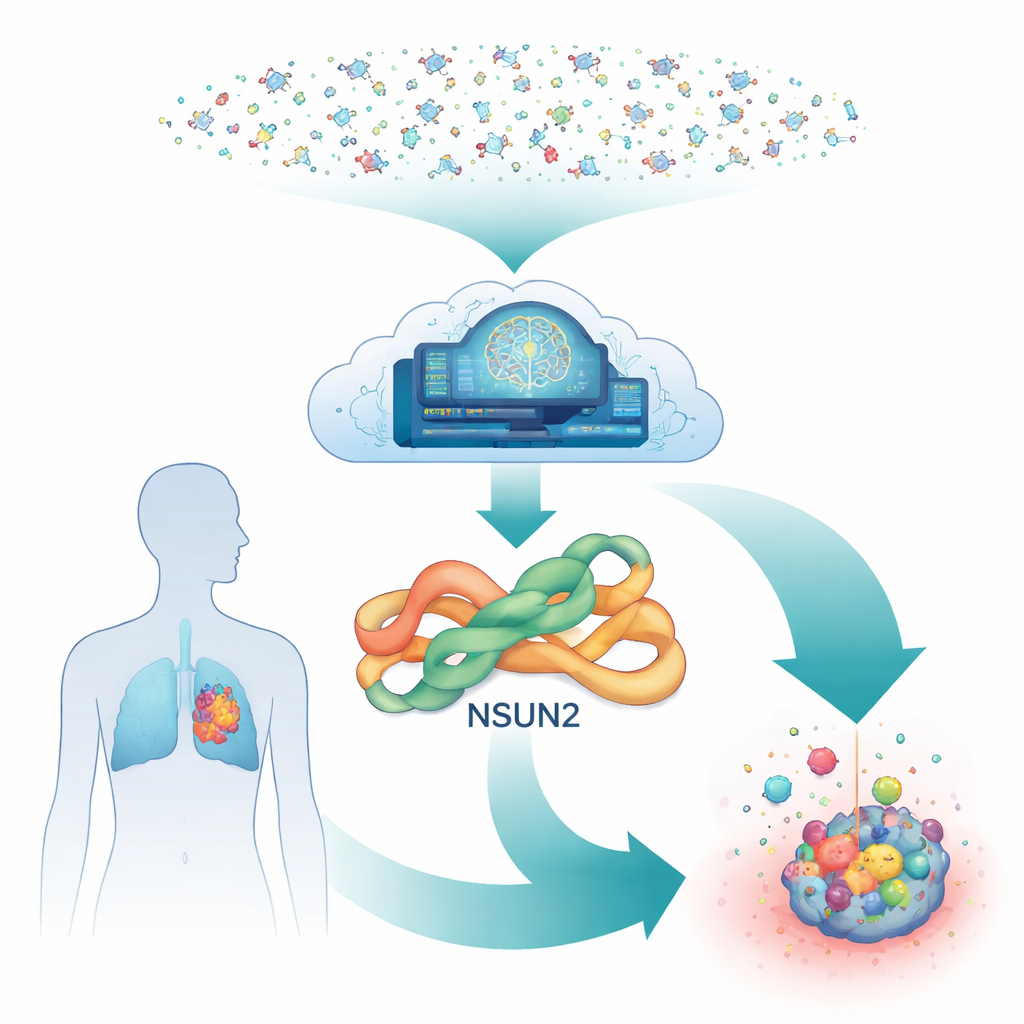
Um interruptor oculto dentro das células cancerosas
No interior de nossas células, uma enzima chamada NSUN2 atua como um marcador químico do RNA, a molécula que ajuda a transformar genes em proteínas. Ao adicionar pequenas marcas químicas ao RNA, a NSUN2 pode tornar mensagens relacionadas ao crescimento mais estáveis e mais fáceis de ler. Muitos tumores — incluindo cânceres de pulmão, estômago, pâncreas e mama — aumentam os níveis de NSUN2, o que impulsiona sua capacidade de se dividir, disseminar e resistir a medicamentos direcionados. Ainda assim, apesar de sua importância, existem pouquíssimos candidatos a fármaco que possam reduzir a atividade da NSUN2 com segurança, especialmente compostos reversíveis que não danifiquem permanentemente a enzima.
Deixando a IA vasculhar um mar de moléculas
A descoberta tradicional de fármacos teria dificuldade em testar milhões de moléculas contra a NSUN2 no laboratório, porque cada experimento exige misturas complexas de RNA e cofatores. Em vez disso, os pesquisadores construíram um fluxo de trabalho totalmente digital. Eles partiram de uma forma tridimensional prevista da NSUN2 humana gerada pelo AlphaFold, um sistema de IA que revolucionou a predição de estruturas. Para garantir que esse modelo fosse confiável, alinharam-no com uma enzima estreitamente relacionada cuja estrutura é conhecida por estudos de raio X. O bolso crítico onde a NSUN2 se liga ao seu cofator natural mostrou-se fortemente conservado, dando à equipe confiança de que o encaixe virtual de potenciais fármacos nesse sítio seria significativo.
De centenas de milhões a um punhado
Com o sítio alvo definido, a equipe recorreu a um vasto banco de dados público de moléculas compráveis. Primeiro, acoplaram um conjunto de treinamento de compostos no bolso da NSUN2 e usaram as pontuações resultantes para ensinar um modelo de aprendizado de máquina quais formas eram mais promissoras. Esse modelo então triou rapidamente cerca de 350 milhões de moléculas e sinalizou aproximadamente 101 milhões como prováveis “hits”. Para reduzir ainda mais o campo, a fração superior foi redockada com cálculos mais refinados, e apenas as melhores 12.000, com forte afinidade prevista, foram mantidas. Estas passaram então por uma bateria de checagens computacionais de segurança que estimaram como o corpo poderia absorver, distribuir, degradar e tolerar cada candidato. Após esses filtros, restaram apenas 34 moléculas que pareciam ao mesmo tempo potentes e com propriedades adequadas a fármacos.
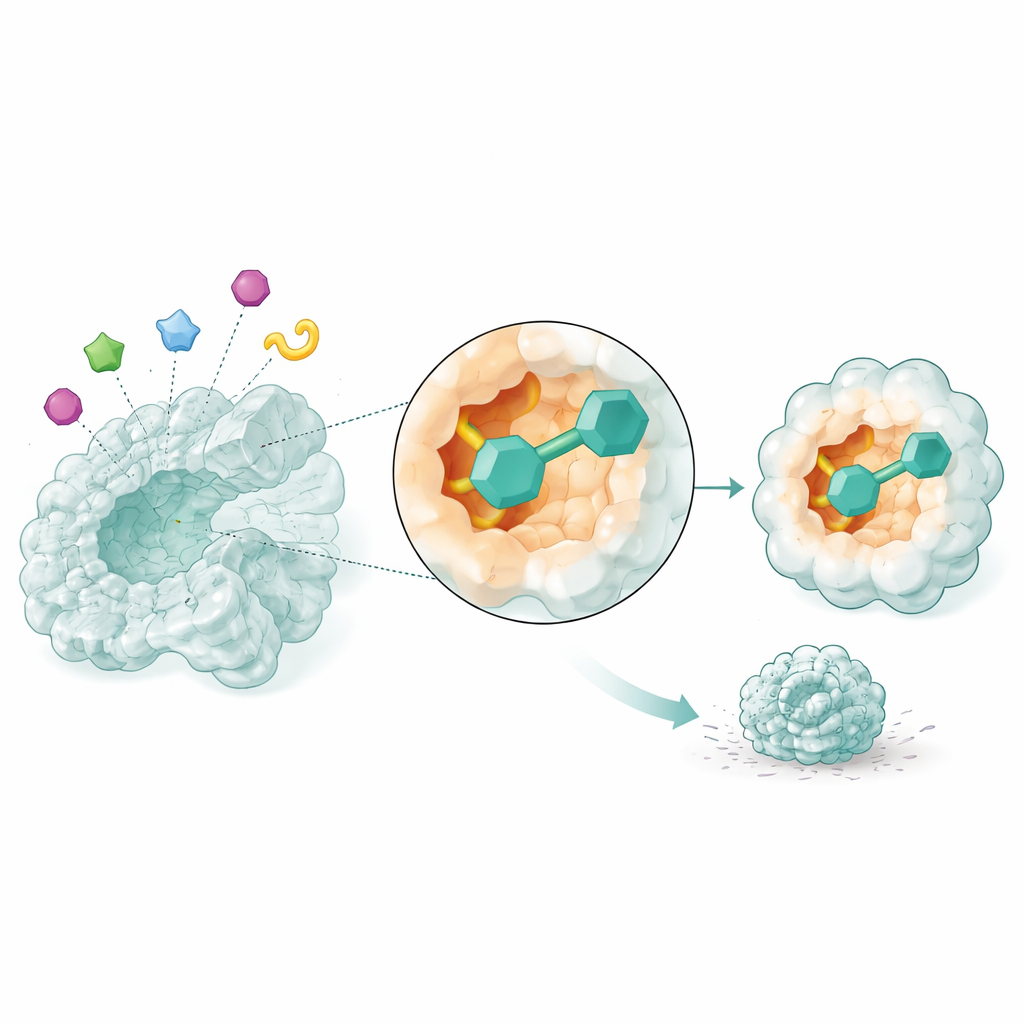
Observando candidatos a fármacos em movimento
Instantâneos estáticos não são suficientes para saber se um fármaco realmente permanecerá ligado ao seu alvo. Os pesquisadores, portanto, usaram simulações de dinâmica molecular, que modelam como os átomos se movem ao longo do tempo, para observar os três candidatos mais promissores interagindo com a NSUN2 durante 50 bilionésimos de segundo. Dois compostos, identificados apenas por seus códigos de banco de dados, formaram complexos especialmente estáveis: a estrutura enzimática permaneceu compacta, suas regiões chave se mantiveram firmes em vez de flácidas, e as pequenas moléculas conservaram um ajuste apertado dentro do bolso enquanto estabeleciam contatos persistentes. Essas simulações sugerem que os dois compostos poderiam bloquear de forma confiável a atividade da NSUN2 em células reais.
O que isso pode significar para tratamentos futuros
Embora todos os resultados deste trabalho provenham de cálculos e ainda precisem ser comprovados em laboratório, o estudo entrega uma lista curta de pontos de partida realistas para novos fármacos que bloqueiem a NSUN2. Porque a NSUN2 ajuda células cancerosas a estabilizar sinais de crescimento e sobrevivência, tais medicamentos poderiam enfraquecer tumores e potencialmente ressensibilizá‑los a terapias direcionadas existentes, particularmente em cânceres de pulmão que se tornaram resistentes. Igualmente importante, o estudo demonstra uma receita geral para usar IA e modelagem baseada em física para explorar espaços químicos imensos de forma rápida e econômica, oferecendo um atalho poderoso rumo à próxima geração de tratamentos oncológicos de precisão.
Citação: Yu, S., Peng, Q., Wei, W. et al. AI-driven virtual screening platform identifies novel NSUN2 inhibitor candidates for targeted cancer therapy: a computational drug discovery approach. npj Precis. Onc. 10, 98 (2026). https://doi.org/10.1038/s41698-026-01296-2
Palavras-chave: NSUN2, epitranscriptômica, triagem virtual por IA, descoberta de fármacos contra o câncer, metilação de RNA