Clear Sky Science · pt
Avaliação de metagenômica de leituras longas para diagnóstico de infecções na corrente sanguínea: um estudo piloto em um hospital terciário na Tailândia
Por que testes mais rápidos para infecções sanguíneas importam
Quando bactérias invadem a corrente sanguínea, cada hora conta. Os médicos precisam escolher rapidamente o antibiótico correto, mas os exames de laboratório atuais podem levar vários dias para identificar o agente e determinar quais medicamentos provavelmente falharão. Este estudo de um grande hospital tailandês explora uma nova forma de acelerar o processo lendo o material genético de todos os micróbios em uma amostra de sangue de uma só vez, usando um sequenciador de DNA portátil. O objetivo é passar de esperar dias por respostas para obter um quadro detalhado da infecção dentro de um único turno de trabalho.
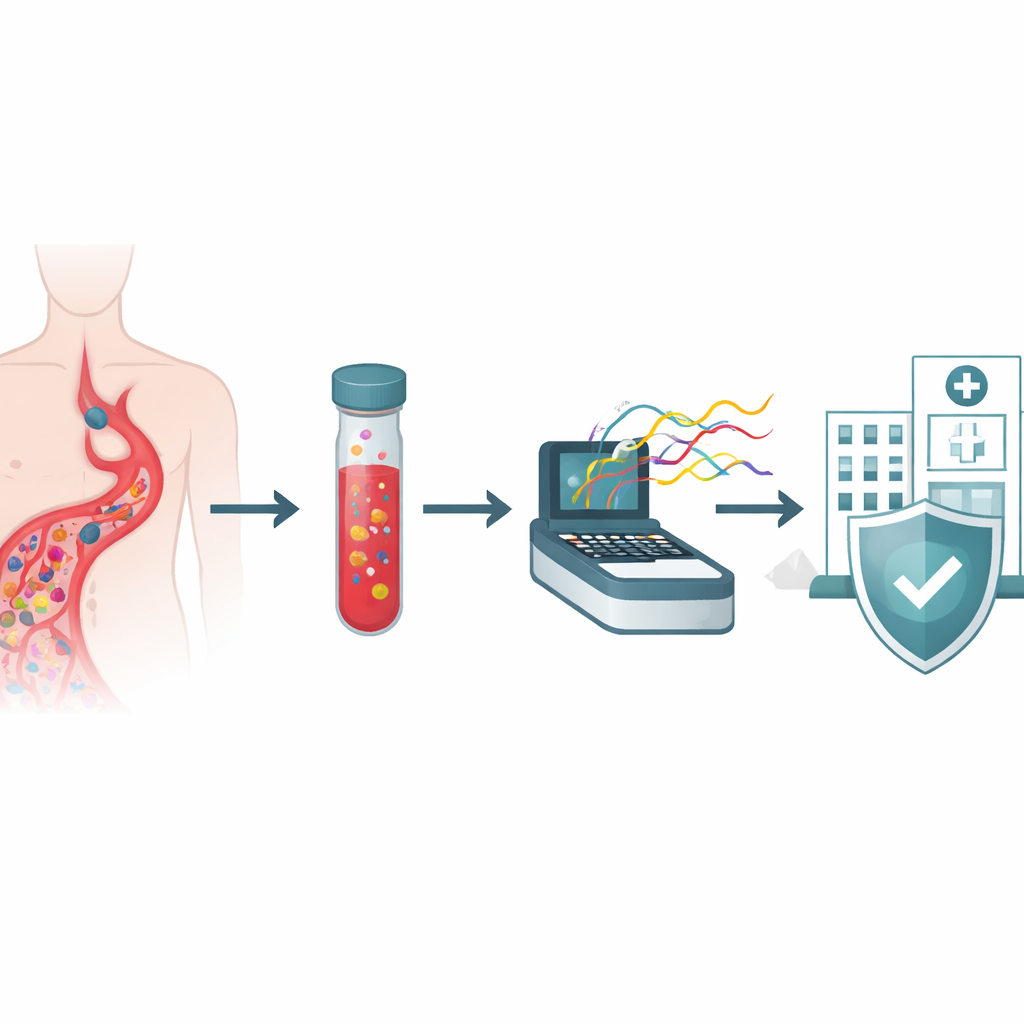
Uma nova maneira de ler os germes no sangue
Os pesquisadores concentraram-se em pacientes que já apresentavam sinais de crescimento bacteriano em frascos de hemocultura padrão, que são usados rotineiramente em hospitais no mundo todo. Em vez de cultivar cada bactéria em placas separadas e executar uma série de testes químicos, eles retiraram líquido diretamente de 40 frascos de cultura positivos e extraíram todo o DNA microbiano. Esse DNA foi então processado em um sequenciador Oxford Nanopore, um dispositivo que puxa longas fitas de material genético por poros minúsculos e lê sua sequência em tempo real. Como o método não depende do cultivo separado de cada organismo, ele pode, em princípio, detectar várias espécies, seus traços de resistência aos medicamentos e suas ferramentas de virulência em um único fluxo de trabalho simplificado.
O que foi encontrado nas infecções sanguíneas na Tailândia
Os testes convencionais das mesmas 40 amostras produziram 45 isolados bacterianos, refletindo que alguns pacientes estavam infectados por mais de uma espécie. O sistema rotineiro do hospital, VITEK, mostrou que duas bactérias intestinais familiares, Escherichia coli e Klebsiella pneumoniae, causaram quase 40% dessas infecções, e que muitas dessas cepas eram resistentes a múltiplos medicamentos. A abordagem por nanopore concordou em grande parte com esse retrato, identificando 43 genomas bacterianos distintos e confirmando que membros do grupo Enterobacterales dominaram. Também detectou algumas espécies incomuns ou mal classificadas, como uma bactéria ambiental chamada Ralstonia mannitolilytica e o micro-organismo gástrico Campylobacter jejuni, que métodos rotineiros haviam perdido ou identificado apenas de forma geral. Em algumas infecções mistas, no entanto, o sequenciamento teve dificuldade em separar completamente micróbios intimamente relacionados quando um estava presente em níveis muito inferiores ao outro.
Explorando resistência e estratégias de camuflagem
Como o novo método lê longos trechos de DNA, ele pode fazer mais do que apenas nomear as bactérias: pode revelar a maquinaria genética que as ajuda a resistir a antibióticos e causar doenças. A equipe vasculhou os genomas em busca de genes de resistência conhecidos e de genes de "virulência" que ajudam os germes a aderir a tecidos, formar biofilmes protetores, roubar ferro ou produzir toxinas. E. coli e K. pneumoniae carregavam muitos desses genes, incluindo aqueles que neutralizam famílias de antibióticos importantes, como beta-lactâmicos e aminoglicosídeos. O sequenciamento também destacou pacotes de resistência potentes em espécies adaptadas a ambientes hospitalares, como Acinetobacter baumannii e Pseudomonas aeruginosa, cujos genomas eram ricos em sistemas de bombeamento de drogas e outras defesas. Ao mesmo tempo, algumas bactérias menos comuns na corrente sanguínea mostraram arsenais relativamente modestos, sugerindo uma ameaça menor, embora ainda relevante. 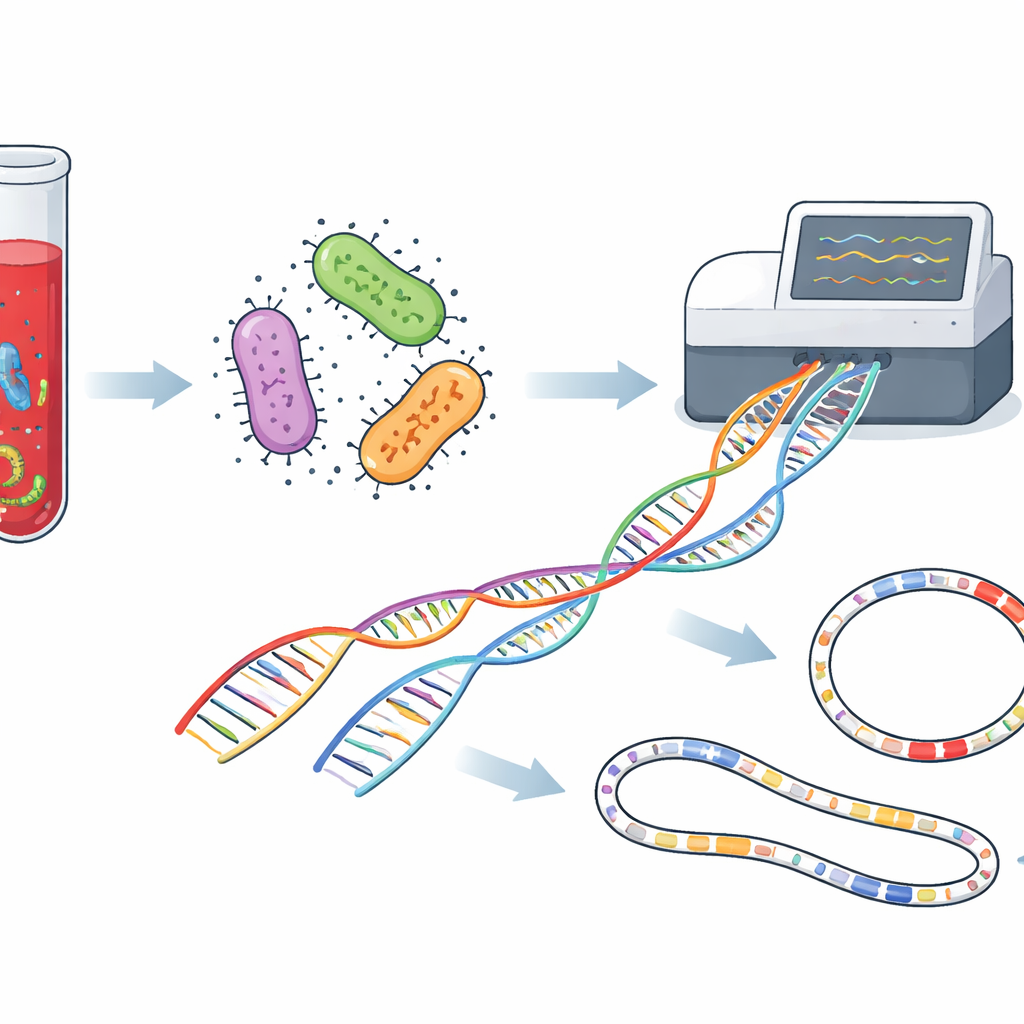
Seguindo a resistência em DNA móvel
Outra vantagem do sequenciamento de leituras longas é sua capacidade de montar cromossomos bacterianos inteiros junto com moléculas de DNA circulares chamadas plasmídeos, que podem saltar entre bactérias e disseminar genes de resistência. Neste estudo, os pesquisadores catalogaram dezenas de tipos de plasmídeos. Alguns estavam fortemente associados a espécies específicas, enquanto outros eram compartilhados entre vários tipos de bactérias, sugerindo intercâmbio gênico em curso no ambiente hospitalar. Muitos carregavam elementos conhecidos por causarem falhas no tratamento, como betalactamases de espectro estendido e carbapenemases — enzimas que inativam alguns dos antibióticos mais importantes. Mapear esses elementos móveis ajuda as equipes de controle de infecções a entender como características perigosas se movem por um hospital ao longo do tempo.
Acelerando respostas para médicos e hospitais
O tempo é onde a nova abordagem mostra a vantagem mais clara. Fluxos de trabalho padrão costumam levar de cinco a sete dias desde o momento em que uma hemocultura fica positiva até o ponto em que a identificação completa e os resultados de sensibilidade a antimicrobianos estão prontos. Em contraste, a configuração por nanopore neste estudo piloto entregou identificações iniciais de espécies dentro de duas a quatro horas após o início da corrida e sinalizou genes-chave de resistência dentro de seis a oito horas. Embora corridas de sequenciamento mais longas tenham melhorado a completude dos genomas, elas não alteraram as principais conclusões clínicas. Embora este tenha sido um estudo pequeno e inicial que ainda não vinculou resultados a desfechos dos pacientes ou analisou custos, ele sugere que integrar o sequenciamento metagenômico de leituras longas em laboratórios hospitalares poderia fornecer informações mais rápidas e mais ricas para orientar o tratamento, apoiar o uso responsável de antibióticos e fortalecer o monitoramento regional de infecções resistentes a medicamentos.
O que isso significa para o cuidado ao paciente
Para o público em geral, a mensagem é que os médicos podem em breve ter um "instantâneo" genético de uma infecção na corrente sanguínea no mesmo dia em que uma cultura fica positiva, em vez de esperar quase uma semana. Esse instantâneo não apenas identifica o germe, mas também destaca muitas de suas vulnerabilidades e seu potencial de disseminar resistência para outros. Embora sejam necessários mais estudos com grupos maiores de pacientes, controles de contaminação mais rigorosos e análises de custo, este estudo piloto tailandês mostra que sequenciadores de DNA de bolso podem nos aproximar de um atendimento rápido e informado pelo genoma para infecções sanguíneas potencialmente fatais.
Citação: Yaikhan, T., Wongsurawat, T., Jenjaroenpan, P. et al. Evaluating long-read metagenomics for bloodstream infection diagnostics: a pilot study from a Thai Tertiary Hospital. Sci Rep 16, 9330 (2026). https://doi.org/10.1038/s41598-026-41247-2
Palavras-chave: infecção na corrente sanguínea, resistência antimicrobiana, sequenciamento metagenômico, tecnologia nanopore, microbiologia clínica