Clear Sky Science · pt
Genômica plastidial comparativa de Hippophae revela relações filogenéticas e fornece marcadores de DNA candidatos para identificação taxonômica
Por que este arbusto resistente importa
O dente-de-leão-do-mar é um arbusto resistente que prospera onde muitas outras plantas fracassam: em encostas frias, secas e ventosas do Planalto Qinghai–Tibete e além. Suas bagas laranja brilhantes são promovidas mundialmente como “superfrutas”, e a planta é amplamente usada para estabilizar solos e recuperar áreas degradadas. Ainda assim, mesmo especialistas têm dificuldade para distinguir suas espécies e subespécies intimamente relacionadas apenas pela aparência. Este estudo faz uma pergunta simples, porém importante: é possível ler o manual de instruções interno da planta — seu DNA — para separar quem é quem e, no processo, oferecer a criadores e conservacionistas uma nova ferramenta poderosa para manejar esse recurso valioso?
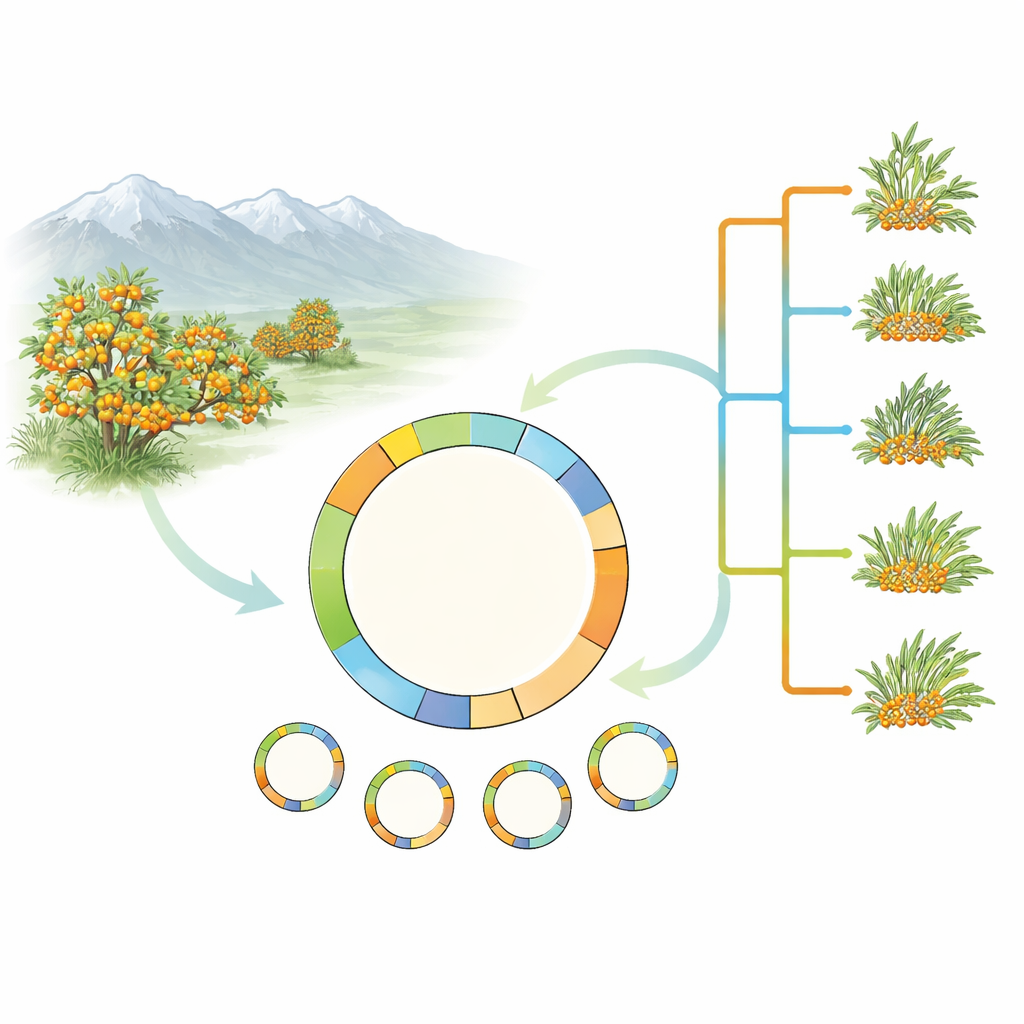
Olhando dentro dos motores verdes da planta
Em vez de enfrentar toda a complexidade do genoma do dente-de-leão-do-mar, os pesquisadores concentraram-se nos plastídios da planta — minúsculos compartimentos verdes dentro das células que realizam a fotossíntese. Os plastídios têm sua própria pequena molécula de DNA circular, herdada majoritariamente pela mãe, que se mostrou extremamente útil para traçar árvores genealógicas de plantas. A equipe coletou e sequenciou genomas plastidiais completos de 17 amostras cobrindo cinco espécies de dente-de-leão-do-mar e várias formas do amplamente distribuído Hippophae rhamnoides. Eles também adicionaram um genoma plastidial recém-assemblado de um tipo cultivado importante, H. rhamnoides subsp. mongolica cv. Prevoskhodnaya, e verificaram cuidadosamente entradas anteriores em bancos de dados em busca de erros.
Um plano compartilhado com diferenças reveladoras
À primeira vista, o DNA plastidial de todas as amostras de dente-de-leão-do-mar parecia notavelmente semelhante. Cada genoma tinha cerca de 155.000 a 156.000 “letras” e seguia o mesmo arranjo em quatro partes encontrado em muitas plantas com flores: duas regiões de cópia única separadas por um par de segmentos duplicados. O mesmo conjunto de genes estava presente e disposto na mesma ordem, e até o equilíbrio geral das quatro letras do DNA variava muito pouco. Essa estabilidade estrutural sugere que, ao longo do tempo evolutivo, o plano plastidial em Hippophae foi conservado. No entanto, quando os pesquisadores ampliaram para detalhes mais finos — como a frequência com que certos “códons” do DNA são usados para soletrar o mesmo aminoácido — eles encontraram padrões sutis específicos de linhagens, indicando uma modelagem lenta e de longo prazo do código em diferentes ramos do gênero.
Desembaraçando a árvore familiar
Usando 78 genes codificadores de proteínas do DNA plastidial, a equipe construiu árvores evolutivas que posicionam o dente-de-leão-do-mar na família mais ampla das rosáceas e então aproximam as relações dentro de Hippophae. As análises confirmaram que o dente-de-leão-do-mar, como grupo, forma uma linhagem natural única, e que H. rhamnoides e suas subespécies também estão fortemente agrupadas. Intrigantemente, uma espécie, H. tibetana, cai consistentemente dentro do grupo de H. rhamnoides na árvore plastidial, embora trabalhos anteriores com DNA nuclear a tenham colocado mais próxima da base do gênero. Esse desacordo entre histórias nucleares e plastidiais sugere hibridização passada ou outros eventos evolutivos complexos e aponta para a necessidade de estudos futuros que combinem conjuntos completos de dados nucleares e plastidiais.
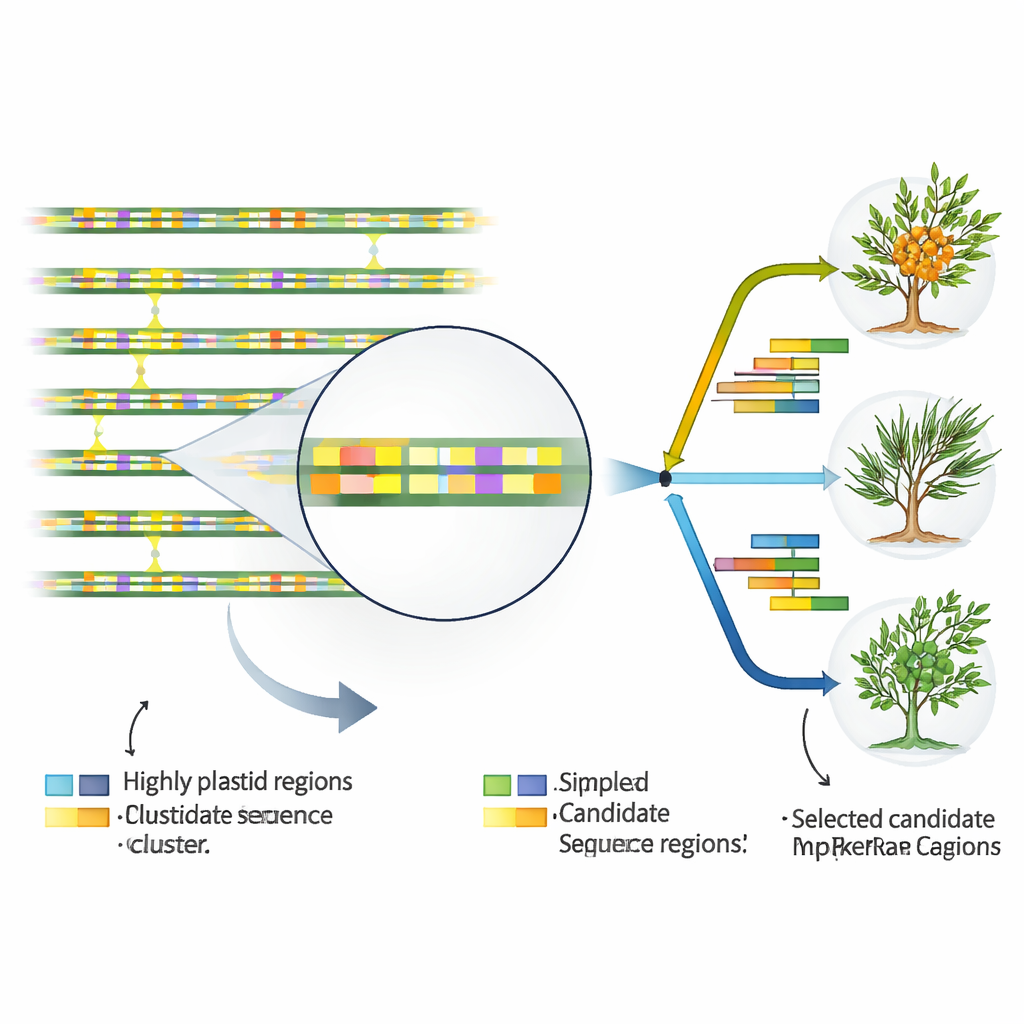
Encontrando os pontos quentes genômicos que marcam identidade
Para transformar o DNA plastidial em ferramentas práticas para taxonomistas e melhoristas, os autores buscaram trechos de sequência que mudam mais rapidamente que o restante. Comparando todos os 17 genomas plastidiais, eles identificaram 46 regiões especialmente variáveis, quase todas situadas entre genes ou dentro de íntrons não codificantes, em vez de nos corpos gênicos propriamente ditos. Também mapearam dezenas de pequenos motivos repetidos conhecidos como repetições de sequência simples, que são particularmente ricos nas letras A e T e se concentram em regiões não codificantes. Algumas dessas repetições e segmentos variáveis mostraram diferenças claras entre espécies e até entre subespécies de H. rhamnoides. Algumas regiões destacaram-se como pontos quentes tanto em comparações ao nível de espécie quanto de subespécie, tornando-as candidatas principais a marcadores de DNA práticos que podem ser alvo de testes laboratoriais simples.
De padrões de DNA a usos no mundo real
Ao mapear tanto a estrutura estável quanto as pequenas, porém informativas, diferenças nos genomas plastidiais do dente-de-leão-do-mar, este estudo entrega uma caixa de ferramentas para identificação confiável baseada em DNA. As regiões de marcadores propostas poderiam ajudar a distinguir espécies de aparência semelhante, verificar a origem de produtos comerciais de bagas, proteger a diversidade genética selvagem e orientar a seleção de progenitores em programas de melhoramento voltados para nutrição, medicina e restauração de terras. Em termos simples, os autores mostram que um manual de instruções cloroplastidial cuidadosamente lido pode revelar quem é quem na família ampliada deste arbusto resistente, abrindo caminho para uma conservação mais inteligente e um uso mais direcionado de uma das culturas de frutos mais resistentes do mundo.
Citação: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
Palavras-chave: dente-de-leão-do-mar, genoma plastidial, marcadores de DNA, taxonomia vegetal, diversidade genética