Clear Sky Science · pt
Primeira visão das características e previsão da resistência medicamentosa de Mycobacterium tuberculosis por sequenciamento do genoma completo na Província de Fujian, China
Por que este estudo importa para a saúde do dia a dia
A tuberculose (TB) é uma doença pulmonar antiga que ainda infecta milhões de pessoas a cada ano. A maior ameaça moderna não é apenas a TB em si, mas os germes da TB que conseguem escapar dos nossos melhores medicamentos. Este estudo da província de Fujian, no sudeste da China, faz uma pergunta simples, porém crucial: ler o código genético completo dos bacilos da TB pode ajudar os médicos a identificar rapidamente quais medicamentos vão funcionar, muito antes de os testes tradicionais terminarem? A resposta pode moldar como os países protegem pacientes e comunidades contra formas difíceis de tratar da TB.
Testes antigos são lentos, mas o tempo corre
Para escolher o tratamento certo, os médicos precisam saber a quais antibióticos a cepa de TB do paciente é resistente. O método tradicional é cultivar a bactéria no laboratório com e sem medicamentos e ver quais impedem o crescimento. Embora confiável, esse processo pode levar até dois meses, período em que os pacientes podem receber tratamento incompleto e continuar a espalhar germes resistentes. Em Fujian, onde a TB continua sendo um problema sério de saúde pública, a taxa geral de resistência medicamentosa foi estimada anteriormente em cerca de um em cada cinco casos de TB. Autoridades de saúde precisam, portanto, de uma forma mais rápida de combinar pacientes aos medicamentos corretos e de monitorar como as cepas resistentes estão se espalhando.
Lendo o manual de instruções do germe da TB
Neste estudo, os pesquisadores analisaram 150 amostras de TB coletadas de pacientes em Fujian entre 2021 e 2022. Para cada amostra, usaram tanto o teste clássico baseado em crescimento quanto um método mais novo chamado sequenciamento do genoma completo. Em vez de observar como os germes se comportam em diferentes medicamentos, o sequenciamento do genoma lê cada letra do DNA da bactéria, revelando mudanças minúsculas — mutações — que são conhecidas por tornar medicamentos específicos menos eficazes. Ao comparar essas pistas genéticas com os resultados laboratoriais tradicionais, a equipe pôde avaliar o quanto os dados de DNA isoladamente conseguem prever a quais medicamentos uma dada cepa de TB é resistente.
Quais famílias de TB estão se espalhando e quão resistentes elas são?
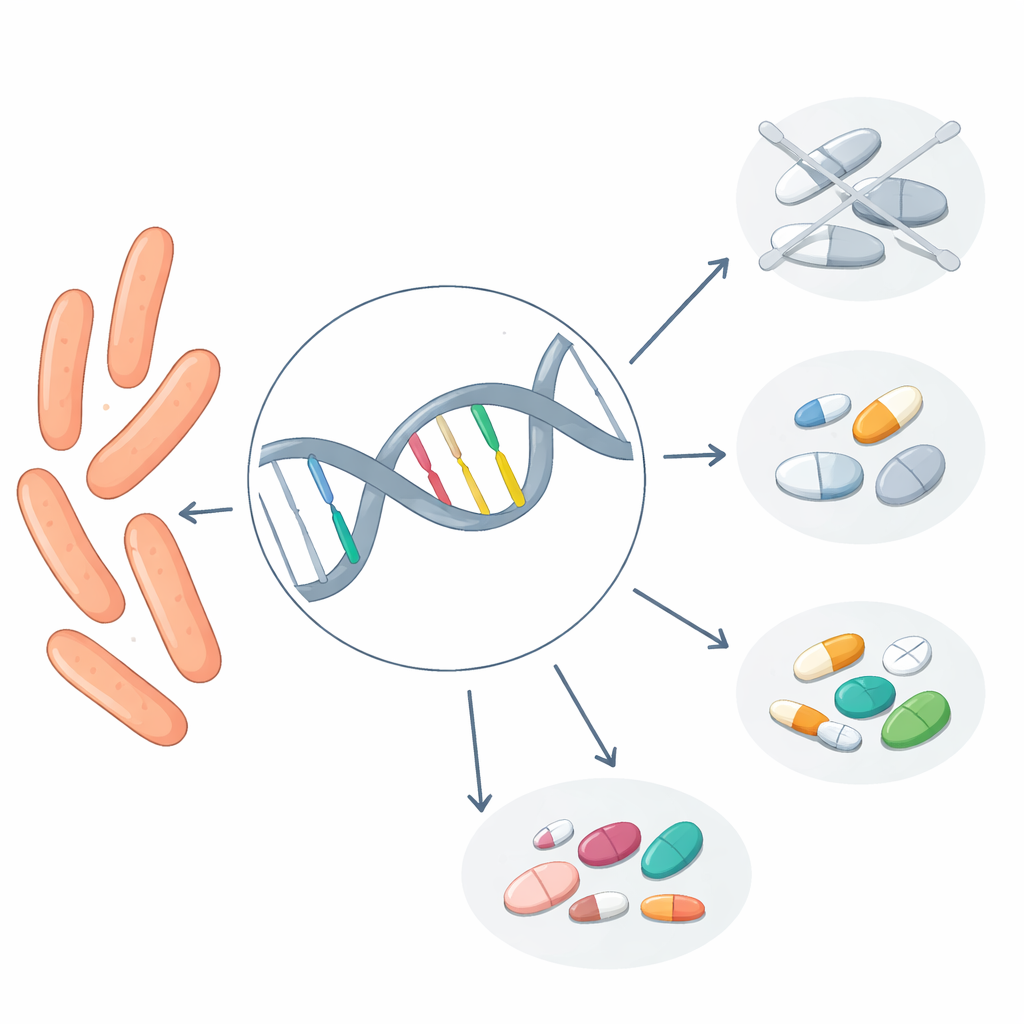
Os dados genéticos também permitiram que a equipe colocasse cada cepa de TB em uma espécie de árvore genealógica. Em Fujian, duas famílias principais dominaram: uma conhecida como Linhagem 2 e outra como Linhagem 4. Juntas, elas compuseram quase todas as amostras. Curiosamente, a resistência medicamentosa era comum, mas distribuída por essas famílias em vez de estar ligada a apenas um ramo. Mais de dois terços das cepas carregavam pelo menos uma mutação associada à resistência. Certas alterações genéticas reapareciam repetidamente, cada uma associada a um medicamento específico. Por exemplo, uma mutação estava frequentemente ligada à resistência à isoniazida, um pilar do tratamento da TB, enquanto outra estava fortemente associada à resistência à rifampicina, um componente central do tratamento padrão. Padrões semelhantes foram observados para outros medicamentos, como fluoroquinolonas e etambutol.
Quão bem a previsão pelo DNA corresponde aos resultados do mundo real?
O teste crucial foi verificar se essas pistas genéticas correspondiam ao que os testes mais lentos baseados em crescimento mostraram. Para três dos medicamentos mais importantes — isoniazida, rifampicina e um grupo chamado fluoroquinolonas — a concordância foi forte. O sequenciamento identificou corretamente cepas resistentes em cerca de três em cada quatro casos e quase nunca classificou equivocadamente uma cepa realmente sensível como resistente. Em outras palavras, quando o DNA indicava que uma cepa deveria ser sensível, geralmente ela era. Para dois medicamentos mais antigos, estreptomicina e etambutol, as previsões genéticas foram menos confiáveis, provavelmente porque os cientistas ainda não conhecem todas as mutações que causam resistência. O método também teve dificuldade em avaliar resistência a vários medicamentos de segunda linha simplesmente porque muito poucas cepas neste estudo eram resistentes a esses fármacos.
O que isso significa para pacientes e saúde pública
Para pessoas com TB e os profissionais de saúde que cuidam delas, a conclusão é alentadora. Esta pesquisa mostra que um único teste de DNA pode revelar rapidamente tanto a linhagem de uma cepa de TB quanto, para vários medicamentos-chave, se essa cepa provavelmente será resistente ao tratamento. Embora os testes tradicionais baseados em cultivo ainda sejam necessários, especialmente para alguns medicamentos, o sequenciamento do genoma completo pode dar aos médicos uma visão inicial e relativamente precisa de quais medicamentos têm maior probabilidade de funcionar. Em lugares como Fujian, e potencialmente ao redor do mundo, combinar essas abordagens pode levar a tratamentos mais rápidos e precisos, menos oportunidades para a doença se espalhar e uma defesa mais forte contra o aumento da TB resistente a medicamentos.
Citação: Wei, S., Zhao, Y., Lin, J. et al. First insight of characteristics and prediction of Mycobacterium tuberculosis drug resistance by whole genome sequencing in Fujian Province, China. Sci Rep 16, 9266 (2026). https://doi.org/10.1038/s41598-026-40398-6
Palavras-chave: tuberculose, resistência a medicamentos, sequenciamento do genoma completo, Fujian China, vigilância de doenças infecciosas