Clear Sky Science · pt
Integração de análise multiômica identifica o gene relacionado ao dano no DNA CLSPN como um biomarcador no câncer gástrico
Por que esta pesquisa importa
O câncer de estômago continua sendo um dos cânceres mais letais do mundo, em grande parte porque costuma ser detectado tardiamente e carece de sinais precoces confiáveis. Este estudo examina em profundidade as “marcas” deixadas quando o DNA é danificado e identifica um gene chamado CLSPN como um marcador promissor que pode ajudar médicos a detectar o câncer gástrico mais cedo, entender sua agressividade e potencialmente ajustar tratamentos com maior precisão.
Procurando sinais de perigo em tumores estomacais
Os pesquisadores partiram de uma ideia simples: se o dano ao DNA contribui para o câncer de estômago, então genes envolvidos em lidar com esse dano podem conter pistas importantes sobre quem adoece e como a doença se comporta. Para testar isso, reuniram vários conjuntos de dados grandes. Isso incluiu RNA-seq em conjunto (bulk), que mede a atividade média dos genes em amostras tumorais inteiras; RNA-seq de célula única, que analisa milhares de células individuais uma a uma; e transcriptômica espacial, que mapeia a atividade gênica de volta ao corte tecidual. Também compilaram uma longa lista de genes já associados ao dano no DNA. Usando esses recursos, investigaram quais genes relacionados ao dano do DNA estavam mais fortemente ligados ao câncer gástrico e à sobrevida dos pacientes.
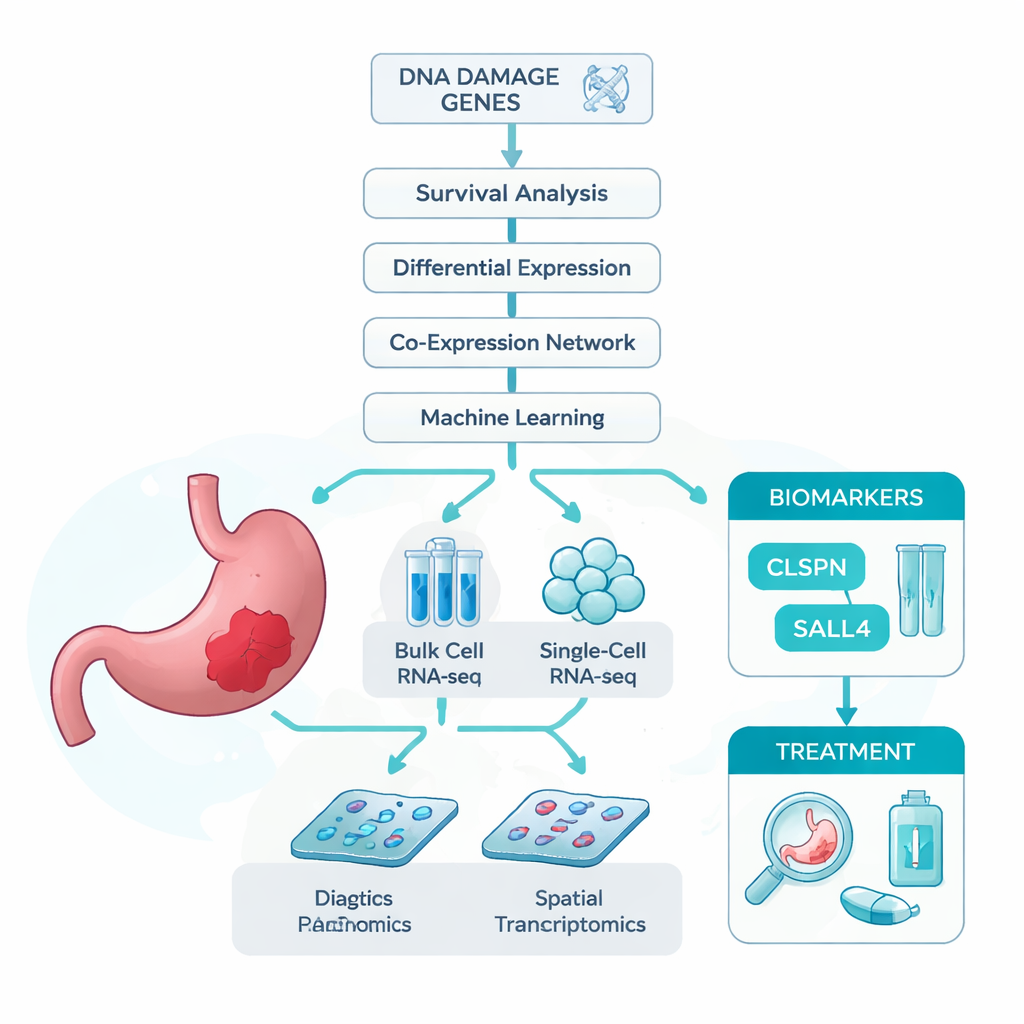
Usando algoritmos inteligentes para encontrar genes-chave
Como milhares de genes mudam no câncer, a equipe recorreu a um conjunto de ferramentas estatísticas e de aprendizado de máquina para reduzir o campo. Primeiro filtraram genes que estavam tanto desregulados nos tumores quanto claramente relacionados ao tempo de sobrevida dos pacientes. Em seguida agruparam genes com padrões de coexpressão e cruzaram isso com a lista de genes de dano ao DNA. Essa triagem em várias etapas produziu 13 genes candidatos fortes. Para ver quais desses eram mais úteis para distinguir tumor de tecido normal, treinaram sete modelos diferentes de aprendizado de máquina, cada um classificando os genes pela sua utilidade na classificação. Em todos os modelos, dois genes — CLSPN e SALL4 — se destacaram consistentemente, com acurácias próximas ou superiores a 97% e áreas sob a curva ROC acima de 0,96, sugerindo que esses genes têm excelente potencial diagnóstico.
Focando no CLSPN dentro do tumor
Entre os dois genes líderes, o CLSPN destacou-se como o mais informativo no geral, então os autores o examinaram com mais detalhe. Em dados de célula única de mais de 30.000 células, o CLSPN estava muito mais ativo em células tumorais do que em células normais ou de suporte vizinhas, apontando para um papel específico no tumor. O mapeamento espacial de cortes de pacientes mostrou um padrão similar: a expressão de CLSPN se agrupava em regiões que os patologistas reconheceram como cancerosas. Quando a equipe separou as células tumorais em grupos de “CLSPN alto” e “CLSPN baixo”, o grupo com CLSPN alto apresentou atividade mais forte em vias relacionadas à replicação do DNA, divisão celular e reparo — processos que, quando hiperativos ou mal direcionados, podem impulsionar crescimento descontrolado. A análise de pseudotempo, que reconstrói como as células mudam ao longo de uma linha do tempo hipotética, sugeriu que à medida que as células tumorais progridem, os níveis de CLSPN tendem a aumentar, indicando que a regulação positiva de CLSPN pode fazer parte da transição para um estado mais maligno.
Relações com o sistema imunológico e resposta ao tratamento
O estudo também explorou como o CLSPN se relaciona com o ambiente tumoral e com potenciais terapias. Tumores com maior expressão de CLSPN mostraram diferentes misturas de células imunes, particularmente macrófagos e certos tipos de células T e NK, sugerindo que CLSPN pode ajudar a moldar um ambiente imuno-supressor. Modelagem de sensibilidade a fármacos indicou que cânceres com mais CLSPN podem ser mais vulneráveis a vários agentes quimioterápicos e alvos terapêuticos, já que níveis elevados de CLSPN se associaram a doses previstas menores necessárias para inibir o crescimento. Importante, quando os autores coraram amostras reais de tecido de 70 pacientes, os níveis da proteína CLSPN eram claramente mais altos no câncer do que no estômago normal e se associaram a tumores maiores, invasão mais profunda, acometimento de linfonodos e menor sobrevida global.
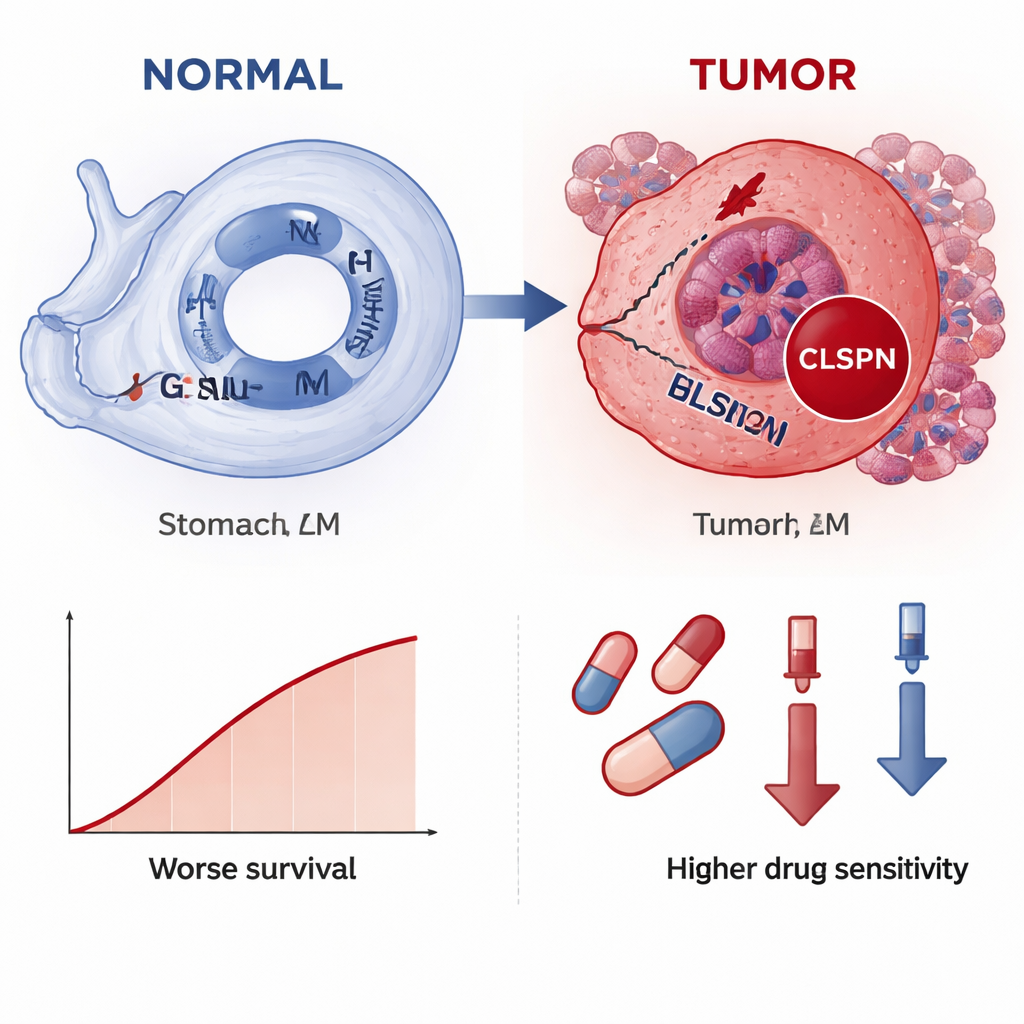
O que isso pode significar para os pacientes
Em termos práticos, o estudo sugere que o CLSPN age como um sinal de alerta para o câncer de estômago: ele se ativa principalmente em células tumorais, brilha mais em doenças mais avançadas e sinaliza maior risco de desfecho ruim. Como pode ser detectado tanto ao nível de RNA quanto por métodos de coloração padrão usados em hospitais, o CLSPN poderia tornar-se um biomarcador prático para ajudar patologistas a confirmar câncer gástrico, estratificar pacientes por risco e, talvez, orientar escolhas terapêuticas. Embora sejam necessários mais testes clínicos antes do uso rotineiro, este trabalho destaca como ler as pegadas do dano no DNA em múltiplas camadas de dados pode revelar novas ferramentas para diagnóstico mais precoce e tratamento mais personalizado do câncer gástrico.
Citação: Ma, Q., Yang, X., Sun, N. et al. Integrating multi-omics analysis identifies DNA damage-related gene CLSPN as a biomarker in gastric cancer. Sci Rep 16, 7789 (2026). https://doi.org/10.1038/s41598-026-39387-6
Palavras-chave: câncer gástrico, dano ao DNA, CLSPN, biomarcador, análise de célula única