Clear Sky Science · pt
Novos genes marcadores para detecção simultânea de Salmonella, EHEC O157:H7 e Cronobacter
Por que isso importa para a segurança alimentar cotidiana
De folhas de salada a hambúrgueres e fórmulas infantis, os alimentos em que confiamos podem, ocasionalmente, abrigar microrganismos perigosos. Três dos culpados mais preocupantes — certas cepas de E. coli, Salmonella e uma bactéria menos conhecida chamada Cronobacter — podem causar doenças graves, especialmente em crianças pequenas e adultos vulneráveis. Este estudo mostra como cientistas estão usando enormes bancos de dados de DNA e testes de laboratório inteligentes para detectar essas três ameaças de uma só vez, de forma rápida e precisa, antes que alimentos contaminados cheguem à sua mesa.
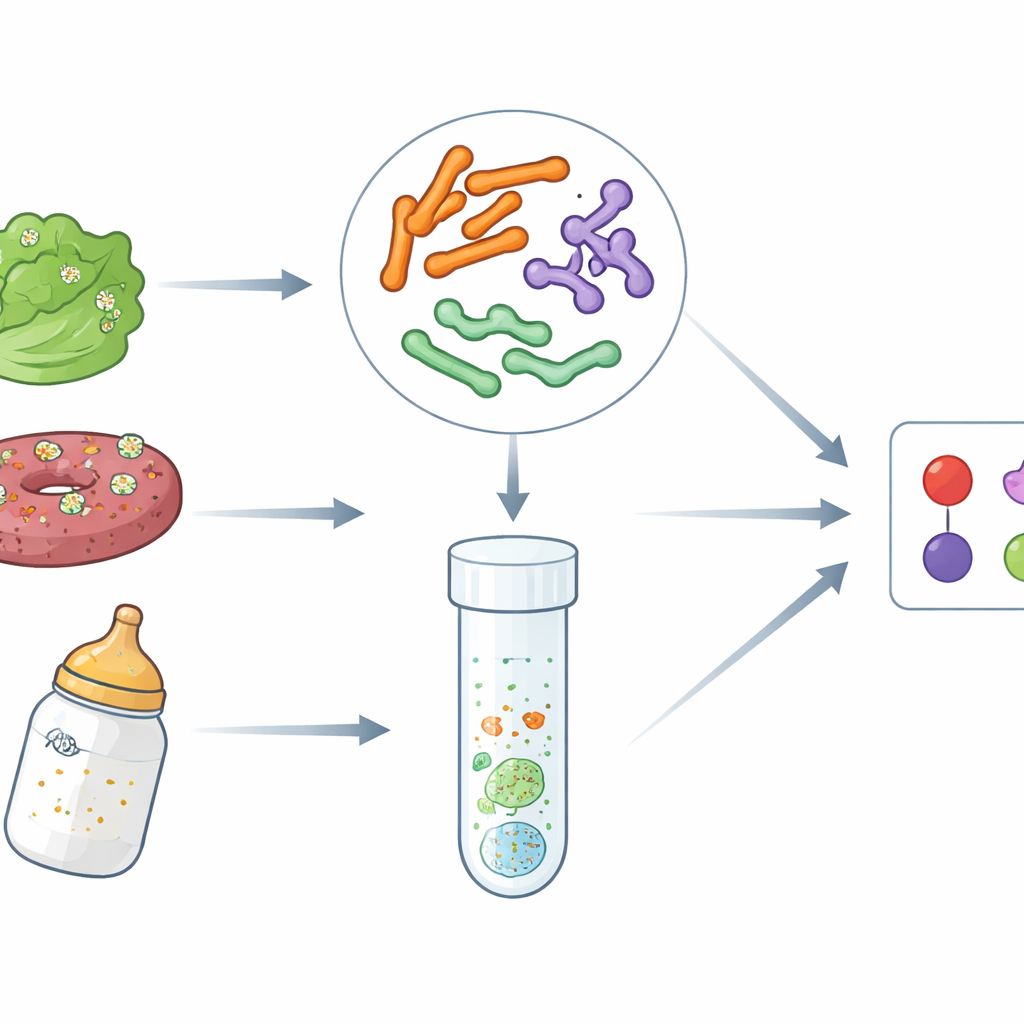
Perigos ocultos em alimentos comuns
As doenças transmitidas por alimentos aumentaram na última década, impulsionadas em parte por cadeias de abastecimento globais e pelo grande volume de alimentos processados e prontos para consumo. A EHEC O157:H7, uma forma altamente tóxica de E. coli, pode causar diarreia com sangue e insuficiência renal. A Salmonella provoca milhões de casos de intoxicação alimentar a cada ano, e a Cronobacter, embora menos conhecida, pode ser fatal para recém-nascidos, especialmente em associação com fórmula infantil em pó. Métodos laboratoriais tradicionais costumam focar em um microrganismo por vez e exigem dias de cultivo, o que atrasa investigações de surtos e triagens de rotina. Os autores propuseram desenvolver testes baseados em DNA mais rápidos que possam sinalizar esses três patógenos juntos em um único procedimento simplificado.
Encontrando “códigos de barras” em um mar de DNA
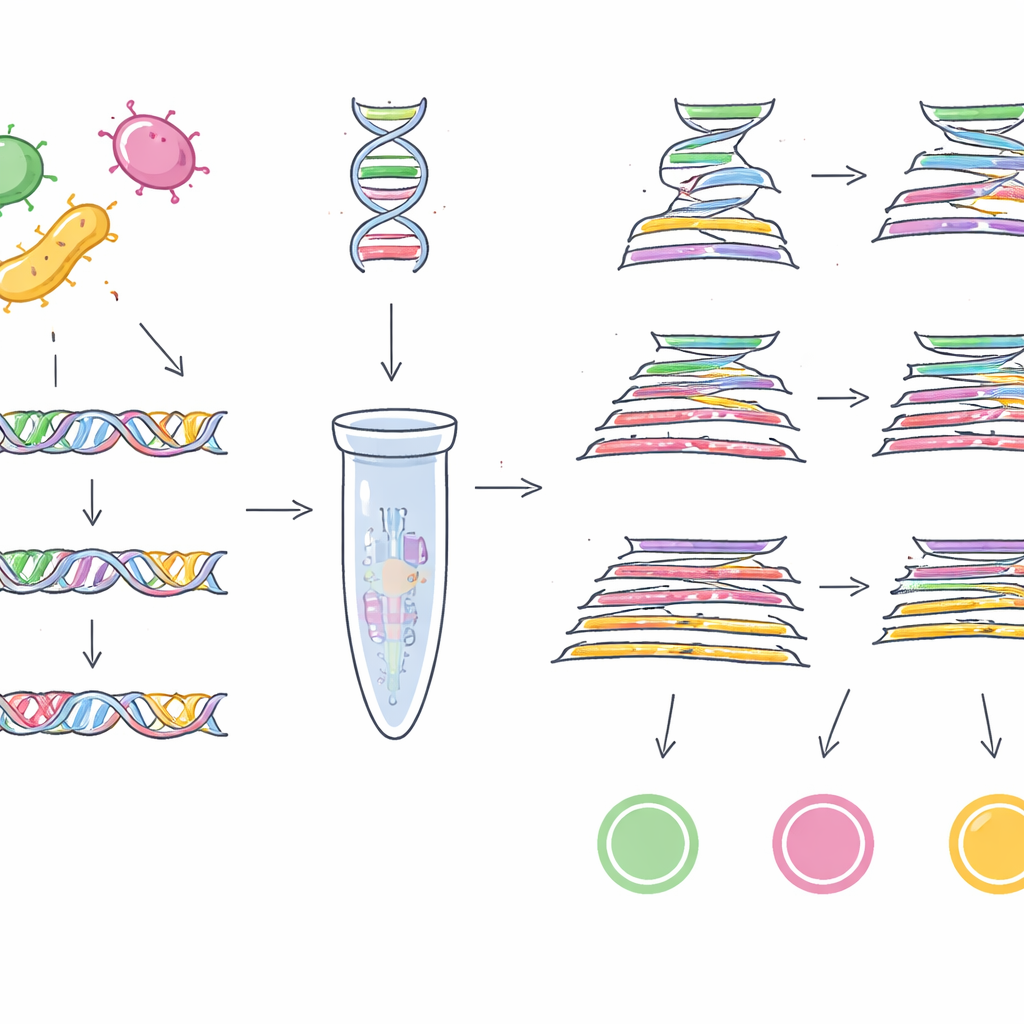
Para isso, a equipe primeiro precisou de “códigos de barras” genéticos confiáveis — trechos curtos de DNA presentes em quase todas as cepas de um microrganismo-alvo, mas ausentes em outros. Em vez de procurar em um punhado de genomas, eles acessaram uma coleção pública enorme de 1,46 milhão de genomas bacterianos de 50 gêneros diferentes. Para EHEC O157:H7, compararam milhares de genomas de E. coli e vasculharam mais de 100.000 famílias de genes acessórios para encontrar sequências de DNA únicas para esse subtipo perigoso. Após várias rodadas de filtragem e checagens cruzadas contra mais de um milhão de genomas não pertencentes a E. coli, se depararam com um gene chamado z0340 como um marcador altamente específico para EHEC O157:H7. Usando estratégia similar em mais de meio milhão de genomas de Salmonella e quase um milhão de outros genomas bacterianos, identificaram outro gene, sbcC, como um marcador confiável para o grupo Salmonella como um todo.
Transformando marcadores em testes do mundo real
Com esses dois novos códigos de barras na mão — além de um gene específico de Cronobacter, ygcB, que o grupo havia descoberto anteriormente — os pesquisadores projetaram testes laboratoriais capazes de detectar os três patógenos de uma só vez. Eles construíram ensaios de PCR multiplex, que atuam como copiadoras moleculares direcionadas a trechos específicos de DNA, e uma versão mais sensível de qPCR TaqMan que mede em tempo real a quantidade de DNA-alvo presente. Quando esses testes foram desafiados com 23 cepas dos três patógenos e 100 cepas de outras bactérias comuns, identificaram corretamente apenas os alvos pretendidos em todas as ocasiões, mostrando 100% de especificidade. A PCR multiplex básica pôde detectar quantidades tão baixas quanto 1 picograma de DNA por microlitro, enquanto a versão TaqMan chegou a 0,5 picograma, indicando alta sensibilidade.
Testando os métodos em alimentos
A precisão em laboratório só é útil se os testes funcionarem em amostras reais e complexas. Para verificar isso, os cientistas contaminaram deliberadamente alface, carne moída e fórmula infantil em pó com quantidades conhecidas de EHEC O157:H7, Salmonella ou Cronobacter. Após etapas padrão de enriquecimento para permitir que quaisquer bactérias presentes se multiplicassem, aplicaram seus ensaios de PCR multiplex e qPCR TaqMan. Em todos os casos, os métodos detectaram corretamente o patógeno introduzido e não produziram falsos positivos nos controles negativos. O desempenho foi consistente entre os três tipos de alimento, sugerindo que gorduras, componentes vegetais ou ingredientes complexos não interferiram de forma perceptível na detecção.
Limitações e melhorias futuras
Apesar dos resultados robustos, os autores observam que seu painel de validação ainda representa apenas uma fração da diversidade microbiana encontrada na natureza. Por exemplo, testaram apenas uma cepa de EHEC O157:H7 em laboratório, apesar de a triagem baseada em genomas ter coberto dezenas de milhares dessas cepas. Também trabalharam com níveis relativamente altos de contaminação em comparação com os números extremamente baixos de bactérias que ainda podem causar doença. Trabalhos futuros precisarão testar muito mais isolados do mundo real, examinar alimentos naturalmente contaminados e adicionar controles internos para se proteger contra substâncias nos alimentos que possam inibir a amplificação de DNA.
O que isso significa para os consumidores
Em termos práticos, este estudo mostra que códigos de barras de DNA bem escolhidos podem permitir que laboratórios de segurança alimentar triem vários microrganismos de alto risco ao mesmo tempo, com alta precisão e em menos tempo do que métodos tradicionais baseados em cultivo. Ao minerar milhões de genomas, os pesquisadores identificaram três assinaturas genéticas — uma para EHEC O157:H7, uma para Salmonella e uma para Cronobacter — que parecem ser ao mesmo tempo altamente específicas e estáveis. Os testes resultantes poderiam fortalecer a vigilância rotineira de alimentos como folhas verdes, carnes e fórmulas infantis, detectando contaminações mais cedo e com maior confiabilidade. Além desses três patógenos, a mesma abordagem orientada por genomas poderia ser usada para projetar testes rápidos para muitos outros microrganismos perigosos, oferecendo uma nova ferramenta poderosa para tornar a cadeia global de alimentos mais segura.
Citação: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Palavras-chave: patógenos transmitidos por alimentos, PCR multiplex, marcadores genômicos, Salmonella e EHEC, detecção de Cronobacter