Clear Sky Science · pt
Estudo piloto sobre consistência de protocolo e reprodutibilidade de métricas de grafo em conectomas ponderados por microestrutura
Por que o mapa de conexões do cérebro precisa de uma verificação de confiabilidade
Médicos e cientistas cada vez mais enxergam o cérebro como um grande mapa de conexões, onde regiões se comunicam por meio de feixes de fibras nervosas. Métodos novos baseados em ressonância magnética podem transformar esse emaranhado em redes matemáticas que talvez revelem sinais precoces de doenças como esclerose múltipla ou Alzheimer. Mas antes que essas medidas possam orientar diagnóstico ou tratamento, precisamos saber algo básico: se escaneamos o mesmo cérebro saudável mais de uma vez, ou em aparelhos diferentes com configurações ligeiramente distintas, obtemos essencialmente a mesma rede de volta?
Do movimento da água aos mapas das rodovias cerebrais
Para construir esses mapas de conexões, os autores usam uma forma de RM que acompanha como moléculas de água se movem no tecido cerebral. Na substância branca, onde longas fibras nervosas isoladas correm agrupadas, a água tende a se mover ao longo das fibras em vez de atravessá‑las. Medindo esse movimento direcional em muitas orientações, algoritmos de computador podem inferir feixes de fibras e montar um “conectoma” — uma matriz que registra quais regiões do córtex cinzento estão ligadas por quais vias da substância branca. Em vez de simplesmente contar quantas fibras virtuais são reconstruídas entre regiões, este estudo concentra‑se em conectomas “ponderados por microestrutura”, onde cada conexão é caracterizada por propriedades do tecido em si, como quão ordenadas estão as fibras ou quão densamente empacotadas elas parecem.
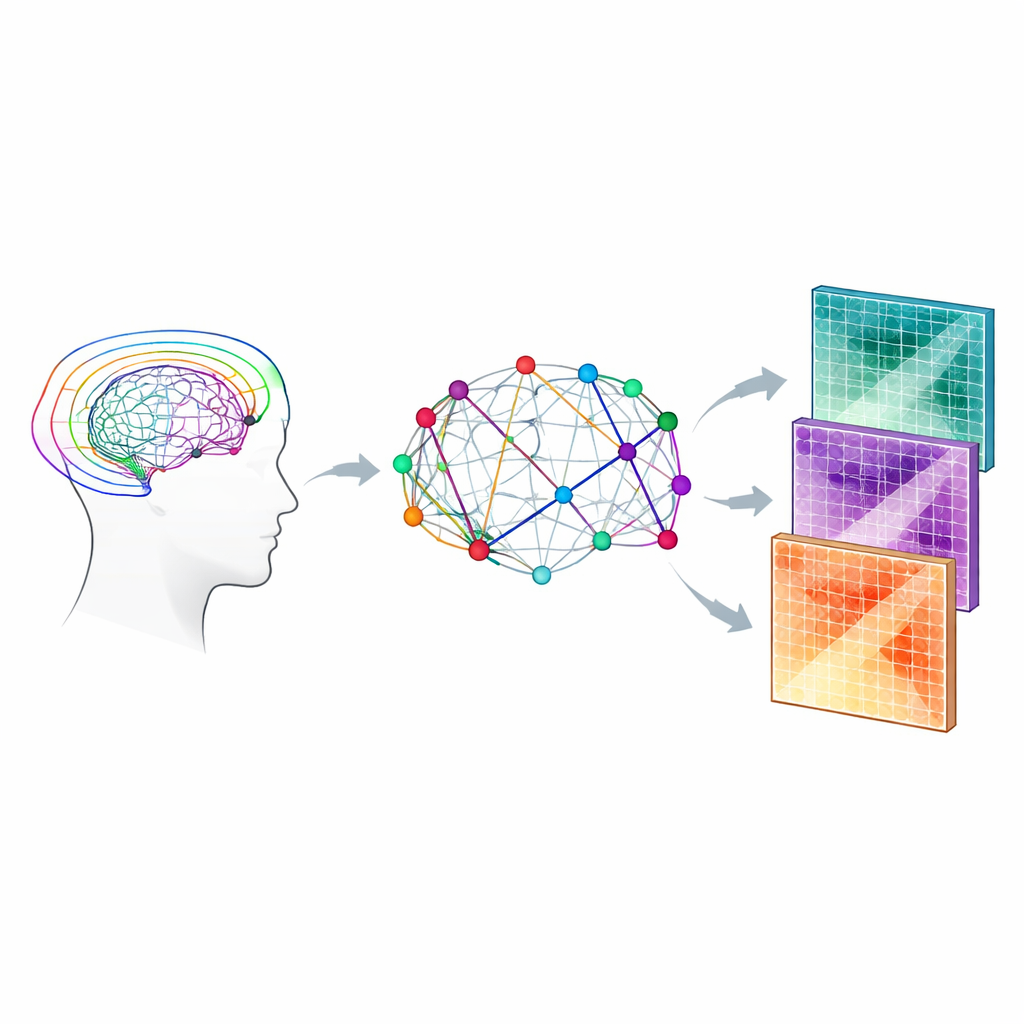
Adicionando detalhe biológico à rede
A equipe combinou duas famílias de modelos que interpretam o sinal de RM por difusão. O primeiro, imageamento por tensor de difusão, resume o quão direcional é o movimento da água e quão rápido ela difunde em média. O segundo, chamado Bingham‑NODDI, vai além ao estimar quanto de cada pequeno volume de tecido é composto por água dentro dos neurites, fora deles, ou em espaços preenchidos por fluido. Usando um protocolo de aquisição relativamente rico de “quatro cascas” projetado para capturar melhor a geometria complexa das fibras, calcularam vários parâmetros microestruturais, incluindo anisotropia fracional e difusividade média (do modelo do tensor) e frações de volume intra‑neurite e extra‑celular (do Bingham‑NODDI). Esses parâmetros foram então propagados ao longo de cada feixe de fibras reconstruído e combinados para fornecer um peso biologicamente informado a cada conexão na rede.
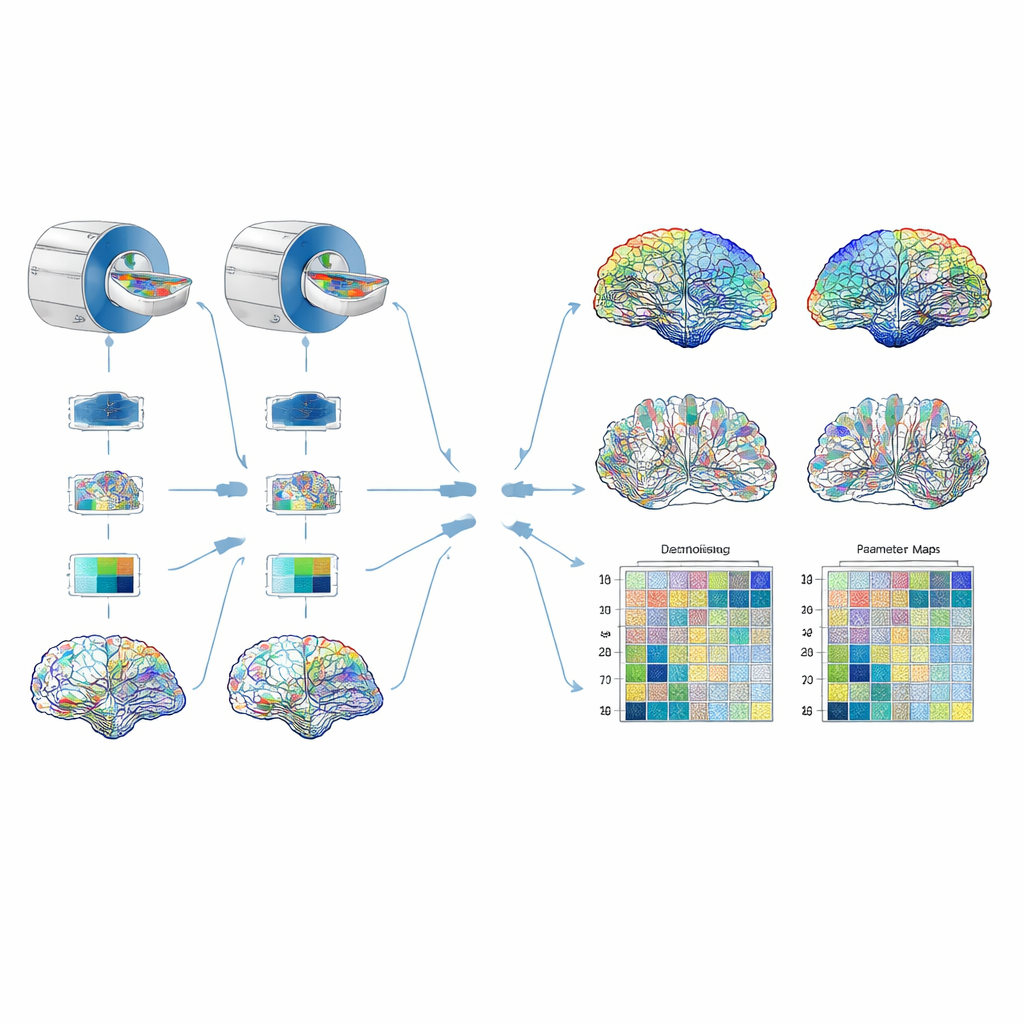
Testando o pipeline
A confiabilidade foi avaliada de três maneiras complementares. Primeiro, os pesquisadores escanearam repetidamente um fantoma físico cuidadosamente projetado — um emaranhado de fibras sintéticas em água salgada que imita características chave do tecido cerebral — para testar quão estáveis eram os parâmetros ao longo de curtos períodos. Em seguida, escanearam quatro voluntários saudáveis em dois hospitais, usando a mesma marca e modelo de aparelho de RM e as mesmas configurações, para sondar diferenças entre locais. Finalmente, compararam o protocolo de quatro cascas contra um protocolo mais curto e convencional de duas cascas, perguntando se ambos produziam valores de parâmetro semelhantes. Para os dados cerebrais, reconstruíram múltiplas versões do conectoma ponderadas por diferentes parâmetros e extraíram medidas de grafo, como eficiência global da rede, quão agrupadas são as conexões e quão fortemente cada região se conecta ao resto do cérebro. Depois verificaram quanto essas medidas mudavam de um site para outro e quanto da variação refletia diferenças reais entre pessoas em vez de ruído de medição.
O que se mostrou confiável
Várias medidas teciduais-chave demonstraram notável consistência. Anisotropia fracional, difusividade média e as frações de volume intra‑neurite e intra‑celular variaram menos de cinco por cento entre exames repetidos, entre sites diferentes e (para a maioria das regiões) entre os protocolos de duas e quatro cascas. Em contraste, quantidades que descrevem quão dispersas são as orientações das fibras — e um parâmetro relacionado de “concentração” — foram mais erráticas e, por isso, foram excluídas da construção da rede. Quando os pesquisadores construíram conectomas ponderados pelas medidas mais estáveis, muitas propriedades da rede, incluindo densidade, eficiência global, coeficiente de cluster médio e força média das conexões, foram reprodutíveis entre sites. Uma exceção foi a modularidade, uma medida de quão claramente a rede se divide em comunidades distintas; essa medida mostrou‑se notavelmente mais sensível a pequenas mudanças nos pesos subjacentes. Conectomas ponderados pela fração de volume extra‑celular tiveram o pior desempenho geral, com várias métricas de grafo mostrando fraco acordo entre sites.
Por que isto importa para a saúde cerebral
O estudo mostra que não basta contar fibras reconstruídas ao buscar marcadores de doença no emaranhado de conexões do cérebro. Ao selecionar cuidadosamente parâmetros microestruturais estáveis para ponderar cada conexão, os pesquisadores podem construir redes mais ricas e biologicamente fundamentadas cujas propriedades chave são repetíveis entre aparelhos e protocolos. Nas condições testadas, conectomas ponderados por anisotropia fracional, difusividade média e fração de volume intra‑neurite mostraram‑se robustos o bastante para que suas estatísticas de rede básicas possam servir como candidatos a biomarcadores em distúrbios que afetam a conectividade cerebral. Ao mesmo tempo, o trabalho sinaliza medidas mais frágeis, como modularidade e alguns índices microestruturais avançados, como características que devem ser tratadas com cautela até que estudos maiores e multicêntricos confirmem sua confiabilidade.
Citação: Cavallo, M., Ricchi, M., Axford, A. et al. A pilot study on protocol consistency and graph metric reproducibility in microstructure-weighted connectomes. Sci Rep 16, 8288 (2026). https://doi.org/10.1038/s41598-026-38964-z
Palavras-chave: conectividade cerebral, ressonância magnética por difusão, conectoma, reprodutibilidade de rede, imagem de microestrutura