Clear Sky Science · pt
ConvAHKG: Grafo de conhecimento híbrido baseado em ação com uma abordagem convolucional de canal duplo para reposicionamento de medicamentos
Encontrando Novos Usos para Medicamentos Antigos
Lançar um medicamento totalmente novo no mercado pode levar mais de uma década e custar bilhões de dólares, e muitos candidatos falham pelo caminho. Este estudo explora um atalho mais inteligente: usar dados e inteligência artificial para descobrir novas doenças que medicamentos existentes, já aprovados, possam tratar com segurança. Os autores apresentam um framework, chamado ConvAHKG, que integra vários tipos de informação biomédica em um mapa conectado único e então utiliza uma rede neural moderna para identificar correspondências promissoras entre drogas e doenças — oferecendo uma rota mais rápida e mais barata para novas terapias.
Um Mapa Rico de Como Drogas e Doenças Interagem
No cerne deste trabalho está um “grafo de conhecimento híbrido”, um mapa gigantesco que conecta drogas, doenças, proteínas, efeitos colaterais, estruturas químicas e vias biológicas. Em vez de armazenar apenas ligações simples de sim/não (por exemplo, “droga A trata doença B”), o mapa registra como uma droga atua sobre uma proteína — se ativa, inibe ou se liga a ela — e como proteínas estão envolvidas nas doenças, como servir de biomarcadores ou alterar sua atividade. O grafo contém mais de 11.000 entidades e 59 tipos de relações, incluindo informações detalhadas sobre classificações de drogas, efeitos adversos, contatos proteína–proteína e subestruturas químicas. Ao capturar essas múltiplas camadas de contexto, o grafo pode refletir mais da complexidade biológica real por trás dos efeitos terapêuticos e das reações adversas. 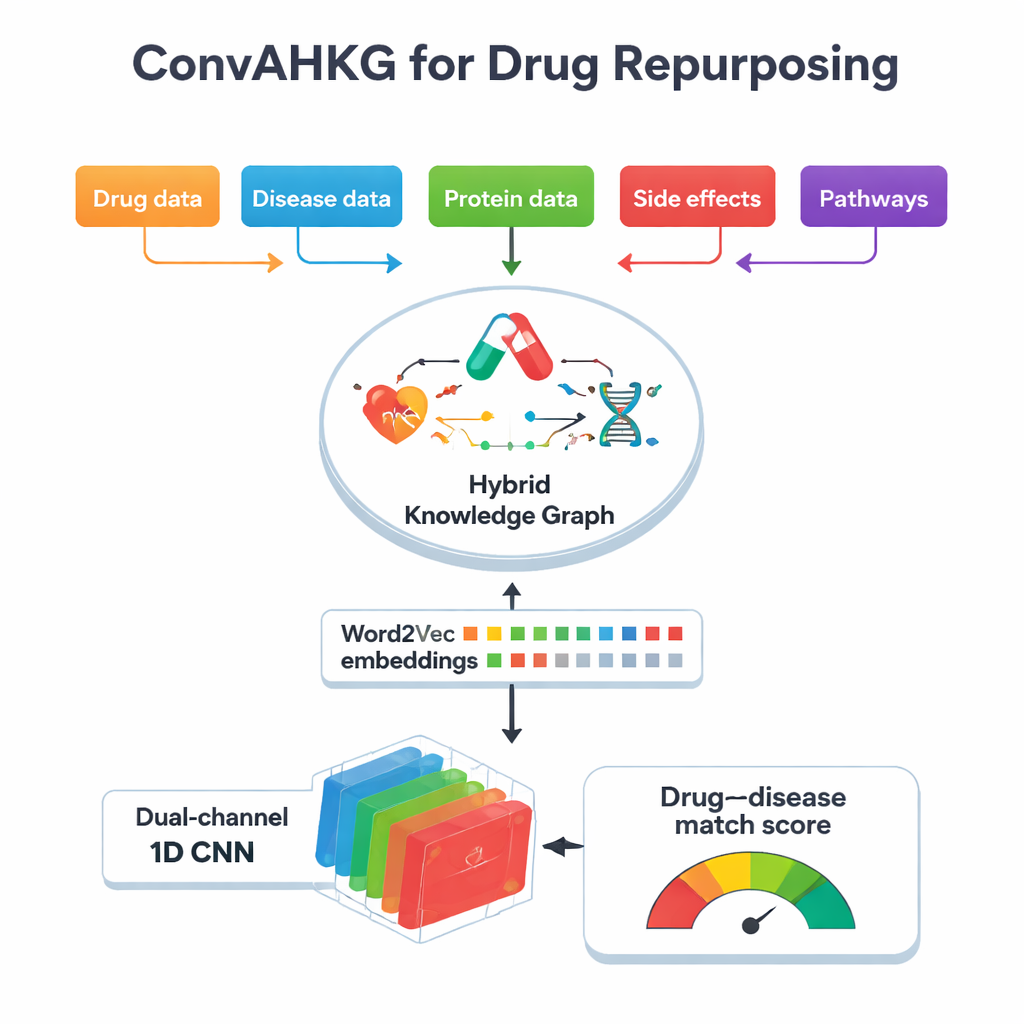
Ensinando ao Computador a Linguagem da Biologia
Para tornar esse mapa complexo utilizável em aprendizado de máquina, a equipe converte cada conexão do grafo em uma “frase” simples de três partes: um head (como uma doença), uma relation (como biomarcador) e um tail (como uma proteína). Em seguida aplicam Word2Vec, um método originalmente desenvolvido para processamento de linguagem natural, para aprender “embeddings” numéricos para cada droga, doença e proteína. Itens que aparecem frequentemente juntos nessas frases acabam próximos uns dos outros neste espaço matemático, de modo semelhante a palavras que compartilham significados semelhantes em textos. Essa abordagem é muito mais simples e rápida do que muitas técnicas de embedding específicas para grafos, mas ainda captura padrões sutis. Em testes contra vários métodos populares de embedding para grafos de conhecimento, o Word2Vec igualou ou superou seu poder preditivo enquanto usava muito menos tempo de computação.
Uma Via Neural Dupla para Decisões Sim/Não sobre Tratamento
Uma vez que cada droga e doença é traduzida em um vetor numérico, o ConvAHKG os alimenta em uma rede neural convolucional unidimensional de canal duplo. Um canal processa o vetor da droga e o outro processa o vetor da doença usando uma sequência de filtros convolucionais que detectam padrões locais e motivos mais amplos, inspirados em designs de reconhecimento de imagens como InceptionNet e AlexNet. Após esse processamento separado, as duas correntes são fundidas e passadas por várias camadas totalmente conectadas que produzem uma única probabilidade: esse par droga–doença representa um tratamento provavelmente eficaz ou mais um efeito colateral prejudicial? Para lidar com o fato de que pares positivos conhecidos são muito mais raros que os negativos, os autores introduzem uma função de perda ponderada que penaliza com mais peso a perda de tratamentos verdadeiros, melhorando o desempenho nesses casos difíceis de encontrar. 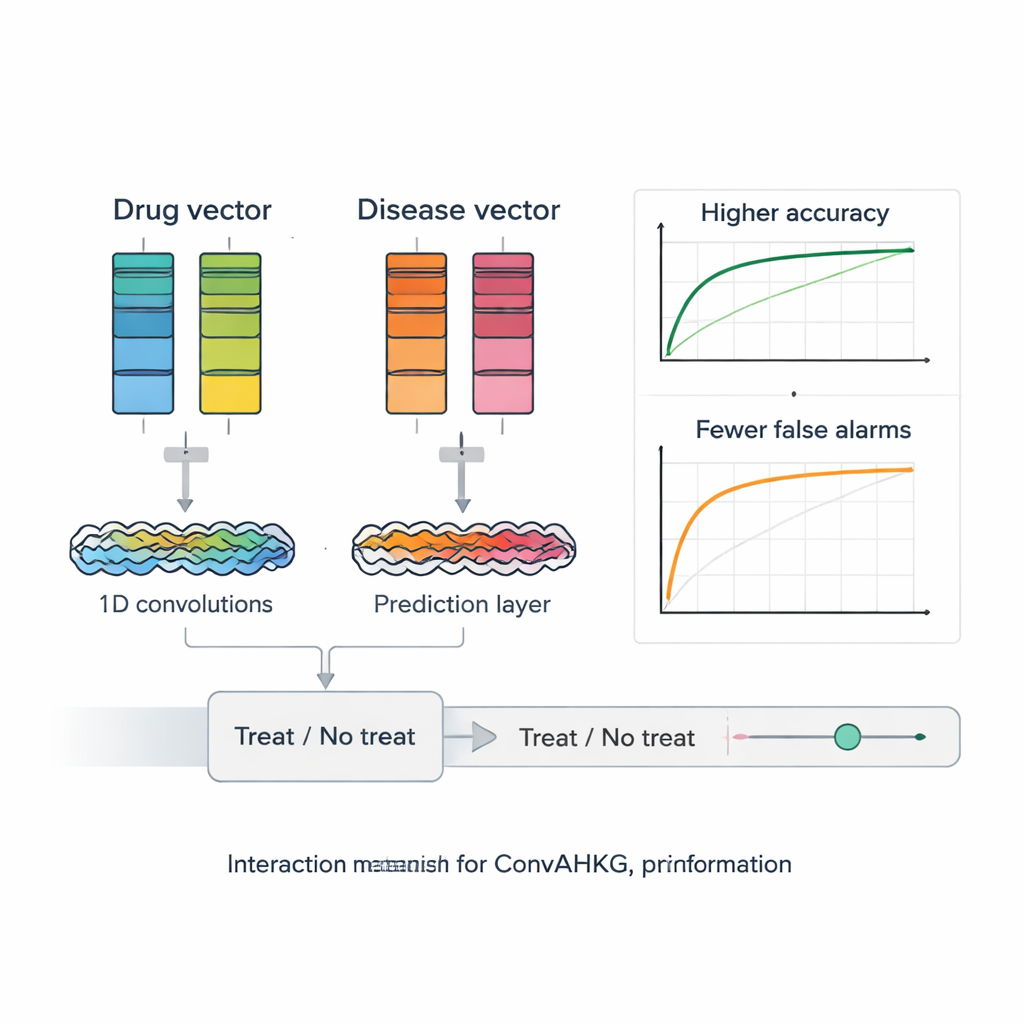
Superando Métodos Existentes e Identificando Candidatos para Câncer
Os pesquisadores testam rigorosamente seu framework contra várias ferramentas de reposicionamento de medicamentos estado da arte que usam fatoração de matrizes, redes neurais em grafos e autoencoders profundos. O ConvAHKG alcança uma área sob a curva ROC de 0,9836 e uma área sob a curva precisão–recall de 0,9686, superando todas as abordagens concorrentes no mesmo conjunto de referência. Em seguida aplicam o modelo ao carcinoma de pulmão de células não pequenas, a forma mais comum e letal de câncer de pulmão no mundo. O ConvAHKG destaca vários medicamentos não rotulados anteriormente como tratamentos para essa doença, incluindo o anticorpo trastuzumabe, que tem como alvo a proteína HER2 e já conta com evidências clínicas de suporte em câncer de pulmão, bem como outros agentes biológicos e até o antibiótico clássico benzilpenicilina. Simulações de docking sugerem que a benzilpenicilina pode se ligar fortemente ao DNA e à topoisomerase II alfa, uma enzima frequentemente elevada nesses tumores, insinuando um possível mecanismo anticâncer que agora merece testes em laboratório.
Por Que Isso Importa para Pacientes
Em termos simples, o ConvAHKG age como um casamenteiro altamente informado entre drogas existentes e doenças, usando um mapa detalhado de ações biológicas e um motor de reconhecimento de padrões poderoso para prever quais medicamentos antigos podem funcionar em novos contextos. Ao tratar drogas testadas em segurança como blocos reutilizáveis em vez de ferramentas de uso único, esse framework pode acelerar a descoberta de terapias para condições como o câncer de pulmão, especialmente onde o desenvolvimento convencional de fármacos é lento ou caro demais. Embora as previsões ainda precisem de validação experimental e clínica cuidadosa, o estudo mostra que combinar conhecimento biológico rico com IA moderna pode reduzir drasticamente o espaço de busca, aproximando tratamentos potencialmente salvadores de vidas de forma mais rápida.
Citação: Khodadadi AghGhaleh, M., Abedian, R., Zarghami, R. et al. ConvAHKG: Action-based hybrid knowledge graph with a dual-channel convolutional approach for drug repurposing. Sci Rep 16, 7592 (2026). https://doi.org/10.1038/s41598-026-38656-8
Palavras-chave: reposicionamento de medicamentos, grafo de conhecimento, aprendizado profundo, câncer de pulmão, descoberta de fármacos