Clear Sky Science · pt
Sequenciamento genômico de Bacillus daqingensis e Alkalicoccus luteus revela insights taxonômicos e mecanismos adaptativos
Vida em Lugares Salinos
De lagos salgados a solos alcalinos, alguns microrganismos prosperam em condições que desidratariam e matariam a maioria das outras formas de vida. Este estudo mergulha no DNA de duas dessas bactérias amantes do sal para entender como sobrevivem em ambientes extremos e para esclarecer onde realmente se posicionam na árvore da vida. Ao comparar seus genomas em detalhe, os pesquisadores mostram que o que se pensava serem espécies bacterianas distintas são, na verdade, o mesmo tipo de organismo, e revelam as estratégias moleculares que esses micróbios utilizam para lidar com intenso estresse salino.
Por que Esses Amantes do Sal São Importantes
As bactérias no centro deste trabalho foram originalmente nomeadas Bacillus daqingensis e Alkalicoccus luteus. Ambas foram isoladas em ambientes salgados e alcalinos, como lagos de sosa e solos salinos, onde a maior parte da vida tem dificuldades. Cientistas suspeitavam que Bacillus daqingensis poderia, na verdade, pertencer ao gênero Alkalicoccus, mas sua sequência genômica completa estava ausente, deixando seu status oficial em limbo. Ao sequenciar e analisar os genomas completos desses microrganismos e compará-los com espécies relacionadas, os autores buscaram resolver esse quebra-cabeça taxonômico e, ao mesmo tempo, entender como membros do gênero Alkalicoccus conseguem sobreviver em condições tão severas.
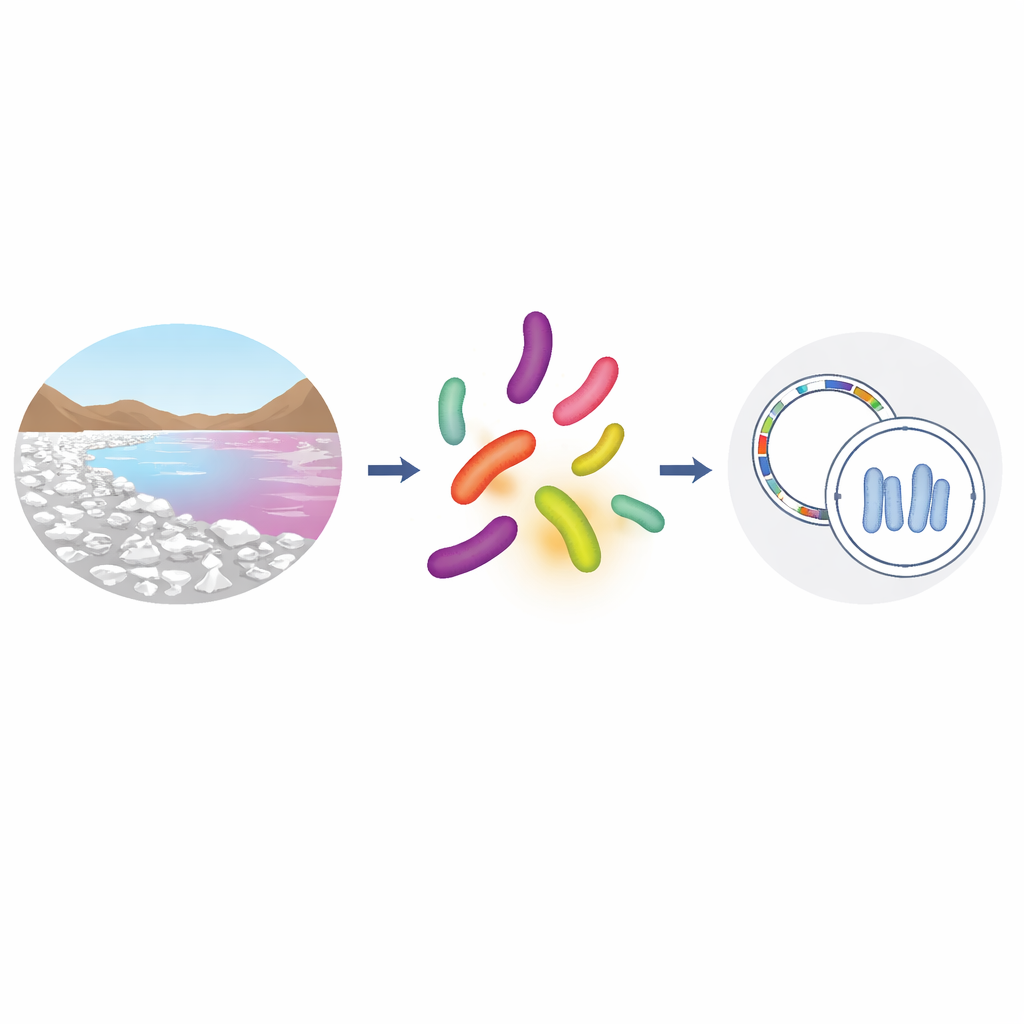
Lendo e Comparando Genomas Microbianos
A equipe cultivou as bactérias em laboratório, extraiu seu DNA e o sequenciou usando métodos de alto rendimento. Em seguida, montaram os milhões de pequenos fragmentos de DNA em mapas genômicos quase completos e verificaram sua qualidade. Tanto Bacillus daqingensis quanto Alkalicoccus luteus revelaram ter genomas de tamanho semelhante, cerca de 3,4 a 3,5 milhões de pares de bases, com conteúdo genético quase idêntico e completude muito alta. Um marcador genético chave, conhecido como gene 16S rRNA, foi essencialmente o mesmo em ambos os organismos: uma comparação encontrou 99,8% de identidade em relação a medições anteriores em laboratório e, crucialmente, as sequências 16S das duas linhagens foram uma correspondência perfeita de 100% entre si.
Decodificando a Sobrevivência em Sal e Estresse
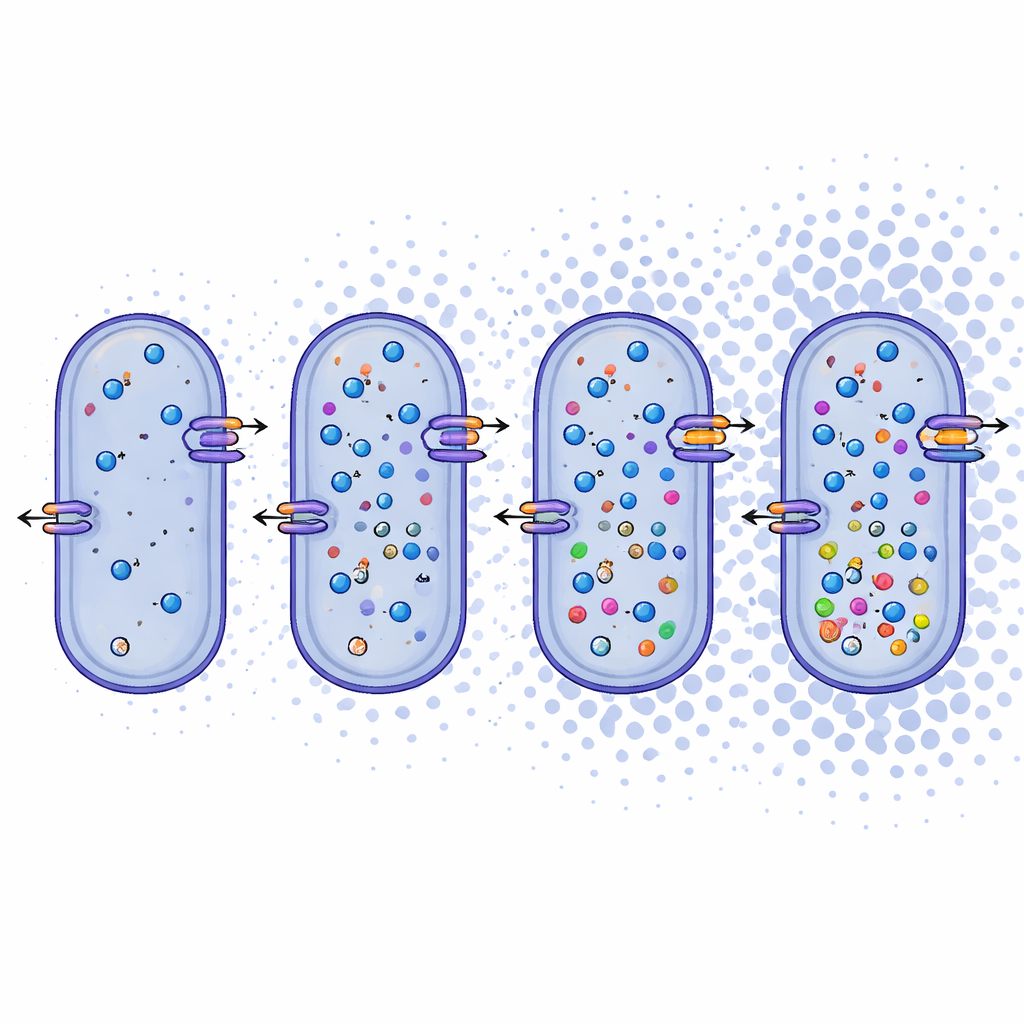
Indo além dos nomes, os pesquisadores examinaram o que os genomas revelam sobre como esses micróbios se sustentam. Eles descobriram que Bacillus daqingensis e todas as espécies de Alkalicoccus analisadas compartilham vias metabólicas centrais, incluindo rotas padrão para a degradação de açúcares e um ciclo modificado chamado desvio do glicooxilato (glyoxylate shunt) que ajuda a conservar carbono sob estresse. Mais marcante, os genomas carregam um repertório rico para lidar com alto teor de sal. As bactérias parecem usar duas táticas complementares: sistemas "salt-in" que movimentam íons inorgânicos como sódio e potássio através da membrana celular, e sistemas "salt-out" que sintetizam ou importam pequenas moléculas orgânicas, como betaína, ectoína e certos aminoácidos, que atuam como amortecedores internos contra a desidratação. Genes para transportadores de íons, antiportadores e a biossíntese desses solutos compatíveis estão presentes em todo o gênero, apontando para uma resposta robusta e flexível ao estresse osmótico.
Provando Quem é Quem
Para resolver a questão taxonômica, os autores compararam genomas inteiros usando diversos critérios numéricos que são agora padrão na sistemática microbiana. A identidade média de nucleotídeos (ANI) mede quão semelhantes são as sequências de DNA ao longo do genoma, enquanto a identidade média de aminoácidos (AAI) faz o mesmo ao nível das proteínas. Entre Bacillus daqingensis e Alkalicoccus luteus, a ANI alcançou 98,2% e a AAI alcançou 98,5% — bem acima dos limites usuais usados para definir a mesma espécie e até o mesmo gênero. Árvores filogenéticas construídas a partir de muitos genes, juntamente com comparações de agrupamentos de proteínas compartilhadas, mostraram que essas duas linhagens se agrupam de forma muito próxima e compartilham mais grupos de genes entre si do que com qualquer outra espécie de Alkalicoccus. Características tradicionais, como forma celular, perfis de ácidos graxos e reações bioquímicas-chave, também foram essencialmente idênticas entre elas.
O Que Isso Significa para os Nomes Microbianos
Reunindo todas as linhas de evidência, o estudo conclui que Bacillus daqingensis não representa um tipo distinto de bactéria. Em vez disso, pertence ao gênero Alkalicoccus e é a mesma espécie que Alkalicoccus luteus, anteriormente conhecida como Bacillus luteus. Os autores propõem formalmente a nova combinação nomenclatural Alkalicoccus daqingensis e tratam essa designação, juntamente com o nome Bacillus mais antigo, como sinônimos posteriores de Bacillus luteus/Alkalicoccus luteus. Para não especialistas, a lição é que o sequenciamento genômico cuidadoso pode revelar quando etiquetas diferentes estão sendo usadas para essencialmente o mesmo microrganismo, ajudando a limpar o sistema de nomenclatura. Ao mesmo tempo, o trabalho destaca como essas bactérias amantes do sal dependem de uma combinação de bombas de íons e moléculas protetoras para permanecer vivas em ambientes que, de outra forma, seriam salinos demais para a vida.
Citação: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Palavras-chave: bactérias halofílicas, sequenciamento do genoma, taxonomia microbiana, adaptação ao estresse salino, Alkalicoccus luteus