Clear Sky Science · pt
Edição do genoma em espécies de Dictyostelia possibilita genética funcional comparativa de amebas sociais
Como Células Individuais Se Unem
Na maior parte do tempo, as amebas são minúsculas solitárias que rastejam no solo, alimentando-se de bactérias. Ainda assim, algumas delas, chamadas amebas sociais, podem de repente se agrupar em um corpo multicelular com uma espécie de “cabeça” e “haste” primitiva. Esse estilo de vida metamórfico oferece aos cientistas uma janela rara sobre como células simples aprendem a cooperar e a se especializar — passos-chave na evolução da vida complexa. O novo estudo descreve um conjunto de ferramentas de edição do genoma que finalmente permite aos pesquisadores investigar esses comportamentos não apenas em uma espécie preferida do laboratório, mas em várias espécies distantes de amebas.
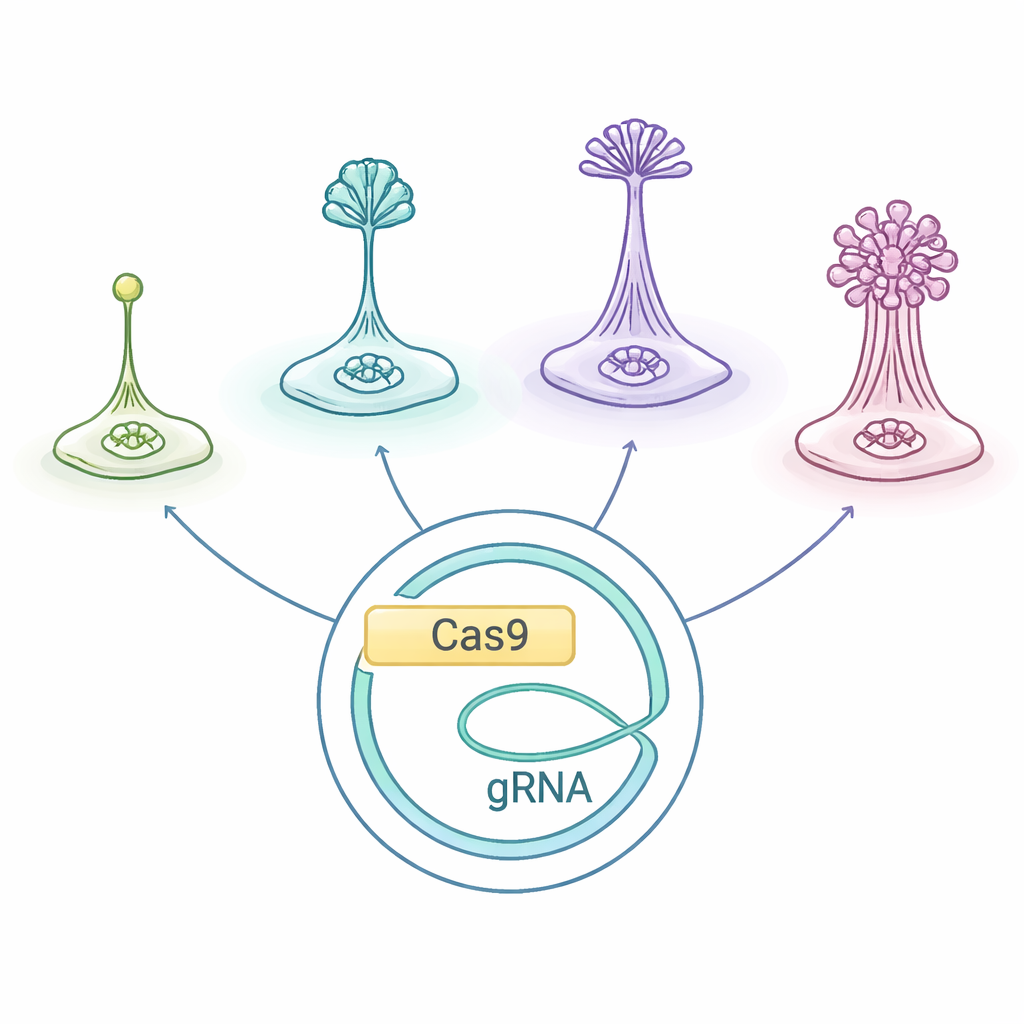
Criaturas Minúsculas com Vidas Sociais Complexas
As amebas sociais, agrupadas como Dictyostelia, vivem como células únicas quando o alimento é abundante. Quando passam fome, começam a emitir sinais químicos de aflição e caminham umas em direção às outras, reunindo-se em uma elevação que forma um pequeno “corpo frutífero”: uma coluna de células do tipo haste, sacrificiais, que erguem esporos resistentes no ar. Diferentes linhagens de Dictyostelia constroem essas estruturas de maneiras distintas e com conjuntos variados de tipos celulares, tornando-as um laboratório natural para investigar como corpos multicelulares e divisão de trabalho evoluíram.
Uma Espécie Modelo Não Era Suficiente
Até agora, quase todo o trabalho molecular concentrou-se em uma única espécie, Dictyostelium discoideum, porque seus genes são relativamente fáceis de manipular. Isso deixou mais de cem outras espécies conhecidas — algumas representando ramos mais antigos da árvore familiar dos Dictyostelia — amplamente inexploradas. Essas espécies negligenciadas têm histórias de vida, sistemas de sinalização e planos corporais distintos. Para entender como a multicelularidade mudou ao longo do tempo, é preciso manipular os mesmos genes em muitas dessas espécies e comparar os resultados lado a lado.
Levando o CRISPR a uma Família Diversa de Amebas
Os pesquisadores adaptaram um sistema de edição gênica CRISPR/Cas9 originalmente otimizado para D. discoideum e testaram se ele funciona ao longo da árvore dos Dictyostelia, incluindo espécies de ramificações iniciais e mais derivadas. Eles usaram um plasmídeo — um trecho extra circular de DNA — que carrega as instruções para as “tesouras moleculares” Cas9, o RNA guia que direciona a Cas9 a um gene escolhido, e um marcador de resistência a drogas. Introduzir esse plasmídeo em diferentes amebas permitiu à equipe cortar dois genes bem estudados, chamados stlA e pkaC, importantes para os sinais que coordenam a agregação e a formação adequada do corpo frutífero. Na ameba do solo Polysphondylium violaceum, essa estratégia produziu de forma confiável mutantes com defeitos de desenvolvimento claros, mostrando que o sistema adaptado pode funcionar fora do modelo habitual.
Testando Genes Através de Espécies
Em seguida, a equipe avançou para espécies mais distantes, incluindo Heterostelium pallidum do Grupo 2 e Cavenderia fasciculata do Grupo 1 — linhagens que divergiram mais cedo na evolução. Usando o mesmo desenho de plasmídeo, eles desativaram o gene pkaC em ambas as espécies e constataram que os mutantes não conseguiam se agregar nem construir corpos frutíferos normais, espelhando os defeitos graves vistos em D. discoideum. Como as mutações por CRISPR criadas por esse método não deixam grandes cassetes de seleção, as linhagens resultantes eram “sem marcador”. Isso facilitou reintroduzir uma versão do gene de D. discoideum e testar se ela podia substituir a versão local. Em todos os casos, o pkaC estrangeiro conseguiu resgatar o passo inicial de agregação, mas não a modelagem posterior de um corpo frutífero maduro — evidência de que o conjunto básico de sinalização é compartilhado, enquanto o controle refinado do tempo e da posição evoluiu de forma específica em cada espécie.
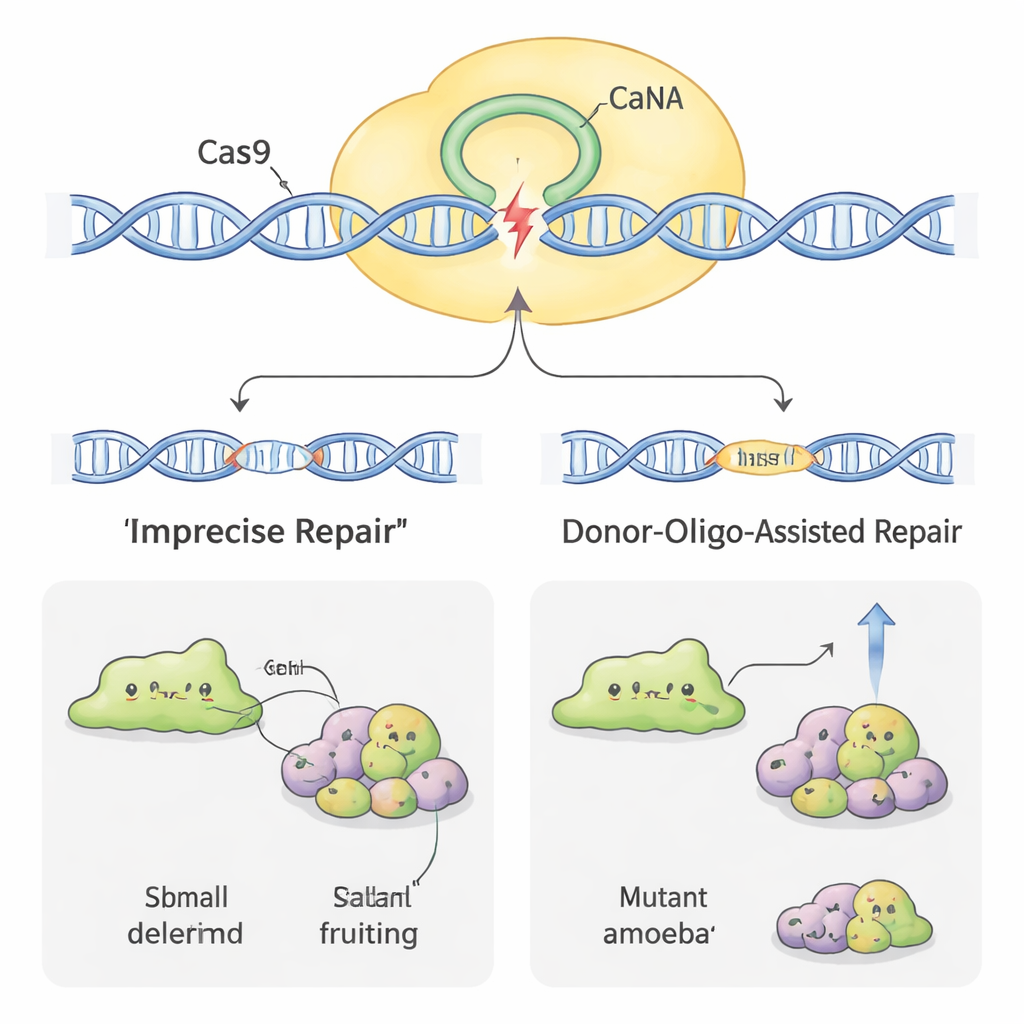
Tornando a Edição Mais Eficiente
Nem todas as amebas cederam à edição do genoma com a mesma facilidade. Em algumas espécies, como H. pallidum, a taxa inicial de sucesso foi muito baixa. Para aumentar a eficiência, os cientistas recorreram a outro artifício: adicionar pequenos trechos de DNA “doador” juntamente com o plasmídeo CRISPR. Esses doadores carregam uma pequena etiqueta e um sinal de parada flankado por regiões curtas que correspondem ao gene alvo. Quando a célula repara o corte da Cas9 usando o doador como molde, ela tende a interromper o gene de maneira reconhecível. Em D. discoideum, isso aumentou a proporção de clones defeituosos e até permitiu à equipe obter mutantes sem usar seleção contínua por drogas. No mais teimoso H. pallidum, combinar o DNA doador com alguns dias de tratamento farmacológico aumentou as taxas de mutação em quase uma ordem de magnitude, transformando eventos antes raros em algo próximo de rotina.
Abrindo uma Janela sobre as Origens da Complexidade
Para um não especialista, os detalhes de desenhos de plasmídeos e modelos de reparo podem soar técnicos, mas o retorno é amplo: um conjunto flexível de ferramentas CRISPR que funciona em vários ramos da árvore familiar das amebas sociais. Com ele, os cientistas podem agora comparar como o mesmo gene molda o desenvolvimento em diferentes espécies e como mudanças sutis na regulação gênica ou na estrutura proteica ajudam a gerar novos tipos celulares e planos corporais. Em outras palavras, este trabalho fornece aos pesquisadores as ferramentas genéticas necessárias para observar, em detalhe vivo, como a evolução mexeu em organismos unicelulares para construir sociedades multicelulares cooperativas.
Citação: Oishi, S., Doi, S., Sekida, T. et al. Genome editing across Dictyostelia species enables comparative functional genetics of social amoebas. Sci Rep 16, 7457 (2026). https://doi.org/10.1038/s41598-026-38605-5
Palavras-chave: amebas sociais, edição genética CRISPR, evolução da multicelularidade, Dictyostelium, diferenciação celular