Clear Sky Science · pt
Registro não rígido automatizado e robusto de imagens microscópicas de seções seriadas usando PiCNoR
Ver tecidos em 3D sem perder os detalhes
A biologia moderna frequentemente depende de transformar fatias finas de tecido em vistas 3D completas de órgãos e cérebros. Mas quando cada fatia microscópica é cortada, corada e imageada, ela pode esticar, rasgar ou deslocar-se. Se essas fatias não forem alinhadas corretamente, a imagem 3D resultante pode ser enganosa. Este artigo apresenta um novo método computacional chamado PiCNoR que ajuda cientistas a alinhar essas imagens de forma mais precisa e automática, de modo que estruturas finas em embriões e cérebros sejam preservadas nas reconstruções 3D.
Por que alinhar fatias é tão difícil
Para construir uma vista 3D, pesquisadores imageiam longas séries de seções ultrafinas retiradas do mesmo pedaço de tecido. Em teoria, cada fatia deveria encaixar perfeitamente sobre a anterior, como cartas em um baralho bem empilhado. Na prática, cada fatia pode deformar-se de maneira ligeiramente diferente durante o corte e a coloração. As cores podem variar, partes podem esticar-se e elementos podem deslocar-se. Métodos tradicionais de alinhamento “rígido” assumem que cada fatia inteira apenas se desloca ou rotaciona, o que muitas vezes não é suficiente. Métodos mais flexíveis, “elásticos”, existem, mas podem ser lentos, exigir ajuste cuidadoso por especialistas ou depender fortemente do brilho da imagem, que pode mudar de fatia para fatia.
Uma nova abordagem: peças locais que funcionam em conjunto
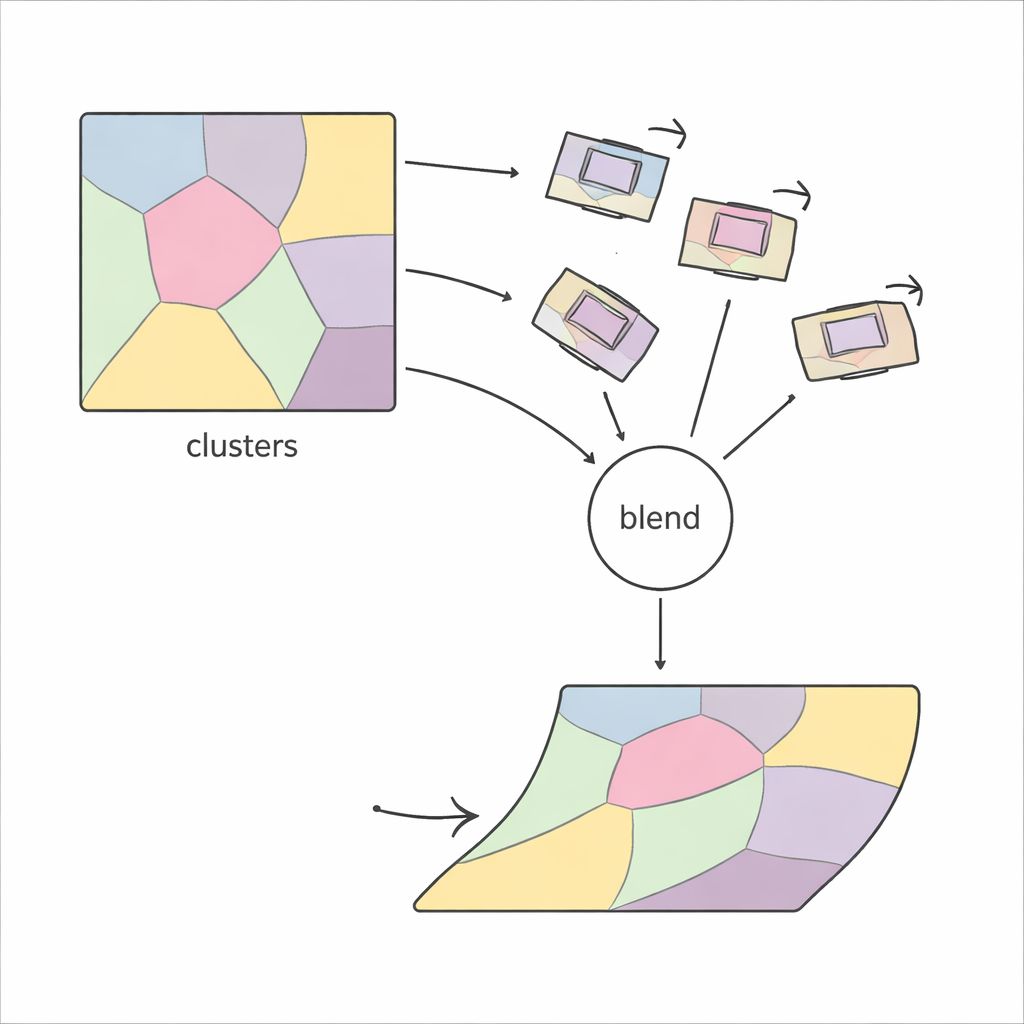
O PiCNoR adota uma visão diferente, mais local, do problema. Em vez de tentar deformar toda a imagem de uma vez, ele primeiro divide cada fatia em muitas regiões com base no padrão de características da imagem. Dentro de cada região, o método encontra pontos correspondentes entre duas fatias vizinhas usando detectores de características robustos, e estima como essa região deve rotacionar e deslocar-se para alinhar-se. Esses movimentos locais são então verificados quanto à plausibilidade e combinados suavemente, de modo que cada pixel da fatia receba um movimento que misture suavemente informações das regiões ao redor. O resultado é um alinhamento flexível, “não rígido”, que ainda se comporta de forma controlada e realista.
Deixar os dados escolherem a complexidade adequada
Um desafio central em qualquer método baseado em regiões é decidir quantas regiões usar: poucas demais, e o método não corrige deformações finas; muitas demais, e torna-se instável e lento. Abordagens anteriores frequentemente dependiam de tentativa e erro, verificando repetidamente a qualidade visual do resultado. O PiCNoR evita esse ajuste manual ao usar uma ferramenta estatística chamada critério de informação bayesiano, que equilibra automaticamente a quantidade de detalhe contra o risco de sobreajuste. Na prática, isso significa que o algoritmo pode decidir por si quantas regiões são necessárias para um dado conjunto de dados, sem supervisão humana, economizando tempo e reduzindo viés.
Manter os resultados confiáveis e eficientes
Nem todo movimento local estimado é confiável — alguns podem ser distorcidos por ruído ou correspondências pobres. O PiCNoR trata disso representando cada região como um nó em um grafo, onde regiões vizinhas influenciam-se mutuamente. Movimentos que parecem irreais em termos de rotação ou deslocamento são substituídos por uma média ponderada dos movimentos mais confiáveis ao redor. Uma representação matemática compacta ajuda a combinar esses movimentos de forma eficiente. Finalmente, o deslocamento de cada pixel é calculado como uma mistura ponderada por probabilidade dos movimentos regionais, garantindo que as transições entre regiões permaneçam suaves, sem dobras ou vincos repentinos no tecido.
Comprovando que funciona em dados biológicos reais
Os pesquisadores testaram o PiCNoR em três conjuntos de dados muito diferentes: seções de embriões humanos da coleção de Kyoto, uma pilha de microscopia eletrônica do cordão nervoso da mosca-das-frutas e uma nova pilha por microscopia de luz do hipocampo de um rato. Nesses exemplos, o PiCNoR produziu consistentemente melhor sobreposição entre fatias do que métodos rígidos padrão e métodos não rígidos amplamente usados. Manteve a continuidade de estruturas delicadas nas vistas 3D e evitou as distorções exageradas às vezes observadas com outras ferramentas. Importante, fez isso usando menos regiões locais do que alguns concorrentes e com custos computacionais que permanecem práticos para pilhas grandes.
O que isso significa para a microscopia 3D no futuro
Para não especialistas, a conclusão é que o PiCNoR oferece uma forma mais confiável de transformar pilhas de imagens microscópicas 2D em reconstruções 3D fiéis. Ao escolher automaticamente quão detalhado deve ser o alinhamento e ao proteger contra correções locais ruins, ele preserva as formas reais dos tecidos enquanto mantém o tempo de processamento gerenciável. Isso facilita para biólogos e patologistas confiarem no que veem em 3D, seja estudando como um embrião se desenvolve ou como células cerebrais estão organizadas, e estabelece a base para análises automatizadas mais precisas de conjuntos de dados microscópicos complexos.
Citação: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Palavras-chave: microscopia 3D, registro de imagem, imagem cerebral, histologia, alinhamento não rígido