Clear Sky Science · pt
Perfis da microbiota intestinal e do resistoma de expatriados suíços na África revelados por metagenômica Nanopore
Por que seus micróbios intestinais mudam quando você vive no exterior
Muitas pessoas passam meses ou anos morando no exterior, frequentemente em locais onde bactérias resistentes a antibióticos são comuns. Este estudo faz uma pergunta simples, mas importante: quando expatriados suíços vivem em países africanos com alta carga de infecções resistentes, a comunidade de micróbios e genes de resistência em seus intestinos muda de maneiras que podem afetar sua saúde e a disseminação mais ampla da resistência antimicrobiana?
A comunidade invisível dentro de nós
Nossos intestinos abrigam trilhões de micróbios, principalmente bactérias, que ajudam a digerir alimentos, educar o sistema imunológico e manter germes nocivos sob controle. Junto a esses micróbios benéficos está o “resistoma” – o conjunto de genes que conferem resistência a antibióticos. Mesmo pessoas saudáveis carregam muitos desses genes. Quando indivíduos se mudam ou viajam por regiões onde bactérias multirresistentes são comuns, podem adquirir silenciosamente novos genes de resistência e os elementos de DNA móvel, chamados plasmídeos, que os disseminam. Entender como isso ocorre é vital para controlar a resistência global a antibióticos.
Comparando expatriados na Europa e na África
Os pesquisadores analisaram amostras de fezes de 72 expatriados suíços saudáveis que retornaram à Suíça: 39 haviam vivido em países africanos e 33 em outros países europeus. Em vez de cultivar bactérias em laboratório, usaram uma tecnologia de sequenciamento de DNA de leitura longa chamada metagenômica shotgun Nanopore, que lê todo o material genético de uma amostra de uma vez. Isso permitiu mapear quais bactérias estavam presentes (a microbiota) e quais genes de resistência a antibióticos e plasmídeos elas carregavam (o resistoma e o plasmidoma). Cada amostra foi sequenciada duas vezes para maior confiabilidade, e softwares sofisticados foram usados para identificar grupos bacterianos e genes de resistência e montar fragmentos genômicos mais longos a partir do DNA misto.
Surpreendente estabilidade dos micróbios intestinais
Apesar de mais pessoas no grupo da África terem sido colonizadas por bactérias intestinais multirresistentes em testes anteriores baseados em cultivo, a composição geral da microbiota intestinal deles parecia notavelmente semelhante à dos expatriados que haviam vivido na Europa. Medidas de diversidade – quantos tipos diferentes de bactérias estavam presentes e quão uniformemente eram representadas – não diferiram por continente, e análises estatísticas não mostraram agrupamento claro de amostras da África versus Europa. Em ambos os grupos, habitantes intestinais familiares como Blautia, Faecalibacterium e Bacteroides dominaram, sugerindo que a residência prolongada no exterior não necessariamente reformula a comunidade bacteriana central em adultos saudáveis.
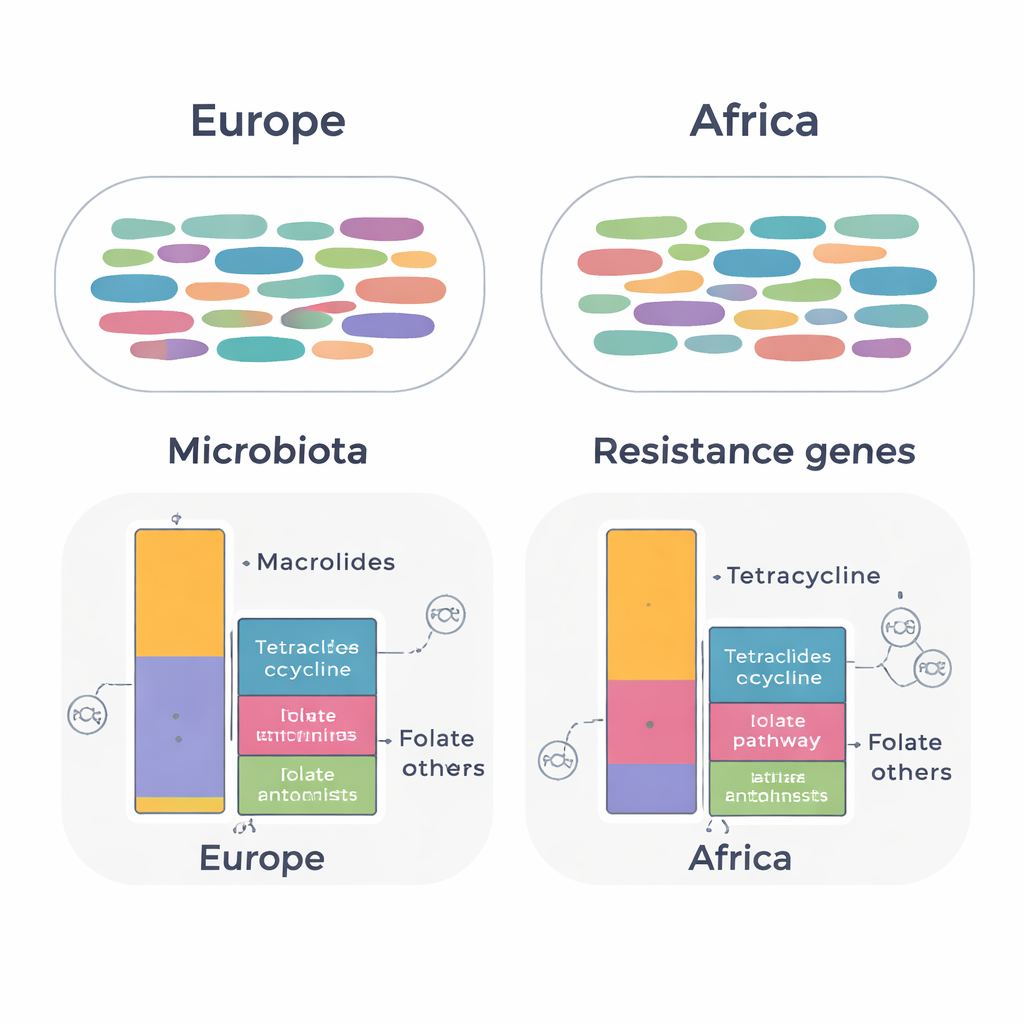
Genes de resistência e DNA móvel contam uma história diferente
Quando a equipe focou nos genes de resistência, surgiram diferenças mais sutis, porém importantes. Em todas as amostras, foram encontrados 134 genes de resistência distintos pertencentes a 14 classes de antibióticos. O padrão total de genes foi amplamente semelhante entre os continentes, mas os expatriados que haviam vivido na África apresentaram níveis mais altos de genes que protegem bactérias contra tetraciclinas e contra drogas que atuam na via do folato (como trimetoprim‑sulfametoxazol). Em contraste, expatriados de países europeus mostraram níveis mais elevados de genes que conferem resistência a macrolídeos. Muitos desses genes estavam ligados a bactérias intestinais comuns, incluindo Ruminococcoides, Bifidobacterium e Bacteroides. Genes clinicamente importantes, como blaCTX-M-15, que pode inativar cefalosporinas avançadas, foram detectados em Escherichia coli em ambos os grupos.
Plasmídeos como transportadores globais da resistência
O estudo também rastreou plasmídeos – pequenos círculos de DNA frequentemente transferíveis que transportam genes de resistência entre bactérias e ambientes. Usando as leituras longas de DNA, os pesquisadores às vezes puderam ver genes de resistência e marcadores de “replicon” de plasmídeos no mesmo fragmento de DNA montado, confirmando que viajavam juntos. Identificaram 46 tipos diferentes de plasmídeos, alguns exclusivos de cada continente e outros compartilhados. Notavelmente, certos plasmídeos carregavam múltiplos genes de resistência e assemelhavam‑se a plasmídeos conhecidos a partir de fontes humanas, animais, alimentares e de águas residuais em diferentes partes do mundo. Um tipo de plasmídeo comumente associado a Enterococcus e encontrado em frango e águas residuais foi mais frequente em amostras fecais de expatriados na África, ressaltando como alimentos, animais e o ambiente podem contribuir para o que acaba em nosso intestino.
O que isso significa para a vida cotidiana e a saúde pública
Para um leitor leigo, a mensagem principal é que simplesmente viver em uma região de alto risco não parece remodelar radicalmente quais bactérias intestinais você abriga, mas pode ajustar a mistura de genes de resistência a antibióticos e dos elementos de DNA móvel que os disseminam. Essas mudanças ocultas, moldadas em parte pelos padrões locais de uso de antibióticos, podem ser relevantes para infecções futuras e para a forma como traços de resistência se movem entre pessoas, animais e o ambiente. O trabalho também mostra que o sequenciamento portátil de leitura longa pode atuar como uma ferramenta de alerta precoce, revelando como genes de resistência e plasmídeos circulam em viajantes e expatriados saudáveis antes de causarem doença.
Citação: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Palavras-chave: microbioma intestinal, resistência a antibióticos, expatriados, plasmídeos, metagenômica