Clear Sky Science · pt
Identificação de genes de assinatura relacionados à ubiquitinação para prever rejeição de transplante renal
Por que o alerta precoce para novos rins é importante
Para pessoas com insuficiência renal, um rim transplantado pode mudar a vida — mas somente se o corpo o aceitar. Mesmo com medicamentos modernos contra rejeição, o sistema imunológico pode danificar silenciosamente um rim novo antes que os exames padrão detectem algum problema. Este estudo explora uma nova maneira de identificar a rejeição mais cedo e com maior precisão, lendo padrões de atividade gênica ligados a um processo celular básico chamado marcação de proteínas, potencialmente ajudando médicos a proteger rins transplantados por mais tempo.
Uma disputa oculta dentro do rim transplantado
Após um transplante renal, o sistema imunológico do receptor examina constantemente o órgão doador, tentando decidir se o tolera ou ataca. Os médicos tipicamente classificam a rejeição em dois tipos principais: uma impulsionada principalmente por células imunes chamadas células T e outra impulsionada por anticorpos circulantes no sangue. Na prática, muitos pacientes exibem uma mistura confusa de ambos, o que complica o diagnóstico e as decisões de tratamento. As ferramentas atuais — exames de sangue como creatinina ou biópsias por agulha — ou detectam o dano tardiamente ou são invasivas demais para uso frequente, deixando uma lacuna na detecção precoce e confiável.
As etiquetas de controle de qualidade da célula como sinal precoce
As células mantêm a ordem anexando pequenas “etiquetas” moleculares às proteínas, marcando-as para reciclagem ou alterando seu comportamento. Esse sistema de marcação, chamado ubiquitinação, também ajuda a controlar respostas imunes e inflamação. Porque atua em um nível alto na cadeia de controle, distúrbios nesse sistema podem aparecer cedo quando o sistema imunológico começa a atacar um rim transplantedo. Os pesquisadores supuseram que medir a atividade dos genes envolvidos nesse processo de marcação poderia fornecer uma leitura sensível de uma rejeição iminente, mesmo antes de danos evidentes ao tecido aparecerem ao microscópio.
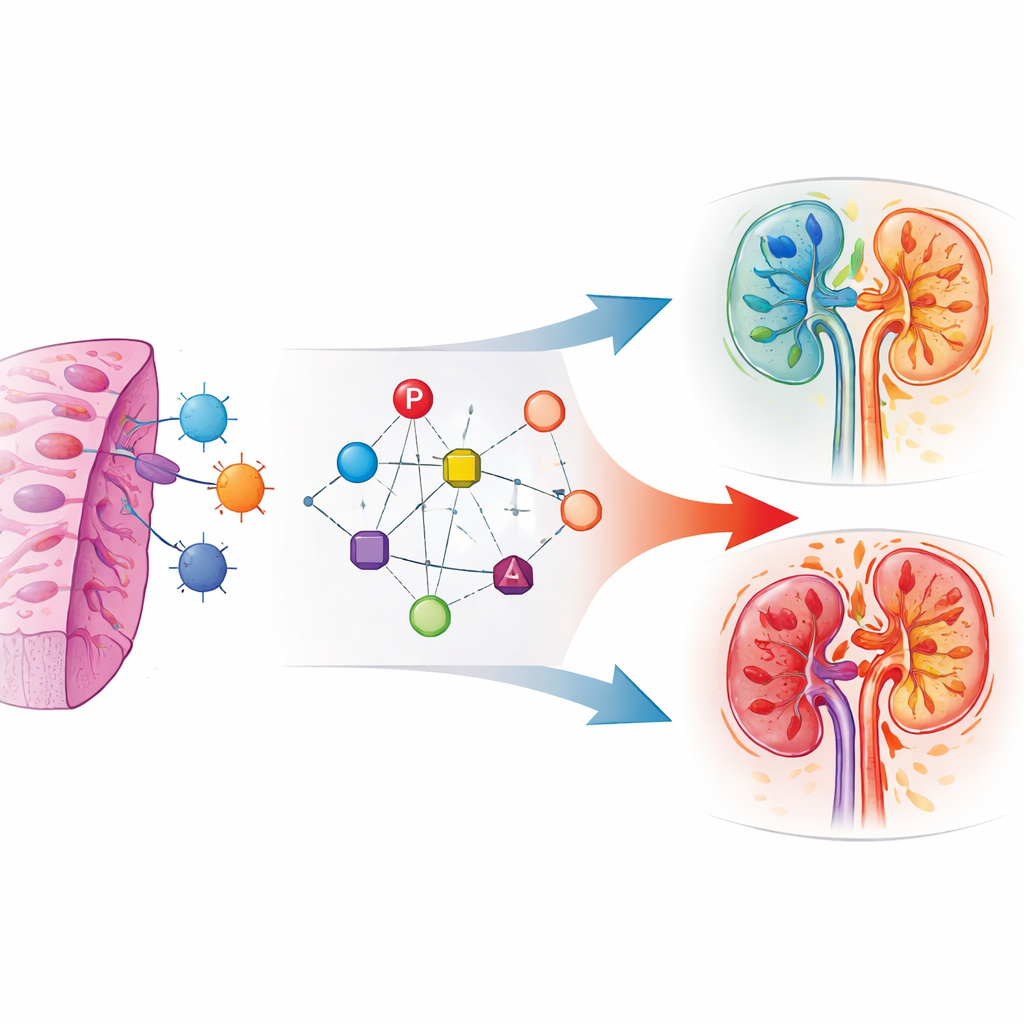
Transformando atividade gênica em uma pontuação de risco
A equipe analisou milhares de amostras de biópsias de receptores de transplante renal armazenadas em bancos públicos de expressão gênica. Primeiro procuraram genes que se comportavam de modo diferente em biópsias com rejeição versus sem rejeição e depois se concentraram naqueles ligados à maquinaria de marcação de proteínas. Seis genes mostraram as diferenças mais fortes e consistentes, especialmente em amostras com rejeição evidente. Os cientistas combinaram a atividade desses genes em uma única “pontuação” que podia ser calculada para cada biópsia. Pontuações mais altas tendiam a aparecer em pacientes com rejeição, e a pontuação teve bom desempenho ao separar casos de rejeição de casos estáveis em vários grupos independentes de pacientes.
Ligando padrões gênicos a tipos específicos de ataque imune
Quando os pesquisadores compararam diferentes tipos de rejeição, encontraram um padrão marcante: os níveis dos seis genes-chave aumentavam gradualmente da ausência de rejeição para a rejeição mediada por anticorpos, eram ainda mais altos na rejeição mediada por células T e atingiam o pico quando ambos os mecanismos estavam presentes simultaneamente. Isso sugere que o padrão gênico funciona como um botão que indica a intensidade e a complexidade do ataque imune, especialmente quando as células T estão fortemente envolvidas. A pontuação também acompanhou mudanças nas populações de células imunes dentro do rim, incluindo células T reguladoras e outras células especializadas que tanto podem danificar quanto proteger o órgão, refletindo uma luta dinâmica entre lesão e reparo.
Do modelo de laboratório a uma potencial ferramenta de beira do leito
Para avançar em direção ao uso clínico, os autores criaram um gráfico simples que traduz o padrão dos seis genes de uma biópsia em um risco estimado de rejeição. Em seguida, verificaram os genes em um pequeno grupo de pacientes transplantados do mundo real usando um método laboratorial padrão. Nos dois pacientes com rejeição mista, dois dos genes se destacaram por níveis particularmente altos, correspondendo aos padrões observados nos conjuntos de dados maiores. Um paciente com outra doença renal, mas sem rejeição formal, também apresentou níveis altos dos seis genes, sugerindo que essa assinatura pode ser um alarme sensível para atividade imune intensa no rim, e não apenas para rejeição clássica. Isso significa que a ferramenta poderia ajudar a sinalizar pacientes que precisam de monitoramento mais próximo, embora ainda exija que os médicos interpretem os resultados no contexto de outras informações clínicas.
O que isso pode significar para pacientes transplantados
Em termos práticos, este estudo sugere que ler um pequeno conjunto de genes de “marcação de proteínas” em uma biópsia renal pode revelar com que intensidade o sistema imunológico está atacando o enxerto, muitas vezes antes que os testes padrão tornem o problema óbvio. Embora sejam necessários estudos prospectivos maiores e o método não substitua o julgamento do médico, uma pontuação baseada em genes poderia um dia ajudar a ajustar doses de medicamentos, programar biópsias de seguimento de forma mais inteligente e detectar problemas cedo o suficiente para salvar mais rins transplantados.
Citação: Shan, Z., Yu, S., Wang, J. et al. Identification of ubiquitination-related signature genes for predicting kidney transplant rejection. Sci Rep 16, 8102 (2026). https://doi.org/10.1038/s41598-026-38022-8
Palavras-chave: rejeição de transplante renal, expressão gênica, ubiquitinação, biomarcadores, resposta imune