Clear Sky Science · pt
O primeiro genoma mitocondrial para Sterictiphorinae (Hymenoptera: Argidae) e insights sobre a filogenia dos Argidae
Por que esses minúsculos comedores de folha importam
As serras da família Argidae podem parecer discretas, mas suas formas jovens, semelhantes a lagartas, conseguem desfolhar plantações e florestas, tornando‑as pragas agrícolas importantes. Ainda assim, ao nível do DNA, especialmente nas mitocôndrias produtoras de energia dentro de suas células, esses insetos têm sido pouco estudados. Este artigo reporta o primeiro genoma mitocondrial completo para uma serra coreana, Sterictiphora koreana, e o utiliza para explorar como essa família repleta de pragas evoluiu ao longo de mais de 160 milhões de anos.
Espiando as usinas de energia de uma serra
Os autores decodificaram todo o DNA mitocondrial de uma única fêmea de S. koreana. Como na maioria dos animais, esse minúsculo genoma “usina” é um anel de DNA que carrega 37 genes que ajudam a célula a obter energia. Em S. koreana, o anel é incomumente longo — cerca de 17.900 letras de DNA, comparado com aproximadamente 15.600 em três espécies relacionadas de Argidae — principalmente porque uma região não codificante rica em A e T se expandiu. Apesar dessa diferença de tamanho, a disposição geral dos genes bate com o padrão típico visto em outras serras, com a maioria dos genes em uma fita de DNA e um conjunto menor na fita oposta, e genes de RNA de transferência formando as clássicas estruturas em trevo, com algumas peculiaridades.

Padões de letras que sugerem laços familiares
O DNA mitocondrial tende a ser fortemente enviesado para as letras A e T em muitos insetos, e essas serras não são exceção. As quatro espécies de Argidae estudadas têm genomas com cerca de 80% de A ou T, mas o equilíbrio não é idêntico. As três espécies previamente conhecidas, todas da subfamília Arginae, são ainda mais ricas em A+T do que S. koreana, que pertence à subfamília Sterictiphorinae. Desequilíbrios sutis na frequência de A em relação a T, e de G em relação a C, diferem entre espécies e entre partes do genoma. Uma espécie, Arge aurora, até inverte alguns desses enviesamentos, destacando‑se entre seus parentes. Os pesquisadores também mostram que certos aminoácidos, como leucina, isoleucina, metionina e fenilalanina, são codificados com mais frequência que outros, refletindo como esse alfabeto enviesado molda as “palavras” genéticas usadas pelas serras.
Genes embaralhados e código de mudança lenta
Embora o plano mitocondrial geral seja conservador, pequenos genes chamados tRNAs tendem a ser deslocados, e suas novas posições podem marcar grandes ramos na árvore familiar das serras. Nas espécies de Arginae, um gene tRNA (trnW) saltou para uma nova posição próxima à região rica em A+T. Em S. koreana, um conjunto diferente de tRNAs (trnK, trnD, trnI e trnM) foi reorganizado em um padrão consistente. Esses rearranjos distintos provavelmente assinalam as duas subfamílias como linhagens separadas. Quando a equipe examinou a rapidez com que os genes codificadores de proteína acumulam mudanças, descobriram que a maioria das alterações é eliminada pela seleção natural, um padrão chamado seleção purificadora. Um gene em particular, cox1, muda especialmente devagar, reforçando sua utilidade como “código de barras” de DNA para distinguir espécies.
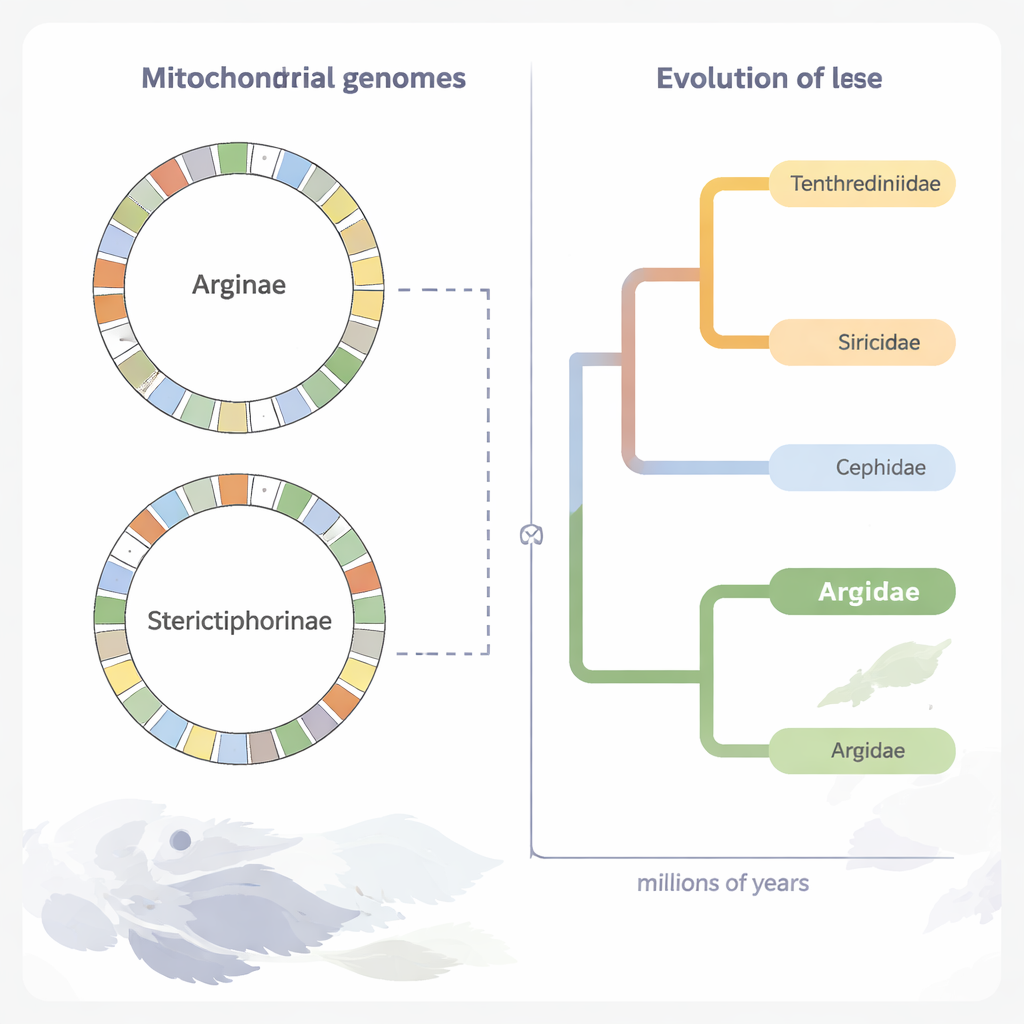
Reconstruindo uma antiga árvore familiar das serras
Usando as porções codificadoras de proteína do DNA mitocondrial de 70 espécies de serras, os pesquisadores reconstruíram uma árvore evolutiva detalhada. Suas análises confirmam que Argidae forma um grupo natural e está intimamente aliado a outra família, Pergidae, dentro da superfamília maior das serras, Tenthredinoidea. Ao integrar evidências fósseis, estimam que a separação entre Argidae–Pergidae e outras famílias de serras ocorreu cerca de 206 milhões de anos atrás, e que os próprios Argidae surgiram há aproximadamente 166 milhões de anos, no Jurássico Médio. As duas principais subfamílias de Argidae, Arginae e Sterictiphorinae, parecem ter se separado no Cretáceo Inferior, por volta de 126 milhões de anos atrás, uma época em que as plantas com flores também estavam se diversificando.
O que isso significa para a ciência e o controle de pragas
Este primeiro genoma mitocondrial de Sterictiphorinae preenche uma lacuna importante em nossa imagem genética dos Argidae. Mostra que características de pequena escala — como comprimento do genoma, ordem dos genes e enviesamentos de letras — podem separar de forma confiável grandes grupos dentro dessa família de pragas e ajudá‑los a se ancorar na árvore mais ampla das serras. Para não‑especialistas, a ideia principal é que, ao ler e comparar os minúsculos anéis de DNA nas usinas celulares dos insetos, os cientistas podem traçar como serras destruidoras de folhas estão relacionadas, estimar quando suas linhagens surgiram e, em última instância, construir uma estrutura mais robusta para identificar espécies e entender sua disseminação em plantações e florestas.
Citação: Park, B., Hwang, U.W. The first mitochondrial genome for Sterictiphorinae (Hymenoptera: Argidae) and insights into argid phylogeny. Sci Rep 16, 7154 (2026). https://doi.org/10.1038/s41598-026-38021-9
Palavras-chave: evolução das serras, genoma mitocondrial, filogenia de insetos, pragas florestais e agrícolas, código de barras de DNA