Clear Sky Science · pt
Uma estrutura adaptativa à estrutura do genoma para estimativa de endogamia baseada em ROH em Penaeus vannamei
Por que as árvores genealógicas de camarões importam para o seu prato
Fazendas de camarão modernas abastecem grande parte dos frutos do mar consumidos no mundo, mas reproduzir repetidamente as mesmas linhagens pode degradar silenciosamente a saúde dos estoques. Quando parentes próximos se cruzam, genes deletérios recessivos podem se combinar, reduzindo crescimento, sobrevivência e resistência a doenças. Este estudo faz uma pergunta aparentemente simples, com grandes implicações para a aquicultura global: como medir a endogamia em camarões de maneira precisa o bastante para manter os estoques saudáveis e produtivos?
Pegadas genéticas escondidas da endogamia
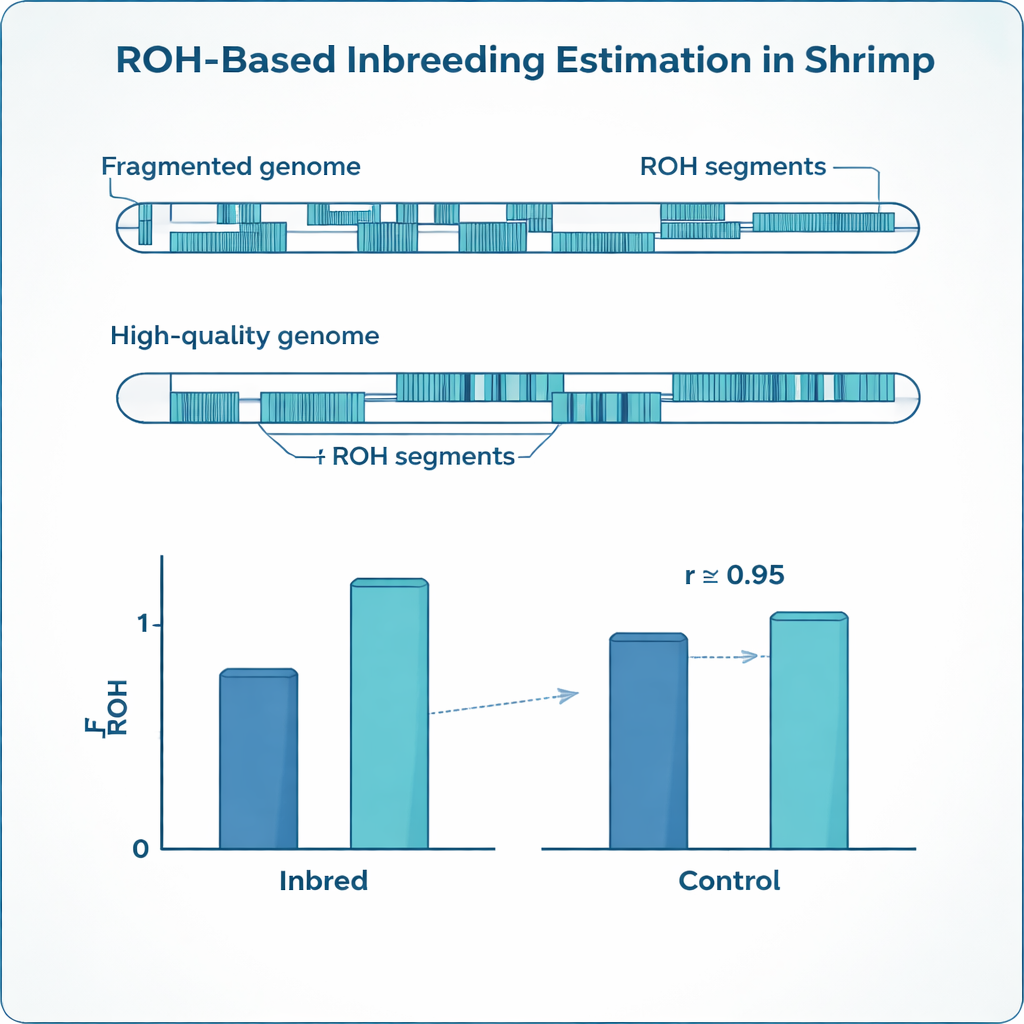
A endogamia deixa marcas detectáveis no DNA. Em vez de portar duas versões levemente diferentes de muitos genes, animais endogâmicos tendem a apresentar longos trechos onde ambas as cópias são idênticas. Os geneticistas chamam esses trechos de “runs of homozygosity”, ou ROH. Somando quanto do genoma de um animal cai nesses trechos, os pesquisadores conseguem estimar seu nível de endogamia com mais precisão do que acompanhando pedigrees em papel, que muitas vezes são incompletos ou contêm erros. Essa medida baseada em ROH, conhecida como FROH, tornou‑se padrão em bovinos, suínos e outros animais de produção, mas genomas de camarão apresentam desafios específicos que tornam métodos prontos pouco confiáveis.
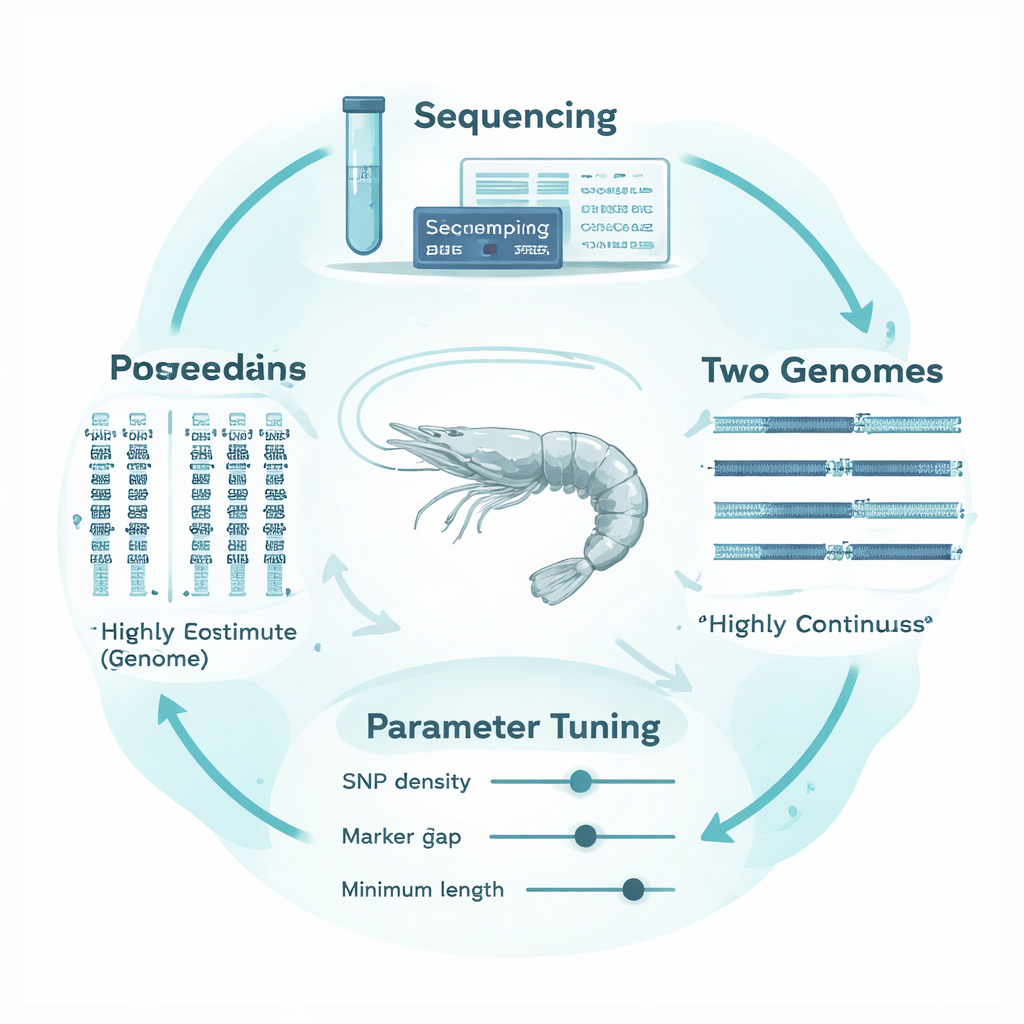
Por que os genomas de camarão são especialmente complicados
O camarão‑branco (Penaeus vannamei), o mais cultivado no mundo, possui genomas altamente fragmentados e complexos. Em vez de longas sequências cromossômicas contínuas, muitos mapas genômicos disponíveis estão quebrados em milhares de pedaços menores, separados por lacunas e regiões repetitivas. Marcadores genéticos estão distribuídos de forma desigual nesse mosaico, e a espécie apresenta diversidade genética muito alta. Métodos e configurações de software originalmente ajustados para genomas de mamíferos bem mapeados podem, portanto, confundir lacunas técnicas com quebras reais em ROH, ou interpretar semelhanças curtas de fundo como sinais verdadeiros de endogamia. O resultado é um alto risco de estimar mal o nível de endogamia de um camarão.
Construindo uma régua de medida sensível à estrutura do genoma
Para resolver isso, os autores projetaram uma estrutura “adaptativa à estrutura do genoma” que ajusta a análise de ROH às particularidades do DNA de camarões. Eles criaram treze famílias de camarões altamente endogâmicas por meio de cruzamentos controlados e sequenciaram profundamente os genomas de cinco dessas famílias e de seus progenitores. De forma crucial, alinharam os mesmos dados de sequenciamento a duas referências genômicas muito diferentes: uma montagem mais antiga e fragmentada e uma versão mais recente e altamente contínua. Usando a ferramenta comum PLINK, testaram sistematicamente como oito parâmetros chave afetavam as chamadas de ROH, com foco em três especialmente sensíveis à estrutura do genoma: quão densos os marcadores devem ser, qual tamanho de lacuna entre marcadores é permitido dentro de um run e qual o comprimento mínimo para que um run seja contabilizado. Construíram janelas genômicas empíricas não sobrepostas para monitorar o espaçamento local de marcadores e dados ausentes, e usaram a “cobertura genômica” dessas janelas, junto com a estabilidade de FROH e dos comprimentos de ROH, como guias objetivas para escolher limites sensatos.
Botões diferentes, mesma imagem de endogamia
As configurações otimizadas mostraram‑se muito diferentes para as duas referências genômicas. O genoma fragmentado exigiu marcadores muito mais densos, lacunas permitidas menores e comprimentos mínimos de runs mais curtos do que a referência de alta qualidade, para evitar fragmentar ROH reais em muitos pedaços pequenos. Ainda assim, após ajustar esses parâmetros separadamente, as estimativas de endogamia de ambas as referências convergiram: o FROH médio nos camarões endogâmicos foi de cerca de 0,24 em ambos os casos, correspondendo de perto ao valor esperado pelos cruzamentos planejados e mostrando forte concordância entre si. Ao mesmo tempo, o genoma mais contínuo revelou menos segmentos de ROH, porém muito mais longos, enquanto o mapa fragmentado fragmentou muitos desses em trechos curtos. O estudo também expôs diferenças marcantes entre irmãos de mesma ninhada: mesmo dentro da mesma família, os níveis de endogamia variaram amplamente, algo que registros de pedigree simples não capturam.
Ferramentas mais precisas para estoques de camarão mais saudáveis
Para não especialistas, a mensagem principal é direta: medir endogamia a partir do DNA pode ser altamente preciso em camarões de cultivo, mas apenas se o método respeitar a estrutura subjacente do genoma. Ao fornecer uma receita prática para ajustar a análise de ROH a genomas de crustáceos fragmentados, este trabalho permite que criadores monitorem a endogamia animal por animal, em vez de depender de árvores genealógicas imperfeitas. Isso, por sua vez, pode ajudar a desenhar planos de acasalamento que mantenham diversidade genética enquanto melhoram crescimento e resiliência, apoiando uma aquicultura de camarão mais sustentável e oferecendo um modelo para outras espécies de aquicultura que enfrentam desafios genômicos semelhantes.
Citação: Zou, X., Zhou, H., Liu, M. et al. A genome-structure adaptive framework for ROH-based inbreeding estimation in Penaeus vannamei. Sci Rep 16, 6769 (2026). https://doi.org/10.1038/s41598-026-37622-8
Palavras-chave: criação de camarões, endogamia, seleção genômica, runs of homozygosity, genética da aquicultura