Clear Sky Science · pt
Quantificação e rastreamento rápidos e sem aprendizado de organoides com OrganoSeg2
Por que pequenos tecidos cultivados em laboratório importam
Em laboratórios ao redor do mundo, cientistas cultivam versões em miniatura de tecidos humanos chamadas organoides. Esses pequenos aglomerados 3D de células podem imitar o comportamento de órgãos ou tumores reais, tornando‑se ferramentas poderosas para estudar doenças e testar tratamentos. Mas há um gargalo: pesquisadores podem coletar milhares de imagens microscópicas em baixa ampliação de organoides e ainda assim ter dificuldade para medir como cada um cresce, muda de forma ou morre ao longo do tempo. Este artigo apresenta o OrganoSeg2, um software redesenhado que transforma essas imagens acinzentadas em medidas ricas e confiáveis de cada organoide — sem precisar de treinamento em inteligência artificial ou de equipamentos de imagem caros.
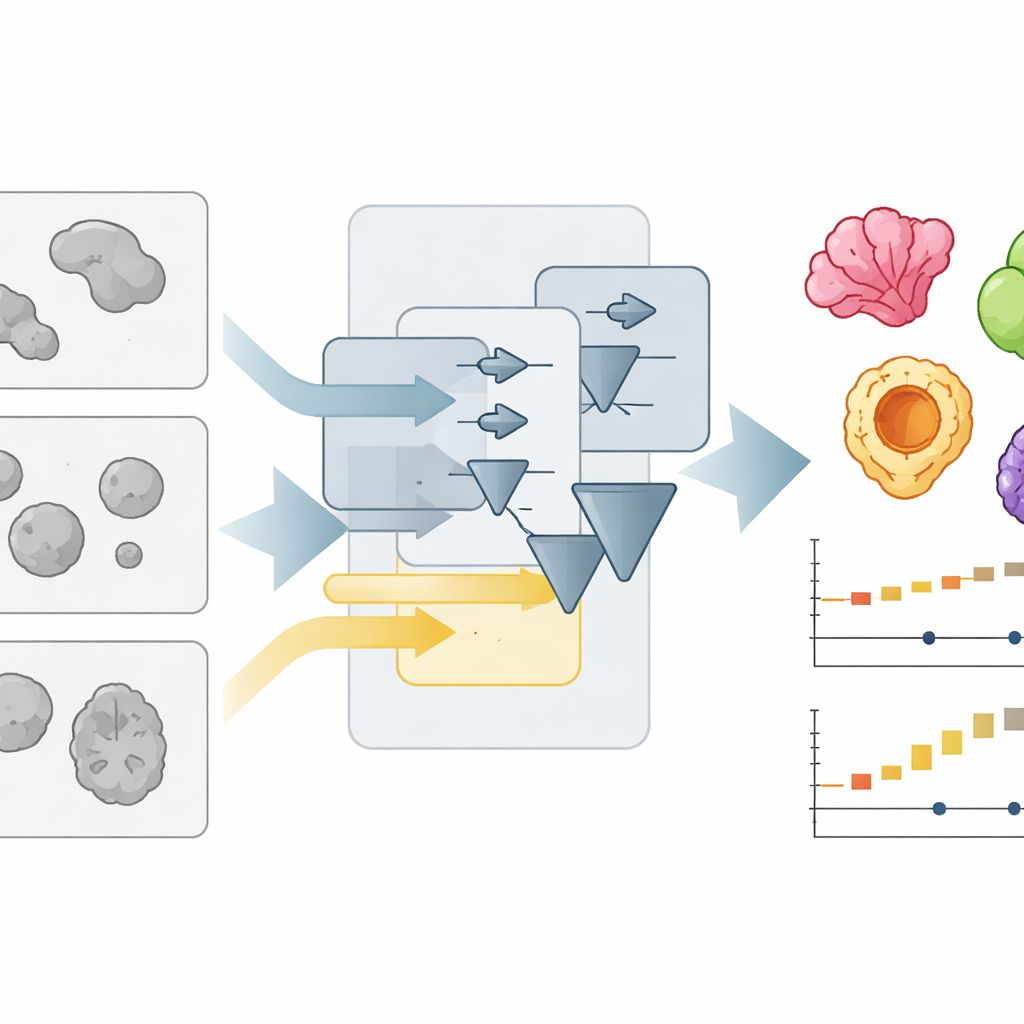
Uma nova forma de interpretar imagens microscópicas congestionadas
Organoides normalmente são fotografados com microscópios de campo claro simples, que os mostram como manchas tênues e sobrepostas. Delinear automaticamente cada mancha — “segmentar” a imagem — é bem mais difícil do que parece, especialmente quando laboratórios usam formatos de cultura, iluminação ou lentes diferentes. Os autores criaram anteriormente o OrganoSeg, um programa capaz de lidar com segmentação básica, mas que ficava lento e incômodo quando coleções de imagens cresciam para centenas. Com o OrganoSeg2, eles reconstruíram o software do zero em uma interface moderna, simplificaram o código interno e tornaram visíveis várias configurações ocultas para que os usuários possam ajustar como o programa separa organoides do fundo, separa vizinhos que se tocam e ignora artefatos nas bordas da imagem. O aplicativo agora registra essas escolhas como metadados, tornando as análises reprodutíveis e compartilháveis.
Acelerando o trabalho sem sacrificar os detalhes
Além da flexibilidade, a equipe focou fortemente em velocidade e experiência do usuário. Em versões anteriores, o software calculava automaticamente todas as possíveis medidas para cada organoide, mesmo quando apenas algumas eram necessárias. O OrganoSeg2, em vez disso, calcula apenas o que o usuário seleciona e reorganiza cálculos relacionados para que etapas demoradas sejam reaproveitadas de forma eficiente. Ele também reduz a quantidade de informação desenhada na tela, mostra rótulos apenas quando necessário e adiciona atalhos de teclado e ferramentas interativas para remover rapidamente detritos ou objetos que não são organoides. Essas escolhas de design reduzem operações comuns — como segmentar imagens, exibir contornos e exportar dados — em aproximadamente dez vezes, tornando prático lidar com imagens grandes em mosaico e experimentos de lapso de tempo longos em um computador comum.
Superando rivais de alta tecnologia em dados reais
Para testar o desempenho do OrganoSeg2, os autores o compararam com várias outras ferramentas de segmentação, incluindo sistemas de deep learning que precisam ser treinados com exemplos rotulados manualmente. Eles reuniram conjuntos de imagens de seis fontes diferentes — como organoides de cólon, pulmão, pâncreas, cérebro e mama, além de corpos embrioides — onde especialistas humanos já traçaram as bordas dos organoides. Usando uma pontuação padrão de precisão que mede quanto os contornos automatizados se sobrepõem aos manuais, o OrganoSeg2 igualou ou superou ferramentas especializadas na maioria dos conjuntos de dados e liderou claramente em imagens desafiadoras de câncer de mama, repletas de materiais dispersos e organoides de formas estranhas. Notavelmente, o OrganoSeg2 alcançou esse desempenho sem precisar de dezenas de milhares de exemplos de treinamento e rodou pelo menos tão rápido quanto os concorrentes, inclusive os baseados em inteligência artificial.
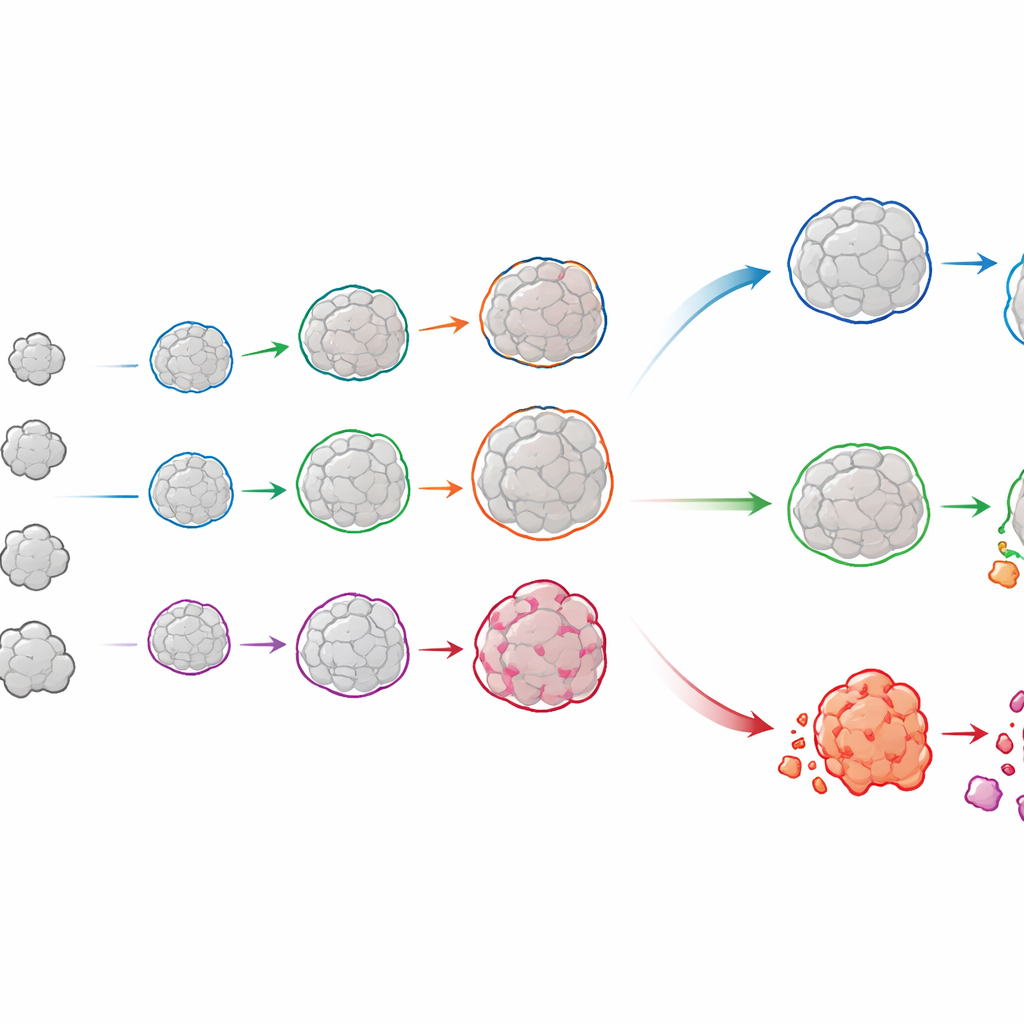
Acompanhando a história de vida de cada organoide
O OrganoSeg2 faz mais do que delinear organoides em imagens isoladas. Ele pode alinhar imagens tiradas em dias diferentes e vincular o mesmo organoide ao longo do tempo, construindo um histórico de crescimento para cada um. Quando os autores aplicaram isso a organoides cultivados diretamente de tumores luminais de mama de pacientes, observaram que organoides individuais raramente cresciam de forma contínua; em vez disso, muitos desaceleravam ou atingiam platôs, refletindo como tumores reais contêm uma mistura de regiões de crescimento rápido e lento. Ajustando essas trajetórias a um modelo simples de crescimento, a equipe pôde quantificar tanto a velocidade com que cada organoide se expandia quanto o tamanho provável que alcançaria. Comparar esses padrões entre pacientes revelou que tumores com crescimento global similar podem ocultar misturas muito diferentes de comportamentos subjacentes — diferenças que podem ser relevantes para prever a resposta ao tratamento.
Observando células cancerígenas viverem e morrer sob radiação
O software também integra imagens de campo claro com corantes fluorescentes que informam sobre a saúde celular. Em experimentos recentes, os autores expuseram organoides de câncer de mama a doses de radiação semelhantes às usadas na clínica e os tingiram com um marcador de células vivas que se acende durante morte celular programada, além de um segundo corante que revela células mortas no ponto final. O OrganoSeg2 usou a imagem de campo claro para definir a forma do organoide e então mediu os sinais fluorescentes dentro de cada um ao longo de vários dias. Isso permitiu à equipe rastrear, organoide por organoide, quando a radiação desencadeou a morte e com que intensidade. Alguns organoides de pacientes quase não responderam, enquanto outros mostraram alta sensibilidade mesmo em doses mais baixas, destacando quão variável pode ser a resposta tumoral.
O que isso significa para pesquisas e cuidados futuros
Em conjunto, o trabalho mostra que um processamento de imagem cuidadoso e ajustável pode rivalizar ou superar métodos complexos de deep learning para uma ampla gama de imagens de organoides, mantendo transparência e facilidade de ajuste. O OrganoSeg2 transforma filmes simples de baixa ampliação de organoides em registros detalhados de como cada pequeno tecido cresce e sobrevive sob diferentes condições. Para pesquisadores básicos, oferece uma maneira robusta de dissecar a diversidade oculta dentro de culturas de organoides. Para estudos sobre câncer em particular, abre a possibilidade de usar organoides derivados de pacientes não apenas para triagens de drogas com resposta sim/não, mas para medições ricas e temporais de crescimento e morte celular que, um dia, podem ajudar a ajustar tratamentos com mais precisão.
Citação: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Palavras-chave: organoides, análise de imagem, pesquisa sobre câncer, microscopia, resposta à radiação