Clear Sky Science · pt
Descobrindo potenciais MTAs, genes candidatos e redes regulatórias de microRNAs envolvidos na tolerância ao estresse por salinidade acionada em Aegilops tauschii iraniana
Por que solos salgados ameaçam nosso pão diário
À medida que as mudanças climáticas aumentam a seca e a água de irrigação se torna mais salina, vastas áreas agrícolas estão ficando salinas demais para o trigo comum. Isso importa para todos que dependem do pão como alimento básico. O estudo resumido aqui recorre a uma gramínea selvagem, Aegilops tauschii, ancestral direto do trigo-bread moderno, para desvendar as ferramentas genéticas ocultas — e pequenas moléculas reguladoras — que ajudam as plantas a lidar com condições salinas. Ao mapear essas defesas naturais, os pesquisadores esperam oferecer aos melhoristas novas maneiras de desenvolver variedades de trigo que permaneçam produtivas mesmo quando o solo fica salobro.
Parente selvagem do trigo como recurso oculto
Aegilops tauschii cresce naturalmente ao longo do Crescente Fértil, incluindo o Irã, onde se adaptou ao longo de milhares de anos a ambientes áridos, secos e frequentemente salgados. Essa espécie doou a porção “D” do genoma que o trigo-bread moderno carrega hoje. Como as variedades de trigo de alto rendimento atuais foram originadas a partir de uma base genética relativamente estreita, muitas vezes lhes faltam a gama completa de características de tolerância ao estresse que ainda existem em seus parentes selvagens. Os autores reuniram 77 ecótipos iranianos de Aegilops tauschii (formas locais) e os cultivaram tanto em condições normais quanto salinas na fase de plântula, medindo características como comprimento de raiz e parte aérea, peso fresco e seco, e área de folha e raiz. A salinidade reduziu drasticamente todos esses traços, confirmando que altos níveis de sal são de fato prejudiciais para plantas jovens.
Lendo as impressões digitais do DNA da tolerância ao sal
Para entender por que algumas plantas selvagens resistiam melhor ao sal do que outras, a equipe recorreu a marcadores de DNA — sequências curtas e fáceis de medir espalhadas pelo genoma que funcionam como códigos de barras para genes próximos. Usando uma combinação de marcadores “aleatórios” e marcadores semi-aleatórios RAMP, eles pontuaram centenas de bandas de DNA e avaliaram quão diversa era a coleção. Encontraram altos níveis de variação genética, com certos sistemas de marcadores, como ISJ9 e OPE03-Xgwm44-7DF, fornecendo poder especialmente forte para distinguir um ecótipo do outro. Essa rica diversidade significa que Aegilops tauschii iraniana ainda abriga muitas variantes genéticas únicas que os melhoristas podem aproveitar. Ao ligar estatisticamente bandas de DNA particulares a traços de plântula sob estresse salino, os pesquisadores identificaram 115 associações marcador–traço, apontando para regiões genômicas que influenciam quão bem raízes, parte aérea e folhas se desenvolvem em ambientes salgados.
Dos marcadores a genes de defesa contra estresse que funcionam
Encontrar um marcador de DNA útil é apenas o primeiro passo; depois, os autores perguntaram quais genes reais ficam próximos a esses marcadores e podem estar desempenhando o papel. Usando o genoma de referência do trigo, eles pesquisaram 500.000 pares de bases ao redor de cada marcador associado e descobriram 254 genes candidatos. Muitos desses genes foram independentemente confirmados por grandes conjuntos de dados de sequenciamento de RNA como tendo sua atividade aumentada ou diminuída quando as plantas enfrentavam estresse ambiental, incluindo frio, calor, escassez de nutrientes e doença. Os genes candidatos foram enriquecidos por funções em respostas de defesa e proteção contra calor e danos oxidativos. Vários codificam proteínas como receptores de resistência a doenças, chaperonas de choque térmico e proteínas do tipo tafina e osmotina, que ajudam a estabilizar as células quando o sal causa perda de água e acúmulo de moléculas reativas de oxigênio. A análise de vias destacou o metabolismo do glutationa, um sistema químico central que as plantas usam para desintoxicar subprodutos induzidos pelo estresse.
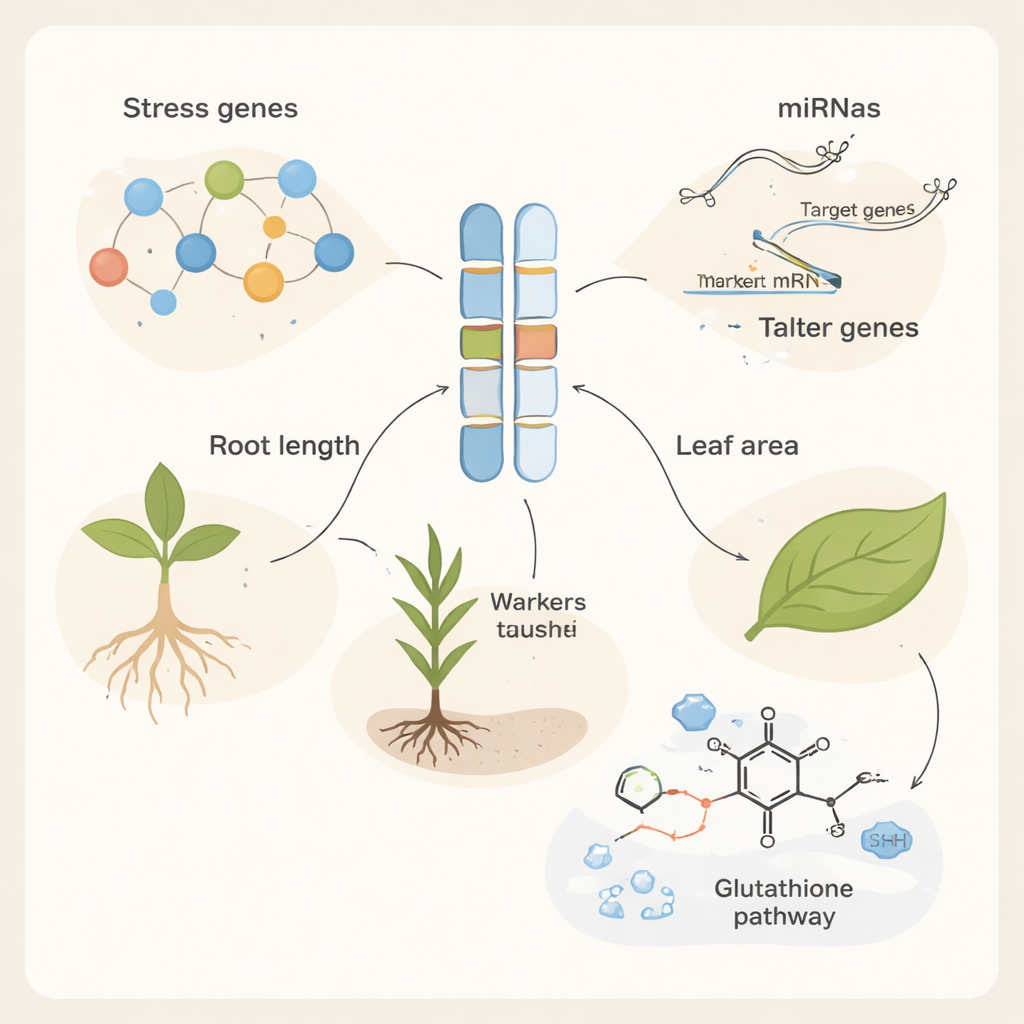
Interruptores de RNA minúsculos que afinam as respostas ao estresse
Genes não atuam isoladamente; são controlados por microRNAs, moléculas de RNA muito curtas que podem desligar ou atenuar a atividade gênica. Os pesquisadores previram quais microRNAs do trigo poderiam visar seus genes candidatos e descobriram 107 microRNAs distintos formando redes regulatórias densas. Muitos desses pequenos reguladores já eram conhecidos por responder à seca, calor, metais ou salinidade. Por exemplo, microRNAs específicos anteriormente ligados à tolerância ao sal, tolerância ao calor ou “memória do estresse” foram encontrados controlando genes-chave de defesa e desintoxicação identificados neste estudo. Alguns genes foram alvo de múltiplos microRNAs, sugerindo que as plantas sobrepõem vários interruptores regulatórios para ajustar finamente sua resposta conforme os níveis de estresse mudam.
Levar a resiliência selvagem aos campos dos agricultores
Juntos, o catálogo de marcadores de DNA diversos, 254 genes candidatos e 107 microRNAs regulatórios oferece um roteiro para melhorar o desempenho do trigo em solos salgados. Melhoristas podem transformar os marcadores mais informativos em testes de laboratório simples para rastrear grandes números de plantas em busca de traços ocultos de tolerância ao sal, uma estratégia conhecida como seleção assistida por marcadores. A longo prazo, os genes mais promissores e seus reguladores microRNA poderiam ser introduzidos deliberadamente ou editados em variedades de trigo sensíveis para reforçar suas defesas naturais. Embora o estudo ainda exija validação experimental sob salinidade em plantas vivas, ele mostra claramente que o parente selvagem Aegilops tauschii possui ferramentas genéticas poderosas que, se usadas com critério, podem ajudar a proteger as colheitas de trigo à medida que a salinidade e as pressões climáticas se intensificam.
Citação: Sabouri, H., Nikkhah, N., Kazerani, B. et al. Uncovering the potential MTAs, candidate genes and microRNAs regulatory networks involved in salinity stress tolerance triggered in Iranian Aegilops tauschii. Sci Rep 16, 6877 (2026). https://doi.org/10.1038/s41598-026-37365-6
Palavras-chave: tolerância à salinidade, melhoramento do trigo, Aegilops tauschii, genes responsivos ao estresse, microRNAs de plantas