Clear Sky Science · pt
Uma estrutura tri-ômica e de aprendizado de máquina identifica biomarcadores prognósticos e assinaturas metabólicas na sepse
Por que isso importa para pessoas com infecções graves
A sepse é uma reação potencialmente fatal a uma infecção que pode levar o sistema imunológico a um estado de hiperatividade e provocar falência de órgãos. Os médicos sabem que identificar a sepse precocemente e ajustar o tratamento para cada paciente pode salvar vidas, mas os exames de sangue atuais são ferramentas imprecisas: muitas vezes dizem pouco sobre quem vai melhorar e quem está em maior risco. Este estudo usa uma combinação poderosa de três tipos de medidas moleculares e aprendizado de máquina moderno para procurar sinais de alerta mais precisos no sangue de pacientes com sepse.
Vendo o sangue por três lentes diferentes
Em vez de focar em um único tipo de molécula, os pesquisadores perfilaram os mesmos pacientes de três maneiras ao mesmo tempo. Mediram quais genes estavam ativados ou desativados (transcriptômica), quais proteínas estavam presentes e ativas (proteômica) e quais pequenas moléculas metabólicas circulavam (metabolômica). Coletaram sangue de 21 pacientes com sepse e 10 voluntários saudáveis e usaram estatística avançada para ver como essas três camadas mudavam em conjunto na doença. Essa visão “tri-ômica” ajuda a superar um problema chave: na sepse, a atividade gênica e os níveis de proteína podem se desvincular, então olhar apenas uma camada pode ser enganoso.
Treinando algoritmos para identificar padrões de alto risco
Entre milhares de genes e proteínas, a equipe primeiro usou um método de rede para encontrar grupos que se moviam em conjunto na sepse. Em seguida, confrontaram esses grupos com proteínas que diferiam claramente entre pacientes e controles saudáveis, chegando a 32 candidatos fortes. Para reduzir ainda mais essa lista, recorreram ao aprendizado de máquina, usando dois algoritmos complementares para eliminar sinais mais fracos e manter apenas os mais informativos. Ao testar como esses genes remanescentes se relacionavam com a sobrevida em um grande conjunto público de dados sobre sepse, dois se destacaram: TPR e ERN1. Pacientes com níveis mais altos de TPR tendiam a sobreviver por mais tempo, enquanto níveis elevados de ERN1 foram associados a desfechos piores.
Ligando células imunes e metabolismo alterado
O estudo não se limitou a genes e proteínas. Ao escanear milhares de metabólitos no sangue dos pacientes, os pesquisadores encontraram 136 pequenas moléculas que acompanharam de perto TPR e ERN1. Muitas faziam parte de vias que lidam com lipídios de membrana celular e ácidos graxos, essenciais para como células imunes sinalizam e como a inflamação se espalha. Ao mesmo tempo, uma análise de célula única — que examina células imunes individuais do sangue em vez de misturá-las — mostrou que TPR e ERN1 são especialmente ativos em monócitos, macrófagos e células natural killer. Em conjunto, esses resultados sugerem que os dois marcadores se situam na encruzilhada entre as células que combatem infecções e a forma como essas células usam e remodelam lipídios e energia durante a sepse.
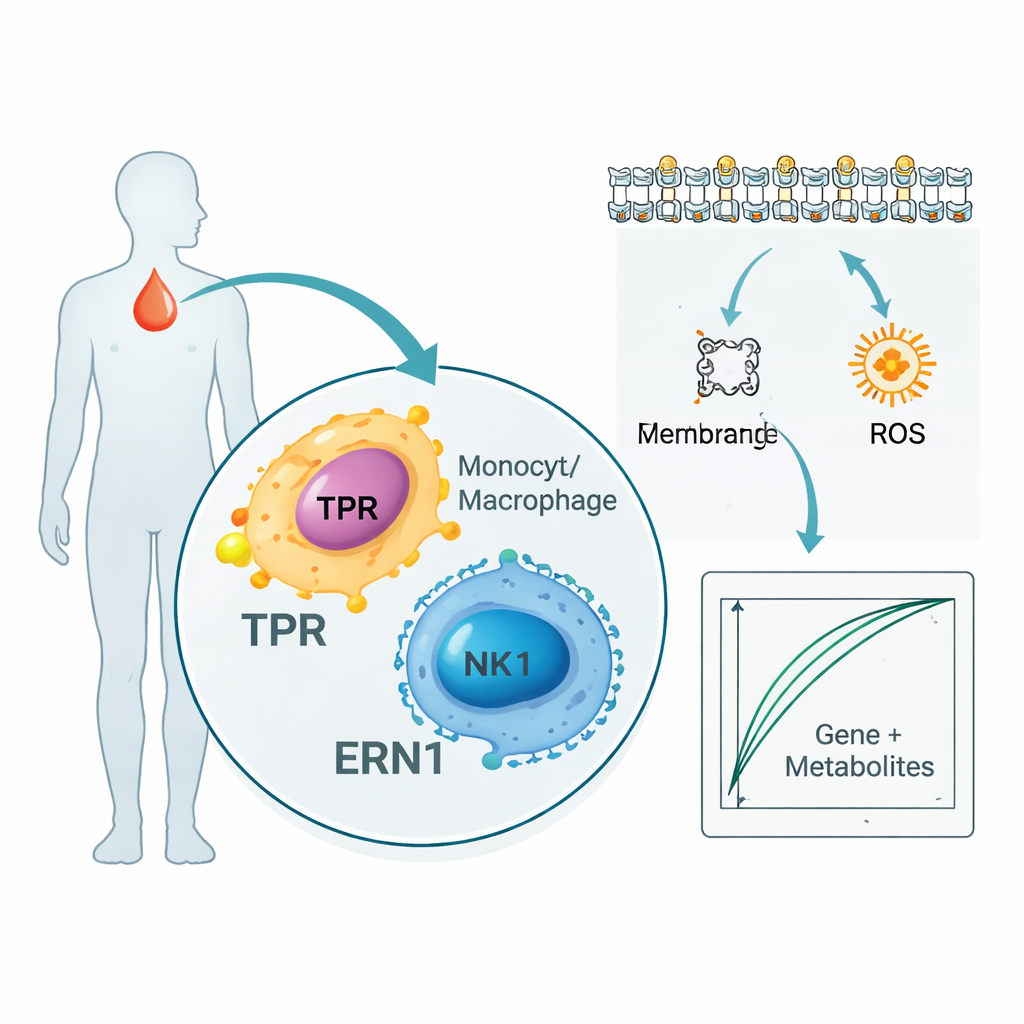
Construindo um teste de sangue como prova de conceito
Para explorar como essas descobertas poderiam se traduzir na prática, os autores combinaram os dois genes com cinco dos metabólitos mais informativos para treinar modelos computacionais simples que separavam pacientes com sepse de pessoas saudáveis. No pequeno conjunto de dados interno, essas assinaturas combinadas de "gene-mais-metabólito" quase perfeitamente identificaram quem tinha sepse. Os pesquisadores também consultaram grandes bancos de dados públicos que vinculam proteínas sanguíneas ao risco de doenças em dezenas de milhares de pessoas e descobriram que os níveis de proteína de TPR e ERN1 estavam consistentemente associados a condições relacionadas à sepse, adicionando outra camada de suporte. Ainda assim, os autores enfatizam que esses modelos são ferramentas em estágio inicial, destinadas a gerar hipóteses, e não testes prontos para uso clínico à beira do leito.
Compostos vegetais como pistas iniciais, não curas
Em uma etapa final, a equipe perguntou se alguma molécula natural poderia influenciar TPR ou ERN1. Eles pesquisaram um banco de dados especializado com quase 500 compostos purificados de medicinas tradicionais chinesas, cada um com seu próprio perfil de atividade gênica. Vários compostos pareceram aumentar ou diminuir fortemente esses dois genes em células cultivadas em laboratório, sugerindo que talvez um dia auxiliem pesquisadores a sondar a biologia da sepse ou a projetar novos medicamentos. No entanto, essas descobertas vêm apenas de correspondência computacional: não mostram que qualquer uma dessas substâncias seja segura ou eficaz em pessoas com sepse.
O que este trabalho realmente nos diz
Este estudo oferece um mapa detalhado em vez de uma solução pronta. Ao entrelaçar três camadas moleculares, dados de célula única e aprendizado de máquina, os autores destacam TPR e ERN1 — e as mudanças metabólicas conectadas a eles — como indicadores promissores de como o sistema imune e o metabolismo ficam desequilibrados na sepse. Para um público leigo, a mensagem principal é que a sepse não é uma doença única, mas um padrão em mudança de estados imunes e metabólicos, e que exames de sangue mais inteligentes podem um dia ajudar os médicos a ver em qual estado um paciente se encontra e ajustar o tratamento em conformidade. Antes que isso aconteça, esses sinais iniciais precisam ser testados e confirmados em grupos de pacientes muito maiores e mais diversos e em experimentos de laboratório que possam provar causa e efeito.
Citação: Li, X., Ke, G., Hu, Y. et al. A tri-omics and machine learning framework identifies prognostic biomarkers and metabolic signatures in sepsis. Sci Rep 16, 6648 (2026). https://doi.org/10.1038/s41598-026-37342-z
Palavras-chave: biomarcadores da sepse, multi-ômica, aprendizado de máquina na medicina, metabolismo imune, diagnósticos de precisão