Clear Sky Science · pt
Análise comparativa do cariótipo de onze espécies de Lilium da China usando FISH com oligo‑sondas de rDNA
Por que os cromossomos do lírio importam além do laboratório
Os lírios de jardim são mais do que flores bonitas e remédios tradicionais: eles também são modelos genéticos que ajudam cientistas a entender como novas espécies de plantas surgem e como classificá‑las corretamente. Este estudo investiga o interior das células de onze espécies chinesas de lírio, muitas usadas como alimento ou medicamento, para ver como seus cromossomos estão organizados e marcados. Ao comparar essas estruturas ocultas, os autores esclarecem quais lírios são realmente parentes próximos e fornecem evidências para resolver debates de longa data sobre as árvores genealógicas dos lírios.
Desembaralhando uma árvore genealógica confusa de lírios
O gênero Lilium contém cerca de 125 espécies espalhadas pelo Hemisfério Norte, com a China como um dos principais centros de diversidade. Por mais de um século, botânicos tentam agrupar essas espécies em seções naturais baseando‑se sobretudo em características visíveis, como a forma da flor. Mas flores parecidas nem sempre indicam parentesco próximo, e estudos genéticos de cloroplastos e núcleos às vezes deram respostas conflitantes sobre como os lírios estão relacionados. Em particular, um grupo chamado Leucolirion e suas duas subseções (6a e 6b), além de várias espécies do sudoeste e centro da China, têm sido difíceis de posicionar com confiança.
Lendo códigos de barras nos cromossomos
Para abordar esse problema, os autores recorreram à citogenética, o estudo dos cromossomos. Todas as onze espécies examinadas compartilham o mesmo conjunto básico de doze cromossomos, geralmente presentes como 24 em diploides; duas populações de Lilium lancifolium eram triploides, com 36 cromossomos. Ao microscópio, cada espécie mostra dois cromossomos maiores e dez menores, mas diferenças sutis em forma e comprimento podem ser difíceis de ver a olho nu. A equipe, portanto, mediu os tamanhos dos cromossomos com precisão e usou uma técnica chamada hibridização in situ por fluorescência (FISH) para ligar etiquetas de DNA fluorescentes a regiões específicas do DNA ribossômico (rDNA), que funcionam como códigos de barras brilhantes ao longo de cada cromossomo.
Encontrando padrões nos genomas dos lírios
Os pesquisadores mapearam dois tipos de rDNA — 5S e 35S — nos cromossomos de cada espécie. A maioria dos lírios tinha um sítio 5S e entre dois e seis sítios 35S, frequentemente em posições características. Por exemplo, quatro espécies tradicionalmente colocadas na subseção Leucolirion 6a (L. leucanthum, L. sargentiae, L. sulphureum e L. regale) compartilharam padrões muito semelhantes de marcas de rDNA nos mesmos pares de cromossomos, apontando para uma relação próxima, embora L. regale mostrasse algumas alterações adicionais. Em contraste, espécies da subseção irmã 6b e alguns lírios do grupo Sinomartagon exibiram arranjos de rDNA distintamente diferentes, ressaltando uma separação real entre esses dois grupos. Fora de Leucolirion, padrões fortemente compartilhados ligaram o amplamente cultivado L. lancifolium a L. pumilum e L. davidii, em concordância com estudos anteriores de sequências de DNA que os agrupavam juntos.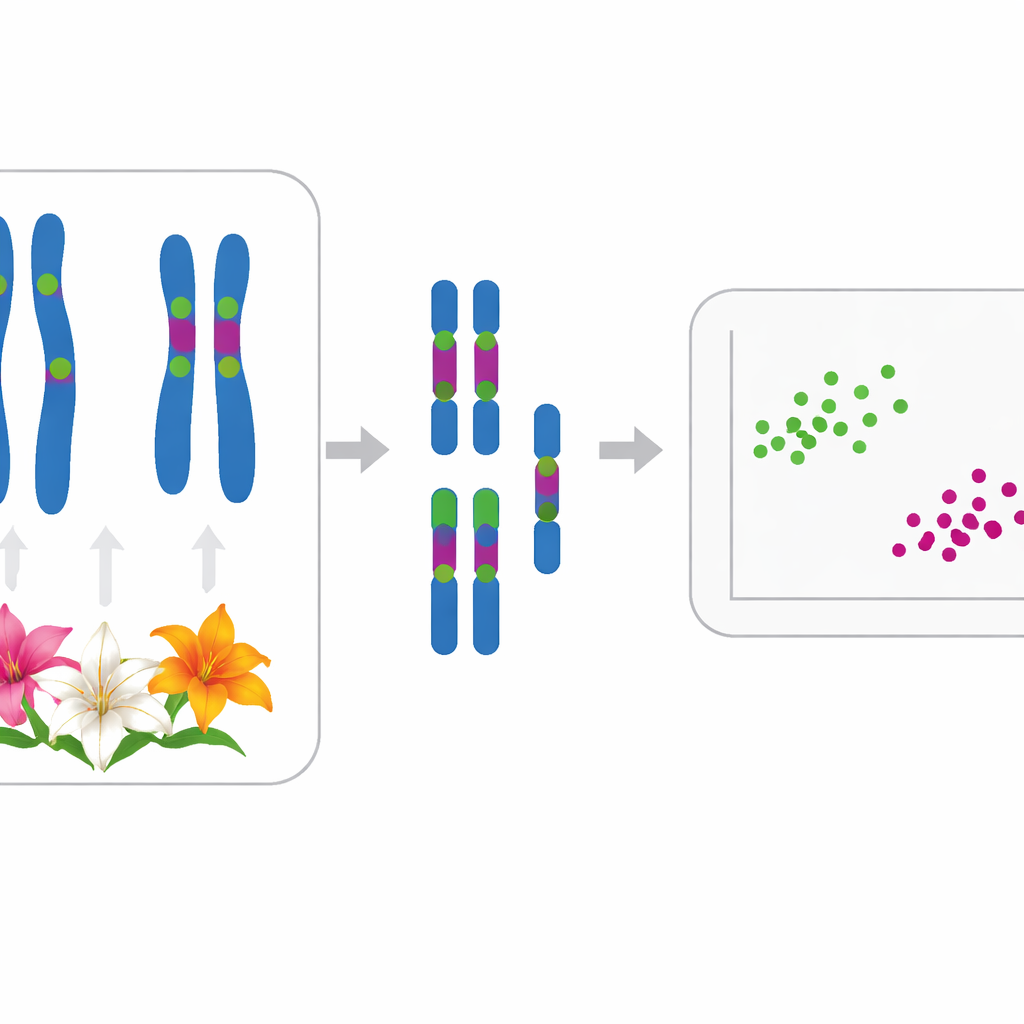
Transformando medições em um mapa de relações
Além das posições dos códigos de barras, a equipe quantificou o quão assimétrico era cada cariótipo — tanto nas posições dos centrômeros (a “cintura” do cromossomo) quanto nos comprimentos cromossômicos. Eles usaram dois índices estatísticos, MCA e CVCL, para capturar essas características e plotaram as onze espécies em um gráfico bidimensional. Cada espécie ocupou sua própria posição distinta, mostrando que mesmo cariótipos aparentemente semelhantes podem ser diferenciados quando medidos com cuidado. Uma análise estatística mais ampla (análise por coordenadas principais) então agrupou os lírios em dois aglomerados principais que correspondem bem à sua história evolutiva inferida. Um aglomerado continha L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale e as formas de L. lancifolium e L. davidii; o outro agrupou L. leucanthum, L. sargentiae, L. sulphureum, L. henryi e L. rosthornii.
O que isso significa para nomeação e uso dos lírios
Ao combinar medições cromossômicas detalhadas com mapas de códigos de barras de rDNA, este estudo mostra que as espécies de lírio diferem mais em seus cariótipos do que se pensava anteriormente e que essas diferenças carregam um sinal evolutivo claro. Em termos práticos, o trabalho apoia tratar a subseção Leucolirion 6a como um grupo natural e bem definido dentro do gênero Lilium, em consonância com propostas de classificação recentes. Para melhoristas, praticantes de fitoterapia e planejadores de conservação, ter uma imagem mais precisa de quem é parente de quem entre os lírios pode orientar cruzamentos, proteger a diversidade genética e garantir que variedades medicinais e comestíveis sejam identificadas e usadas corretamente.
Citação: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Palavras-chave: Lilium, cromossomos, hibridização in situ por fluorescência, evolução de plantas, citotaxonomia