Clear Sky Science · pt
Desenvolvimento e avaliação preliminar de ensaios de PCR em tempo real para seis bactérias do ácido lático
Micróbios amigos por trás dos alimentos do dia a dia
Muitos dos alimentos que enfileiram as prateleiras dos supermercados — de iogurte e queijo a picles e vegetais fermentados — devem seu sabor e possíveis benefícios à saúde a bactérias amigas conhecidas como probióticos. Mas, para aproveitar esses “bons micróbios” de forma segura e confiável, as empresas precisam ter absoluta certeza de quais espécies bacterianas estão realmente presentes em seus produtos. Este estudo descreve novos testes laboratoriais que podem identificar de forma rápida e precisa seis bactérias probióticas promissoras usadas em alimentos, ajudando a conectar a microbiologia de ponta com os alimentos que consumimos diariamente.
Por que essas bactérias probióticas são importantes
As seis bactérias no centro deste trabalho pertencem a um grupo mais amplo chamado bactérias do ácido láctico, usadas há muito tempo na fermentação. Pesquisas recentes sugerem que elas fazem muito mais do que azedar leite ou repolho. Algumas linhagens de Ligilactobacillus agilis e Ligilactobacillus salivarius podem ajudar a combater germes intestinais prejudiciais, reduzir inflamação e apoiar a integridade da barreira intestinal. Limosilactobacillus fermentum foi associada a melhor controle da pressão arterial e efeitos antioxidantes em estudos com animais. Lactobacillus johnsonii parece ajudar a equilibrar os micróbios intestinais de maneiras que podem proteger vários órgãos. Pediococcus pentosaceus e Weissella cibaria mostram potencial para reduzir o colesterol, combater deterioração e até apoiar a saúde bucal. Com essa variedade de benefícios potenciais, a indústria alimentícia está ansiosa para usar essas espécies mais amplamente — mas apenas se puder identificá‑las com confiança.
O desafio de diferenciar micróbios semelhantes
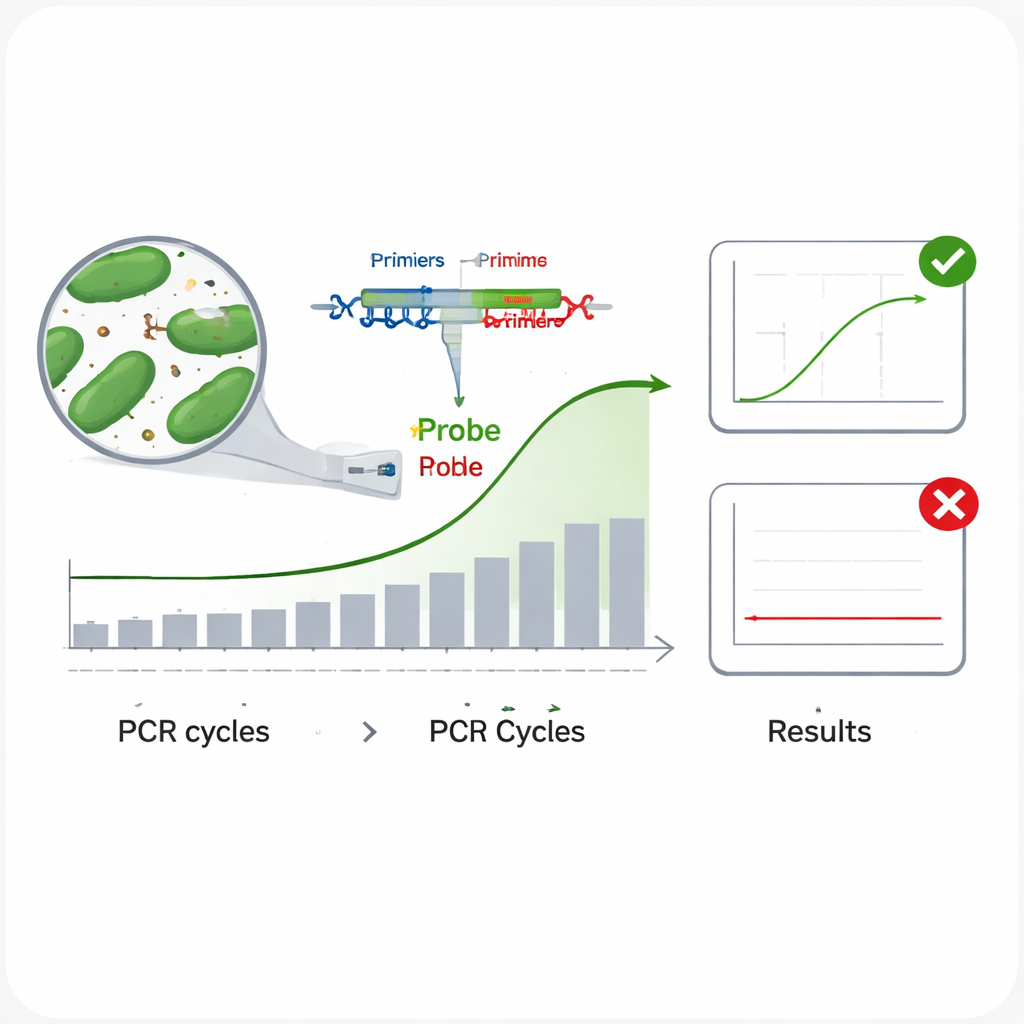
Métodos tradicionais de identificação bacteriana — cultivá‑las no laboratório e realizar testes bioquímicos — são lentos e trabalhosos. Métodos modernos baseados em DNA, especialmente a PCR em tempo real, são muito mais rápidos. Na PCR em tempo real, pequenos trechos de DNA chamados primers e uma sonda fluorescente miram uma sequência única do código genético do microrganismo; quando o microrganismo correto está presente, a máquina detecta um sinal luminoso conforme o DNA é copiado ciclo após ciclo. O problema é que bactérias intimamente relacionadas podem compartilhar DNA muito semelhante, de modo que regiões genéticas comumente usadas, como o gene 16S rRNA, às vezes não conseguem distinguir uma espécie da outra. Isso pode levar a testes que não detectam o alvo (falsos negativos) ou que reagem para a espécie errada (falsos positivos), ambos inaceitáveis para rotulagem de produtos e segurança.
Projetando “códigos de barras” moleculares mais precisos
Para superar esse problema, os pesquisadores vasculharam sequências genômicas completas para encontrar curtos trechos de DNA que fossem altamente conservados dentro de cada espécie alvo e claramente diferentes de outras bactérias. Para cada uma das seis probióticas, eles projetaram um conjunto correspondente de primers e uma sonda com comprimento, composição de bases, temperatura de fusão e propensão mínima a formar estruturas secundárias ou a se ligar entre si cuidadosamente ajustados. Verificações por computador usando o banco de dados BLAST e softwares de alinhamento de sequência confirmaram que as regiões de DNA selecionadas eram estáveis dentro da espécie e distintas de não‑alvos. A equipe então definiu uma mistura padrão de reação e um programa de aquecimento para que todos os testes pudessem ser executados em condições consistentes e práticas no mesmo tipo de aparelho de PCR em tempo real.
Colocando os novos ensaios à prova
Os cientistas avaliaram em seguida o desempenho de cada ensaio na prática. Para testar a inclusividade — se um ensaio consegue detectar várias linhagens diferentes da mesma espécie —, eles rodaram cada ensaio em múltiplas amostras de DNA de sua bactéria alvo. Em todos os casos, todas as linhagens testadas produziram uma curva de amplificação clara, sugerindo baixo risco de deixar de detectar alvos genuínos. Para verificar a especificidade — se o ensaio ignora espécies não‑alvo —, desafiaram cada teste com DNA de 13 outras bactérias intestinais, incluindo lactobacilos relacionados e microrganismos comuns do intestino como Escherichia coli. Nenhuma dessas produziu sinal, indicando risco muito baixo de alarmes falsos. A equipe também examinou a eficiência de amplificação executando uma série de diluições decimais do DNA e confirmou que todos os seis ensaios copiaram seus alvos com eficiência de cerca de 95–100%, próximo do ideal. Por fim, mediram a precisão repetindo corridas em dois níveis de DNA e observaram que variações mínimas entre repetições e entre experimentos separados ficaram bem abaixo dos limites aceitos.
O que isso significa para os alimentos do futuro
Em termos simples, os autores desenvolveram seis testes de “impressão digital” de DNA afinados que conseguem distinguir as principais espécies probióticas de forma rápida, precisa e confiável. Embora alertem que são necessários testes mais amplos com mais linhagens, mais espécies não‑alvo e instrumentos de PCR adicionais antes da adoção rotineira pela indústria, os resultados iniciais são encorajadores. Para os consumidores, avanços como este ajudam a garantir que alimentos anunciados como contendo probióticos específicos realmente contenham os microrganismos corretos, apoiando assim rotulagem honesta, melhor controle de qualidade e pesquisas mais confiáveis sobre como esses pequenos parceiros afetam nossa saúde.
Citação: Li, SJ., Cui, B., Li, W. et al. Development and preliminary evaluation of real-time PCR assays for six lactic acid bacteria. Sci Rep 16, 6165 (2026). https://doi.org/10.1038/s41598-026-37047-3
Palavras-chave: probióticos, bactérias do ácido lático, PCR em tempo real, microbiologia de alimentos, identificação microbiana