Clear Sky Science · pt
Identificador integrado de bactérias em chip para BSI usando correspondência aproximada de k-mers
Por que detectar germes mais rápido importa
Para pacientes que recebem transplantes de células-tronco que salvam vidas, infecções na corrente sanguínea podem transformar a recuperação em uma emergência médica em poucas horas. Os médicos sabem que cada minuto conta, mas as ferramentas de laboratório atuais para identificar as bactérias culpadas podem ser lentas ou exigir computadores potentes. Este estudo apresenta um chip de computador diminuto e energeticamente eficiente — chamado PC-CAM — que pode escanear rapidamente o DNA de amostras de pacientes e sinalizar bactérias perigosas em tempo real, potencialmente à beira do leito hospitalar.
O risco de infecção após um tratamento que salva o intestino
Alguns pacientes transplantados desenvolvem uma complicação grave em que as células imunes do doador atacam o intestino do paciente. Um tratamento promissor é o transplante de microbiota fecal, em que micróbios intestinais saudáveis de um doador são introduzidos no paciente. Embora isso possa resgatar o intestino, às vezes traz um perigo adicional: bactérias nocivas do intestino podem escapar para a corrente sanguínea, causando infecções potencialmente fatais. Para tratar essas infecções de forma eficaz, os médicos precisam identificar rapidamente quais espécies bacterianas estão presentes, mas os testes tradicionais podem levar horas a dias e podem deixar de detectar linhagens desconhecidas.
De montar genomas lentamente para analisar fragmentos de DNA rapidamente
Os sequenciadores de DNA modernos podem ler material genético diretamente de amostras de sangue ou fezes quase em tempo real. O gargalo não é mais a leitura do DNA, mas interpretá-lo. Métodos convencionais tentam primeiro reconstruir genomas inteiros a partir de milhões de fragmentos curtos de DNA e depois comparar esses genomas montados com uma biblioteca de referência — um processo computacionalmente pesado. Os autores substituem isso por uma estratégia mais simples: fragmentam o DNA em pedaços curtos de comprimento fixo, chamados k-mers, e procuram esses pedaços diretamente em um banco de dados de sequências bacterianas conhecidas. Em vez de exigir uma correspondência perfeita letra por letra, o sistema tolera um certo número de diferenças, o que lhe permite lidar com os erros inevitáveis do sequenciamento de DNA e com as mutações naturais. 
Um chip de memória inteligente projetado para buscas em DNA
No coração do PC-CAM está um tipo especializado de memória chamado content-addressable memory, que pode comparar dados de entrada com tudo o que armazena ao mesmo tempo. Os pesquisadores projetaram uma versão de "busca aproximada" dessa memória (ACAM) que pode ser ajustada para aceitar quase-correspondências em vez de exatas. Cada fragmento curto de DNA é codificado e armazenado como uma linha nessa memória. Quando um novo fragmento de uma amostra de paciente chega, o chip ativa uma linha de busca por todas as linhas simultaneamente e mede com que rapidez pequenos sinais elétricos se descarregam. Ajustando duas tensões de controle, o sistema define um limiar para quantas discrepâncias tolerará, ajustando efetivamente quão permissiva a correspondência deve ser. Essa comparação em nível de hardware permite que o chip peneire padrões muito mais rápido e com menos energia do que um computador de uso geral.
Quão bem o chip encontra bactérias reais
A equipe testou o PC-CAM em conjuntos de dados do mundo real de pacientes que haviam passado por transplante de microbiota fecal, comparando as bactérias detectadas no sangue e nas fezes com os resultados de uma análise genômica completa baseada em software. Mesmo quando o chip armazenou apenas um pequeno subconjunto cuidadosamente escolhido de fragmentos de DNA de cada genoma bacteriano, ele concordou em grande parte com o método computacionalmente mais caro, identificando corretamente patógenos-chave em vários pacientes. Em experimentos ampliados usando leituras de DNA simuladas de várias bactérias e diferentes taxas de erro, a sensibilidade do chip (sua capacidade de capturar correspondências verdadeiras) aumentou à medida que ele foi permitido tolerar mais diferenças, enquanto a especificidade (sua capacidade de evitar alarmes falsos) diminuiu em níveis de tolerância muito altos. Os autores mostram que etapas simples de pós-processamento — como exigir múltiplos fragmentos concordantes ou descartar correspondências fracas — podem reduzir esses falsos positivos. 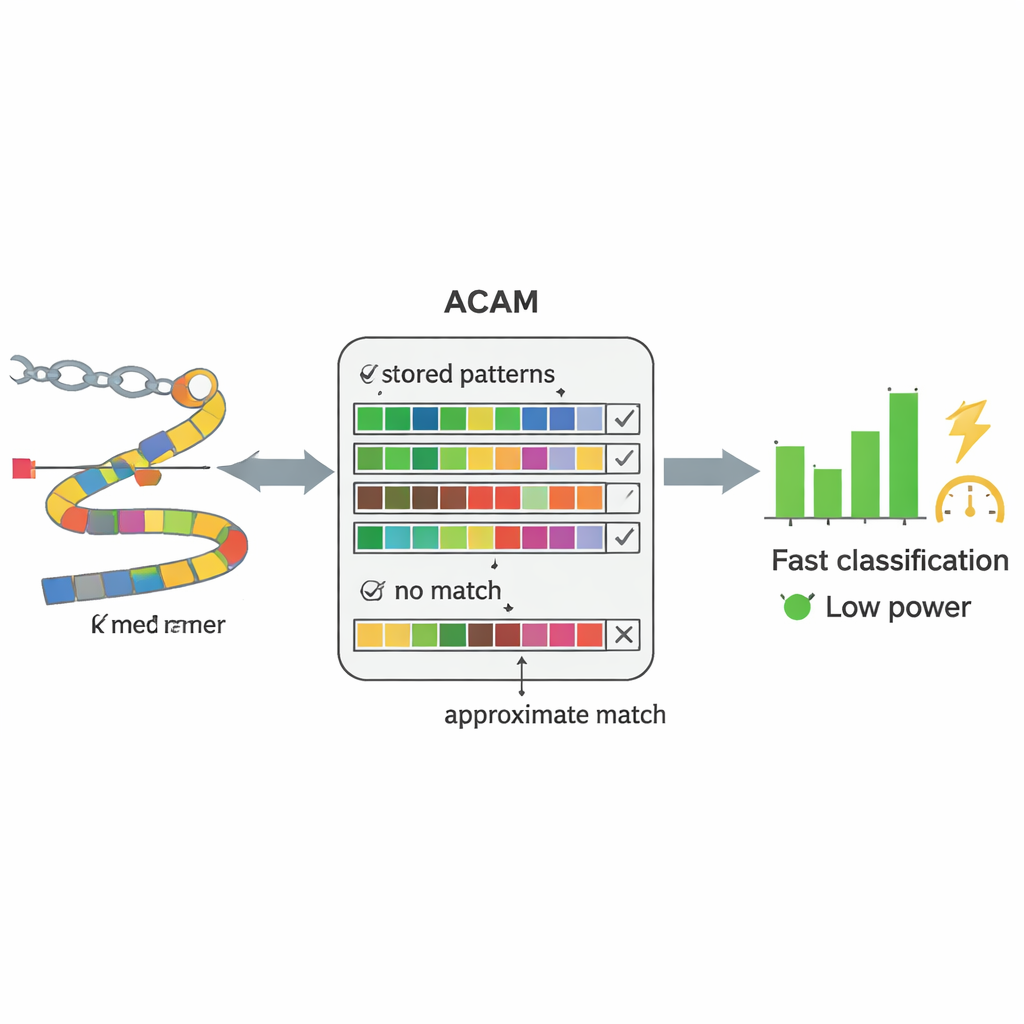
Hardware minúsculo com grande velocidade e baixo consumo
O PC-CAM integra a memória ACAM com um pequeno processador RISC-V em um chip de apenas alguns milímetros quadrados, fabricado em tecnologia padrão de 65 nanômetros. Medições em hardware real mostram que ele pode classificar cerca de 960.000 leituras curtas de DNA por segundo enquanto consome cerca de 1,27 miliwatts de potência — menos do que muitos relógios digitais de pulso. Comparado com uma ferramenta de software líder executando em um processador desktop de alto desempenho, o chip foi aproximadamente 1.900 vezes mais rápido para esse tipo de tarefa de classificação. Embora sua precisão seja modestamente reduzida por armazenar uma versão diluída de cada genoma, os autores argumentam que essa compensação é aceitável quando velocidade e consumo de energia são as restrições principais, como em cuidados emergenciais ou dispositivos portáteis.
O que isso significa para pacientes e além
Em termos simples, o estudo mostra que um chip minúsculo e de baixo consumo pode funcionar como um mecanismo de busca especializado para DNA bacteriano, detectando germes perigosos em amostras de sangue ou fezes quase instantaneamente. Embora não substitua a análise genética completa em um grande laboratório, ele pode fornecer orientação rápida e local sobre quais bactérias estão presentes, ajudando os médicos a escolher antibióticos mais cedo e com mais precisão. A mesma abordagem pode ser ampliada para monitorar resistência a antibióticos, checar alimentos e água quanto à contaminação ou vigiar plantações quanto a doenças — tudo usando hardware compacto que traz análises sofisticadas de DNA para fora do centro de dados e mais perto de onde as decisões precisam ser tomadas.
Citação: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Palavras-chave: infecção na corrente sanguínea, detecção rápida de patógenos, sequenciamento de DNA, lab-on-a-chip, microbioma