Clear Sky Science · pt
Montagem de transcriptoma de comprimento total e desenvolvimento de marcadores SSR para Spinibarbus hollandi usando sequenciamento PacBio SMRT
Por que um modesto peixe de rio é importante
Ao longo dos rios do sul da China nada Spinibarbus hollandi, um peixe semelhante à carpa valorizado tanto para a mesa quanto como espécie ornamental. Os criadores gostariam de produzi‑lo de forma mais eficiente, mas o peixe cresce lentamente, atinge a maturidade tardiamente e produz relativamente poucos ovos. O estudo descrito aqui usa ferramentas de sequenciamento de DNA e RNA de ponta para construir uma “lista de peças” genética detalhada para essa espécie. Essas informações genéticas podem, em última instância, ajudar os melhoristas a selecionar peixes mais resistentes e de crescimento mais rápido e apoiar a conservação das populações selvagens.
Transformando muitos tecidos em um mapa genético
Para capturar o máximo de informação genética possível, os pesquisadores coletaram seis tecidos diferentes — coração, brânquia, cérebro, nadadeira, fígado e gônada — de seis machos e fêmeas adultos. Desse material extraíram RNA, a molécula que carrega cópias dos genes ativos dentro das células. Usando uma tecnologia chamada PacBio SMRT, que lê trechos muito longos de cópias de RNA, montaram o primeiro transcriptoma de comprimento total de S. hollandi. Em termos simples, construíram um catálogo de alta resolução com 15.197 genes distintos e 23.403 sequências de transcritos, a maioria muito mais longa e mais completa do que o que métodos antigos de leituras curtas poderiam produzir.
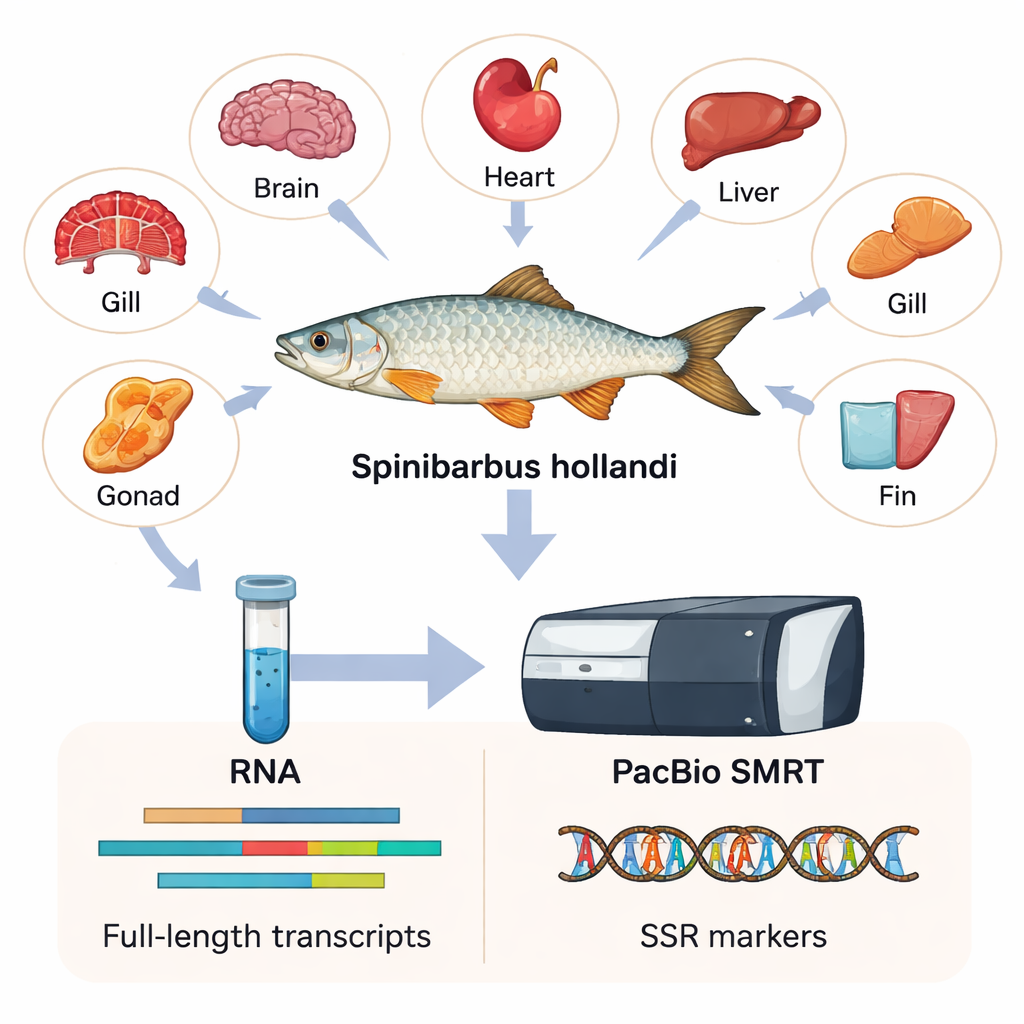
O que os genes revelam sobre o peixe
Em seguida, a equipe investigou o que esses genes realmente fazem. Compararam cada sequência com grandes bancos de dados públicos que agrupam genes por função. Mais de 95% dos genes puderam ser associados a entradas conhecidas, uma taxa de sucesso muito elevada que sinaliza boa qualidade dos dados. Muitos genes se enquadraram em categorias relacionadas a atividades celulares básicas, como metabolismo, transmissão de sinais e desenvolvimento, e as sequências mais se assemelharam a genes de outros peixes da família das carpas. Isso confirma que o novo transcriptoma é biologicamente consistente e fornece uma base para identificar genes ligados a características como taxa de crescimento, tolerância ao estresse e reprodução em S. hollandi.
Camadas ocultas de controle no RNA
Além de identificar genes, os cientistas também examinaram como esses genes são controlados. Encontraram 373 casos de splicing alternativo, em que o mesmo gene é cortado e remontado de maneiras diferentes para gerar mensagens de RNA distintas. O padrão mais comum manteve trechos de RNA que frequentemente são removidos em outras espécies, sugerindo uma forma particular de como esse peixe ajusta finamente suas proteínas. Também descobriram 2.397 RNAs longos não codificantes — moléculas de RNA que não produzem proteínas, mas podem regular quando e onde outros genes são ativados. Em conjunto, essas descobertas mostram que S. hollandi usa um conjunto rico de controles ao nível do RNA que pode influenciar crescimento, maturação sexual e adaptação a ambientes locais.
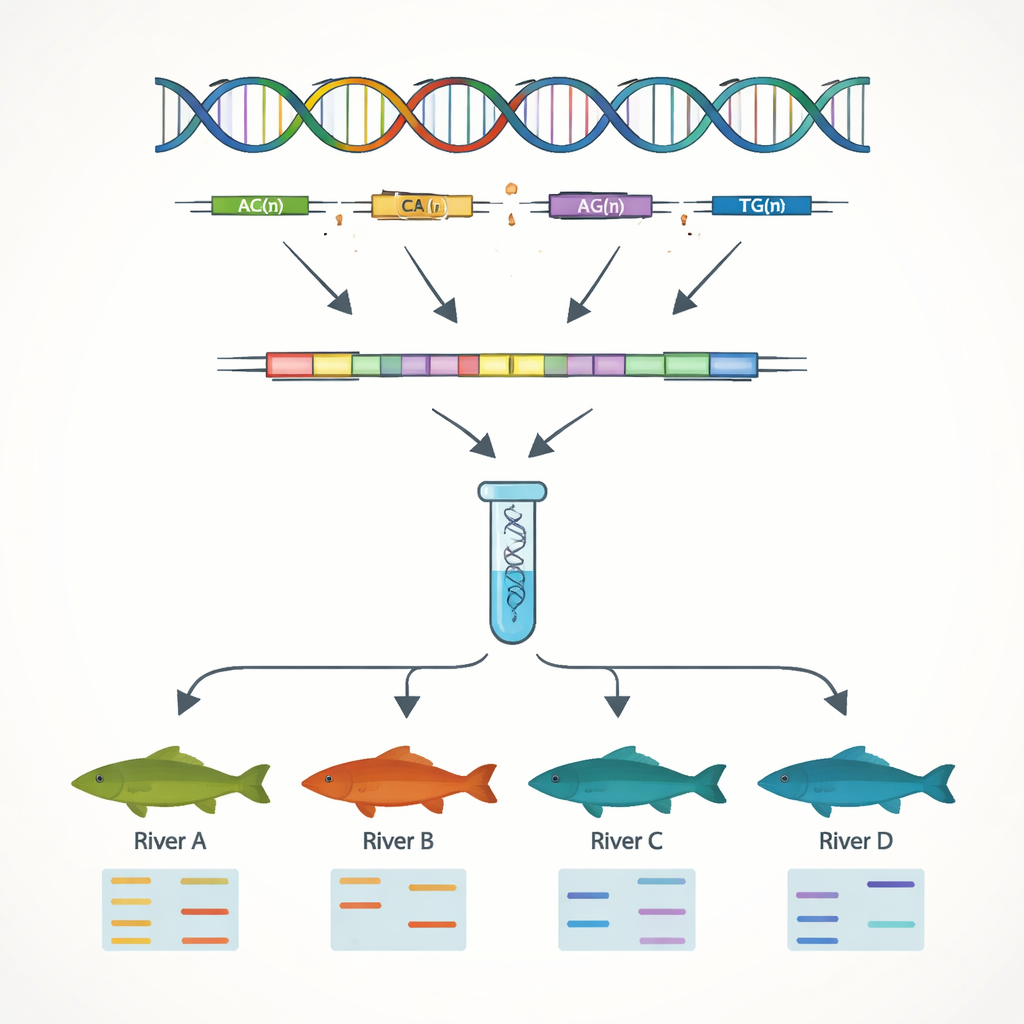
Construindo marcos de DNA para melhoramento e conservação
Um objetivo central do trabalho foi desenvolver marcadores de DNA simples que permitam distinguir indivíduos e populações. Focando nas sequências gênicas, os autores procuraram repetições simples em sequência, ou SSRs — motivos curtos de DNA como “AC” ou “AAT” repetidos muitas vezes em sequência. Esses trechos tendem a variar entre indivíduos, tornando‑se úteis como códigos genéticos. Eles identificaram 7.449 locais SSR desse tipo e desenharam dezenas de primers curtos de DNA para amplificá‑los em laboratório. Treze desses marcadores mostraram ser altamente variáveis e confiáveis quando testados em 51 peixes de quatro sistemas fluviais. Usando apenas esses 13 marcadores, a equipe conseguiu detectar claramente diferenças genéticas entre populações do rio Yangtzé e as do rio das Pérolas, refletindo as cadeias montanhosas que limitam a mistura natural entre bacias.
O que isso significa para criadores e rios
Para não especialistas, a principal conclusão é que os autores criaram uma referência genética detalhada e de alta qualidade para S. hollandi e um conjunto de marcadores de DNA práticos. Esse conjunto de ferramentas ajudará pesquisadores a identificar genes por trás do crescimento lento ou da baixa fertilidade, auxiliará melhoristas a selecionar reprodutores com características desejáveis e permitirá aos conservacionistas monitorar a diversidade genética entre sistemas fluviais. Embora sejam necessários mais estudos para vincular genes específicos ao desempenho em viveiros ou no ambiente natural, este estudo estabelece a base molecular para transformar um peixe tradicional de rio em uma espécie de aquicultura moderna e gerida de forma sustentável.
Citação: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Palavras-chave: Spinibarbus hollandi, transcriptoma de peixe, sequenciamento PacBio, marcadores microssatélite, genética da aquicultura