Clear Sky Science · pt
ONCOPLEX: um modelo de hipergráfico inspirado em oncologia que integra conhecimentos biológicos diversos para previsão de genes motoras do câncer
Por que esta pesquisa importa
O câncer é impulsionado por um pequeno número de alterações genéticas poderosas escondidas entre milhares de mudanças inofensivas. Identificar esses verdadeiros genes “motores” é essencial para diagnósticos melhores e tratamentos direcionados, mas é como localizar alguns líderes em um vasto e ruidoso público. Este estudo apresenta o ONCOPLEX, uma nova estrutura de inteligência artificial que vê os genes não individualmente, mas no contexto das vias biológicas em que atuam em conjunto, oferecendo uma maneira mais precisa de identificar os genes que realmente alimentam os tumores.
Vendo genes do câncer em seus bairros biológicos
A maioria dos métodos atuais examina genomas de câncer em busca de mutações que aparecem com frequência incomum ou que se destacam em redes gênicas simples. Essas abordagens ajudam, mas a biologia raramente é tão simples. Genes geralmente atuam em grupos dentro de vias que controlam crescimento celular, reparo de DNA e muitos outros processos. O ONCOPLEX abraça essa complexidade ao representar genes como pontos e vias como grupos sobrepostos maiores que podem conter muitos genes ao mesmo tempo. Esse tipo de estrutura, conhecido como hipergráfico, permite que o modelo considere relações entre múltiplos genes diretamente, em vez de fragmentá-las em muitos pares separados.
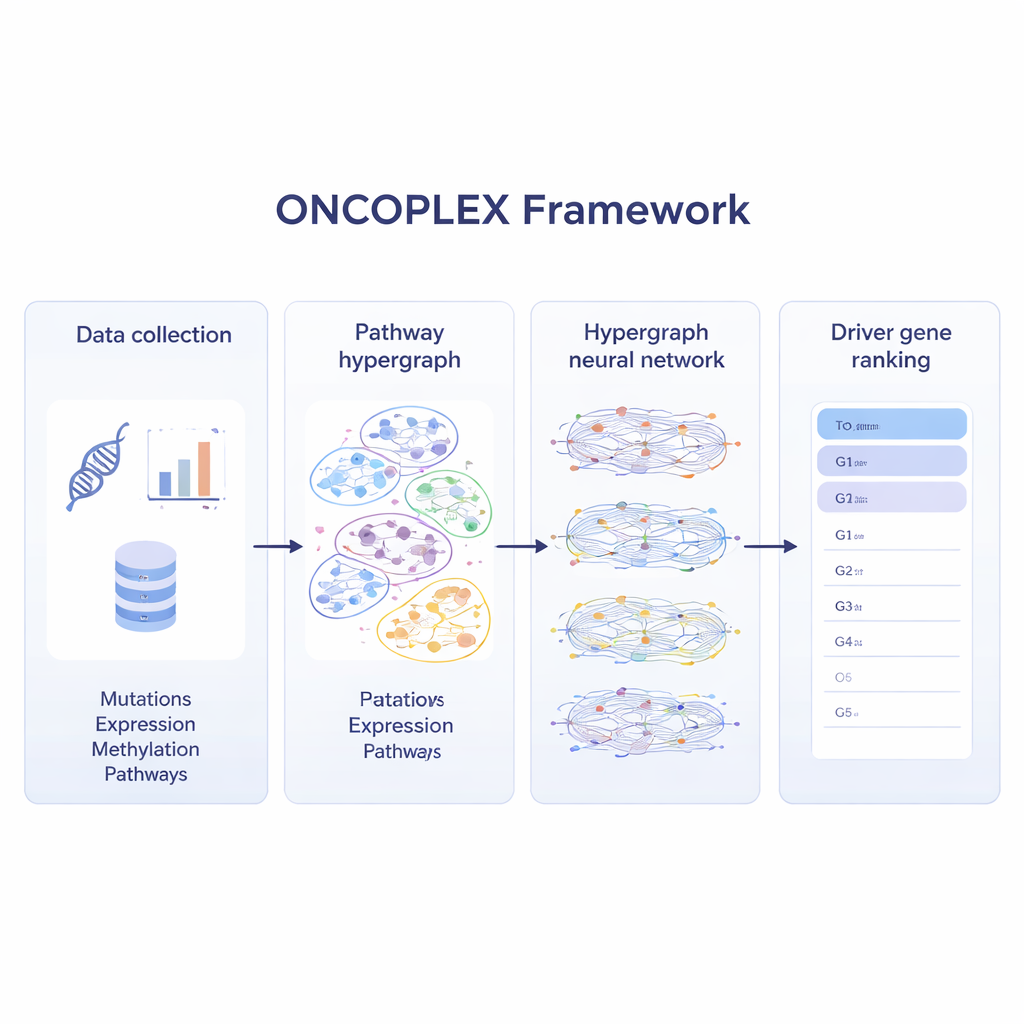
Misturando várias camadas de dados do câncer
Para tirar o máximo proveito dos conjuntos de dados modernos sobre câncer, o ONCOPLEX combina vários tipos de informação sobre cada gene. Ele usa frequências de mutação, mudanças na atividade gênica, marcas químicas no DNA (metilação) e um conjunto rico de características biológicas, como conservação evolutiva e anotações funcionais. Essas características são associadas a cada gene no hipergráfico. Uma rede neural especializada então propaga informação através das vias, permitindo que a representação de cada gene seja moldada tanto por seus próprios dados quanto pelo comportamento dos genes com os quais trabalha. O modelo é treinado usando genes já conhecidos como motores do câncer, ao mesmo tempo em que aprende a partir de muitos genes não rotulados que podem ser importantes, mas ainda não reconhecidos.
Superando ferramentas existentes em vários cânceres
Os pesquisadores testaram o ONCOPLEX em dados do The Cancer Genome Atlas, tanto agrupando muitos tipos tumorais quanto examinando 11 cânceres individuais, incluindo mama, pulmão, fígado, bexiga e cabeça e pescoço. Eles o compararam com vários dos principais métodos baseados em grafos e hipergráficos. Em todas as avaliações, o ONCOPLEX foi melhor em distinguir genes motores conhecidos dos muito mais comuns não-motores e em posicionar potenciais motores nas primeiras posições de suas listas. Sua vantagem foi especialmente evidente ao olhar para os genes de maior rank, onde a identificação precisa é mais valiosa para experimentos subsequentes e tradução clínica.
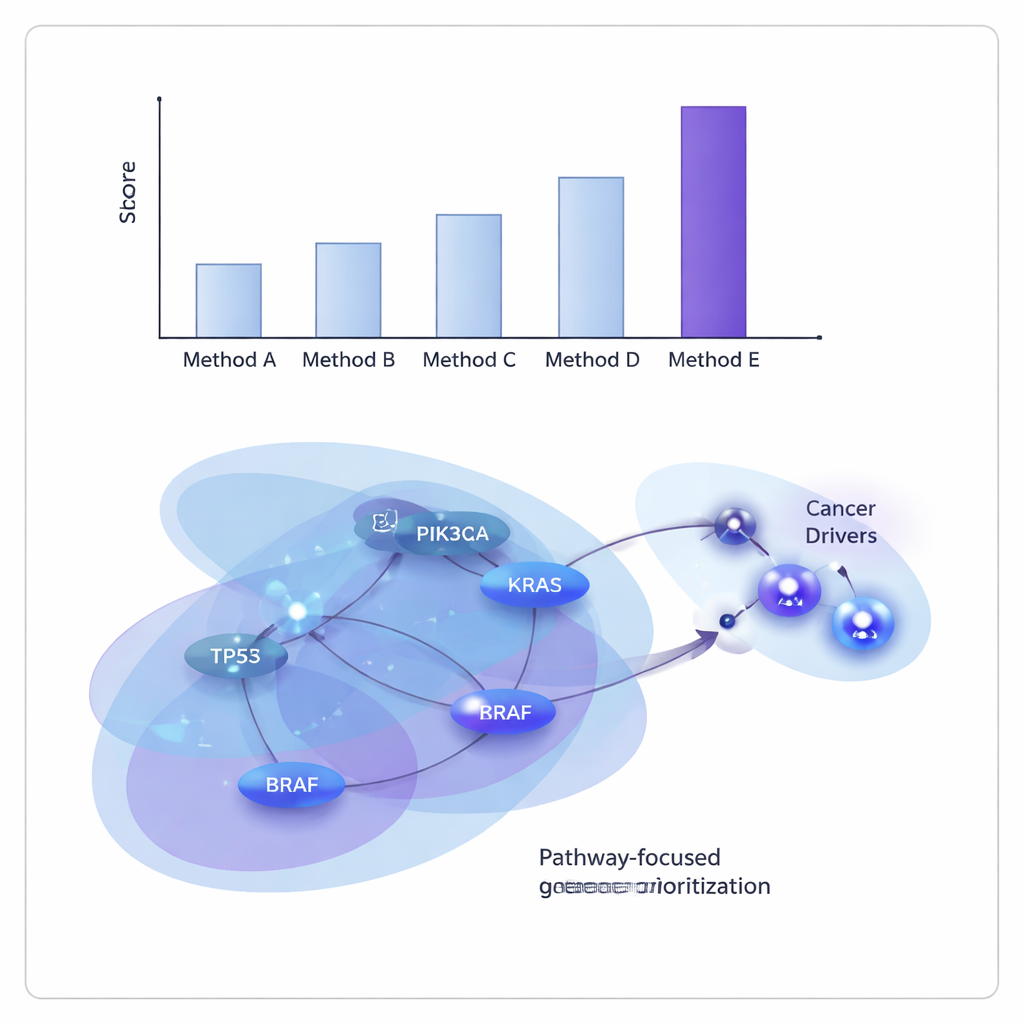
Revelando culpados compartilhados e específicos de câncer
Além dos números de desempenho bruto, as listas ranqueadas do ONCOPLEX recuperaram muitos genes conhecidos do câncer, como KRAS, BRAF e membros da via de sinalização PI3K–AKT, confirmando que o modelo captura biologia bem estabelecida. Também destacou candidatos promissores que ainda não são firmemente reconhecidos como motores em certos tipos de câncer, incluindo genes como GRB2 e MAPK3 em câncer de mama e SHC1 em câncer de estômago. Quando a equipe examinou os genes de topo com análise de enriquecimento de vias, encontraram assinaturas fortes de vias conhecidas do câncer, incluindo sinalização ErbB e PI3K–AKT–mTOR, bem como vias relacionadas ao sistema imune, sugerindo que o ONCOPLEX está mirando em redes que têm relevância clínica.
Forças, limites e próximos passos
Ao mostrar que características biológicas mais ricas melhoram consistentemente suas previsões, o ONCOPLEX demonstra o valor de fundir várias fontes de dados dentro de uma estrutura centrada em vias. Ao mesmo tempo, o estudo revela uma limitação: como muitos cânceres compartilham um grande número de vias, o modelo às vezes favorece genes de atuação ampla “pan-câncer” em detrimento daqueles realmente específicos de um tipo tumoral. Os autores sugerem que trabalhos futuros devem refinar como a informação de vias é usada para que sinais comuns e específicos do câncer possam ser separados com mais clareza.
O que isso significa para pacientes e clínicos
Para não especialistas, a conclusão principal é que o ONCOPLEX oferece uma maneira mais biologicamente realista de procurar os genes que impulsionam o câncer. Ao olhar para os genes na companhia dos seus pares—dentro de vias em vez de isolados—ele melhora nossa capacidade de identificar tanto motores conhecidos quanto previamente negligenciados, mesmo em cânceres onde pouco se sabe atualmente. Esse tipo de ferramenta pode ajudar pesquisadores a priorizar quais genes estudar em laboratório, guiar a busca por novos alvos medicamentosos e, em última instância, apoiar estratégias de tratamento mais precisas e conscientes das vias em oncologia.
Citação: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Palavras-chave: genes motores do câncer, redes neurais em hipergráficos, integração multi-ômica, análise de vias, oncologia de precisão