Clear Sky Science · pt
IL2Pepscan: Uma estrutura de aprendizado de máquina para prever peptídeos que induzem IL-2 e sua identificação em proteomas virais globais
Ensinando o sistema imune com pequenos fragmentos de proteína
Vacinas modernas e terapias contra o câncer dependem cada vez mais de estimular o sistema imune de forma precisa, em vez de atacar a doença com tratamentos generalizados. Este estudo explora como pequenos fragmentos de proteína, chamados peptídeos, podem ser selecionados para ativar um potente mensageiro imune, a interleucina‑2 (IL‑2). Usando modelos computacionais avançados, os autores vasculham tanto dados imunológicos conhecidos quanto catálogos de proteínas de milhares de vírus para encontrar agulhas peptídicas em um palheiro molecular que podem ajudar a projetar vacinas e imunoterapias melhores.
Por que a IL-2 importa para a saúde e a doença
A IL‑2 é uma pequena molécula sinalizadora que atua como um fator de crescimento para células imunes chave conhecidas como células T. Quando essas células encontram pela primeira vez uma ameaça — como um vírus ou uma célula cancerosa — elas podem liberar IL‑2, que incentiva então as células T a se multiplicarem, se especializarem e lembrarem do invasor. A IL‑2 também ajuda a manter células T reguladoras que impedem que o sistema imune ataque os próprios tecidos do corpo. Por causa desse papel duplo, a IL‑2 tem sido usada como droga para tratar cânceres como o melanoma, e está sendo estudada para doenças autoimunes. Mas administrar IL‑2 diretamente pode ser tóxico para pacientes, por isso há um interesse crescente em projetar peptídeos seguros que façam o corpo produzir IL‑2 de maneira mais controlada e direcionada.
Aprendendo o “sabor” dos peptídeos que induzem IL-2
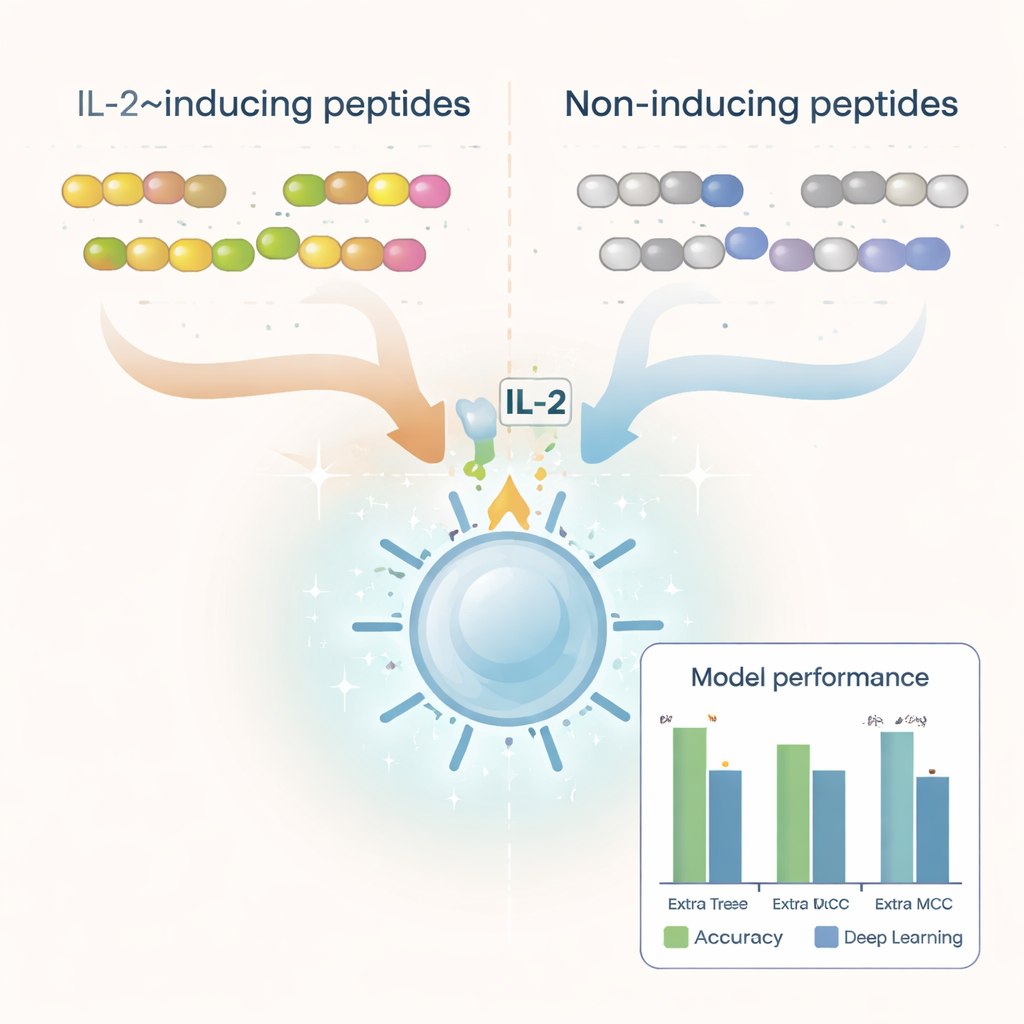
Os pesquisadores começaram com milhares de sequências peptídicas que já tinham sido testadas em experimentos de laboratório e rotuladas como indutoras de IL‑2 ou não. Eles limparam esse conjunto de dados para remover duplicatas, blocos construtores incomuns e peptídeos muito curtos ou muito longos, terminando com mais de 6.000 exemplos bem caracterizados. Ao examinar os blocos construtores (aminoácidos) que compõem esses peptídeos, descobriram diferenças claras entre os dois grupos. Peptídeos que induzem IL‑2 tendiam a ser mais ricos em aminoácidos hidrofóbicos, ou repelentes de água, como leucina e alanina, enquanto peptídeos não indutores apresentavam maior proporção de resíduos polares e carregados. Certos padrões curtos, ou motivos, como “LEGS” e “ALEG”, apareceram apenas em peptídeos indutores de IL‑2, sugerindo assinaturas estruturais que podem ajudar a desencadear a ativação imune.
Treinando máquinas para identificar padrões que reforçam a imunidade
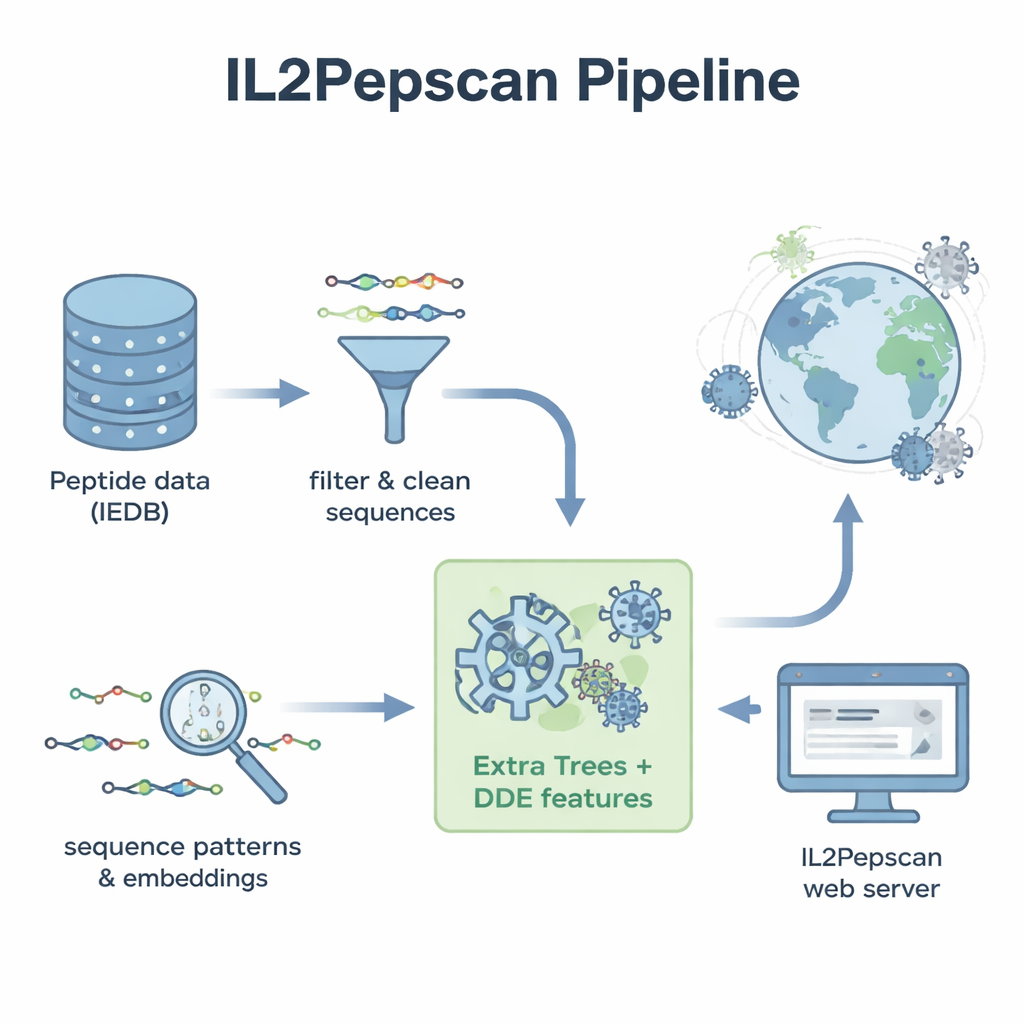
Para transformar esses padrões em uma ferramenta prática de predição, a equipe converteu cada peptídeo em descrições numéricas que capturam sua composição e a ordem dos aminoácidos. Eles testaram uma variedade de métodos de aprendizado de máquina — incluindo algoritmos populares como florestas aleatórias (random forests), máquinas de vetor de suporte (SVM) e árvores com boosting — além de arquiteturas de aprendizado profundo frequentemente usadas em tarefas de linguagem e imagem. Também exploraram um grande “modelo de linguagem” de proteínas chamado ProtBERT, originalmente treinado em centenas de milhões de sequências proteicas, e o ajustaram (fine‑tuning) para reconhecer melhor sinais relacionados à IL‑2. Após testes extensivos com validação cruzada e um conjunto de teste independente, o destaque foi um modelo chamado Extra Trees combinado com um conjunto de características conhecido como desvio dipeptídico da média esperada (DDE). Esse modelo alcançou perto de 80% de acurácia e uma forte pontuação de correlação, superando várias abordagens de aprendizado profundo.
Escaneando o mundo viral em busca de gatilhos imunes ocultos
Munidos com seu melhor modelo, os autores lançaram uma rede muito mais ampla. Reuniram sequências proteicas de referência de mais de 14.000 vírus, fatiaram essas proteínas em cerca de 156 milhões de peptídeos sobrepostos e pediram ao modelo para prever quais poderiam induzir IL‑2. Entre os candidatos com pontuação mais alta estavam peptídeos de famílias virais bem conhecidas, incluindo flavivírus como Nilo Ocidental, Zika, Febre Amarela e Hepatite C, bem como de Influenza e SARS‑CoV‑2. Muitos peptídeos promissores provinham de proteínas de envelope ou nucleocapsídeo — os mesmos tipos de proteínas que outros estudos mostraram capazes de provocar respostas de IL‑2 em animais. O modelo também apontou potenciais peptídeos indutores de IL‑2 codificados por bacteriófagos, vírus que infectam bactérias, sugerindo um panorama ainda mais amplo de sequências relevantes para o sistema imune.
Do algoritmo à ferramenta acessível
Para tornar o trabalho utilizável além do laboratório de computação, os autores construíram um servidor web público chamado IL2Pepscan. Pesquisadores podem colar sequências de peptídeos ou proteínas no site para estimar seu potencial de indução de IL‑2, projetar novas variantes mutando posições, escanear proteínas inteiras em busca de pontos quentes ou procurar por motivos conhecidos ligados à IL‑2. Embora o estudo ainda não confirme experimentalmente cada peptídeo previsto, a concordância com achados laboratoriais existentes sugere que o IL2Pepscan pode reduzir de forma confiável o número de candidatos a serem testados. Para não especialistas, a conclusão é que algoritmos bem treinados podem peneirar enormes conjuntos de dados biológicos para identificar pequenos fragmentos proteicos que talvez um dia ajudem vacinas e imunoterapias a induzir uma resposta imune mais potente — e mais precisa.
Citação: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Palavras-chave: interleucina-2, vacinas peptídicas, aprendizado de máquina, proteoma viral, imunoterapia