Clear Sky Science · pt
Análise estrutural da ligação de OCT4 a nucleossomos humanos de LIN28B
Como as células acessam instruções genéticas ocultas
Cada célula do seu corpo carrega o mesmo DNA, ainda que apenas uma fração dessas instruções genéticas seja utilizada em um dado tipo celular. Grande parte desse controle decorre de como o DNA é compactado ao redor de proteínas chamadas histonas, formando estruturas conhecidas como nucleossomos. Essa compactação estreita pode esconder trechos-chave de DNA da maquinaria celular que lê os genes. O estudo descrito aqui investiga como uma proteína especial, OCT4, consegue localizar e ligar-se ao seu DNA-alvo mesmo quando esse DNA está enrolado e parcialmente oculto dentro de nucleossomos — um processo central para a identidade de células-tronco e para o reprogramamento celular.
Por que os fatores pioneiros são importantes para células-tronco
OCT4 pertence a um grupo pequeno, porém poderoso, de proteínas chamadas fatores de transcrição pioneiros. Ao contrário da maioria das proteínas que se ligam ao DNA, os pioneiros conseguem penetrar em regiões compactadas e “desligadas” do genoma e ajudam a ativar genes, desempenhando papel crucial na definição da identidade celular e no reprogramamento de células adultas de volta a estados semelhantes a células-tronco. OCT4 atua em conjunto com parceiros como SOX2, KLF4 e c-MYC para induzir a pluripotência, a propriedade que permite às células-tronco se tornarem quase qualquer tipo celular. Entender exatamente como o OCT4 se prende ao DNA enrolado em nucleossomos é essencial para decodificar como as células mudam de destino e para projetar maneiras mais precisas de manipular a identidade celular em pesquisa e medicina.
Testando se diferenças entre espécies importam
A maioria dos estudos estruturais de nucleossomos usa proteínas de histona de rãs (Xenopus laevis) ou de humanos, porque essas proteínas são muito parecidas, embora não idênticas. Pequenas diferenças em suas sequências de aminoácidos poderiam, em princípio, alterar como o DNA é enrolado ou como proteínas regulatórias como o OCT4 se ligam. Em trabalhos anteriores, os autores mostraram que o OCT4 se liga a uma sequência regulatória específica do gene humano LIN28B quando esse DNA está enrolado em nucleossomos feitos com histonas de rã. No novo estudo, eles fizeram uma pergunta simples, mas importante: o OCT4 se comporta da mesma forma quando os nucleossomos são montados com histonas humanas em vez de histonas de rã?
Construindo e sondando nucleossomos de LIN28B
Para responder, os pesquisadores reconstituíram nucleossomos em laboratório usando um segmento de 182 pares de bases do DNA de LIN28B e histonas humanas ou de rã, montadas por um método cuidadoso de “diálise lenta” que imita condições celulares. Ensaios em gel confirmaram que ambos os tipos de octâmeros de histona formaram nucleossomos de maneira eficiente. Em seguida, eles examinaram como esses nucleossomos se posicionam sobre o DNA de LIN28B. Experimentos em gel e cortes de DNA seguidos de sequenciamento (MNase-seq) mostraram que o DNA de LIN28B pode adotar múltiplas posições sobre o núcleo de histonas, e esse comportamento não mudou se os nucleossomos foram aquecidos à temperatura corporal. Crucialmente, a origem das histonas — rã ou humana — não fez diferença perceptível em como o DNA foi posicionado nem em quão fortemente o OCT4 se ligou.
Visualizando OCT4 no nucleossomo
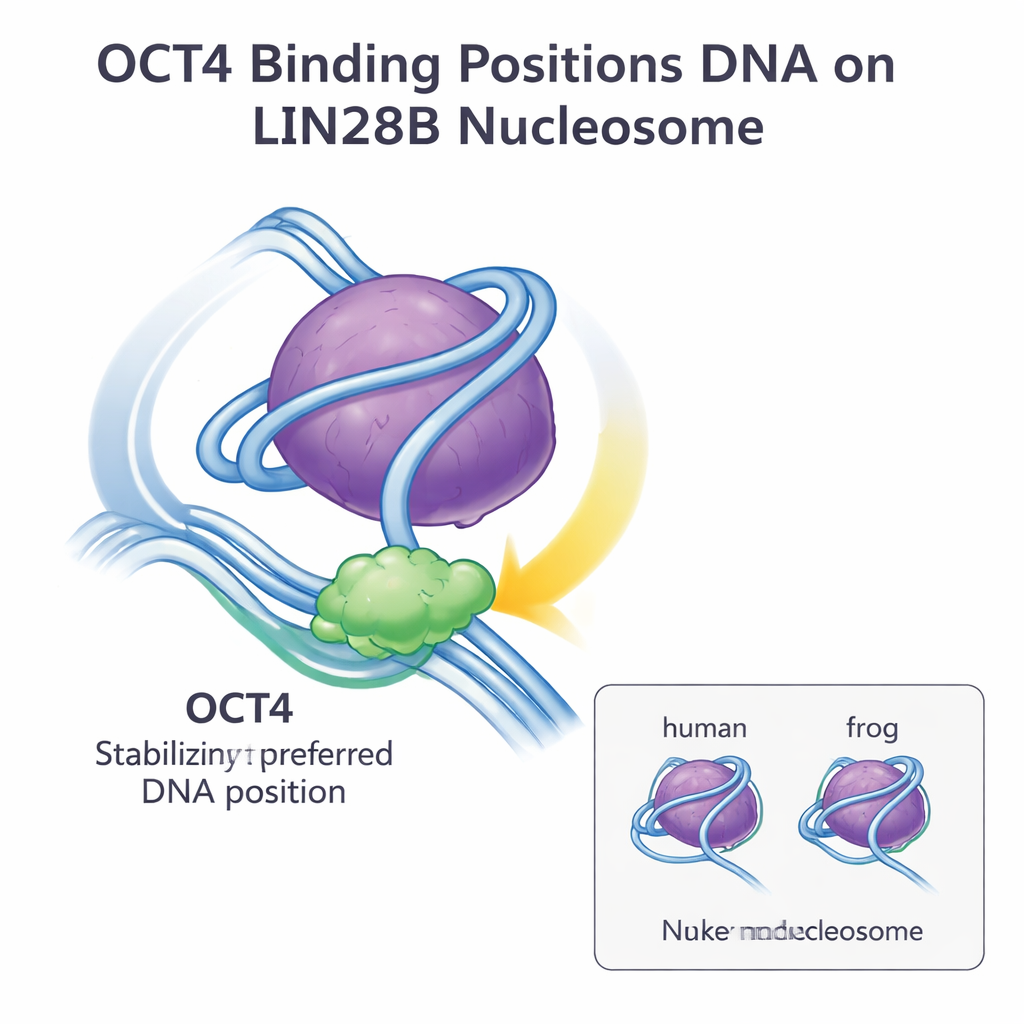
A equipe então usou microscopia eletrônica crio (cryo-EM) para visualizar a estrutura do OCT4 ligado a nucleossomos de LIN28B contendo histonas humanas. A partir de cerca de 15.000 partículas, eles reconstruíram um mapa tridimensional em aproximadamente 6 angströms de resolução. As imagens revelaram que ambas as partes do OCT4 que se ligam ao DNA contactam o mesmo trecho exposto de DNA próximo ao ponto de entrada e saída do nucleossomo, a chamada região do linker. Esse é exatamente o sítio e a orientação observados anteriormente quando o OCT4 estava ligado a nucleossomos feitos com histonas de rã. Ao ajustar o modelo antigo no novo mapa de cryo-EM, o encaixe foi excelente, indicando que a arquitetura geral do complexo OCT4–nucleossomo de LIN28B é essencialmente idêntica entre as duas espécies.
Uma estratégia geral para abrir a cromatina
Em conjunto, esses achados mostram que pequenas diferenças de sequência entre histonas de rã e humanas não alteram como o OCT4 reconhece e se liga ao nucleossomo de LIN28B. O DNA de LIN28B naturalmente ocupa várias posições possíveis sobre o núcleo de histonas, mas a ligação do OCT4 seleciona e estabiliza uma posição preferida, tornando sítios adicionais de ligação mais acessíveis ao OCT4 e seus parceiros. Essa estratégia de “posicionamento e estabilização do DNA” parece ser uma forma geral pela qual fatores pioneiros ganham acesso à cromatina fechada e promovem a ligação cooperativa de outros reguladores. Para o público geral, a conclusão é que o desenho básico do nucleossomo e a maneira como proteínas regulatórias chave como o OCT4 interagem com ele são altamente conservados entre espécies, reforçando a ideia de que insights de organismos-modelo podem informar de forma confiável nosso entendimento do controle gênico humano e da biologia de células-tronco.
Citação: Sinha, K.K., Halic, M. Structural analysis of OCT4 binding to human LIN28B nucleosomes. Sci Rep 16, 5704 (2026). https://doi.org/10.1038/s41598-026-35959-8
Palavras-chave: fatores de transcrição pioneiros, OCT4, estrutura do nucleossomo, acessibilidade da cromatina, regulação gênica em células-tronco