Clear Sky Science · pt
Estrutura de aprendizado de máquina para análise de splicing alternativo de mRNA identifica uma assinatura de progressão no adenocarcinoma colorretal
Por que esta pesquisa importa para pacientes
O câncer colorretal está entre os tipos mais comuns e letais, e os médicos ainda enfrentam dificuldades para prever quais tumores permanecerão controlados e quais retornarão agressivamente após o tratamento. Este estudo introduz uma nova forma de ler sinais ocultos no RNA tumoral — as mensagens que as células usam para fabricar proteínas — e usa aprendizado de máquina para transformar esses sinais em uma pontuação de risco simples que pode ajudar a ajustar o grau de agressividade do tratamento para cada paciente.
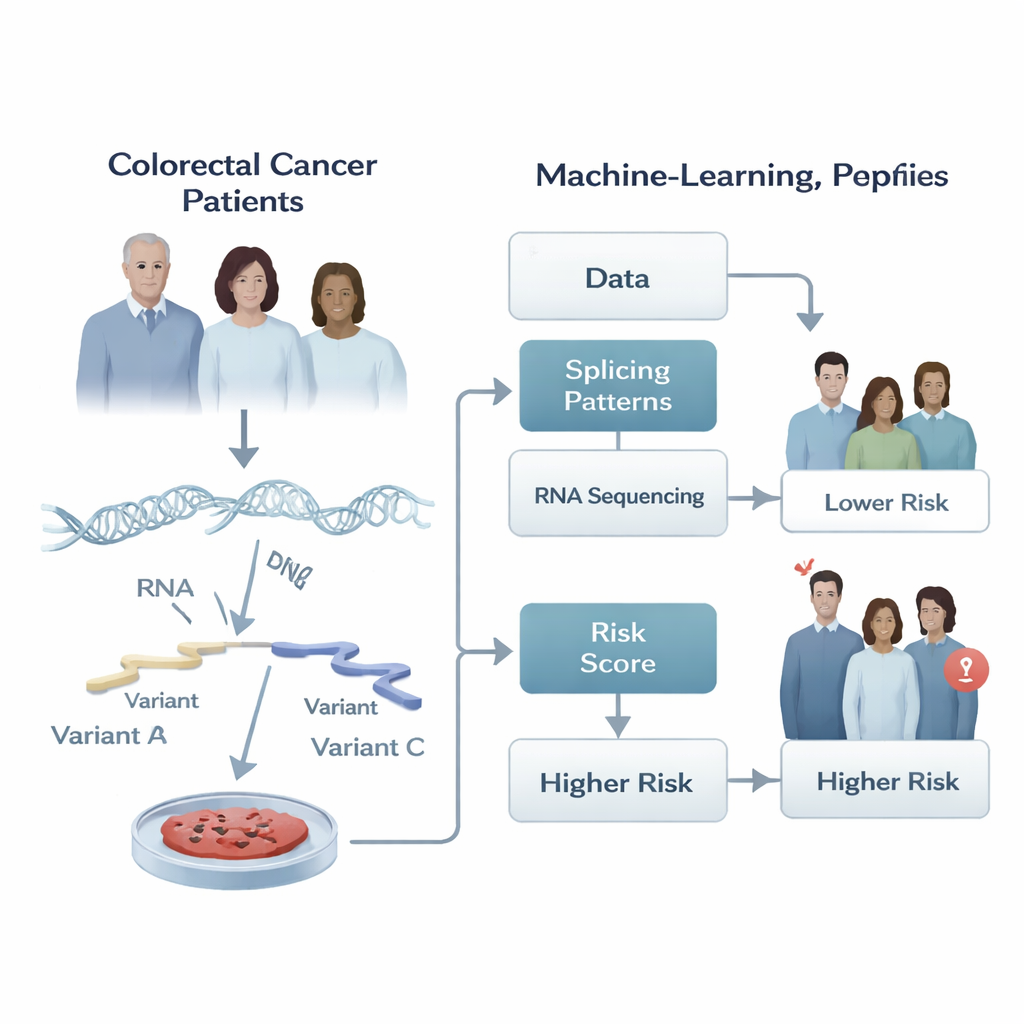
Cortes e edições ocultas em genes do câncer
Nossos genes não são lidos de maneira fixa. Quando uma célula copia o DNA para o RNA, ela pode cortar e colar trechos da mensagem de RNA em combinações diferentes, um processo chamado splicing alternativo. Essa edição permite que um único gene produza várias versões de uma proteína, como diferentes ferramentas a partir do mesmo kit. Em células saudáveis, essa flexibilidade é rigidamente controlada. No câncer, porém, o corte e a colagem podem sair do controle, criando versões de proteínas que ajudam o tumor a crescer, se espalhar e resistir ao tratamento. Os autores supuseram que o padrão dessas edições de RNA ao longo de um tumor poderia conter pistas poderosas sobre como esse câncer provavelmente se comportará ao longo do tempo.
Transformando padrões de RNA em uma pontuação de risco
Os pesquisadores analisaram dados de sequenciamento de RNA de tumores de 266 pacientes com adenocarcinoma colorretal do The Cancer Genome Atlas e de outros 348 pacientes de um estudo independente. Para cada tumor, quantificaram com que frequência escolhas específicas de splicing eram usadas, resumindo-as com um número entre zero e um. Em seguida, construíram um pipeline passo a passo de aprendizado de máquina que primeiro triava milhares de eventos de splicing em busca de qualquer ligação com o tempo em que os pacientes permaneceram livres de progressão tumoral, e depois reduziu cuidadosamente essa lista evitando sinais redundantes ou sobrepostos. O resultado final foi uma "assinatura" compacta de apenas cinco eventos de splicing específicos cujo comportamento combinado melhor acompanhou se o câncer de um paciente progrediu mais cedo ou mais tarde.
Classificando pacientes em grupos de menor e maior risco
Usando essa assinatura de cinco eventos, a equipe definiu uma pontuação numérica de risco para cada paciente somando as medições de splicing, ponderadas pela força da relação de cada uma com a progressão. Pacientes cujos tumores apresentavam preferência por três dos padrões de splicing tendiam a evoluir pior, enquanto dois padrões se associaram a desfechos melhores. A pontuação dividiu os pacientes de forma nítida em grupos de baixo e alto risco: tanto na coorte original quanto no grupo de validação independente, aqueles com pontuações altas experimentaram progressão do câncer significativamente mais cedo. Ao traçarem curvas de tempo até a progressão, as duas linhas se separaram claramente, indicando que esse conjunto pequeno de edições de RNA capturou diferenças significativas no comportamento tumoral entre centenas de indivíduos.
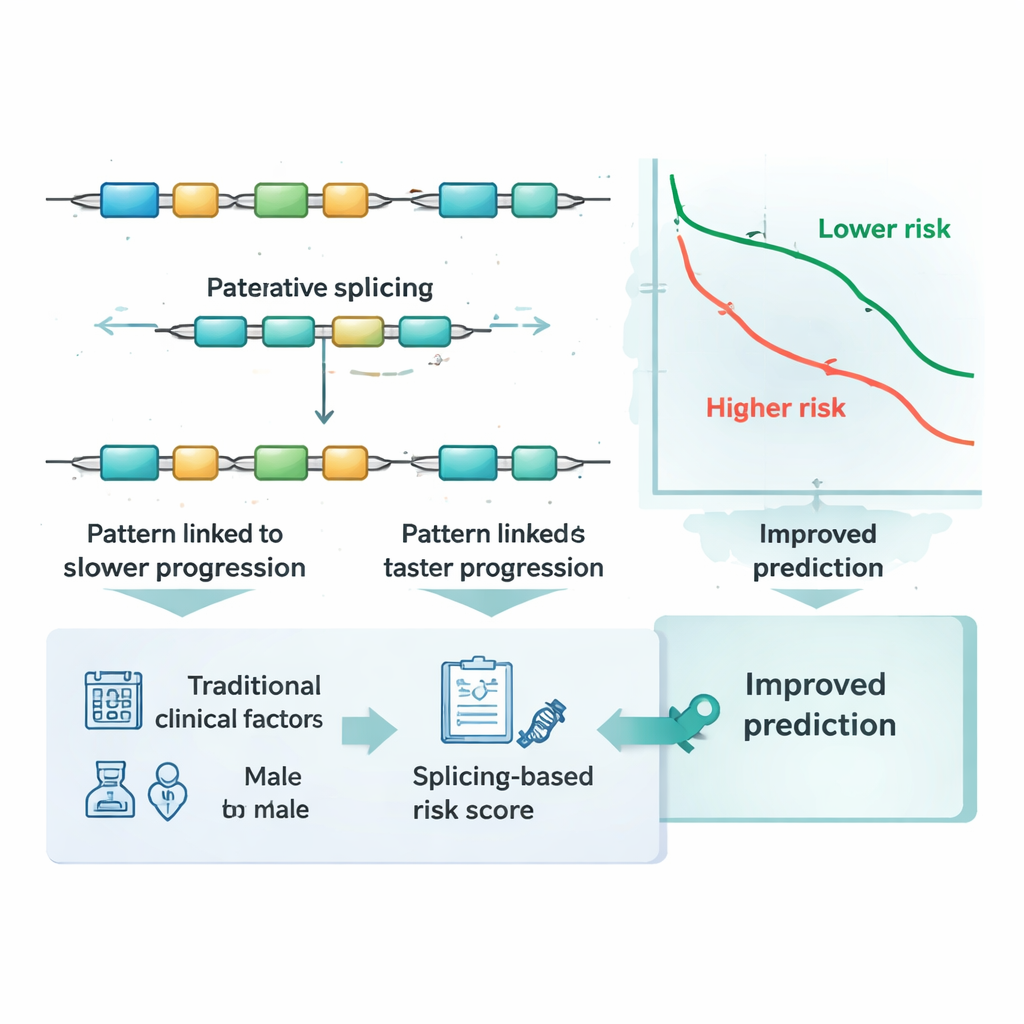
Além do estadiamento padrão e de marcadores conhecidos
Atualmente, os médicos se baseiam no estadiamento tumoral, na idade e em outras características clínicas para estimar risco, e às vezes em alterações específicas de DNA ou níveis de atividade gênica. Os pesquisadores investigaram se a pontuação baseada em splicing agregava informação além dessas medidas estabelecidas. Usando testes de acurácia dependentes do tempo, mostraram que previsões baseadas apenas em estadiamento, idade e sexo melhoraram de forma perceptível quando a pontuação de risco de splicing foi adicionada. Também compararam a pontuação a dezenas de marcadores moleculares já conhecidos no câncer colorretal e a vários métodos estatísticos comuns. Em ambos os grupos principais de pacientes, a assinatura de cinco eventos de splicing igualou ou superou essas alternativas e melhorou a predição quando usada em conjunto com elas, sugerindo que captura informações que outros marcadores deixam passar.
O que isso pode significar para cuidados futuros
Para o público leigo, a mensagem principal é que a forma como um tumor "edita" seu RNA pode revelar o quão perigoso ele provavelmente será. Este estudo demonstra que monitorar apenas cinco edições específicas de RNA em tumores colorretais pode classificar pacientes em grupos com diferenças significativas na probabilidade de permanecerem livres de progressão. Embora esse trabalho ainda precise ser traduzido em testes laboratoriais práticos e avaliado em ensaios clínicos prospectivos, aponta para um futuro em que os médicos poderiam usar essa pontuação no momento do diagnóstico para decidir quem precisa de tratamento mais agressivo e acompanhamento mais próximo, e quem pode evitar o tratamento excessivo com segurança. Mais amplamente, oferece um quadro reutilizável para minerar padrões de splicing de RNA em outros cânceres, refinando prognósticos e orientando terapias verdadeiramente personalizadas.
Citação: Maimekov, U., Nosrati, M., Mahmoud, A. et al. Machine learning framework for mRNA alternative splicing analysis identifies a signature of progression in colorectal adenocarcinoma. Sci Rep 16, 7106 (2026). https://doi.org/10.1038/s41598-026-35903-w
Palavras-chave: câncer colorretal, splicing alternativo, sequenciamento de RNA, aprendizado de máquina, prognóstico do câncer