Clear Sky Science · pt
Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning
Por que isso importa para fazendas e alimentação
A alfafa é um pilar da agricultura moderna, alimentando vacas leiteiras e contribuindo para solos mais saudáveis. Ainda assim, o melhoramento de alfafa — plantas que resistam ao inverno, a danos e forneçam ração de alta qualidade — tem sido dificultado pela grande complexidade de sua genética. Este estudo apresenta uma nova forma de transformar longas e confusas listas de marcadores de DNA em mapas claros de causa e efeito que mostram quais partes do genoma realmente impulsionam características importantes do caule e quais apenas aparecem associadas.
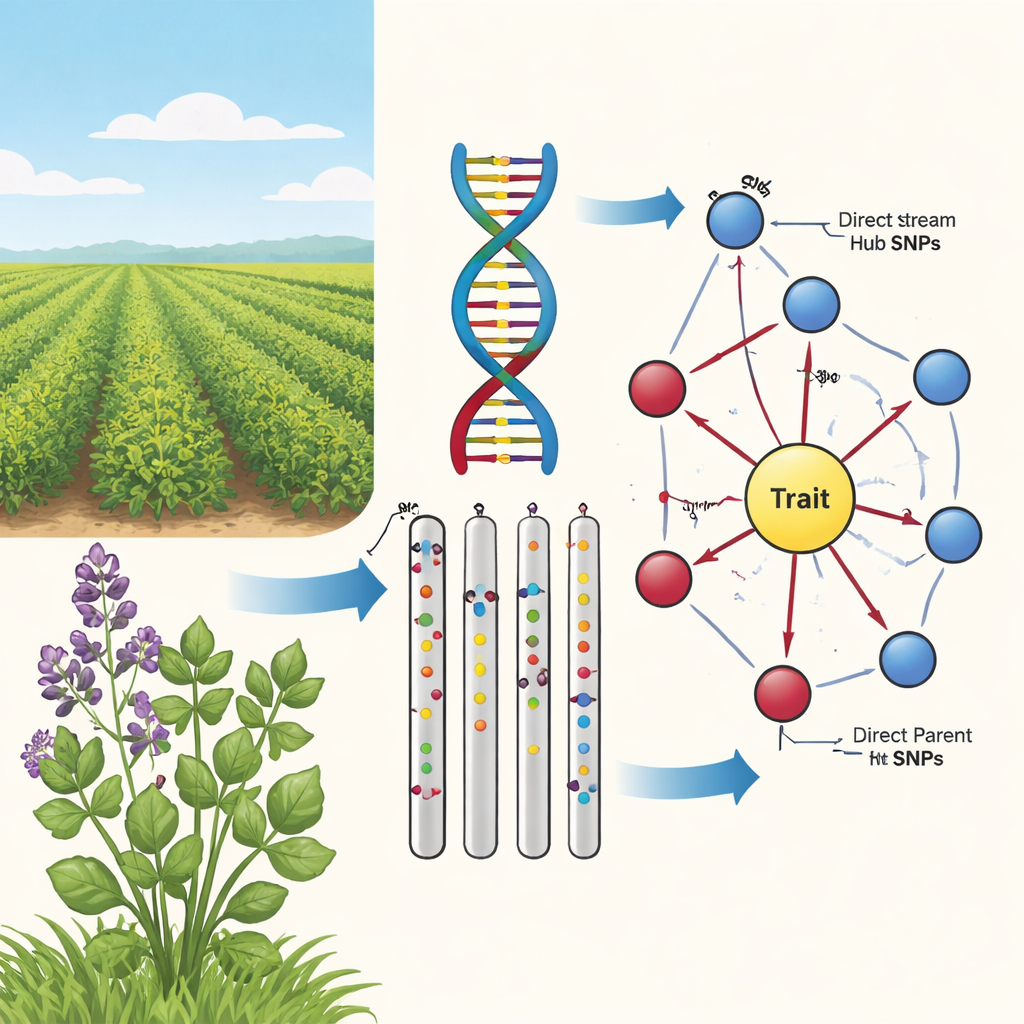
De vínculos soltos a causa e efeito
Estudos tradicionais de associação genômica varrem o genoma em busca de variações no DNA, chamadas SNPs, que tendem a aparecer junto a um traço, como cor do caule ou sobrevivência no inverno. Na alfafa, entretanto, a situação é especialmente emaranhada: ela tem quatro cópias de cada cromossomo, grandes trechos de DNA se movem juntos e as plantas são geneticamente muito misturadas. Isso cria uma “névoa de correlação” onde muitos marcadores parecem importantes, mas apenas alguns influenciam de fato o traço. Os autores defendem que os melhoristas precisam de mais do que ligações estatísticas simples; precisam saber quais marcadores estão nos caminhos causais reais do genótipo para os traços visíveis da planta.
Como funciona o novo quadro
Os pesquisadores construíram um quadro em duas etapas que combina aprendizado de máquina moderno com ideias da teoria de grafos causais. Primeiro, usaram uma técnica chamada Double Machine Learning para triagem de cerca de 2.400 SNPs em 500 genótipos de alfafa. Essa etapa remove a influência de fatores ocultos, como antecedentes familiares e geografia, usando componentes principais do genoma como proxies. O resultado é uma visão mais limpa de quais marcadores ainda mostram efeito direto sobre traços como cor do caule, depois de controlar essas influências de confusão. Nessa visão filtrada, picos fortes e estáveis de sinal apareceram principalmente nos cromossomos 2 e 4, e marcadores-chave mostraram tamanhos de efeito cujos intervalos de confiança claramente excluíam zero, sugerindo influência causal real.
Transformando marcadores em mapas genéticos
Na segunda etapa, a equipe utilizou um algoritmo de aprendizado de grafos causais, conhecido como algoritmo PC, para conectar os marcadores mais promissores em uma rede direcional. Nesses diagramas, os nós representam SNPs e o traço, e as setas mostram a direção de influência mais provável. Ao aparar arestas que conflitam com a biologia básica (por exemplo, traços não podem alterar o DNA subjacente) e mantendo apenas SNPs que alimentam o traço, os autores obtiveram mapas compactos e biologicamente plausíveis. Essas redes em “girassol” revelam uma estrutura em camadas: um anel interno de SNPs Pais Diretos que se conectam diretamente ao traço, e um anel externo de SNPs Hubs a Montante que influenciam múltiplos pais, mas não tocam o traço diretamente.
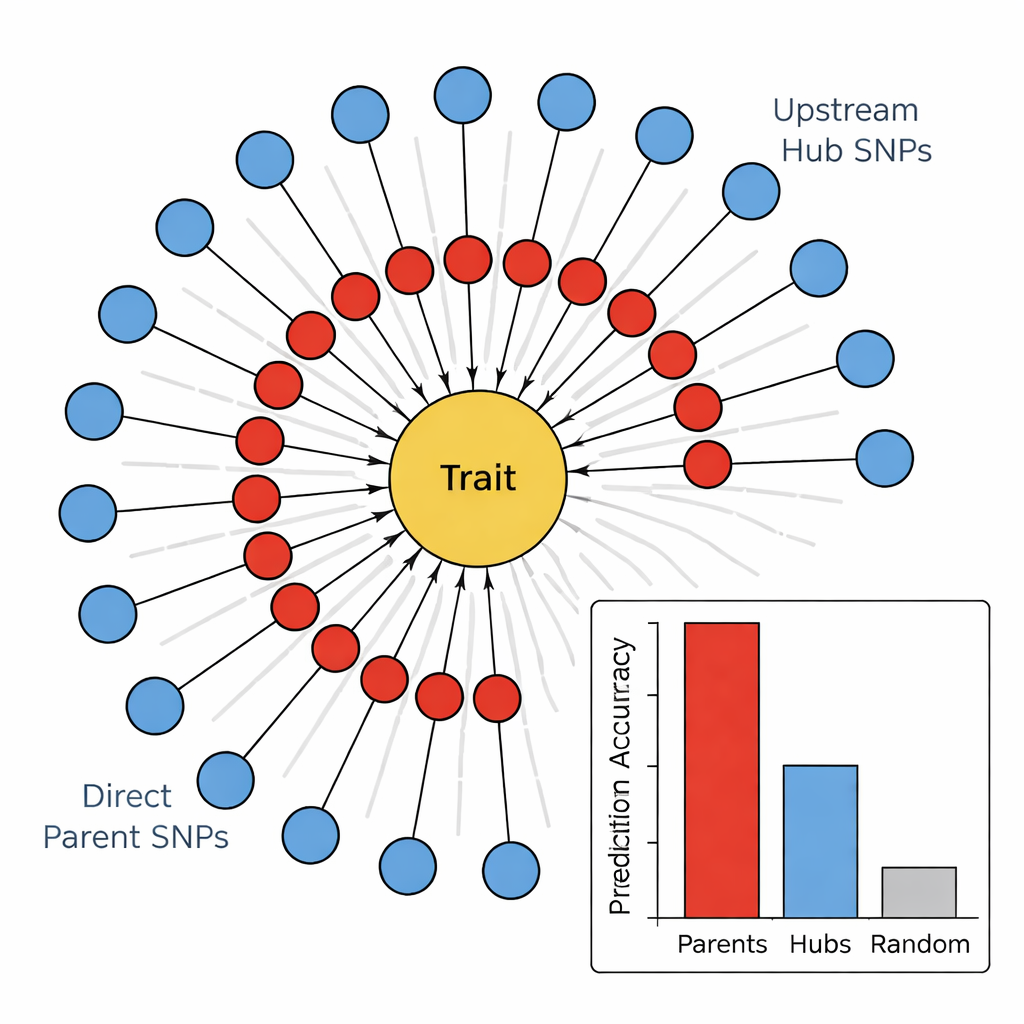
Executores versus diretores no genoma
Para testar se essa hierarquia era significativa, os autores compararam quão bem diferentes grupos de marcadores podiam prever quatro traços relacionados ao caule: cor do caule, preenchimento do caule, resistência do caule e dano de inverno. Em todos os traços, os SNPs Pais Diretos foram consistentemente os melhores preditores, frequentemente explicando várias vezes mais variação do que marcadores aleatórios ou os Hubs a Montante. Em contraste, os hubs mostraram poder preditivo fraco ou até negativo, apesar de serem altamente conectados na rede. Quando a equipe ligou esses SNPs a genes conhecidos, surgiu um padrão: Pais Diretos frequentemente coincidiam com enzimas ou proteínas estruturais que atuam diretamente nas paredes celulares, pigmentos ou danos por estresse, enquanto Hubs tendiam a corresponder a fatores de transcrição e proteínas regulatórias que ajustam amplamente vários caminhos ao mesmo tempo.
O que isso significa para o melhoramento futuro da alfafa
Para melhoristas e geneticistas, o estudo oferece uma forma de cortar os resultados ruidosos de associação e focar nas mudanças de DNA que realmente movem a agulha para traços específicos. Os autores mostram que combinar uma triagem desconfundida com grafos causais pode atuar como uma salvaguarda contra overfitting, transformando longas listas de candidatos em redes pequenas e interpretáveis alinhadas com a biologia conhecida. Em termos práticos, os SNPs Pais Diretos se tornam marcadores de alta precisão para selecionar plantas com caules melhores ou maior sobrevivência no inverno, enquanto os Hubs a Montante apontam para interruptores mestres que podem remodelar respostas amplas ao estresse, porém com possíveis trade-offs. Essa visão estrutural do genoma cria uma base para uma seleção genômica mais confiável em culturas complexas e para integrar camadas futuras de dados, como expressão gênica e metabolismo, em modelos coerentes de causa e efeito do desempenho das plantas.
Citação: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Palavras-chave: alfalfa genetics, causal graph learning, genomic selection, plant breeding, polyploid crops