Clear Sky Science · pt
Genômica comparativa de Pseudomonas aeruginosa multirresistente não suscetível à colistina revela linhagens emergentes na Tailândia
Por que esse microrganismo hospitalar importa para todos
Pseudomonas aeruginosa é um microrganismo hospitalar que ataca pessoas quando estão mais vulneráveis — após cirurgias, em respiradores ou em casos de queimaduras graves ou doenças pulmonares. Durante anos, médicos confiaram numa poderosa droga de “último recurso” chamada colistina quando outros antibióticos falham. Este estudo examina cepas de Pseudomonas de hospitais por toda a Tailândia que deixaram de responder à colistina e a muitos outros antibióticos. Ao sequenciar o DNA completo dessas bactérias, os pesquisadores mostram como novas linhagens altamente resistentes a medicamentos estão se espalhando, e por que isso deve preocupar pacientes, clínicos e sistemas de saúde em todo o mundo.
Rastreando uma infecção difícil de tratar pela Tailândia
A equipe concentrou-se em 29 cepas de Pseudomonas aeruginosa coletadas em 2021–2022 em hospitais que participam do programa nacional de vigilância da Tailândia para resistência a antibióticos. Todas essas cepas eram multirresistentes: resistiam a várias classes importantes de antibióticos, incluindo medicamentos normalmente usados para infecções graves. De forma crucial, também não eram totalmente suscetíveis à colistina, o fármaco muitas vezes reservado para casos com risco de vida. A maioria das amostras veio de urina, mas outras foram obtidas de sangue, escarro, pus e fluidos de drenos cirúrgicos — refletindo os diferentes tipos de infecções que esse microrganismo pode causar em pacientes hospitalizados.
Lendo as “impressões digitais” genéticas das bactérias
Usando uma combinação de sequenciamento de DNA de leituras curtas e longas, os pesquisadores montaram genomas de alta qualidade para cada cepa. Em seguida, compararam esses genomas para classificar as bactérias em famílias genéticas, conhecidas como tipos de sequência. Foram encontradas nove tipos de sequência distintos, revelando diversidade substancial. Um deles, rotulado ST5340, nunca havia sido descrito antes. Ele mostrou ser intimamente relacionado a um clone internacional de alto risco conhecido, ST357, diferindo em apenas um dos sete genes housekeeping padrão. Apesar dessa proximidade, o ST5340 destacou‑se porque todas as suas isoladas resistiam a todos os antibióticos testados, marcando‑o como uma linhagem particularmente preocupante.
Linhagens de alto risco emergentes e sua disseminação
Ao alinhar pequenas diferenças de DNA chamadas polimorfismos de nucleotídeo único em 108 genomas tailandeses de Pseudomonas (as 29 novas mais 79 de bancos de dados públicos), a equipe construiu uma árvore filogenética das cepas que circulam no país. Essa análise destacou vários aglomerados dominantes centrados em ST5340, ST357, ST654 e ST235 — linhagens já conhecidas, ou agora emergentes, como “de alto risco” porque frequentemente resistem a múltiplos medicamentos e causam surtos hospitalares. O ST5340, em particular, apareceu em várias províncias e regiões, sugerindo que está se espalhando amplamente em vez de estar confinado a um único hospital. Outros clones globais de alto risco, como ST654 e ST235, também estavam presentes, enquanto algumas linhagens de importância global, como ST244, estavam ausentes — provavelmente porque o estudo incluiu somente cepas não suscetíveis à colistina.
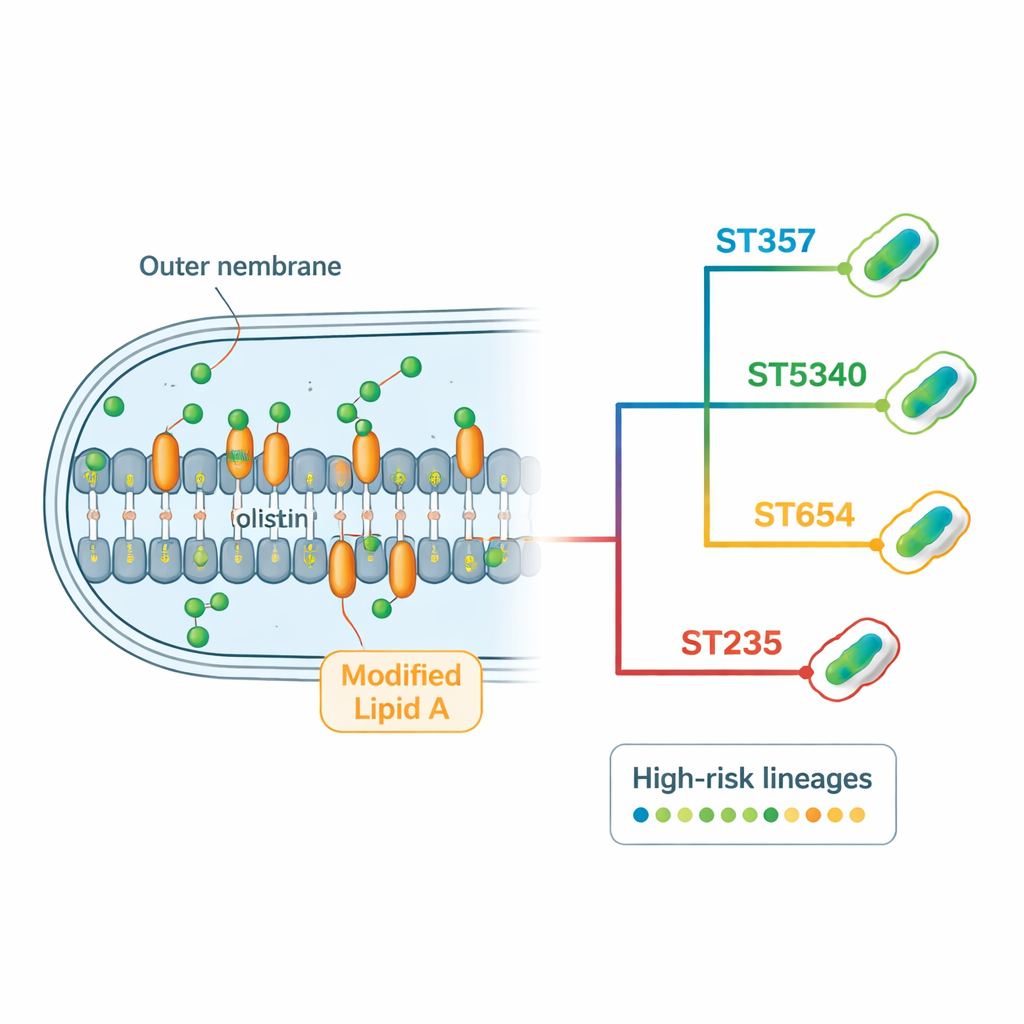
Como essas bactérias burlam os antibióticos
A análise genômica revelou um “resistoma” denso — o conjunto completo de genes e mutações de resistência que cada cepa carrega. Muitas isoladas codificavam vários tipos de beta‑lactamases, enzimas que degradam antibióticos comuns como penicilinas, cefalosporinas e carbapenêmicos. O gene de carbapenemase blaNDM‑1, associado à resistência a alguns dos fármacos hospitalares mais potentes, apareceu em quase todas as cepas, às vezes em cópias múltiplas. As bactérias também possuíam genes que modificam quimicamente os aminoglicosídeos, além de bombas de efluxo potentes que funcionam como “bombeamento” molecular para expulsar drogas da célula. Especificamente para colistina, a equipe não encontrou genes de resistência móveis, mas identificou alterações recorrentes em genes cromossômicos envolvidos na membrana externa celular e em sua regulação. Certas mutações em proteínas regulatórias e em enzimas que constroem o lipídio A mostraram forte ligação com resistência à colistina, especialmente nas linhagens dominantes ST357 e ST5340.
O que isso significa para pacientes e hospitais
Ao combinar vigilância nacional com sequenciamento genômico moderno, este estudo mostra que os hospitais da Tailândia enfrentam uma ameaça crescente de um clone de alto risco recém‑reconhecido, ST5340, ao lado de cepas problemáticas globais estabelecidas. Essas bactérias não são apenas resistentes à colistina, mas também a muitos outros medicamentos-chave, reduzindo drasticamente as opções de tratamento quando pacientes desenvolvem infecções graves. Para leitores leigos, a mensagem é clara: a resistência a antibióticos não é um risco abstrato no futuro, mas uma realidade presente que pode afetar diretamente os desfechos de cirurgias, tratamentos em terapia intensiva e terapias oncológicas. Os autores defendem que vigilância genômica contínua, controle de infecções mais rigoroso e uso criterioso de antibióticos são urgentemente necessários para impedir que essas linhagens altamente resistentes se tornem ainda mais disseminadas e difíceis de conter.
Citação: Wankaew, N., Arigul, T., Kruasuwan, W. et al. Comparative genomics of colistin-nonsusceptible multidrug-resistant Pseudomonas aeruginosa reveals emerging lineages in Thailand. Sci Rep 16, 5968 (2026). https://doi.org/10.1038/s41598-026-35520-7
Palavras-chave: Pseudomonas aeruginosa, resistência a antibióticos, colistina, vigilância genômica, infecções hospitalares