Clear Sky Science · pt
Uma rede neural gráfica informada por física para aproximar afinidade de ligação baseada em docking para DYRK2 no reposicionamento de fármacos para Alzheimer
Por que isso importa para o Alzheimer
A doença de Alzheimer está aumentando no mundo todo, mas a maioria dos medicamentos atuais apenas alivia sintomas em vez de interromper a doença. Testar novos fármacos em laboratório é lento e caro, especialmente para proteínas cerebrais menos estudadas que podem ser importantes para memória e saúde dos neurônios. Este estudo explora um atalho inteligente: usar um modelo de inteligência artificial que incorpora princípios físicos para prever o quão bem medicamentos existentes para Alzheimer podem se ligar a uma proteína pouco explorada chamada DYRK2, potencialmente abrindo novos caminhos para tratamento.
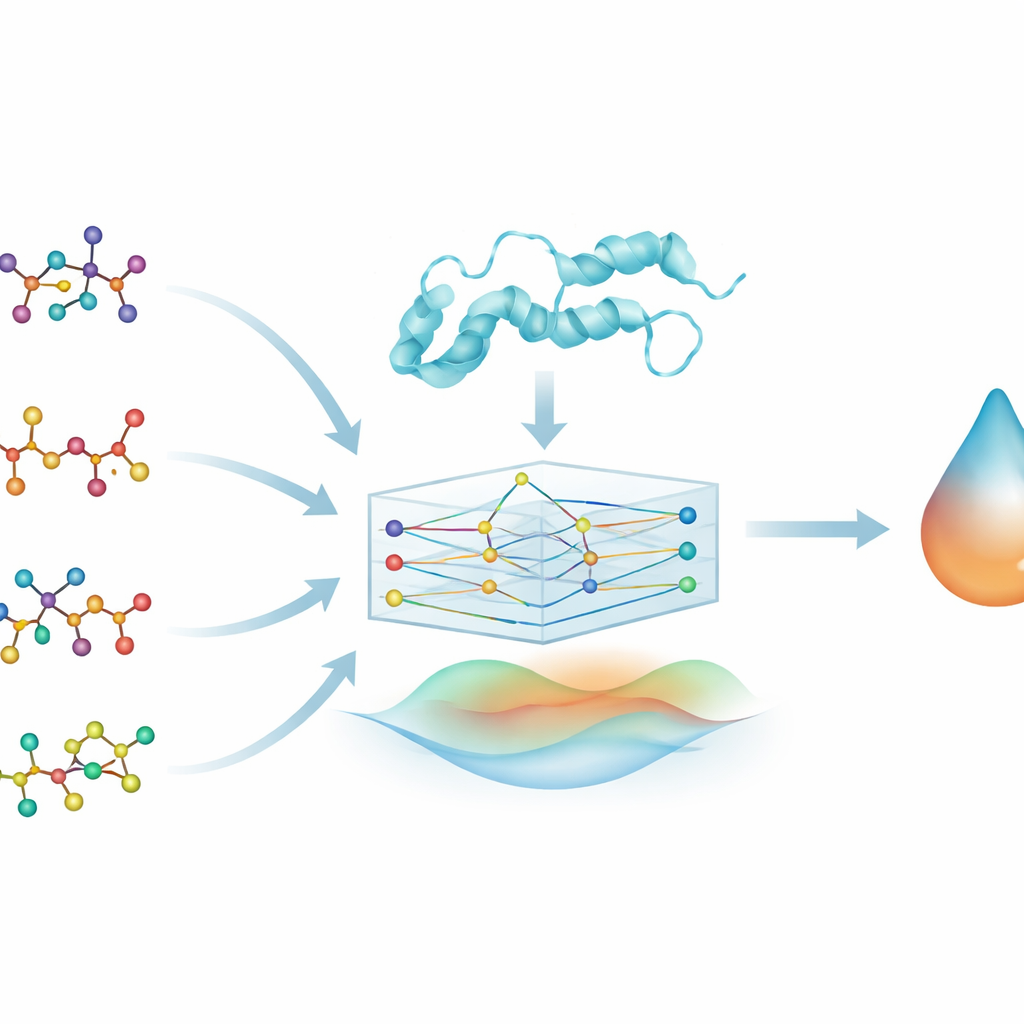
Uma nova forma de olhar medicamentos antigos
Em vez de projetar compostos totalmente novos do zero, os pesquisadores focam no reposicionamento de medicamentos — encontrar novos usos para remédios já aprovados e conhecidos por serem relativamente seguros. Eles examinam quatro fármacos familiares no tratamento do Alzheimer (brexpiprazol, donepezila, galantamina e rivastigmina) e investigam o quão fortemente cada um pode se ligar à DYRK2, uma quinase envolvida no crescimento e na função das células nervosas. A DYRK2 foi pouco estudada na doença de Alzheimer, mas evidências iniciais a ligam a sinapses, axônios e memória, tornando-a um alvo intrigante que pode complementar as terapias atuais.
Transformando moléculas em redes
Para explorar essas relações entre fármaco e proteína, a equipe transforma cada molécula em um grafo: átomos se tornam nós e ligações químicas viram arestas que os conectam. Fazem algo similar para a proteína DYRK2, representando sua sequência de aminoácidos como uma cadeia de unidades conectadas. Um tipo de modelo de aprendizado de máquina chamado rede neural gráfica (GNN) trabalha naturalmente com esses dados em forma de grafo, transmitindo informação ao longo das conexões para aprender padrões de forma e química. Isso permite que o modelo, chamado PhysDual-GCN, “leia” tanto o fármaco quanto a DYRK2 como redes interativas, em vez de simples sequências ou listas de características.
Mesclando física com inteligência artificial
A maioria das ferramentas de deep learning em descoberta de fármacos aprende apenas a partir de dados, o que pode tornar seus processos internos difíceis de interpretar. Aqui, os autores incorporam deliberadamente ideias físicas básicas sobre como átomos interagem. Além das características aprendidas pelo grafo, o PhysDual-GCN calcula dois termos clássicos de energia: um que capta atração e repulsão elétrica entre cargas parciais e outro que descreve as forças de van der Waals. Essas energias baseadas em física são combinadas com a representação interna da GNN antes da saída que prediz a intensidade de ligação. Na prática, o modelo é treinado para imitar o comportamento de programas de docking padrão — em particular o AutoDock Vina e ferramentas relacionadas —, mas fazendo isso de forma mais rápida, ao mesmo tempo que permanece ancorado em princípios físicos familiares.
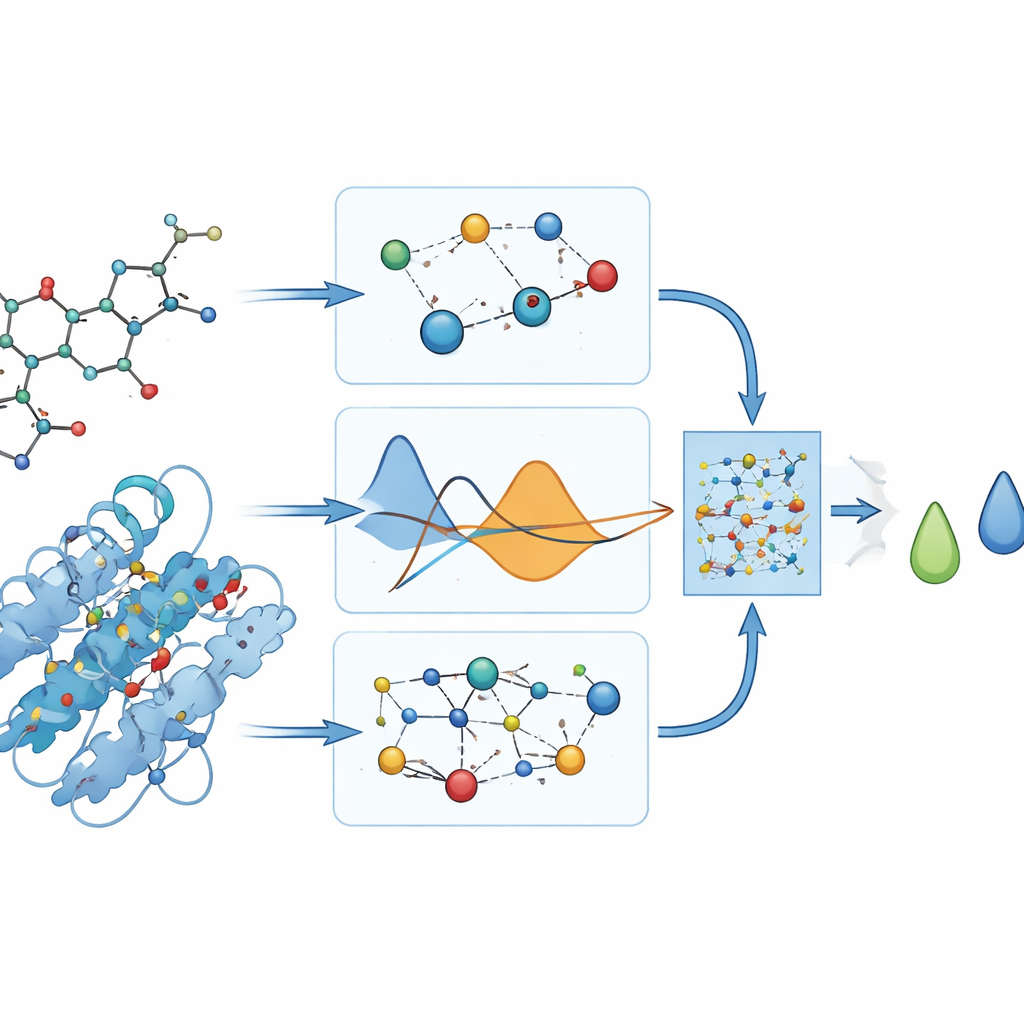
O que o modelo realmente prevê
Como não existem medições laboratoriais de quão fortemente esses fármacos se ligam à DYRK2, os autores recorrem a programas de docking para fornecer escores de ligação “de referência” em unidades de energia. Eles cuidadosamente evitam usar esses escores no processo de treinamento e, em vez disso, empregam-nos apenas depois para avaliar o quanto o PhysDual-GCN aprendeu. Para os quatro medicamentos para Alzheimer, o modelo reproduz os valores de docking com pequenos erros médios (cerca de um terço de quilocaloria por mol) e classifica corretamente os compostos: donepezila e brexpiprazol aparecem como os ligantes mais fortes, enquanto galantamina e rivastigmina mostram-se mais fracas, mas ainda relativamente estáveis. Esses resultados indicam que a GNN informada por física pode funcionar como um substituto computacional para execuções de docking mais lentas.
Promessas e limites da abordagem
Apesar desses números encorajadores, os autores enfatizam que o estudo tem limites claros. Foram examinados apenas quatro medicamentos, e todas as avaliações dependem de outros programas computacionais em vez de experimentos bioquímicos reais. A proteína DYRK2 é modelada principalmente como um grafo unidimensional da sequência, não como uma estrutura tridimensional completa, de modo que o modelo ainda não pode levar em conta a forma detalhada dos bolsões de ligação. As energias físicas em si são simplificadas, usando parâmetros e cortes padrão de campos de força. Como resultado, o trabalho deve ser visto como uma prova de conceito: demonstra que redes neurais gráficas guiadas por física podem acompanhar de perto escores clássicos de docking em um cenário com poucos dados, mas ainda não prova que as previsões correspondem à realidade em tubos de ensaio ou na clínica.
O que isso significa para pesquisas futuras sobre Alzheimer
Para não especialistas, a mensagem principal é que algoritmos inteligentes e conscientes da física podem ajudar cientistas a explorar novos alvos para Alzheimer, como a DYRK2, muito mais rapidamente do que métodos tradicionais isoladamente. Ao destacar donepezila e brexpiprazol como possíveis ligantes promissores para DYRK2 e oferecer uma forma transparente de aproximar resultados de docking, o PhysDual-GCN fornece um ponto de partida para estudos laboratoriais mais aprofundados. Com bibliotecas de fármacos maiores, informação 3D proteica mais rica e validação experimental, esse tipo de modelo pode se tornar uma ferramenta prática para triagem de candidatos a tratamento e orientar esforços de reposicionamento de medicamentos com o objetivo de desacelerar ou alterar o curso da doença de Alzheimer.
Citação: Gider, V., Budak, C. A physics-informed graph neural network to approximate docking-based binding affinity for DYRK2 in Alzheimer’s drug repurposing. Sci Rep 16, 8357 (2026). https://doi.org/10.1038/s41598-026-35102-7
Palavras-chave: Doença de Alzheimer, reposicionamento de medicamentos, redes neurais gráficas, ligação proteína–ligante, quinase DYRK2