Clear Sky Science · pt
Diversidade genética de Pseudomonas aeruginosa isolada de amostras clínicas usando marcador molecular ISSR em um hospital universitário de assistência terciária
Por que os germes hospitalares importam para todos nós
Qualquer pessoa que já passou tempo em um hospital — seja como paciente ou visitando um familiar — depende de antibióticos que funcionem quando mais são necessários. Mas alguns microrganismos estão ficando tão resistentes que até nossos medicamentos mais fortes têm dificuldade em detê‑los. Este artigo explora um desses causadores de doenças, uma bactéria chamada Pseudomonas aeruginosa, e mostra como cientistas em um hospital indiano mapearam sua diversidade genética oculta para entender melhor por que é tão difícil controlá‑la.
Um germem persistente nos hospitais modernos
Pseudomonas aeruginosa é um adversário escorregadio. Ela prospera em ambientes úmidos, desde tubos de ventilação até curativos, e ataca especialmente pessoas com defesas enfraquecidas por doença, queimaduras ou longas internações. Pode causar infecções graves nos pulmões, sangue, trato urinário e feridas. O que a torna especialmente perigosa é sua habilidade de resistir a muitos antibióticos ao mesmo tempo, transformando infecções rotineiras em crises potencialmente fatais e elevando custos e tempo de internação em todo o mundo.
Olhando abaixo da superfície da infecção
Para avaliar quão diversa essa bactéria é dentro de um único hospital, os pesquisadores coletaram 100 amostras bacterianas de sangue, urina, escarro e swabs de ferida colhidos durante os cuidados rotineiros em um grande hospital universitário no leste da Índia. Eles focaram em 18 cepas resistentes a múltiplos fármacos e testaram como cada uma reagia a um amplo painel de antibióticos. Preocupantemente, mais de quatro em cada cinco amostras eram resistentes a medicamentos-chave como cefoperazona, meropenem e imipeném — fármacos frequentemente reservados como última linha quando outros falham. Alguns antibióticos, incluindo alguns menos usados, ainda apresentaram melhor atividade, sugerindo opções terapêuticas remanescentes, embora reduzidas. 
Lendo os “códigos de barras” das bactérias
Contar quais medicamentos falharam foi apenas parte da história. A equipe também quis saber se essas infecções provinham de uma única “super‑cepa” bem‑sucedida se espalhando pelo hospital, ou de muitas linhagens não relacionadas chegando e evoluindo de forma independente. Para isso, usaram uma abordagem de impressão digital do DNA chamada ISSR, que destaca os trechos de código genético entre sequências repetidas curtas. Quando amplificados por PCR e separados em gel, esses trechos formam um padrão de bandas que funciona como um código de barras para cada cepa. Usando 17 primers informativos, os pesquisadores geraram 95 bandas de DNA distintas e então compararam os padrões entre as 18 cepas com ferramentas computacionais que agrupam impressões digitais semelhantes.
Muitos primos distantes, não um superbug
As comparações genéticas revelaram que o hospital não estava lidando com um único clone dominador. Em vez disso, as cepas se agruparam em vários clusters distintos, com escores de similaridade variando de parentes bastante próximos a primos geneticamente muito distantes. Alguns isolados que se comportaram de forma semelhante nos testes de sensibilidade a drogas mostraram‑se geneticamente diferentes, enquanto outros aparentados compartilhavam elementos de resistência. Gráficos de componentes principais e diagramas em forma de árvore reforçaram a imagem de múltiplas linhagens coexistindo na mesma unidade, em vez de uma cepa dominante varrendo o local. Essa diversidade provavelmente surge à medida que as bactérias trocam genes, sofrem mutações e se adaptam sob exposição contínua a antibióticos e ao sistema imunológico humano. 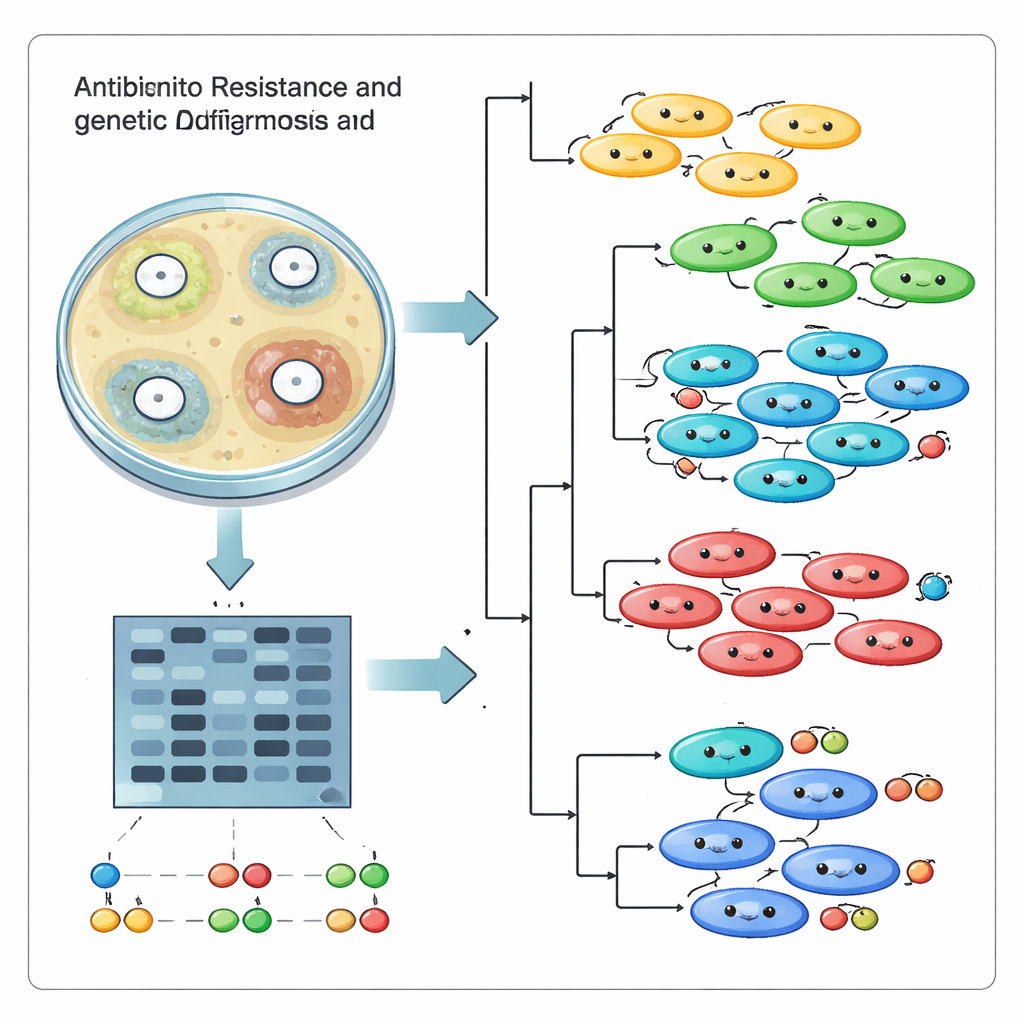
O que isso significa para pacientes e hospitais
Para os hospitais, esses achados transmitem uma mensagem clara: acompanhar apenas quais antibióticos falham não basta. Como cepas geneticamente distintas podem exibir padrões de resistência semelhantes — e cepas próximas podem se comportar de forma diferente — as equipes de saúde precisam tanto de testes rotineiros de susceptibilidade a fármacos quanto de vigilância genética periódica para acompanhar como a população bacteriana muda ao longo do tempo. A abordagem ISSR usada aqui é relativamente simples e de baixo custo, tornando‑a atraente para ambientes com recursos limitados, embora os autores ressaltem que combiná‑la com sequenciamento de genoma completo em estudos futuros proporcionaria um quadro mais completo.
Uma paisagem oculta que exige vigilância
Em termos práticos, este estudo mostra que dentro de um único hospital Pseudomonas aeruginosa não é um inimigo único, mas uma multidão de causadores de problemas relacionados, porém distintos, muitos já armados contra múltiplos antibióticos. Ao mapear essa paisagem oculta de diversidade, os pesquisadores fornecem ferramentas e insights que podem ajudar médicos a escolher tratamentos mais direcionados e equipes de controle de infecção a desenhar estratégias de contenção mais inteligentes. O monitoramento contínuo desses padrões genéticos será essencial para manter uma vantagem sobre esse microrganismo adaptável e garantir a segurança do atendimento hospitalar aos pacientes.
Citação: Mishra, P., Sahoo, D. & Sahu, M.C. Genetic diversity of Pseudomonas aeruginosa isolated from clinical samples with ISSR molecular marker in a tertiary care teaching hospital. Sci Rep 16, 5315 (2026). https://doi.org/10.1038/s41598-026-35090-8
Palavras-chave: Pseudomonas aeruginosa, resistência a antibióticos, infecções hospitalares, diversidade genética, tipagem molecular