Clear Sky Science · pt
Montagem do genoma em nível cromossômico com resolução de haplótipos de uma camélia oleaginosa autohexaplóide Camellia osmantha
Por que uma árvore que produz óleo de cozinha é importante
Muita gente conhece as camélias como arbustos ornamentais, mas alguns de seus parentes são verdadeiros pilares na cozinha. O óleo extraído das sementes de camélia é valorizado em partes da Ásia como um óleo de cozinha favorável ao coração, rico em gorduras saudáveis e compostos vegetais protetores. Uma espécie em ascensão é a Camellia osmantha, uma árvore resistente e de alto rendimento que pode produzir muito mais óleo por hectare do que variedades tradicionais. Para aproveitar plenamente seu potencial, os cientistas precisam entender seu plano genético. Este estudo oferece exatamente isso: um mapa detalhado e de alta resolução do DNA da árvore, abrindo caminho para colheitas melhores, óleo mais saudável e árvores capazes de prosperar em um mundo em aquecimento.

Uma nova árvore oleaginosa com grande potencial
Camellia osmantha é uma espécie de camélia oleaginosa reconhecida recentemente. Reúne várias características valorizadas pelos agricultores: forte tolerância ao calor, ao frio e à seca, além de produção de óleo excepcionalmente alta — cerca do dobro das camélias comerciais típicas aos apenas cinco anos de idade. Como muitas plantas cultivadas selecionadas para rendimento, apresenta um genoma especialmente complexo: em vez das duas cópias usuais de cada cromossomo, carrega seis. Essa natureza “autohexaplóide” faz com que seu DNA seja enorme, aproximadamente cinco vezes maior que o genoma humano, e repleto de sequências repetidas. Tal complexidade tornou difícil construir um mapa genômico limpo e preciso com tecnologias anteriores.
Desvendando um quebra‑cabeça genético muito grande
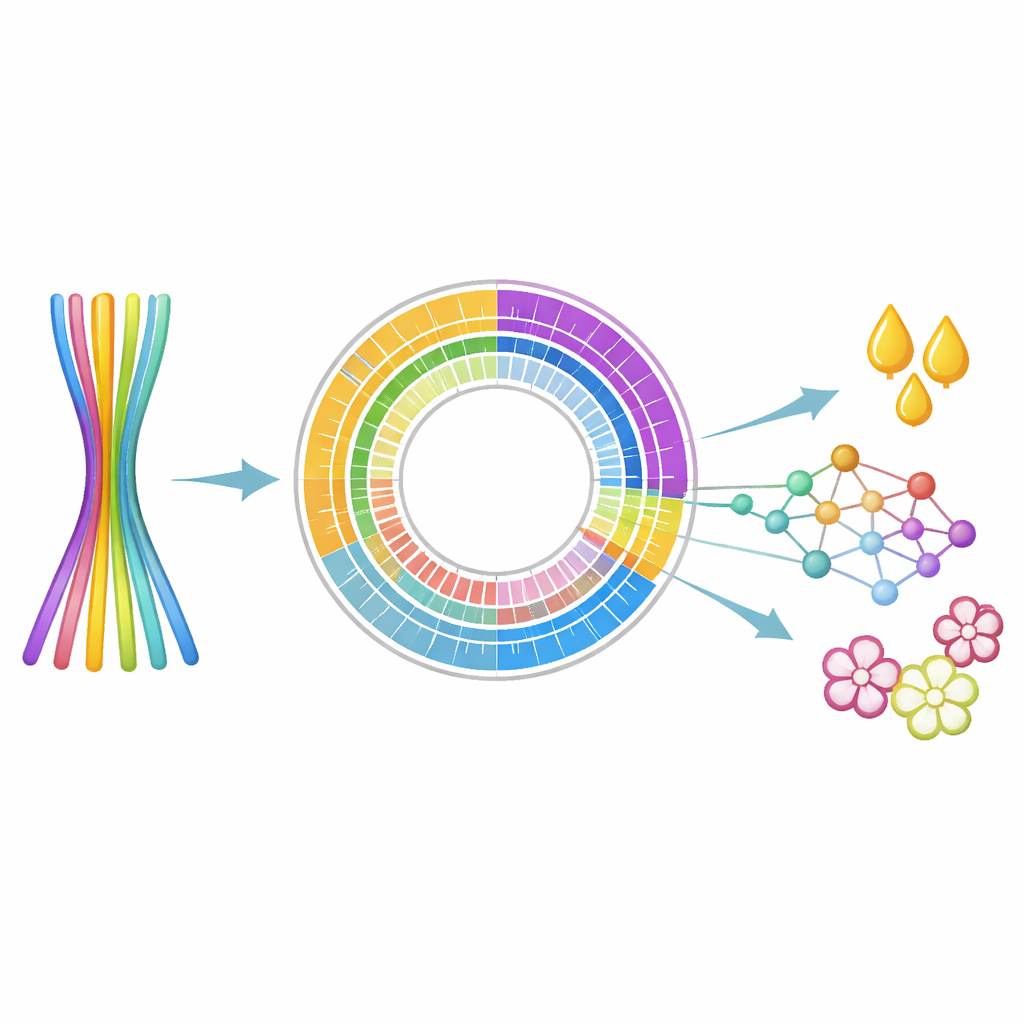
Para enfrentar esse desafio, os pesquisadores combinaram vários métodos avançados de sequenciamento de DNA. Leituras longas e altamente precisas da plataforma PacBio HiFi forneceram trechos de código genético com milhares de letras, enquanto dados de Hi‑C capturaram como os pedaços de DNA se dobram e se organizam dentro da célula — pistas que ajudam a juntar fragmentos em cromossomos inteiros. Também coletaram dados de RNA de folhas para ver quais genes estão realmente ativados. Usando novos algoritmos de montagem projetados para plantas poliplóides, a equipe montou um genoma de 14,38 bilhões de pares de bases e, crucialmente, o separou em seis “haplótipos” distintos mas correspondentes, cada um representando um conjunto completo de cópias dos cromossomos.
Seis cópias completas, vistas claramente pela primeira vez
A montagem final ancorou 11,08 bilhões de pares de bases em 90 estruturas longas semelhantes a cromossomos, organizadas em seis versões de 15 cromossomos. Uma versão, chamada Haplótipo 1, foi especialmente completa e limpa, com apenas um pequeno número de lacunas e indicadores mostrando mais de 95% de completude. Ao longo do genoma, os cientistas catalogaram uma vasta paisagem de DNA repetido, especialmente elementos de terminal longo (LTR) que compõem quase metade da sequência. Sobre esse mapa estrutural, identificaram 60.212 genes codificadores de proteínas e confirmaram que quase todos carregam partes funcionais reconhecíveis, sugerindo que o conjunto gênico é ao mesmo tempo amplo e confiável.
Genes ligados ao óleo e à floração
Com o genoma em mãos, a equipe buscou especificamente genes associados a características de interesse. Encontraram 3.269 fatores de transcrição — chaves “interruptoras de controle” para outros genes — e 2.655 genes semelhantes a genes conhecidos de resistência a doenças, que podem ajudar melhoristas a selecionar árvores que resistam a pragas e patógenos. Do ponto de vista agrícola, o mais empolgante foi a identificação de 80 genes envolvidos na síntese de óleos e gorduras, incluindo enzimas que iniciam a fabricação de lipídios e outras que ajustam os tipos de ácidos graxos armazenados nas sementes. Também catalogaram 497 genes relacionados ao tempo de floração e ao desenvolvimento floral, alavancas importantes para adaptar árvores a diferentes climas e estações de cultivo.
Uma base para melhores árvores e melhor óleo
Ao resolver cada uma das seis cópias cromossômicas e anotar cuidadosamente dezenas de milhares de genes, este trabalho transforma uma massa enorme e emaranhada de DNA em um manual de referência utilizável para Camellia osmantha. Melhoristas e biólogos moleculares agora podem rastrear quais versões de genes estão ligadas a maior rendimento de óleo, melhor qualidade do óleo, maior resistência a doenças ou resiliência ao calor e à seca. Em termos práticos, o estudo fornece um roteiro para desenvolver novas variedades de camélia oleaginosa mais produtivas, mais robustas e mais adequadas a alimentar pessoas em um clima em mudança — tudo isso a partir de uma imagem mais clara do que existe dentro das células desta árvore notável.
Citação: Zhang, Z., Hao, B., Li, M. et al. Haplotype-resolved chromosome-level genome assembly of an autohexaploid oil camellia tree Camellia osmantha. Sci Data 13, 395 (2026). https://doi.org/10.1038/s41597-026-06786-3
Palavras-chave: Camellia osmantha, genoma de planta, culturas poliplóides, óleos comestíveis, melhoramento de culturas