Clear Sky Science · pt
HMI-LUSC: Um Conjunto de Dados de Imagens Hiperespectrais Histológicas para Carcinoma Epidermoide de Pulmão
Vendo o Câncer em Novas Cores
O câncer de pulmão continua sendo uma das doenças mais letais do mundo, em parte porque identificar cada última célula cancerosa em uma lâmina de microscópio é difícil e demorado. Patologistas normalmente se apoiam em tecido corado de rosa e roxo visto ao microscópio, um método que captura a estrutura, mas perde pistas químicas sutis. Este artigo apresenta o HMI-LUSC, a primeira coleção aberta de imagens microscópicas de carcinoma epidermoide de pulmão capturadas não apenas em três cores, mas em dezenas de faixas estreitas de cor, oferecendo a computadores e clínicos uma visão muito mais rica do que distingue células tumorais de suas vizinhas saudáveis.
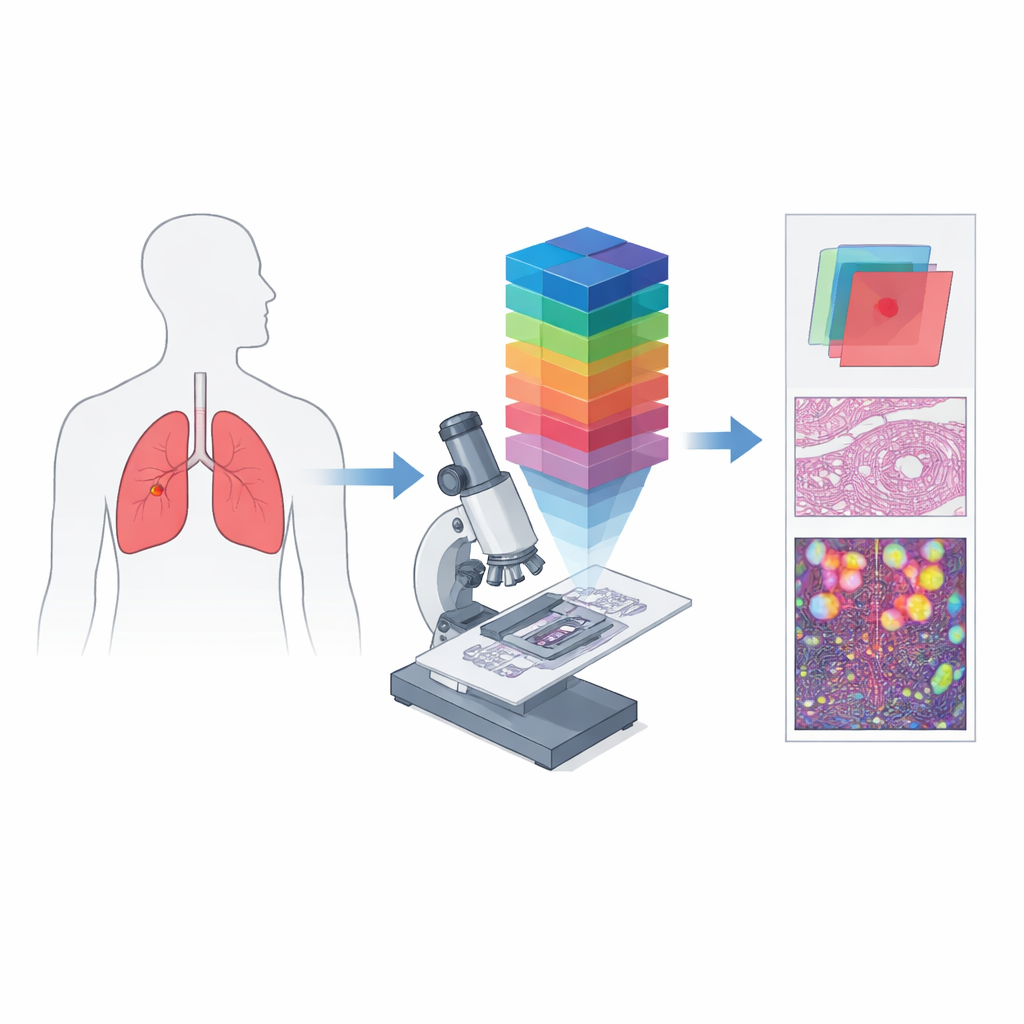
De Imagens Simples em Cores a Impressões Digitais Espectrais
A patologia digital convencional funciona de maneira semelhante à câmera de um telefone: registra canais vermelho, verde e azul para aproximar o que o olho vê. O imageamento hiperespectral vai vários passos além, dividindo a luz em muitos comprimentos de onda próximos, produzindo um “cubo de dados” tridimensional no qual cada pequeno ponto do tecido tem seu próprio espectro de cor detalhado. Quando essa ideia é combinada com um microscópio, ela se torna imageamento microscópico hiperespectral, capaz de capturar tanto a estrutura fina quanto informações espectrais ricas no nível de células individuais. Esses dados podem revelar diferenças em como os tecidos absorvem e refletem a luz que são invisíveis em imagens padrão, criando “assinaturas” espectrais únicas para regiões cancerosas e não cancerosas.
Construindo uma Nova Biblioteca para o Estudo do Câncer de Pulmão
Os autores criaram o HMI-LUSC para suprir uma lacuna clara: antes deste trabalho, não existia um conjunto de dados hiperespectral público para lâminas de câncer de pulmão, tornando difícil testar e comparar métodos de diagnóstico baseados em computador. Eles coletaram tecido de dez pacientes submetidos a cirurgia de tumor pulmonar, prepararam lâminas padrão coradas com hematoxilina e eosina e as digitalizaram em alta resolução. Patologistas experientes marcaram áreas tumorais e normais, e regiões representativas foram reimagens com um microscópio hiperespectral construído sob medida. Cada imagem resultante cobre um pequeno fragmento de tecido, mas abrange 61 comprimentos de onda entre 450 e 750 nanômetros, com resolução de 3088 por 2064 pixels. Para cada região, o conjunto de dados inclui o cubo espectral bruto, uma renderização RGB convencional e máscaras que delineiam onde o tecido tumoral está presente.
Transformando Contornos Brutos em Mapas ao Nível Celular
Embora marcações em nível de lâmina sejam úteis, treinar algoritmos modernos frequentemente exige informação ao nível de células individuais. Traçar manualmente cada célula é impraticável, então a equipe desenvolveu um fluxo de trabalho semi-automático. Primeiro, agruparam pixels em clusters com base em sua similaridade espectral usando um método padrão de visão computacional. Em seguida, patologistas inspecionaram esses clusters sobrepostos à imagem do tecido e os classificaram em quatro categorias: células tumorais, células não tumorais, tecido não celular como estroma ou sangue, e fundo vazio. Um segundo patologista revisou e ajustou esses resultados, com discordâncias resolvidas por consenso. O resultado é um conjunto de máscaras detalhadas pixel a pixel que capturam misturas sutis de tipos celulares e zonas de fronteira confusas, fornecendo material de ensino muito mais rico para sistemas de aprendizado de máquina.
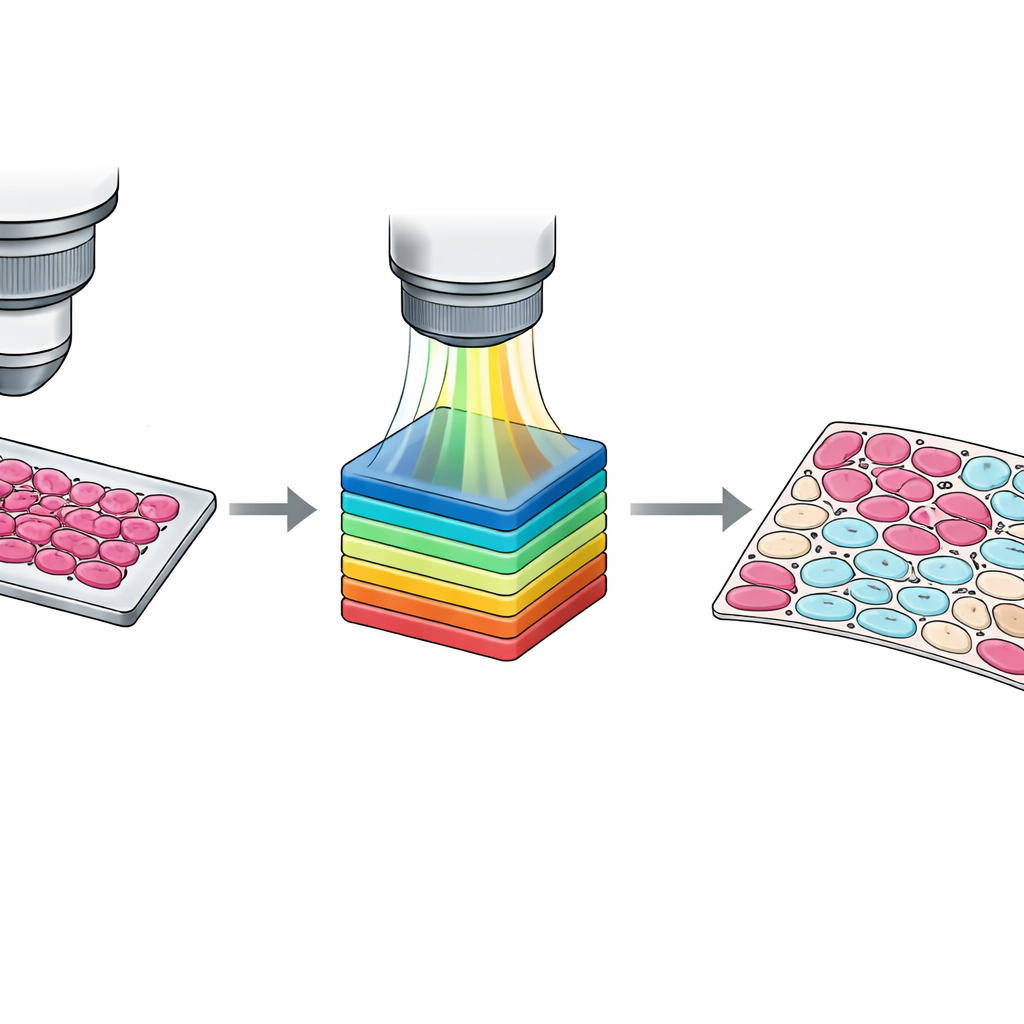
Garantindo Dados Nítidos e Confiáveis
Para tornar o conjunto de dados confiável, os autores testaram minuciosamente seu sistema de imageamento. Verificaram que o microscópio pode resolver padrões finos de cerca de um mícron — pequeno o suficiente para distinguir células individuais — e que o ruído de imagem é baixo na maior parte dos comprimentos de onda. Também compararam o espectro medido de uma fonte de luz padrão com curvas de referência e com uma câmera hiperespectral comercial, encontrando excelente concordância. Por fim, demonstraram como os dados podem ser usados executando modelos computacionais de referência, desde métodos clássicos de aprendizado de máquina até redes simples de aprendizado profundo, para segmentar regiões tumorais. Mesmo sem grande otimização, esses modelos obtiveram precisão sólida, mostrando que o conjunto de dados é bem adequado como um benchmark para métodos futuros.
O Que Isso Significa para o Futuro do Cuidado do Câncer de Pulmão
HMI-LUSC não substitui grandes coleções de lâminas padrão, nem é ainda uma ferramenta clínica por si só. Em vez disso, oferece aos pesquisadores uma janela cuidadosamente curada sobre como as células tumorais pulmonares diferem do tecido próximo através de muitos comprimentos de onda da luz. Ao tornar esses dados, rótulos e código abertamente disponíveis, os autores fornecem um campo de testes comum para desenvolver e comparar algoritmos que usam informação espectral, desde classificadores simples até redes neurais avançadas. A longo prazo, esse trabalho pode ajudar computadores a auxiliar patologistas a identificar tumores com mais precisão e rapidez, e pode revelar padrões espectrais ligados ao tipo de tumor ou à resposta ao tratamento que imagens ordinárias não conseguem mostrar.
Citação: Yan, Z., Huang, H., Guo, Y. et al. HMI-LUSC: A Histological Hyperspectral Imaging Dataset for Lung Squamous Cell Carcinoma. Sci Data 13, 415 (2026). https://doi.org/10.1038/s41597-026-06766-7
Palavras-chave: imageamento hiperespectral, câncer de pulmão, patologia digital, segmentação de tumor, conjunto de dados de imagens médicas