Clear Sky Science · pt
Perfil metabolômico e transcriptômico de duas espécies intimamente relacionadas do gênero Oldenlandia
Por que essas ervas humildes importam
Duas pequenas plantas daninhas usadas na medicina tradicional asiática, Oldenlandia diffusa e Oldenlandia corymbosa, são amplamente consumidas para problemas que vão de inflamação a doenças hepáticas e câncer. Ainda assim, apesar de sua longa história em remédios à base de plantas e de sua mistura frequente no mercado, sabemos surpreendentemente pouco sobre como elas realmente diferem internamente: quais ingredientes químicos produzem, em quais partes da planta e quais genes controlam esses ingredientes. Este estudo revela esse mundo oculto ao fornecer um mapa detalhado tanto das moléculas quanto da atividade gênica em diferentes tecidos das duas espécies.
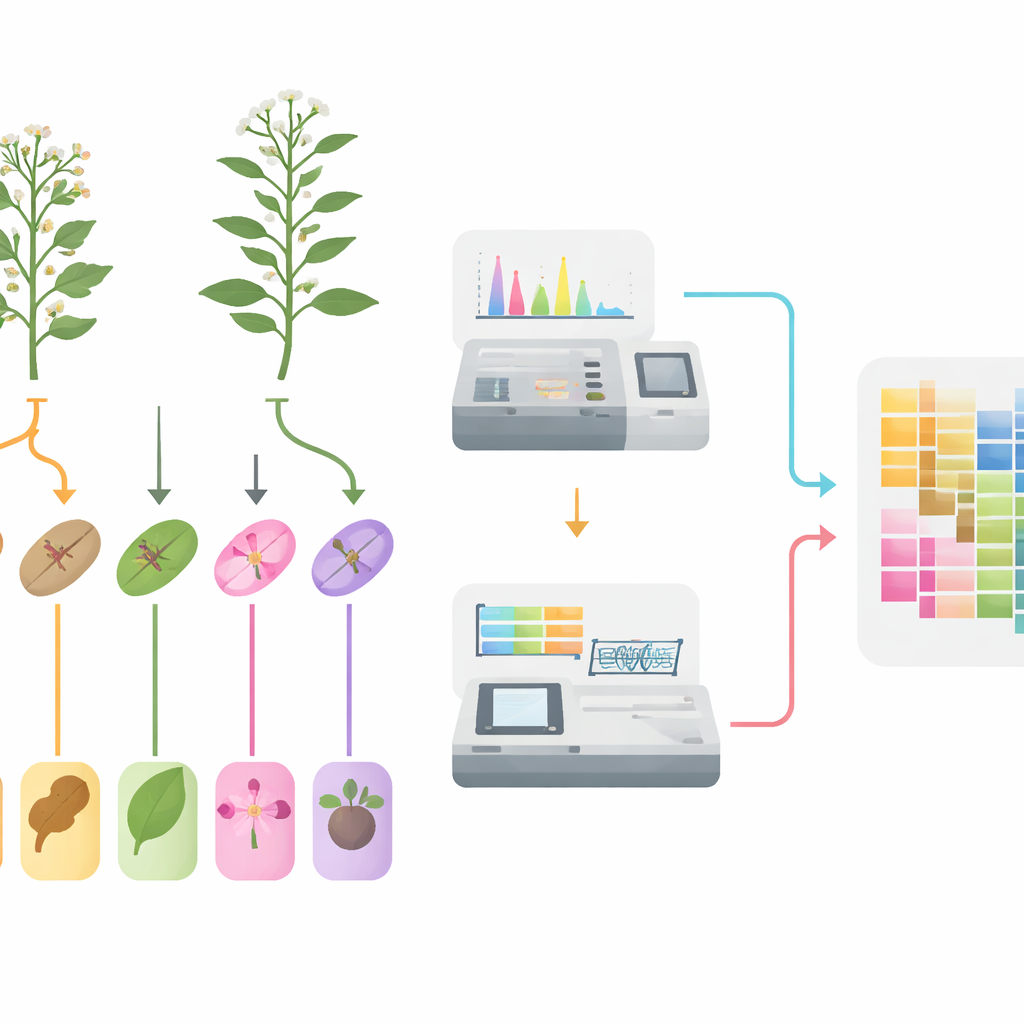
Do campo às amostras congeladas
Os pesquisadores começaram cultivando as duas espécies lado a lado nas mesmas condições de campo para evitar viés ambiental. Durante o período de floração, separaram cuidadosamente cinco tecidos — raízes, caules, folhas, flores e frutos — de várias plantas de cada espécie. Para capturar um retrato confiável da variação natural, agruparam material de muitos indivíduos e criaram seis réplicas biológicas para cada tipo de tecido. Cada amostra de tecido foi então dividida em duas: uma parte para medir pequenas moléculas e outra para ler quais genes estavam ativados.
Fazendo o inventário de milhares de compostos vegetais
Para catalogar a composição química das plantas, a equipe usou uma abordagem sensível baseada em espectrometria de massa que pode rastrear um grande número de metabólitos vegetais conhecidos em uma única análise. Em 60 amostras, detectaram 1.342 moléculas distintas, dominadas por grupos já suspeitos de serem importantes para a medicina: quase um quarto eram flavonoides, seguidos por ácidos fenólicos, alcaloides e terpenoides. Análises estatísticas mostraram que as amostras de tecido se agrupavam claramente por tipo, e os controles de qualidade confirmaram que as medições eram estáveis e reprodutíveis. A comparação do mesmo tecido entre as duas espécies revelou numerosas moléculas muito mais abundantes em uma espécie do que na outra, especialmente em vias relacionadas a pigmentos de cor, compostos de defesa e outros metabólitos especializados.
Lendo os manuais de instruções das plantas
Paralelamente, os cientistas extraíram RNA dos mesmos tecidos para ver quais genes estavam ativos, capturando assim as instruções internas das plantas no momento da amostragem. O sequenciamento de alto rendimento gerou mais de 500 gigabases de dados de alta qualidade e levou à identificação de 37.644 genes em Oldenlandia diffusa e 20.825 genes em Oldenlandia corymbosa. Novamente, as amostras do mesmo tecido se agruparam, reforçando a confiabilidade dos dados. Ao comparar tecidos, a equipe encontrou milhares de genes que se comportavam de forma diferente entre raízes e partes aéreas, ou entre caules, folhas, flores e frutos. Muitos desses genes estão envolvidos na captação de energia, no metabolismo básico e em enzimas que modificam compostos vegetais — exatamente os tipos de atividades que determinam onde compostos medicinais são produzidos e armazenados.
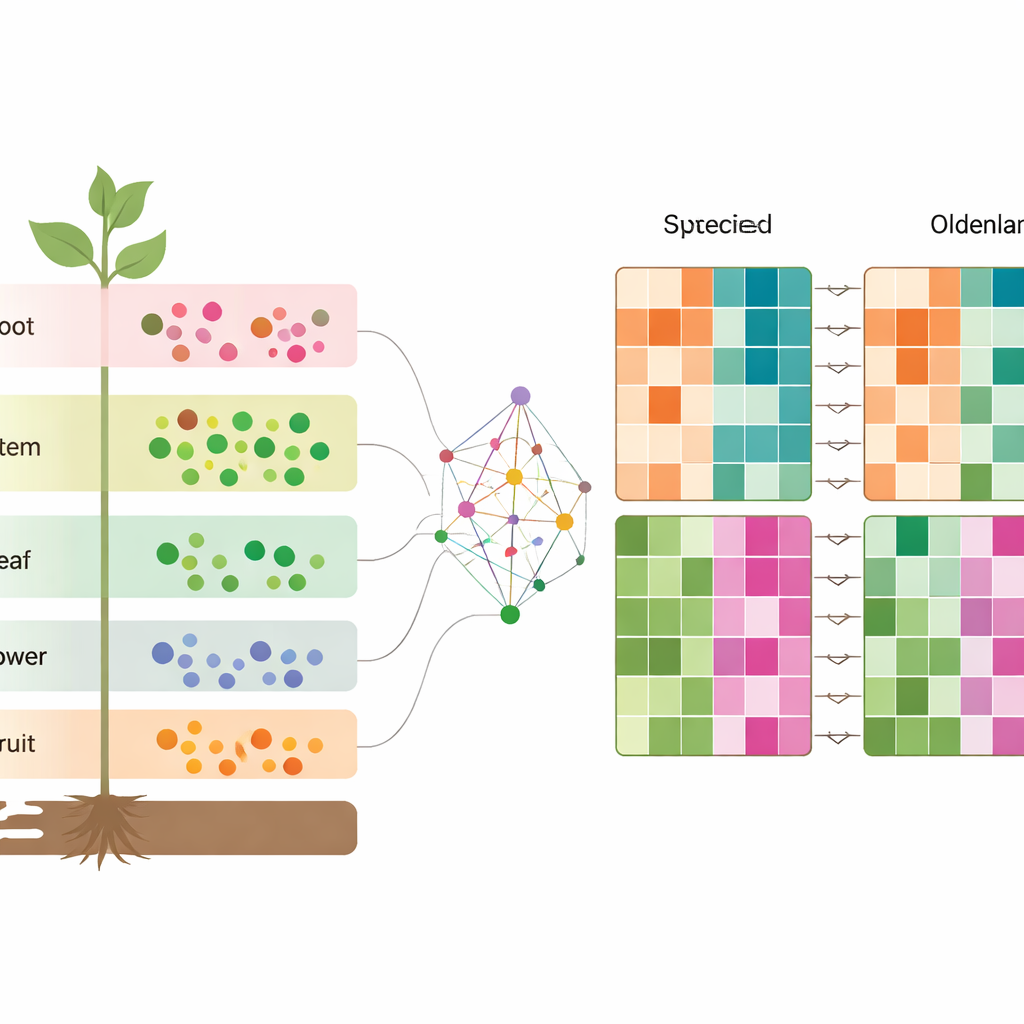
Focalizando as diferenças entre as duas espécies
Para entender o que realmente separa as espécies, os autores parearam genes de O. diffusa e O. corymbosa que são contrapontos diretos e, em seguida, compararam sua atividade em cada tecido. Descobriram milhares de genes mais ou menos expressos em uma espécie em relação à outra em raízes, caules, folhas, flores e frutos. Esses genes pertenciam a vias que sintetizam e processam compostos-chave, incluindo terpenoides, fenóis derivados da fenilpropanoide e diversas moléculas contendo nitrogênio. Quando combinados com os dados metabolômicos, isso revela um quadro em camadas: cada tecido tem sua própria impressão química e genética, e essas impressões mudam de maneiras características entre as duas ervas intimamente relacionadas.
O que isso significa para a medicina e pesquisas futuras
Para não especialistas, a principal conclusão é que essas duas plantas medicinais semelhantes na aparência não são intercambiáveis. Por baixo da aparência parecida, raízes, caules, folhas, flores e frutos diferem tanto nas quantidades de pequenas moléculas importantes quanto na atividade de genes que produzem essas moléculas. Ao disponibilizar esse grande conjunto de dados cuidadosamente validado, o estudo fornece um atlas de referência que outros cientistas podem explorar para identificar quais ingredientes podem ser responsáveis por efeitos específicos na saúde e quais genes poderiam ser alvo para cultivar ou modificar plantas com propriedades mais consistentes e potentes. Em última análise, esse tipo de mapeamento profundo pode ajudar a transformar misturas herbais tradicionais em medicamentos mais bem compreendidos e usados com maior precisão.
Citação: Chen, P., Huang, Z., Wen, Y. et al. Metabolomic and Transcriptomic Profiling of Two Closely Related Species within the Genus Oldenlandia. Sci Data 13, 378 (2026). https://doi.org/10.1038/s41597-026-06745-y
Palavras-chave: Oldenlandia, plantas medicinais, metabolômica, transcriptômica, metabólitos secundários de plantas