Clear Sky Science · pt
Montagem do genoma em nível de cromossomo de Homatula variegata da bacia do rio Yangtze
Um peixinho de riacho com uma grande história genética
Nos riachos de corrente rápida e leitos pedregosos que alimentam o alto curso do rio Yangtze na China vive um pequeno loach listrado chamado Homatula variegata. É apreciado tanto na culinária quanto em aquários domésticos, mas até agora quase nada se sabia sobre seu plano genético. Este estudo entrega o primeiro mapa quase completo do genoma da espécie, cromossomo a cromossomo, abrindo caminho para conservação mais inteligente, reprodução mais eficiente e compreensão mais profunda de como a vida se adapta a águas frias e velozes de montanha.
Por que mapear o DNA de um peixe de aparência modesta?
Embora este loach atinja apenas cerca de 14 centímetros, desempenha um papel desproporcional nos ecossistemas fluviais locais e na aquicultura regional. Ele prospera em riachos de altitude média com fundos de seixos e correntes constantes, alimentando‑se de insetos, detritos orgânicos e peixes pequenos. Por ser saboroso e colorido, há interesse crescente em cultivá‑lo como espécie nativa ornamental e alimentar. Ainda assim, criar e proteger uma espécie é muito mais difícil sem uma referência genética precisa. Um genoma completo funciona como uma lista detalhada de peças e um diagrama de fiação, revelando os genes que moldam crescimento, coloração, resistência a doenças e a capacidade de lidar com água fria e rápida. Até agora, nenhum loach desse ramo da família de peixes possuía uma referência de tão alta qualidade, deixando uma lacuna importante na genética de peixes de água doce.
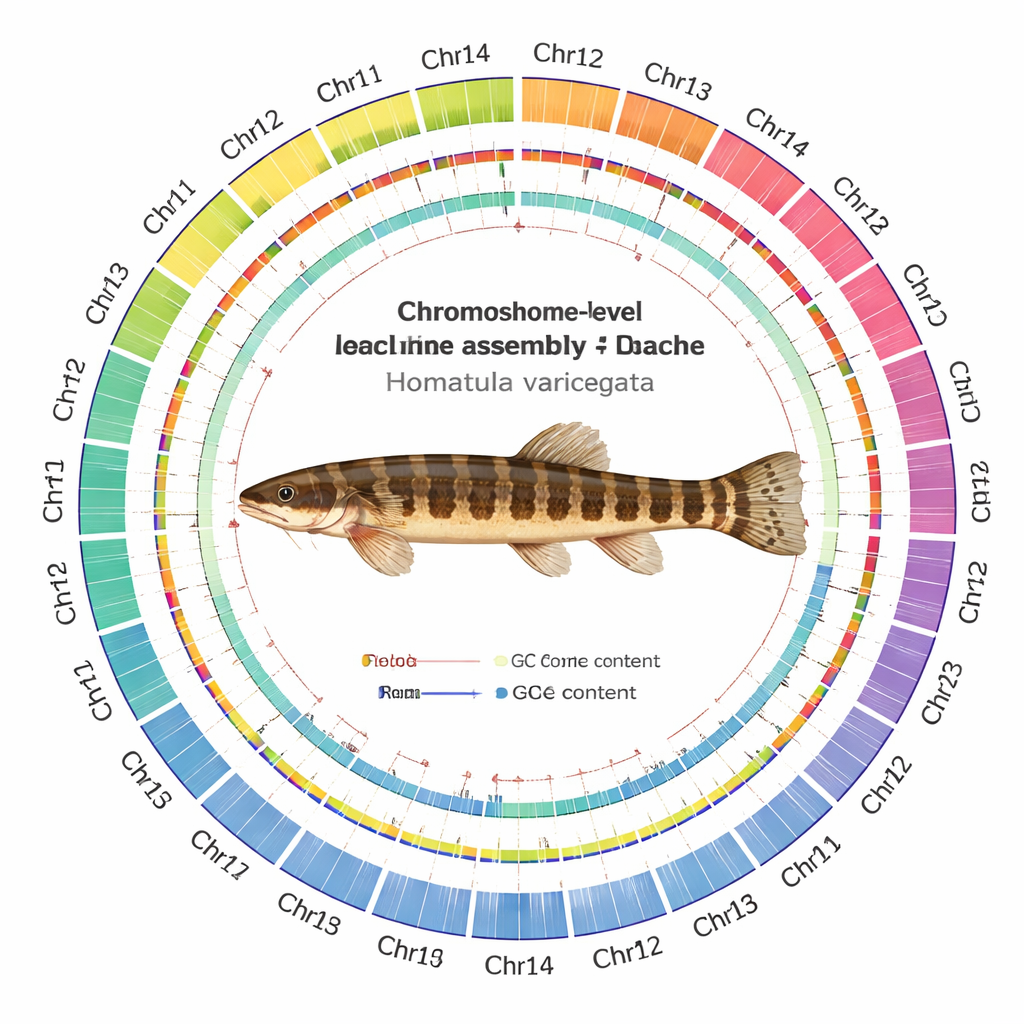
Construindo um mapa de DNA cromossomo a cromossomo
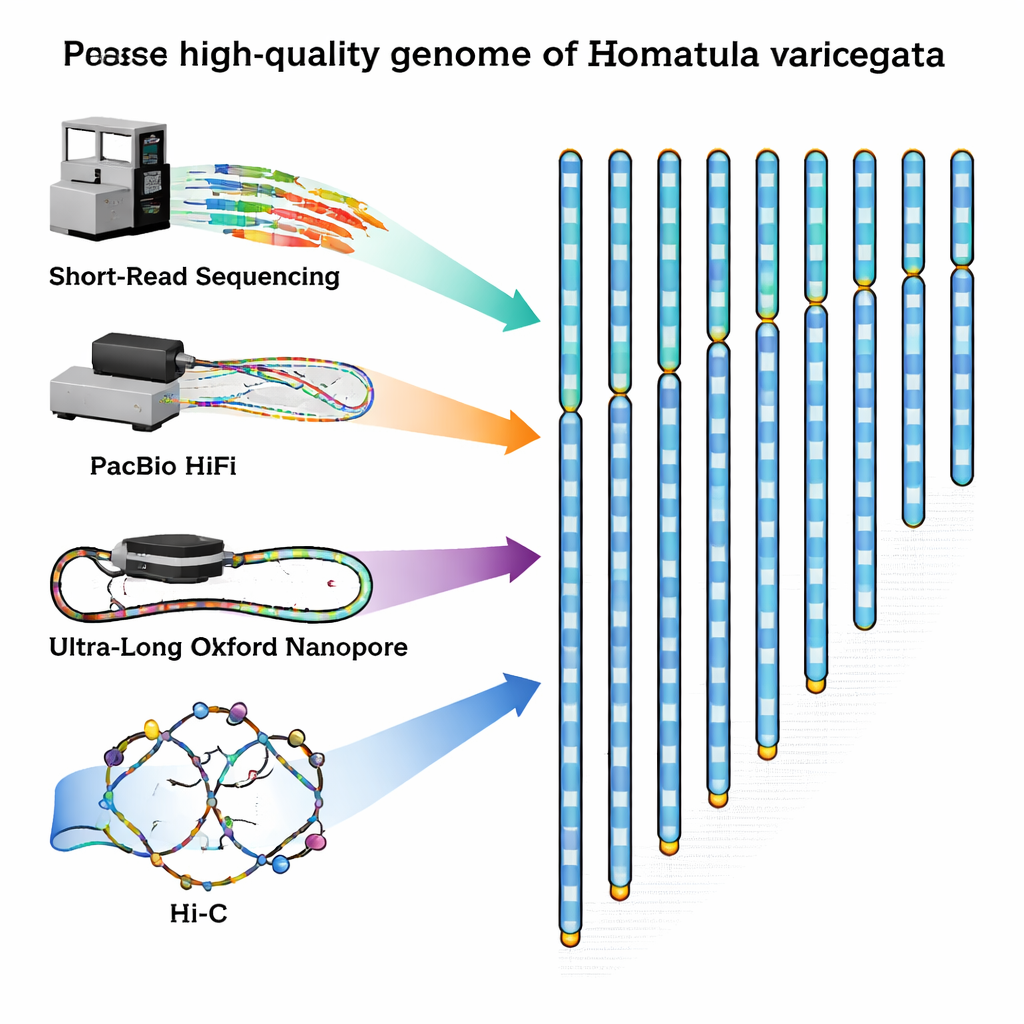
Para preencher essa lacuna, os pesquisadores capturaram um loach macho adulto saudável no rio Qingyi, um afluente do Yangtze, e extraíram cuidadosamente DNA e RNA do seu sangue. Em seguida, combinaram vários métodos de sequenciamento de ponta, cada um com pontos fortes diferentes. Máquinas de leitura curta da Illumina produziram um grande número de fragmentos de DNA altamente precisos. A tecnologia PacBio HiFi forneceu fragmentos um pouco maiores com excelente precisão, enquanto dispositivos Oxford Nanopore geraram fitas ultra‑longas que podem atravessar regiões repetitivas difíceis de decodificar. Finalmente, um método chamado Hi‑C capturou como as fitas de DNA se dobram e interagem dentro do núcleo celular, fornecendo um mapa de contatos 3D que ajuda a ligar fragmentos em cromossomos completos na ordem correta.
O que o novo genoma revela
Ao tecer esses dados com softwares modernos de montagem e verificações de qualidade cuidadosas, a equipe produziu um genoma com 641 milhões de letras de DNA, organizado de forma ordenada em 24 cromossomos. Notavelmente, cada cromossomo foi montado como uma peça contínua, com 22 sem lacunas e apenas pequenas lacunas em outros dois. Eles puderam identificar 24 prováveis centrômeros — o “cinturão” central de cada cromossomo — e detectar a maioria das tampas teloméricas protetoras nas extremidades cromossômicas. Os cientistas catalogaram 24.479 genes codificadores de proteína e foram capazes de atribuir prováveis funções a cerca de 93% deles comparando‑os com grandes bases de dados internacionais. Também mapearam o panorama de DNA repetitivo, encontrando que mais de um quarto do genoma é composto por elementos genéticos móveis, especialmente transposons de DNA, que podem saltar pelo genoma e às vezes impulsionar a evolução.
Testando a qualidade por baixo do capô
Números de alto nível só são significativos se o mapa subjacente for confiável. Portanto, a equipe submeteu a montagem a uma bateria de testes. Leituras de todas as plataformas de sequenciamento alinharam‑se de volta ao novo genoma em taxas muito altas, com cobertura uniforme ao longo da maior parte dos cromossomos. Ferramentas independentes que contam padrões curtos de DNA sugeriram que quase todo o conteúdo de sequência esperado está presente, e testes padrão de completude gênica mostraram que a grande maioria dos genes universais de peixes está intacta. Os mapas de contato Hi‑C formaram padrões limpos e quadrados ao longo de cada cromossomo, com pouco sinal disperso entre eles, indicando que os segmentos estão corretamente unidos em vez de embaralhados.
Do mapa de DNA ao impacto no mundo real
Para um não especialista, este trabalho pode soar como um triunfo técnico por si só, mas suas implicações são práticas e amplas. Ter um genoma quase de ponta a ponta para Homatula variegata dá aos cientistas uma referência contra a qual podem comparar populações selvagens, rastrear diversidade genética e detectar sinais de endogamia ou adaptação local. Criadores podem buscar marcadores de DNA ligados a traços desejáveis, como crescimento rápido, robustez ou coloração marcante, acelerando o melhoramento seletivo enquanto preservam o caráter natural da espécie. Ecologistas podem explorar como esse loach evoluiu para viver em riachos de montanha frios e rápidos, lições que também podem informar o manejo de espécies relacionadas. Em resumo, esse genoma em nível de cromossomo transforma um modesto peixe de rio em um modelo poderoso para entender — e proteger — a rica vida dos ecossistemas de água doce asiáticos.
Citação: Tang, Y., Wu, Q., Wang, Y. et al. A chromosome level genome assembly of Homatula variegata from the Yangtze River basin. Sci Data 13, 303 (2026). https://doi.org/10.1038/s41597-026-06667-9
Palavras-chave: genoma de peixe, montagem de cromossomo, biodiversidade de água doce, genética da aquicultura, loathe do rio Yangtze