Clear Sky Science · pt
Um recurso curado de genomas quimolitotroautotróficos e genes marcadores para previsão de vias de fixação de CO₂
Micróbios que ajudam a equilibrar o orçamento de carbono da Terra
Ocultos em solos, oceanos e ambientes extremos, certos micróbios conseguem construir sua própria biomassa usando dióxido de carbono (CO₂) como a principal fonte de carbono. Esses químicos microscópicos são cruciais para manter o ciclo do carbono da Terra em equilíbrio e podem inspirar novas formas de capturar CO₂ industrial. Ainda assim, até agora, os cientistas não dispunham de um método simples e confiável para olhar o DNA de um micróbio e identificar qual estratégia de fixação de CO₂ ele utiliza. Este estudo apresenta um catálogo de genes curado e uma nova ferramenta computacional, AutoFixMark, desenvolvida para preencher essa lacuna.
Múltiplas rotas para transformar ar em biomassa
Nem todos os organismos que fixam CO₂ o fazem da mesma maneira. Micróbios evoluíram pelo menos sete vias naturais que convertem CO₂ em matéria orgânica. Algumas, como o ciclo de Calvin–Benson–Bassham, comum em plantas e muitas bactérias, são bem conhecidas; outras, como a via glicina redutiva descoberta apenas em 2020, ainda estão pouco mapeadas. Essas vias estão distribuídas por muitos ramos da árvore da vida e frequentemente reutilizam enzimas similares, o que torna surpreendentemente difícil distingui-las apenas pela sequência do genoma. Softwares existentes conseguem prever capacidades metabólicas amplas, mas não foram otimizados nem testados exaustivamente para identificar com precisão as rotas específicas de fixação de CO₂.
Construindo um mapa de referência limpo de micróbios que fixam CO₂
Os pesquisadores começaram reunindo duas coleções de genomas cuidadosamente verificadas. Primeiro, selecionaram 15 micróbios bem estudados cujas vias de fixação de CO₂ foram detalhadas. Esses organismos de referência, abrangendo vários grupos bacterianos e arqueanos, serviram como modelos para definir as enzimas-chave verdadeiramente distintivas de cada via. Em seguida, criaram um conjunto de referência com 347 genomas quimolitotroautotróficos — micróbios que obtêm energia de produtos químicos inorgânicos e constroem biomassa a partir de CO₂. Cada genoma desse conjunto maior foi ligado, manualmente a partir da literatura, a vias específicas de fixação de CO₂, fornecendo um conjunto de verdade robusto para testar previsões.
Genes marcadores e regras simples em vez de caixas-pretas
Usando os 15 genomas de referência, a equipe identificou “genes marcadores” para cada uma das sete vias de fixação de CO₂ e os mapeou para identificadores padronizados de KEGG Orthology (KO). Em vez de depender de aprendizado de máquina opaco, eles codificaram regras transparentes sobre como esses marcadores se combinam. Algumas reações podem ser realizadas por qualquer uma de várias enzimas alternativas, tratadas por uma regra “one_of”. Outras dependem de complexos multissubunidade e devem ter “all_of” um conjunto definido de KOs. Para a via glicina redutiva, onde nem todos os componentes são totalmente compreendidos, a ferramenta usa regras “at_least” que exigem um número mínimo de subunidades presentes. Essas regras lógicas são armazenadas em um arquivo JSON legível por máquina que forma a base de conhecimento central do AutoFixMark.
Uma ferramenta leve que supera softwares estabelecidos
O próprio AutoFixMark é um programa pequeno baseado em regras escrito em Python. Ele recebe como entrada uma lista de IDs de KO dos genes no genoma de um micróbio, tipicamente produzida por uma ferramenta separada chamada KofamScan, e então verifica quais regras de marcadores são satisfeitas para cada uma das sete vias. Os autores compararam o AutoFixMark com duas ferramentas amplamente usadas de anotação metabólica, METABOLIC e gapseq, usando seu conjunto de referência de 347 genomas. As três ferramentas tiveram bom desempenho em vias clássicas como o ciclo de Calvin, o ciclo tricarboxílico redutivo e a via Wood–Ljungdahl. Porém, o AutoFixMark claramente superou as demais em vias mais novas ou menos comuns, como o ciclo 3-hidroxi-propionato/4-hidroxi-butirato, o ciclo dicarboxilato/4-hidroxi-butirato e a via glicina redutiva, algumas das quais nem sequer são cobertas pelos softwares concorrentes.
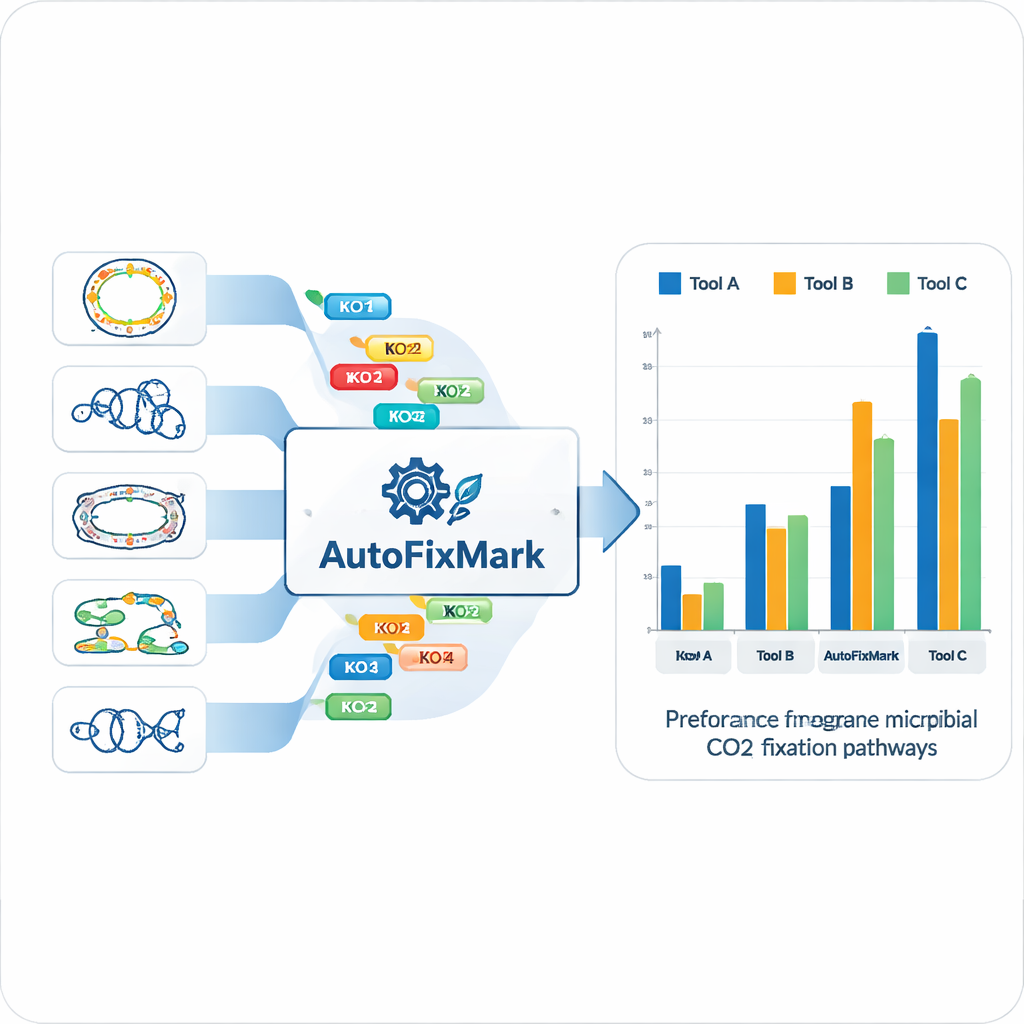
O que esses resultados significam para estudos climáticos e ecológicos
Os conjuntos de genes curados, o programa AutoFixMark e a coleção completa de genomas de referência estão publicamente disponíveis. Isso significa que pesquisadores podem agora rastrear tanto micróbios isolados quanto genomas montados a partir de metagenomas para ver quais estratégias de fixação de CO₂ eles estão geneticamente aptos a usar. É importante ressaltar que os autores enfatizam que o AutoFixMark prevê potencial genético, e não se uma via está ativa em condições reais. Muitas dessas rotas bioquímicas podem operar em sentido reverso, dependendo do balanço energético da célula. Ainda assim, dispor de um método robusto e transparente para sinalizar micróbios que fixam CO₂ ajudará cientistas a mapear onde e como a vida retira carbono da atmosfera, orientar experimentos sobre vias emergentes e apoiar o desenho de futuras biotecnologias baseadas em CO₂.
Citação: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Palavras-chave: fixação microbiana de carbono, metabolismo autotrófico, Anotação de genoma, captura de CO2, metagenômica