Clear Sky Science · pt
Um conjunto de dados anotado de Gram em hemoculturas positivas
Por que respostas rápidas sobre infecções importam
Quando bactérias ou fungos entram na corrente sanguínea, cada hora sem o tratamento correto pode fazer a diferença entre a vida e a morte. Os médicos dependem de um exame laboratorial rápido chamado coloração de Gram para identificar o tipo de microrganismo presente e escolher antibióticos precoces. Mas interpretar essas lâminas coradas ao microscópio é uma tarefa manual especializada que leva tempo e pode variar entre tecnólogos. Este estudo descreve uma nova coleção de imagens de lâminas de hemocultura reais, cuidadosamente anotada, construída para ajudar computadores a aprender a ler Gram automaticamente e apoiar um atendimento mais rápido e confiável.
Convertendo lâminas hospitalares reais em dados
Os pesquisadores reuniram 57 tipos diferentes de bactérias e fungos cultivados a partir de frascos de hemocultura positivos de pacientes, como parte do fluxo de trabalho hospitalar cotidiano. De janeiro a maio de 2024, assim que uma hemocultura indicava positividade, a equipe preparou esfregaços corados pela técnica de Gram em lâminas de vidro e confirmou a espécie exata usando um método de identificação de alta precisão chamado espectrometria de massa MALDI-TOF. Sem alterar as rotinas normais ou coletar amostras adicionais, a equipe então capturou imagens digitais de alta resolução de campos típicos sob microscópio de imersão em óleo 100×, resultando em 505 imagens coloridas de grande tamanho que espelham o que os tecnólogos veem na prática real.
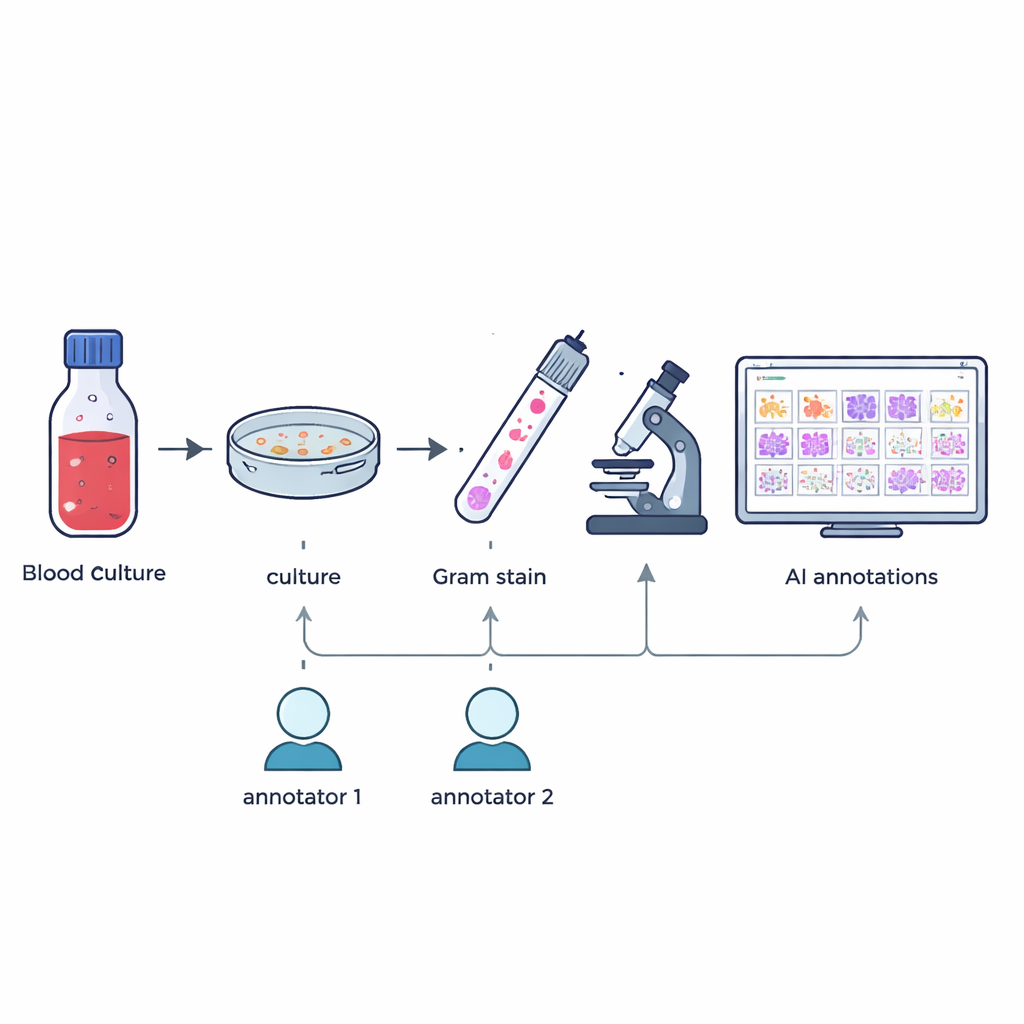
Rotulagem cuidadosa de formas minúsculas
Construir um conjunto de ensino útil para inteligência artificial exige saber exatamente onde cada microrganismo aparece em cada imagem. Dois tecnólogos em microbiologia experientes desenharam independentemente caixas ao redor de células microbianas individuais ou aglomerados em cada imagem, guiados apenas pelo que viam ao microscópio. Uma ferramenta de software customizada comparou os dois conjuntos de marcações: caixas que se sobrepunham suficientemente foram mescladas, e quaisquer discrepâncias ou desentendimentos foram sinalizados. Um especialista sênior com mais de 20 anos de experiência revisou manualmente esses casos. Esse processo em várias etapas produziu 7.528 anotações verificadas que destacam cocos (células arredondadas), bacilos (células em forma de bastonete) e fungos, ao mesmo tempo em que excluem objetos parciais ou duvidosos.
O que o conjunto de dados contém
O recurso final combina várias camadas de informação. Todas as 505 imagens são fornecidas como arquivos JPEG de alta resolução, e as caixas finais verificadas por especialistas estão armazenadas no formato padrão COCO JSON, amplamente usado em pesquisa de visão computacional. Arquivos extras vinculam cada imagem à sua espécie microbiana, se é Gram-positiva ou Gram-negativa, seu grupo de forma amplo, o tipo de frasco de hemocultura de onde veio e quanto tempo a cultura levou para ficar positiva. Como cada imagem contém apenas uma espécie, todas as caixas dentro de uma mesma imagem compartilham os mesmos traços biológicos. Os usuários podem optar por um único arquivo grande de anotações ou arquivos separados por imagem, e um script Python simples está incluído para visualizar qualquer imagem com suas caixas sobrepostas.
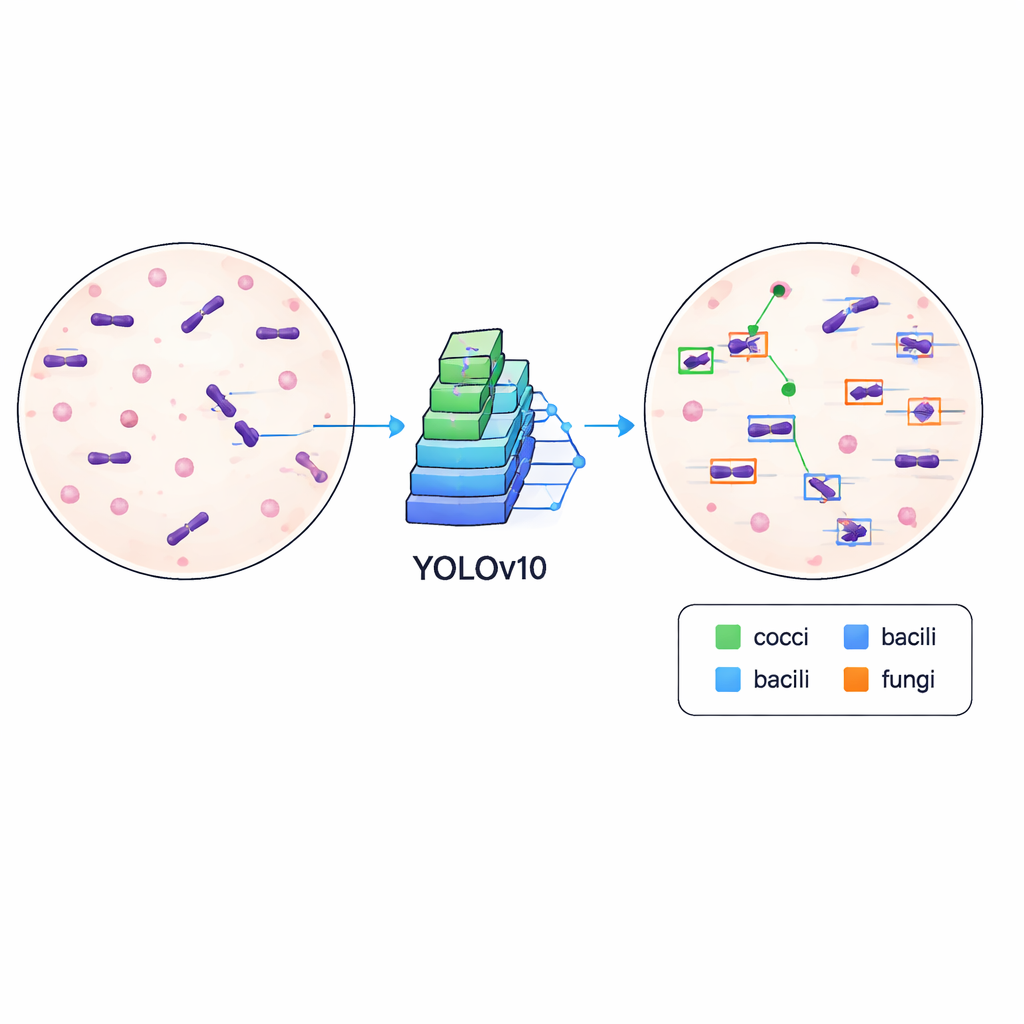
Ensinando computadores a detectar microrganismos
Para demonstrar que o conjunto de dados é não apenas organizado, mas também prático, os autores treinaram um algoritmo moderno de detecção de objetos conhecido como YOLOv10 para localizar e classificar microrganismos nas imagens. Eles dividiram os dados em conjuntos de treinamento e validação e executaram o modelo por 500 ciclos de treinamento em uma placa gráfica de alto desempenho, acompanhando quão bem ele aprendeu a desenhar caixas precisas e distinguir entre diferentes tipos celulares. O sistema treinado alcançou uma precisão média (mAP) de aproximadamente 84,6% em um limiar padrão de correspondência, indicando que ele pode localizar e rotular microrganismos de forma confiável em variadas aparências de lâminas, incluindo diferenças na intensidade da coloração, detritos de fundo e foco.
Como esse recurso pode ser usado
Como os dados seguem formatos comuns, eles podem ser integrados a muitos pipelines de visão computacional existentes. Pesquisadores podem primeiro treinar um sistema simplesmente para separar microrganismos verdadeiros de detritos, ajudando laboratórios a filtrar sinais falso-positivos de culturas. Também é possível agrupar microrganismos em formas amplas, correspondendo ao que os clínicos precisam para um relatório inicial chamado “Nível 1” que orienta as escolhas antibióticas preliminares. Um objetivo mais ambicioso é distinguir espécies individuais por pistas visuais sutis. Os autores observam limitações: algumas células estão agrupadas, algumas lâminas provêm de uma única fonte por espécie e o foco pode variar — exatamente como na vida real. Ainda assim, cada caixa incluída foi cuidadosamente verificada, tornando o conjunto de dados um ponto de partida confiável.
O que isso significa para os pacientes
Em termos simples, este trabalho transforma lâminas de hemocultura de rotina em um campo de treinamento compartilhado para softwares inteligentes. Ao tornar tanto as imagens quanto as marcações de especialistas publicamente disponíveis, o estudo reduz a barreira para equipes ao redor do mundo construírem e testarem ferramentas de IA que possam ler colorações de Gram de forma rápida e consistente. Embora esses sistemas não substituam microbiologistas humanos, eles podem ajudar a sinalizar infecções perigosas mais cedo, reduzir erros de interpretação e apoiar um uso melhor de antibióticos. Para os pacientes, isso pode se traduzir em tratamento mais rápido e mais preciso quando mais importa.
Citação: Yi, Q., Gou, X., Zhu, R. et al. An annotated dataset of Gram stains from positive blood cultures. Sci Data 13, 294 (2026). https://doi.org/10.1038/s41597-026-06651-3
Palavras-chave: infecções da corrente sanguínea, coloração de Gram, conjunto de dados de imagens médicas, inteligência artificial, diagnóstico em microbiologia