Clear Sky Science · pt
Primeira Montagem e Anotação de Genoma em Nível de Cromossomo de uma Arraia Doce-de-Água Ameaçada (Fontitrygon garouaensis) da África
Um Morador Raro do Rio Recebe o Holofote Genômico
Nos rios turvos da África Ocidental vive uma arraia incomum que fez o que quase todos os seus parentes tubarões e arraias não fizeram: mudou-se permanentemente para água doce. Esta arraia lisa de água doce, Fontitrygon garouaensis, também é ameaçada e pouco estudada. O artigo por trás desta matéria entrega o primeiro mapa completo do seu DNA em nível de cromossomo, oferecendo uma ferramenta poderosa para entender como uma linhagem marinha tão antiga se adaptou à vida em rios e como podemos protegê-la melhor.
Por Que Esta Arraia é Importante
Tubarões e arraias pertencem a um dos ramos mais antigos da árvore evolutiva dos vertebrados, separados dos ancestrais dos peixes ósseos há centenas de milhões de anos. Ainda assim, apesar de sua importância evolutiva, seus genomas permanecem pouco mapeados, especialmente para espécies que vivem em águas africanas. Fontitrygon garouaensis é particularmente especial: é a única arraia conhecida adaptada de forma completa aos sistemas de água doce africanos, e apresenta características corporais distintivas, como uma fileira de espinhos dorsal reduzida ou ausente. Como migrar de mares salgados para rios de água doce é raro e fisiologicamente desafiador para tubarões e arraias, esta espécie oferece um experimento natural sobre como animais reconfiguram sua biologia para enfrentar novos ambientes.
Construindo um Mapa Genético de Referência
Para desvendar o plano genético da arraia, os pesquisadores coletaram uma fêmea adulta do rio Níger, na Nigéria, e extrairam DNA e RNA de alta qualidade de vários tecidos. Em seguida, usaram uma estratégia “híbrida” que combina três abordagens avançadas de sequenciamento. O sequenciamento de curto alcance Illumina fornece um enorme número de pequenos fragmentos de DNA, o sequenciamento de longo alcance PacBio HiFi gera trechos muito mais longos e contínuos, e o sequenciamento Hi-C captura como o DNA se dobra e interage dentro do núcleo celular. Ao tecer esses conjuntos de dados com softwares especializados, a equipe montou um genoma de cerca de 4,19 bilhões de letras de DNA, organizado em 41 fragmentos em escala de cromossomos—comparável em tamanho a alguns dos maiores genomas de tubarões conhecidos.
O Que o Genoma Revela
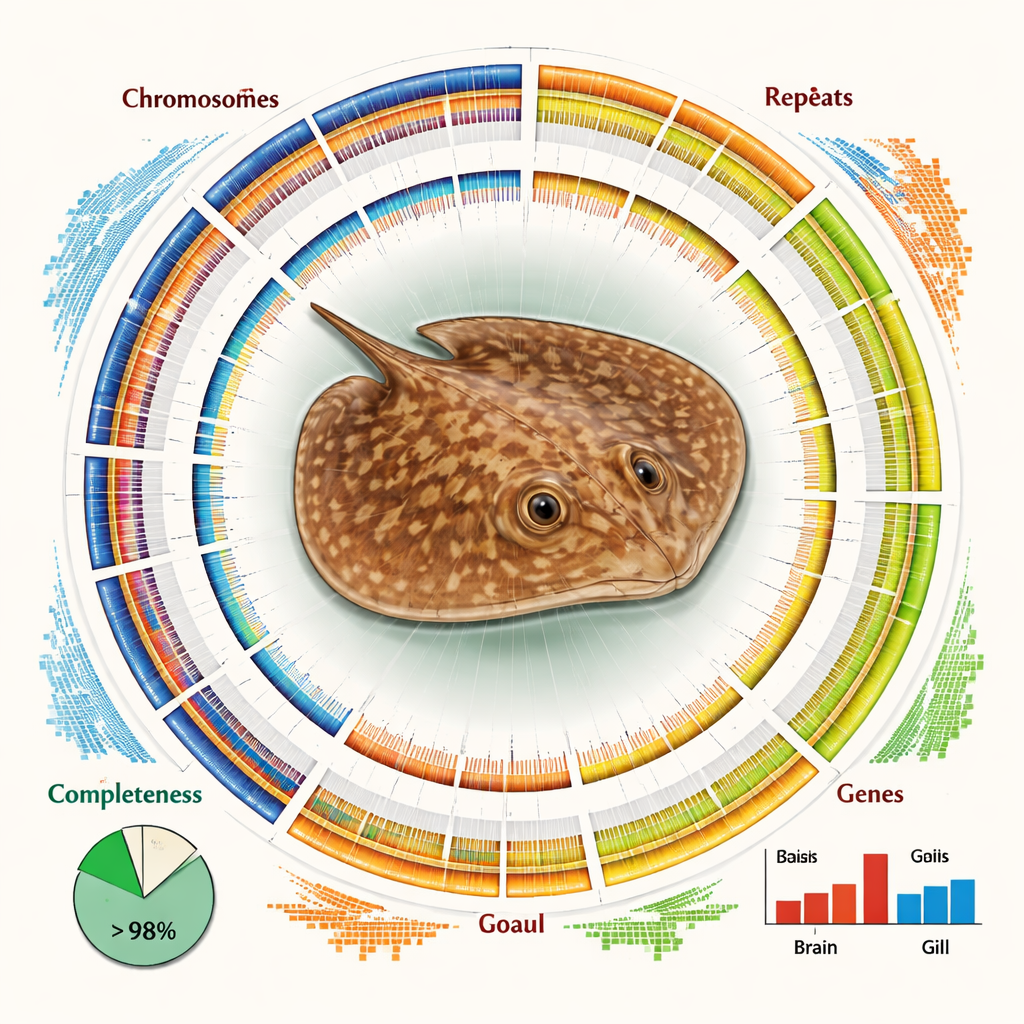
A montagem final é ao mesmo tempo grande e notavelmente completa. Verificações de qualidade independentes mostram que mais de 93% dos genes vertebrados centrais esperados estão presentes e intactos, e mais de 84% da sequência total de DNA está atribuída com confiança a cromossomos específicos. O genoma é dominado por DNA repetitivo—trechos de sequência que ocorrem muitas vezes—representando cerca de dois terços de seu comprimento. Muitos desses repetidos pertencem a elementos genéticos móveis, como LINEs e LTRs, que se copiaram e se inseriram ao longo do genoma ao longo do tempo evolutivo. Apesar dessa complexidade, os pesquisadores identificaram quase 30.000 genes codificadores de proteínas e puderam atribuir funções prováveis a mais de 98% deles usando bases de dados internacionais de proteínas e vias metabólicas.
Pistas sobre a Vida em Água Doce e a Evolução
Ter um mapa em nível de cromossomo permitiu à equipe fazer mais do que apenas listar genes. Ao comparar os cromossomos da arraia com os de tubarões e arraias relacionados, eles descobriram uma história de remanejamento estrutural—quebras, fusões e rearranjos de segmentos cromossômicos inteiros—que distingue essa linhagem. Essas mudanças podem ter ajudado a moldar as características únicas e o nicho ecológico da espécie. Os autores também examinaram a atividade gênica em dois tecidos-chave: as brânquias, que mediam a respiração e o equilíbrio salino com a água circundante, e o cérebro. Encontraram diferenças claras em quais genes estão ativados, com genes das brânquias enriquecidos em vias envolvidas no uso de energia e no metabolismo de gorduras, sugerindo ajustes bioquímicos necessários para sobreviver em água doce.
Uma Nova Base para a Conservação
No seu cerne, este trabalho transforma uma arraia de rio obscura e ameaçada em um dos peixes cartilaginosos mais bem caracterizados em nível de DNA. Para não especialistas, isso significa que os cientistas agora dispõem de um manual de referência detalhado da espécie, desde seus cromossomos até genes individuais. Essa referência pode orientar estudos futuros sobre como ela lida com a mudança na qualidade da água, como suas populações estão estruturadas ao longo dos rios e como se relaciona com outras arraias. Igualmente importante, fornece uma base genômica para o planejamento da conservação, oferecendo novas maneiras de monitorar a diversidade genética, identificar populações distintas que valham a pena proteger e entender como este raro especialista em água doce pode responder às pressões ambientais em curso.
Citação: Nneji, L.M., Oladipo, S.O., Oyebanji, O.O. et al. First Chromosome-level Genome Assembly and Annotation of an Endangered Freshwater Stingray (Fontitrygon garouaensis) from Africa. Sci Data 13, 302 (2026). https://doi.org/10.1038/s41597-026-06646-0
Palavras-chave: arraia de água doce, montagem do genoma, evolução dos elasmobrânquios, genômica da conservação, biodiversidade dos rios africanos