Clear Sky Science · pt
Dados temporalmente multiômicos de expressão gênica ao longo da diferenciação de células polihormonais derivadas de células-tronco embrionárias humanas
Como as Células Aprendem a se Tornar Órgãos
Nossos corpos começam como pequenos aglomerados de células idênticas que, de alguma forma, aprendem a se tornar tecidos muito diferentes, do cérebro ao pâncreas. Este estudo acompanha esse processo de aprendizagem no laboratório, usando células-tronco embrionárias humanas enquanto são conduzidas para se tornarem células pancreáticas precoces. Ao acompanhar a atividade de milhares de genes ao longo do tempo em múltiplos níveis, o trabalho cria um mapa de referência rico que pode ajudar cientistas a entender melhor o desenvolvimento humano e, a longo prazo, aprimorar estratégias para tratar doenças como o diabetes.
Observando as Células Escolherem um Caminho
Células-tronco embrionárias humanas são especiais porque podem se transformar em quase qualquer tipo celular do corpo. Neste estudo, os pesquisadores direcionaram essas células para um destino específico: uma linhagem pancreática chamada células polihormonais, que podem produzir hormônios-chave como insulina e glucagon. Eles imitaram o desenvolvimento inicial em uma placa, alterando o meio de cultura passo a passo, movendo as células primeiro para um estado primitivo semelhante ao intestino chamado endoderme, e em seguida para células pancreáticas produtoras de hormônios ao longo de 17 dias. Amostras foram coletadas em dez pontos de tempo cuidadosamente escolhidos para capturar toda a jornada da célula flexível até a célula especializada produtora de hormônio. 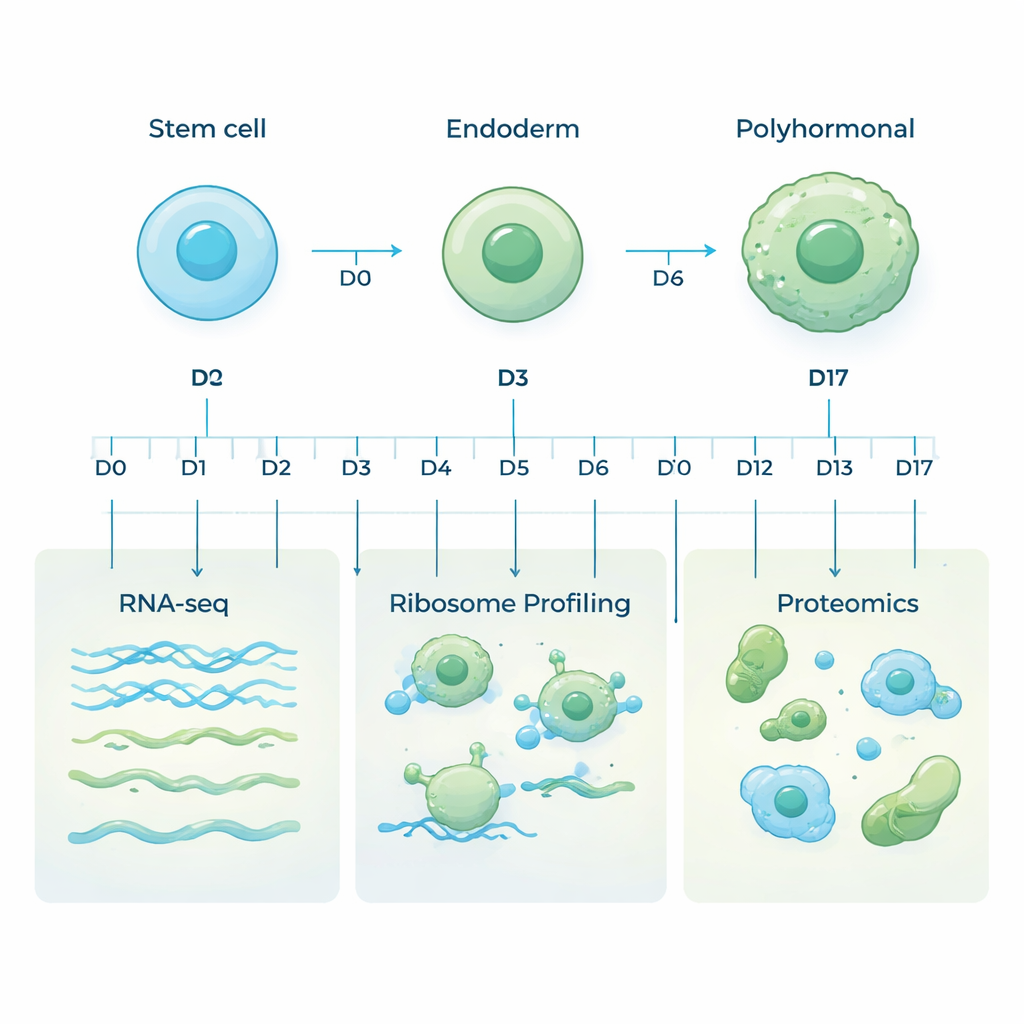
Olhando por Dentro em Três Níveis
A maioria dos estudos analisa apenas o RNA mensageiro (mRNA), as moléculas que carregam as instruções gênicas. Mas o mRNA é apenas parte da história: nem toda mensagem é traduzida em proteína, e as próprias proteínas podem ser produzidas ou degradadas em ritmos diferentes. Para obter uma visão mais completa, a equipe usou três abordagens complementares nas mesmas amostras. O sequenciamento de RNA mediu quais genes estavam sendo transcritos para mRNA. O perfilamento de ribossomos rastreou quais mensagens estavam sendo ativamente lidas pelas máquinas celulares de fabricação de proteínas. A proteômica baseada em espectrometria de massa mediu então as proteínas realmente presentes. Juntas, essas camadas revelam como a atividade gênica é controlada à medida que as células mudam de identidade.
Acompanhando Sinais-Chave da Identidade Celular
Para verificar se as células realmente seguiram a rota de desenvolvimento pretendida, os cientistas monitoraram genes marcadores bem conhecidos. No início, marcadores clássicos de células-tronco como OCT4 e NANOG estavam altos e então diminuíram à medida que a diferenciação progrediu. Quando as células entraram no estágio de endoderme, marcadores como KIT e SOX17 aumentaram. Nas fases finais, marcadores polihormonais — insulina (INS) e glucagon (GCG) — surgiram fortemente tanto ao nível do RNA quanto ao nível proteico, confirmando que as células haviam adotado uma identidade pancreática produtora de hormônios. Embora um dos replicados biológicos tenha progredido por essas fases um pouco mais lentamente do que o outro, ambos seguiram o mesmo caminho geral, refletindo pequenas diferenças naturais e não problemas técnicos. 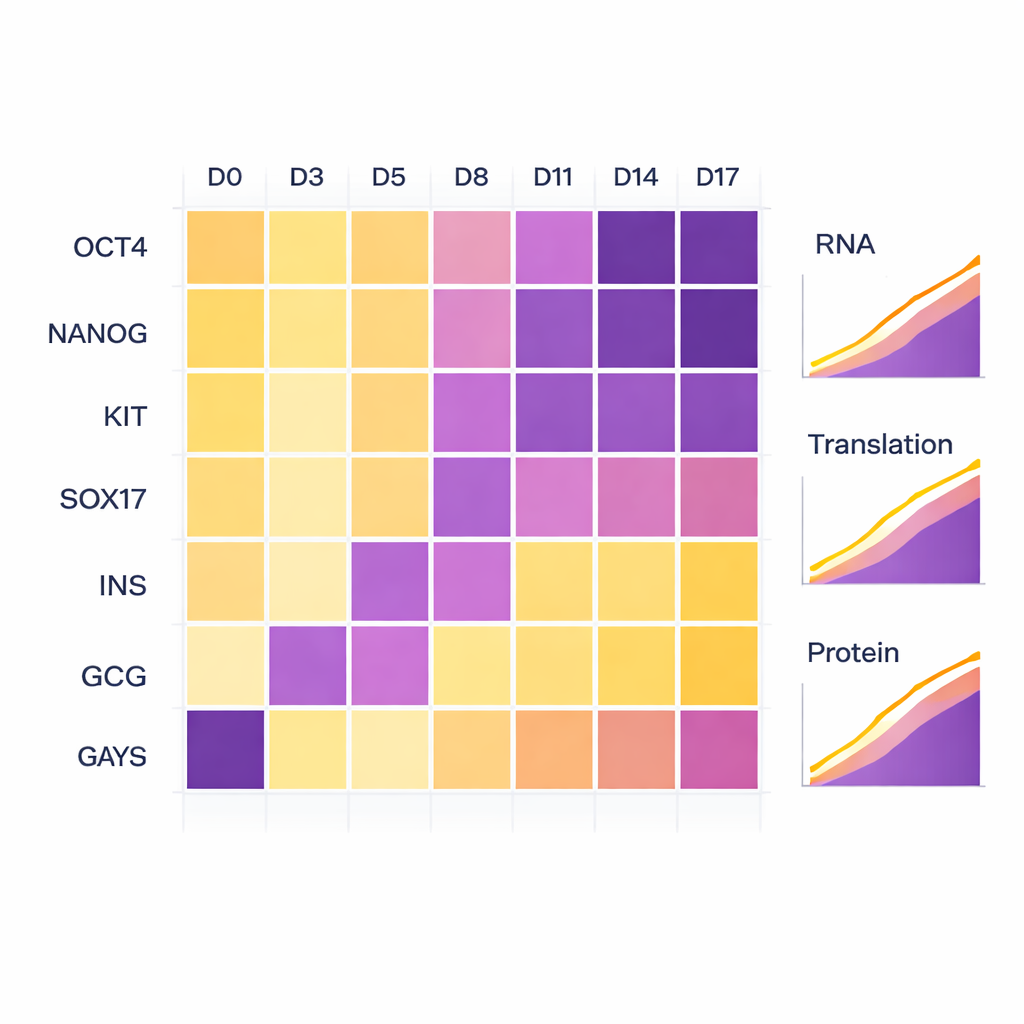
Verificações de Qualidade para um Recurso Confiável
Como este trabalho se destina a servir como um recurso para a comunidade, os autores dedicaram esforço extensivo à checagem da qualidade e consistência dos dados. Para cada um dos três métodos, eles avaliaram a precisão do sequenciamento e das medições, a cobertura dos genes e o grau de concordância entre experimentos repetidos. Os estágios de células-tronco e polihormonais mostraram diferenças claras e reproduzíveis nos níveis de RNA, tradução e proteína. Análises de componentes principais — mapas estatísticos que agrupam amostras semelhantes — mostraram que os pontos de tempo se alinharam em ordem, com estágios iniciais e tardios claramente separados e replicados biológicos formando aglomerados firmes. Os dados de proteômica sozinhos acompanharam de forma confiável quase 7.500 proteínas ao longo de todos os pontos de tempo, com relativamente poucas medições ausentes, ressaltando a profundidade do conjunto de dados.
Uma Base para Descobertas Futuras
Os autores disponibilizam todos os dados brutos e processados publicamente, junto com scripts de análise e arquivos de referência, para que outros pesquisadores possam reutilizar e reanalisar o conjunto de dados. Além de descrever como um tipo celular se transforma em outro, este trabalho oferece uma imagem detalhada e resolvida no tempo de como as mensagens gênicas, sua tradução e as proteínas resultantes interagem durante uma grande transição do desenvolvimento. Para não especialistas, a conclusão principal é que o destino celular é controlado por várias camadas de regulação que atuam em conjunto ao longo do tempo, e que esse conjunto de dados fornece um “filme” de alta resolução dessas mudanças. Cientistas agora podem usar este recurso para investigar por que alguns genes mudam cedo e outros tarde, como diferentes órgãos podem seguir regras semelhantes ou distintas, e como guiar melhor células-tronco rumo a destinos de interesse médico.
Citação: Keskin, A., Shayya, H.J., Patel, A. et al. Temporal multiomics gene expression data across human embryonic stem cell-derived polyhormonal cell differentiation. Sci Data 13, 278 (2026). https://doi.org/10.1038/s41597-026-06606-8
Palavras-chave: células-tronco, desenvolvimento do pâncreas, expressão gênica, multiômica, células polihormonais