Clear Sky Science · pt
Montagem do genoma sem lacunas de telômero a telômero de Opsariichthys evolans (Cypriniformes: Cyprinidae)
Um peixe de riacho com uma história genômica
Riachos de montanha que correm rapidamente no sudeste da China e em Taiwan abrigam um pequeno e colorido peixe chamado Opsariichthys evolans. Embora pouco conhecido fora da região, essa espécie é uma peça-chave ecológica e uma obra de arte natural, com listras brilhantes e cores reprodutivas marcantes. Por mais de um século, cientistas debateram como classificá-la e em que lugar ela se encaixa na árvore genealógica dos peixes de água doce. Este estudo entrega uma peça central desse quebra-cabeça: o primeiro genoma completo e sem lacunas de O. evolans, lido de uma extremidade cromossômica à outra.
Por que este peixe importa
O. evolans vive em córregos límpidos e com correnteza, onde ajuda a manter o equilíbrio das teias alimentares e funciona como um indicador sensível da qualidade da água. Os machos desenvolvem listras laterais vivas e tubérculos granulares na cabeça e ao redor dos olhos durante a estação reprodutiva, além de um focinho escuro, quase arroxeado. Essas características chamativas, combinadas com a preferência da espécie por águas rápidas, tornam-na ideal para estudar como os animais se adaptam ao ambiente. Ao mesmo tempo, mudanças provocadas por humanos — poluição, fragmentação de habitat e espécies invasoras — estão reduzindo suas populações, tornando importante compreender sua biologia para fins de conservação.
Uma confusão nominal de longa data
Por décadas, biólogos debateram se O. evolans pertencia ao gênero Opsariichthys ou a Zacco. Taxonomistas antigos descreveram a espécie como Zacco evolans, baseando sua decisão principalmente em características externas como formato das nadadeiras e listras do corpo. Estudos posteriores, mais detalhados, mostraram que o padrão de listras e os tubérculos reprodutivos diferem daqueles do visualmente semelhante Zacco platypus. Estudos com DNA mitocondrial sugeriram que O. evolans se encaixa melhor em Opsariichthys, mas alguns dados de genes nucleares indicaram uma afinidade maior com Zacco. Sem um genoma completo, o quadro evolutivo permanecia turvo e o debate sobre seu lugar correto na árvore dos peixes continuou.

Lendo cada letra do genoma
Para responder a essas questões, os pesquisadores coletaram um exemplar macho selvagem em um rio da província de Anhui, China, e preservaram cuidadosamente nove tecidos diferentes. Em seguida, combinaram várias tecnologias de sequenciamento de DNA de ponta, cada uma com suas vantagens, para ler o código genético do animal. Fragmentos curtos e altamente precisos ajudaram a polir a sequência, enquanto leituras longas e ultra-longas das plataformas PacBio e Oxford Nanopore atravessaram regiões difíceis e costuraram os cromossomos de ponta a ponta. A tecnologia Hi-C, que captura como o DNA se dobra dentro da célula, foi usada para organizar os fragmentos em cromossomos de comprimento total. O resultado final é um genoma telômero a telômero, sem lacunas, de cerca de 0,89 bilhões de pares de bases, organizado em 39 cromossomos com uma peça contínua de DNA para cada um.
O que o genoma revela
O genoma final passou por rígidos controles de qualidade, capturando mais de 99% dos genes conservados esperados e alinhando-se de perto com sequências conhecidas de peixes relacionados. Quase metade do genoma consiste em sequências repetidas, muitas delas “genes saltadores” que podem se mover e remodelar o genoma ao longo do tempo evolutivo. A equipe identificou quase 30.000 genes codificadores de proteínas e milhares de RNAs não codificantes, a maioria deles vinculável a funções conhecidas usando grandes bancos de dados biológicos. Comparando este novo genoma com os de dois parentes próximos — Opsariichthys bidens e Zacco platypus — os cientistas constataram que a estrutura cromossômica geral é altamente similar, confirmando laços evolutivos estreitos. Dentro desse quadro, eles localizaram genes e vias candidatas provavelmente envolvidos na coloração das listras corporais e nas adaptações à vida em correntes rápidas, oferecendo pistas sobre como sua aparência distinta e modo de vida evoluíram.
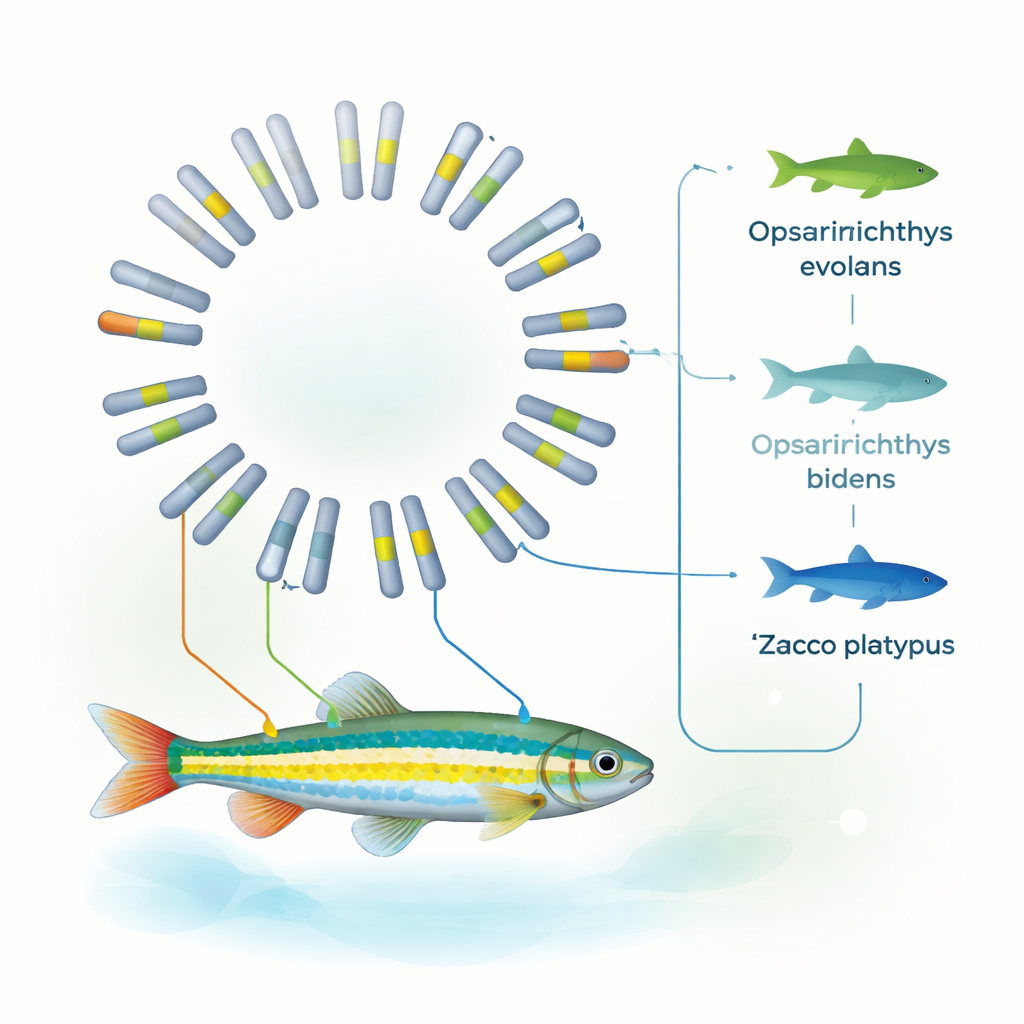
Clarificando seu lugar na árvore genealógica dos peixes
Usando famílias de genes compartilhadas entre dez espécies de peixes diferentes, a equipe reconstruiu uma árvore evolutiva detalhada. A análise indica que O. evolans divergiu de Z. platypus há aproximadamente 8 a 19 milhões de anos e que sua estrutura genômica é especialmente próxima à de O. bidens. Junto com evidências mitocondriais anteriores, esses padrões apoiam inserir O. evolans firmemente no gênero Opsariichthys, e não em Zacco. Em outras palavras, o genoma completo agora corrobora o que observações cuidadosas das listras, da cor do focinho e das estruturas reprodutivas já sugeriam: a aparência pode enganar, mas quando morfologia e um genoma completo concordam, as fronteiras taxonômicas ficam muito mais claras.
Por que um genoma completo muda o jogo
Para não especialistas, a conquista aqui é como passar de um mapa borrado e rasgado para um atlas nítido em alta resolução de uma espécie. Com um genoma completo e sem lacunas, os cientistas agora podem traçar a origem das cores marcantes de O. evolans, sua forma hidrodinâmica para viver em águas rápidas e suas relações com outros piabanhos do Leste Asiático com precisão sem precedentes. Esse recurso ajudará a refinar a classificação de peixes, orientar esforços de conservação para ecossistemas de riachos vulneráveis e aprofundar nossa compreensão de como pequenas diferenças no DNA podem gerar a rica diversidade observada em peixes de água doce.
Citação: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Palavras-chave: montagem do genoma, peixe de água doce, telômero a telômero, evolução de peixes, genômica comparativa