Clear Sky Science · pt
Metabarcoding e dados metagenômicos ao longo de gradientes ambientais aquáticos nas costas da França e do Chile
Vida oculta em mares em mudança
Ao longo das costas do mundo, de lagunas tranquilas a fiordes dramáticos, a vida microscópica está constantemente se adaptando a condições em transformação. Esses minúsculos organismos impulsionam os ciclos de carbono e nutrientes que sustentam a pesca, a qualidade da água e até o clima. Ainda assim, muitas águas costeiras, especialmente ambientes complexos como lagunas e fiordes, foram pouco exploradas em nível genético. Este estudo buscou mudar isso ao criar um conjunto de dados aberto e rico sobre micróbios costeiros da França e do Chile, oferecendo uma nova janela sobre como a vida marinha responde a um ambiente em constante alteração.
Costas como laboratórios naturais
As águas costeiras raramente são estáveis. Tempestades, afluxo de rios, evaporação e marés podem variar temperatura e salinidade em curtas distâncias e períodos. Nutrientes que alimentam algas microscópicas podem aumentar ou diminuir abruptamente, e atividades humanas introduzem ainda mais perturbações. Essa variação cria um mosaico de habitats que selecionam por diferentes comunidades microbianas e estimulam novas adaptações. Para capturar essa complexidade, os pesquisadores amostraram 26 locais ao longo das costas francesa e chilena, incluindo lagunas, estuários, fiordes, portos, praias, águas costeiras e um sítio em alto mar. Alguns locais na França foram visitados mensalmente durante um ano para acompanhar as estações, enquanto os locais chilenos foram amostrados no outono austral, fornecendo um amplo instantâneo de mundos costeiros contrastantes. 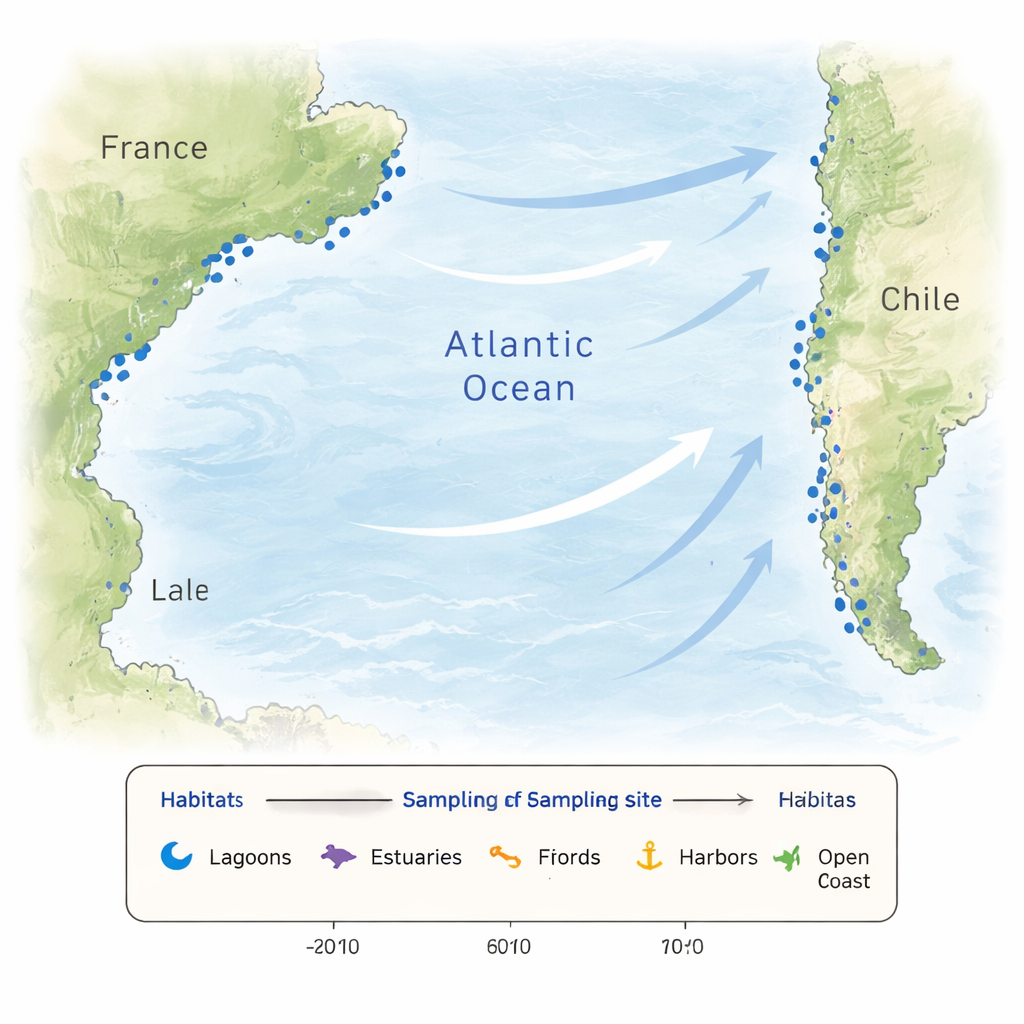
De baldes de água a impressões digitais de DNA
Em cada local, a equipe coletou grandes volumes de água do mar, principalmente da superfície iluminada pelo sol, mas também de camadas mais profundas em fiordes selecionados e em águas de alto mar. Mediram condições ambientais básicas como temperatura, salinidade e nutrientes, além de indicadores de atividade biológica como clorofila (um indicador de algas), matéria orgânica dissolvida, produção bacteriana e respiração. No laboratório, os micróbios foram concentrados em filtros finos e seu DNA foi extraído. Um conjunto de testes concentrou-se em um gene marcador padrão (16S rRNA), que funciona como um código de barras para identificar bactérias e arqueias. Essa abordagem de metabarcoding revelou mais de 53.000 variantes de DNA distintas e mostrou que algumas amostras compartilhavam tão pouco quanto três, ressaltando quão diferentes comunidades vizinhas podem ser.
Reconstruindo genomas a partir de uma sopa genética
A segunda linha de análise seguiu uma rota mais ambiciosa: metagenômica do tipo shotgun, na qual todo o DNA de uma amostra é sequenciado de uma vez. Usando métodos avançados de montagem e binning, a equipe reconstruiu 1.372 genomas provisórios, conhecidos como genomas montados a partir de metagenomas ou MAGs. Muitos desses genomas não puderam ser associados a espécies conhecidas, e apenas cerca de 4% se alinharam com espécies microbianas formalmente descritas. Em alguns grupos, como certas bactérias e arqueias adaptadas a condições incomuns, mais da metade das proteínas previstas não tinha função conhecida. Os pesquisadores também construíram um catálogo maciço de genes com mais de 23 milhões de genes não redundantes, encontrando que aproximadamente 31% não tinham correspondentes nos principais bancos de referência. Isso indica um reservatório profundo de biologia não caracterizada residindo nas águas costeiras.
Habitat extremos, ferramentas inéditas
Alguns sítios, especialmente lagunas hiper-salgadas na França, destacaram-se como pontos quentes de novidade genética. Ali, os níveis de salinidade variaram de praticamente água do mar normal a mais de duas vezes a salinidade oceânica em apenas alguns meses. Essas condições estressantes podem favorecer micróbios extremotolerantes dotados de enzimas que continuam funcionando sob alto sal ou temperatura. Tais enzimas são cada vez mais procuradas para usos industriais em detergentes, biocombustíveis, remediação de poluição e processamento de alimentos. Ao relacionar medições ambientais detalhadas com dados de genes e genomas, esse conjunto de dados ajuda a apontar onde esses organismos e ferramentas bioquímicas incomuns têm maior probabilidade de ser encontrados. 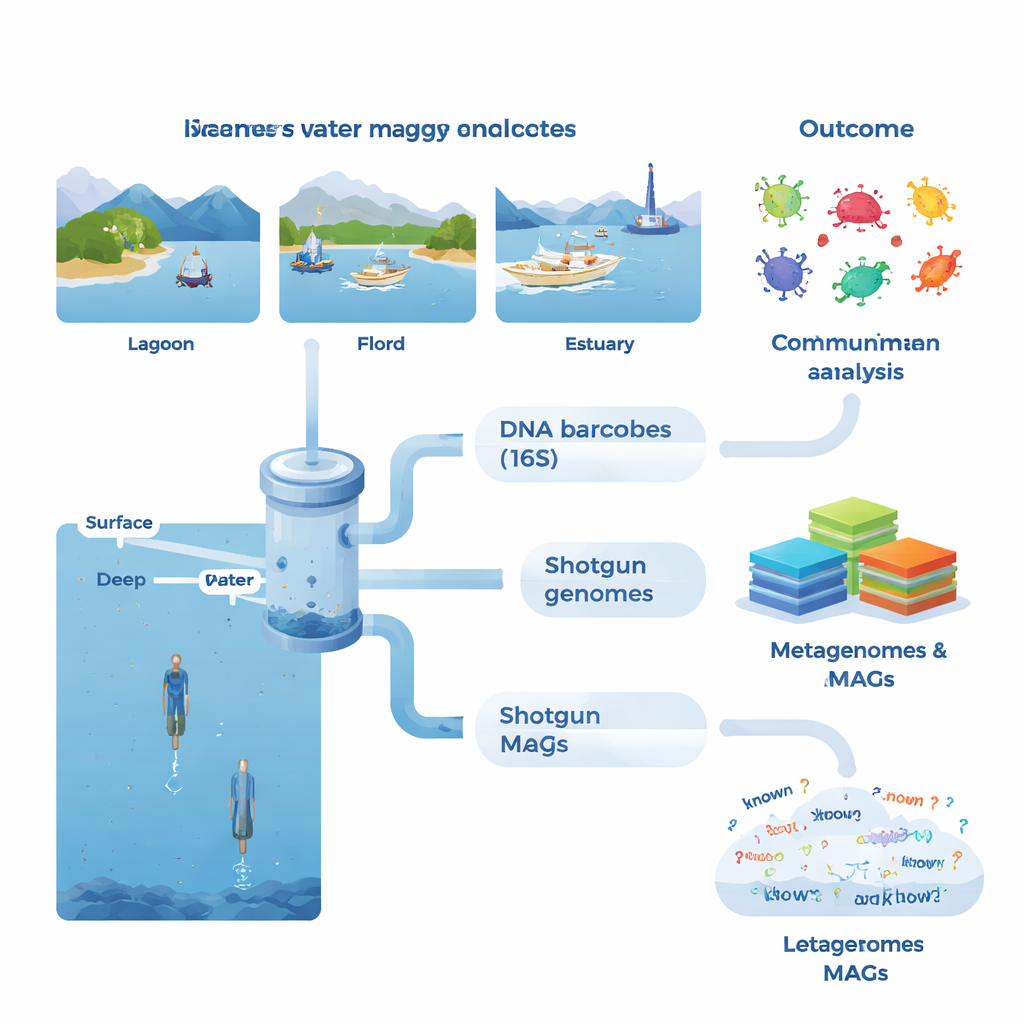
Um recurso público para o futuro dos oceanos
Em vez de apresentar uma única descoberta, este trabalho entrega um recurso aberto e cuidadosamente validado que outros cientistas podem explorar. Todas as sequências de DNA, reconstruções de genomas, catálogos de genes e medições ambientais estão arquivados publicamente, junto com o código computacional usado para processá-los. Para não especialistas, a mensagem-chave é que micróbios costeiros são ao mesmo tempo diversos e cheios de surpresas, especialmente em ambientes negligenciados como lagunas e fiordes. À medida que pesquisadores acessam esses dados, estarão mais bem equipados para entender como a vida microscópica ao longo de nossas costas responde ao aquecimento, poluição e perturbações — e para aproveitar genes inéditos que poderiam beneficiar a biotecnologia e a gestão ambiental.
Citação: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
Palavras-chave: microbiomas costeiros, metagenômica, lagunas e fiordes, biodiversidade marinha, DNA ambiental