Clear Sky Science · pt
MaAsLin 3: refinando e estendendo modelos lineares multivariáveis generalizados para descoberta de associações em meta-ômicas
Por que vizinhos minúsculos do intestino importam
Nossos corpos abrigam trilhões de microrganismos que ajudam a digerir alimentos, treinam o sistema imunológico e podem até influenciar nosso humor. À medida que o sequenciamento de DNA tornou fácil catalogar essas comunidades microbianas, surgiu uma questão crucial: quais micróbios específicos andam de mãos dadas com doenças como a doença inflamatória intestinal ou com traços cotidianos como idade e dieta? Responder isso é surpreendentemente difícil. Os dados são ruidosos, cheios de zeros e relatados como percentuais em vez de contagens reais. Este artigo apresenta o MaAsLin 3, uma nova ferramenta estatística projetada para extrair sinais mais claros de dados de microbioma bagunçados, para que os pesquisadores possam vincular micróbios à saúde humana e ao ambiente de forma mais confiável.
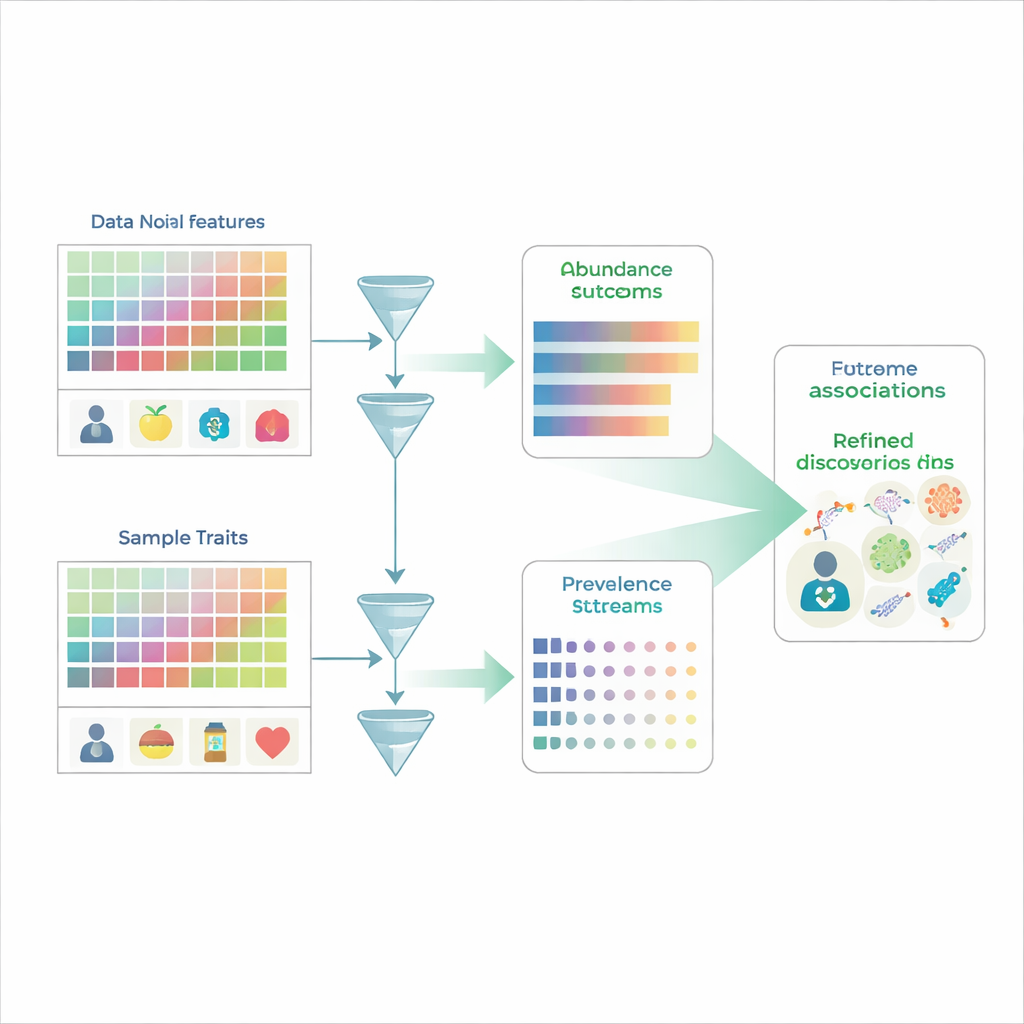
Procurando padrões em uma multidão barulhenta
Estudos tradicionais de microbioma funcionam um pouco como contar rostos em uma plateia: os pesquisadores medem a abundância relativa de centenas ou milhares de espécies microbianas em muitas pessoas e então perguntam quais espécies diferem, por exemplo, entre grupos doentes e saudáveis. Mas os dados de microbioma são restritos a percentuais que somam 100%, então se uma espécie aumenta, pelo menos outra parece diminuir mesmo que sua quantidade real não tenha mudado. Além disso, muitas espécies simplesmente não são detectadas em uma amostra, produzindo muitos zeros que podem refletir ausência real ou limites de detecção. Métodos comuns de análise tipicamente embaralham duas questões distintas — se um microrganismo está presente ou não, e quanto dele existe quando está presente — tornando fácil interpretar mal a biologia subjacente.
Separando presença de quantidade
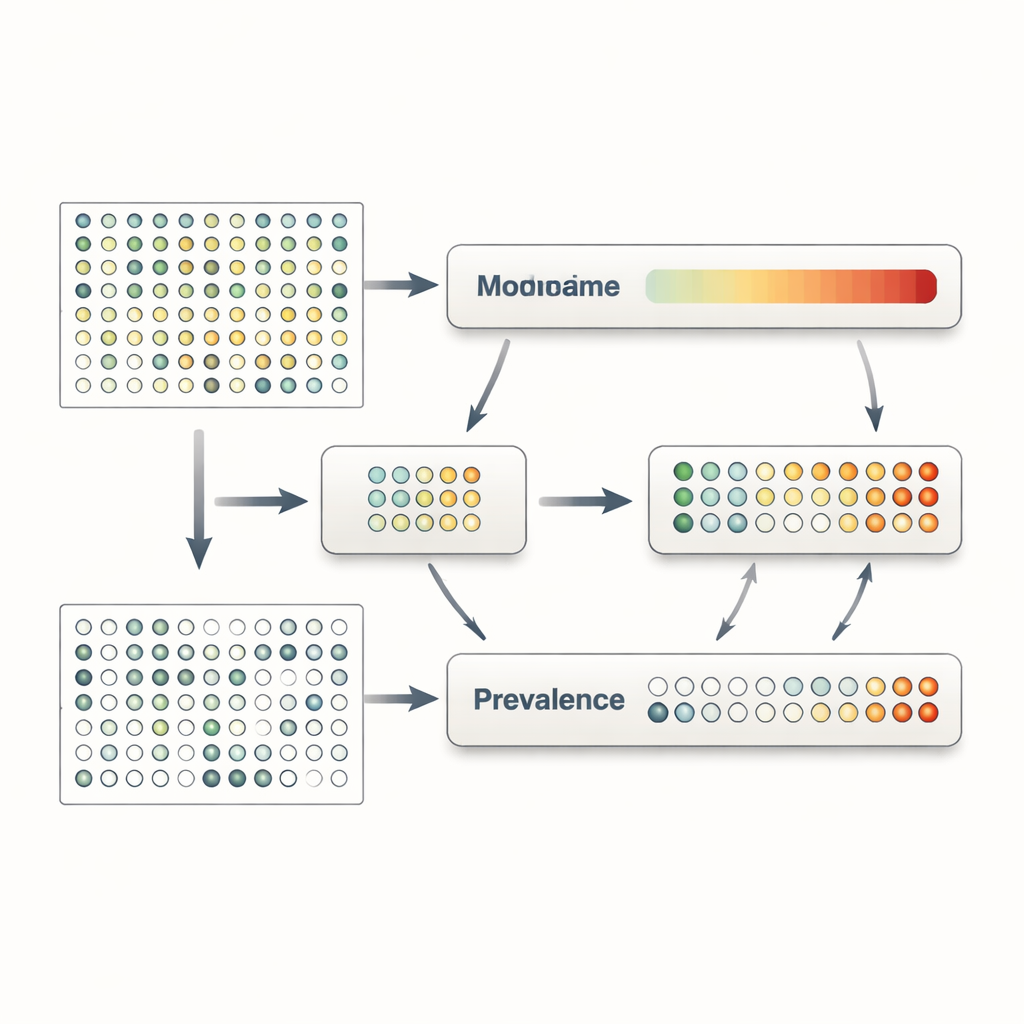
O MaAsLin 3 enfrenta esses problemas tratando explicitamente presença e quantidade como fenômenos separados, porém relacionados. Para cada característica microbiana — como uma espécie, gene ou via metabólica — ele constrói dois modelos em paralelo. Um modelo analisa a prevalência, perguntando com que frequência a característica é detectada em amostras com diferentes traços. O outro modelo foca na abundância, perguntando como o nível da característica muda apenas entre as amostras em que ela é detectada. Ao dividir os dados dessa maneira, o MaAsLin 3 evita o atalho comum de preencher zeros com números arbitrariamente pequenos, o que pode distorcer os resultados. Em seguida, ele combina os dois efeitos em um quadro geral de como cada característica se relaciona com cada traço, permitindo ainda que os pesquisadores vejam se uma associação se refere principalmente à presença, à quantidade ou a ambos.
Ficando mais perto das quantidades do mundo real
Uma complicação adicional na ciência do microbioma é que a maioria das medições é relativa: elas nos dizem qual fração da comunidade total uma espécie ocupa, não quantas células realmente existem. No entanto, perguntas biológicas frequentemente dependem da abundância absoluta — por exemplo, se a contagem de células de um patógeno cruza um limiar que pode desencadear doença. O MaAsLin 3 oferece duas soluções complementares. Quando experimentos incluem informações extras, como quantidades conhecidas de um organismo de referência ou estimativas da carga microbiana total, o método pode transformar percentuais relativos em estimativas de contagens absolutas e modelá-las diretamente. Quando tais dados não estão disponíveis, o MaAsLin 3 compara o comportamento de cada característica ao padrão típico entre todas as características, o que, sob suposições realistas, aproxima o que seria visto em uma escala absoluta. Simulações extensas e testes em conjuntos de dados reais com abundâncias absolutas medidas experimentalmente mostram que essa estratégia recupera com precisão as tendências subjacentes e supera várias ferramentas amplamente usadas.
Revelando sinais ocultos em doenças intestinais
Para mostrar o que esses avanços significam na prática, os autores aplicaram o MaAsLin 3 a uma grande coorte bem estudada de pessoas com e sem doenças inflamatórias intestinais, como doença de Crohn e colite ulcerativa. Trabalhos anteriores já haviam identificado muitas alterações microbianas nessas condições, mas o MaAsLin 3 acrescentou várias camadas de nuance. Confirmou a maioria das ligações conhecidas ao mesmo tempo em que esclareceu que cerca de três quartos das associações envolviam mudanças na presença das espécies, e não em quão abundantes elas eram quando presentes. Em outras palavras, a inflamação intestinal frequentemente coincidia com perda completa de certos micróbios benéficos ou com falha na detecção deles, em vez de apenas uma redução moderada em seus níveis. O método também revelou micróbios cuja presença sozinha — independentemente da quantidade — se correlacionou fortemente com a perturbação da comunidade intestinal relacionada à doença.
O que isso significa para estudos futuros e cuidados
Para não especialistas, a mensagem principal é que a forma como analisamos dados de microbioma pode moldar dramaticamente quais micróbios consideramos importantes para a saúde. Ao lidar melhor com zeros, separar presença de quantidade e aproximar contagens reais de células, o MaAsLin 3 fornece uma lente mais nítida para descobrir marcadores microbianos confiáveis de doença, dieta e ambiente. Seus resultados em doença inflamatória intestinal sugerem que muitas mudanças clinicamente relevantes envolvem micróbios que desaparecem ou aparecem de novo, e não apenas aqueles que mudam lentamente de abundância. Essa distinção é importante para desenhar terapias: se a doença está ligada à perda total de espécies benéficas, estratégias que reintroduzam ou protejam esses micróbios podem ser mais eficazes do que abordagens que apenas tentam ajustar o equilíbrio geral da comunidade. Assim, o MaAsLin 3 equipa os pesquisadores com um conjunto de ferramentas mais preciso e flexível para transformar medições complexas de microbioma em insights biológicos acionáveis.
Citação: Nickols, W.A., Kuntz, T., Shen, J. et al. MaAsLin 3: refining and extending generalized multivariable linear models for meta-omic association discovery. Nat Methods 23, 554–564 (2026). https://doi.org/10.1038/s41592-025-02923-9
Palavras-chave: microbioma, doença inflamatória intestinal, modelagem estatística, abundância absoluta, prevalência microbiana