Clear Sky Science · pt
Construção de sequências de DNA complexas e diversas usando junções de três vias de DNA
Construindo Novas Histórias Genéticas
A biologia moderna pode ler e editar o DNA com velocidade impressionante, mas escrever sequências genéticas longas e personalizadas ainda fica atrás. Essa lacuna atrasa desde o desenvolvimento de novos medicamentos até a criação de materiais mais sustentáveis. Este estudo apresenta o “Sidewinder”, uma nova forma de unir fragmentos de DNA que busca tornar a escrita de genes complexos e sob medida tão confiável e escalável quanto sua leitura.
Por que a Montagem de DNA Precisa de uma Reavaliação
Toda célula funciona com DNA, uma longa cadeia de letras químicas que codificam as instruções da vida. Cientistas só conseguem sintetizar quimicamente trechos curtos de DNA, então genes mais longos precisam ser montados a partir de muitas peças pequenas, como frases reconstruídas a partir de palavras cortadas. Métodos existentes usam bordas complementares nesses fragmentos para guiar quais peças se unem. Mas essas bordas passam a fazer parte do DNA final, o que significa que não podem ser livremente otimizadas para uma montagem perfeita sem também alterar o gene. À medida que os projetos ficam mais longos e intrincados, esse compromisso embutido leva a mais erros, rendimentos menores e limites práticos no que se pode construir.
Um Caminho Lateral que Guia Sem Deixar Vestígios
O Sidewinder resolve esse problema adicionando uma terceira fita auxiliar de DNA que nunca aparece no produto final. Os fragmentos de DNA são preparados com duas características em suas extremidades: curtos “toeholds” que formarão a conexão final sem emendas, e “códigos de barras” (barcodes) mais longos projetados apenas para reconhecer seus parceiros previstos. Quando misturados a uma temperatura controlada, os barcodes em fragmentos vizinhos se encontram e se enrolam em um helicoide lateral temporário, formando uma junção de três vias que posiciona os toeholds correspondentes. Uma enzima então sela os fragmentos principais de DNA. Por fim, os barcodes auxiliares são removidos, deixando uma sequência contínua e limpa, sem cicatrizes ou etiquetas extras. 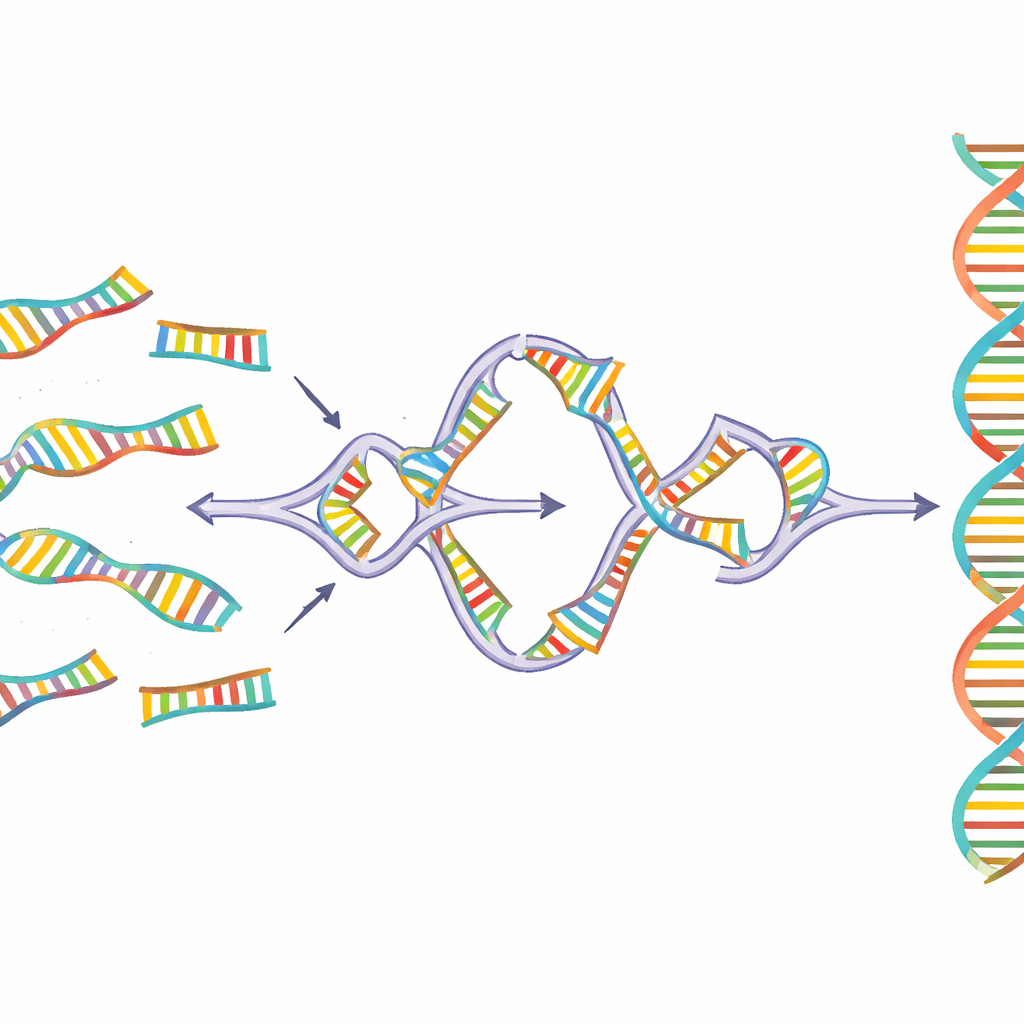
De Dezenas de Fragmentos a Genes Difíceis
Para demonstrar o que o Sidewinder pode alcançar, os autores montaram construções de DNA a partir de 5, 10, 20 e até 40 fragmentos separados em uma única reação. Métodos concorrentes de ponta falharam além de apenas alguns fragmentos, produzindo misturas confusas ou não funcionando, enquanto o Sidewinder consistentemente gerou um único produto no tamanho correto. Sequenciamento de leitura longa confirmou que, em um teste com 40 fragmentos, mais de 96% das leituras eram produtos verdadeiros do Sidewinder e todos esses foram montados na ordem perfeita. A equipe então testou o método em sequências de “modo difícil”: um gene humano com conteúdo extremamente alto de G e C, e um segmento proteico semelhante à seda repleto de repetições. Sequências assim frequentemente derrotam montagens padrão porque se autoapegam de maneiras confusas. O Sidewinder ainda produziu montagens quase perfeitas, mesmo quando todas as junções deliberadamente compartilhavam a mesma sequência de toehold — algo que seria quase impossível de controlar com técnicas antigas.
Muitos Genes ao Mesmo Tempo e Oceanos de Variantes
Porque os barcodes do Sidewinder definem de forma única quem pode emparelhar com quem, múltiplos genes podem ser montados no mesmo tubo sem contaminação cruzada. Os pesquisadores misturaram fragmentos para três proteínas marcador de cores diferentes e as montaram em uma única reação. Com os primers adequados, eles puderam amplificar seletivamente qualquer um dos genes ou a mistura, e o sequenciamento mostrou que cruzamentos incorretos entre os projetos foram extremamente raros. 
O Que Isso Significa para a Bioengenharia Futura
A principal conquista do Sidewinder é separar as “instruções de montagem” da história final do DNA. Ao mover a informação orientadora para uma fita lateral removível, os cientistas podem projetar junções extraordinariamente específicas e confiáveis sem serem forçados a comprometer o gene em si. O resultado é um modo de uso geral para construir sequências de DNA longas, complexas e altamente variadas com precisão que rivaliza, e em alguns aspectos melhora, a qualidade dos fragmentos iniciais. À medida que ferramentas como a IA propõem projetos genéticos cada vez mais ousados, técnicas como o Sidewinder podem se tornar essenciais para transformar essas propostas em moléculas reais para medicina, materiais, agricultura e além.
Citação: Robinson, N.E., Zhang, W., Ghosh, R. et al. Construction of complex and diverse DNA sequences using DNA three-way junctions. Nature 651, 491–500 (2026). https://doi.org/10.1038/s41586-025-10006-0
Palavras-chave: montagem de DNA, biologia sintética, bibliotecas de genes, nanotecnologia de DNA, engenharia de proteínas