Clear Sky Science · pt
Blindagem metabólica dependente de poliaminas regula o splicing alternativo
Como moléculas minúsculas ajudam as células a ler seus genes
Dentro de cada célula, o mesmo roteiro de DNA pode ser lido de várias maneiras, permitindo que um número limitado de genes produza uma grande diversidade de proteínas. Essa flexibilidade depende de um processo chamado splicing alternativo, que edita as mensagens de RNA antes de serem transformadas em proteínas. Este artigo revela que pequenas moléculas carregadas positivamente, chamadas poliaminas, orientam discretamente essa etapa de edição, atuando como uma espécie de escudo protetor que ajuda as células a decidir quais versões de RNA produzir. Como o splicing alternativo é crucial no câncer, na função cerebral e em células-tronco, descobrir essa camada oculta de controle tem implicações amplas para a saúde e a doença.
Pequenos ajudantes carregados em toda célula
Poliaminas são moléculas pequenas e flexíveis que carregam múltiplas cargas positivas. As células as produzem a partir de nutrientes básicos, e elas há muito são reconhecidas como auxiliares do crescimento e da sobrevivência, especialmente em células que se dividem rapidamente, como tumores. Os autores perguntaram se as poliaminas também funcionam como sinais, e não apenas como combustível. Ao bloquear parcialmente a produção de poliaminas em células de câncer de próstata e em camundongos, eles mediram como proteínas e RNA mudaram ao longo do tempo. Descobriram que, muito antes de os níveis totais de poliaminas caírem drasticamente, houve uma forte onda de alterações na fosforilação de proteínas — marcas químicas que ligam ou desligam chaves proteicas — especialmente em componentes da máquina de edição de RNA celular, o spliceossomo.
Reconfigurando o editor de RNA da célula
Focando especificamente no RNA, a equipe usou sequenciamento profundo para acompanhar o splicing alternativo quando a síntese de poliaminas foi inibida. Centenas de segmentos de RNA foram omitidos ou incluídos de forma diferente, em linhagens de câncer, tipos celulares normais e tecidos de camundongo. Essas mudanças não foram simplesmente um efeito colateral da divisão celular mais lenta ou de outro processo dependente de poliaminas conhecido, chamado hipusinização. Em vez disso, quando os pesquisadores reabasteceram as células com poliaminas externas, muitos deslocamentos no splicing voltaram ao normal. Tanto fármacos quanto ferramentas genéticas que reduziram poliaminas produziram padrões de splicing semelhantes, e uma redução adicional de poliaminas com uma combinação de drogas intensificou ainda mais as mudanças, confirmando que o efeito estava intimamente ligado à disponibilidade de poliaminas.
Um alvo oculto: o módulo de splicing SF3
Para identificar onde, na maquinaria de splicing, as poliaminas atuam, os autores compararam a assinatura de splicing causada pela redução de poliaminas com um amplo mapa de referência gerado ao silenciar individualmente mais de 300 fatores de splicing conhecidos. A correspondência mais próxima apontou para uma parte específica do spliceossomo chamada subcomplexo SF3, que ajuda a reconhecer sinais-chave no RNA. A análise computacional de dados públicos de ligação proteína–RNA apoiou esse vínculo: RNAs cujo splicing foi alterado pela perda de poliaminas eram especialmente propensos a serem ligados por proteínas SF3. Quando a equipe desativou parcialmente componentes SF3 geneticamente ou com um fármaco, os efeitos no splicing da depleção de poliaminas foram em grande parte anulados, mostrando que a atividade intacta do SF3 é necessária para essa nova via regulatória. 
Blindagem metabólica: como poliaminas bloqueiam a marcação proteica
Mais a fundo, os pesquisadores notaram que os sítios de fosforilação mais fortemente afetados nas proteínas SF3 se agrupavam em trechos curtos ricos em aminoácidos carregados negativamente. Modelagem molecular e experimentos de ressonância magnética nuclear mostraram que poliaminas se acomodam nessas manchas ácidas, formando múltiplos contatos eletrostáticos e cobrindo parcialmente resíduos de serina próximos onde grupos fosfato são normalmente adicionados. Esse “abraço” físico reduz a acessibilidade desses pontos para quinases proteicas — as enzimas que adicionam fosfatos. Em experimentos em tubo de ensaio, adicionar poliaminas bloqueou diretamente uma quinase chamada CK1 de fosforilar proteínas SF3. Em células, inibir CK1 e seu parente próximo CK2 atenuou as mudanças de splicing causadas pela perda de poliaminas, e camundongos especialmente modificados cuja proteína SF3A3 não possuía três sítios-chave de fosforilação tornaram-se amplamente insensíveis aos deslocamentos de splicing dependentes de poliaminas. 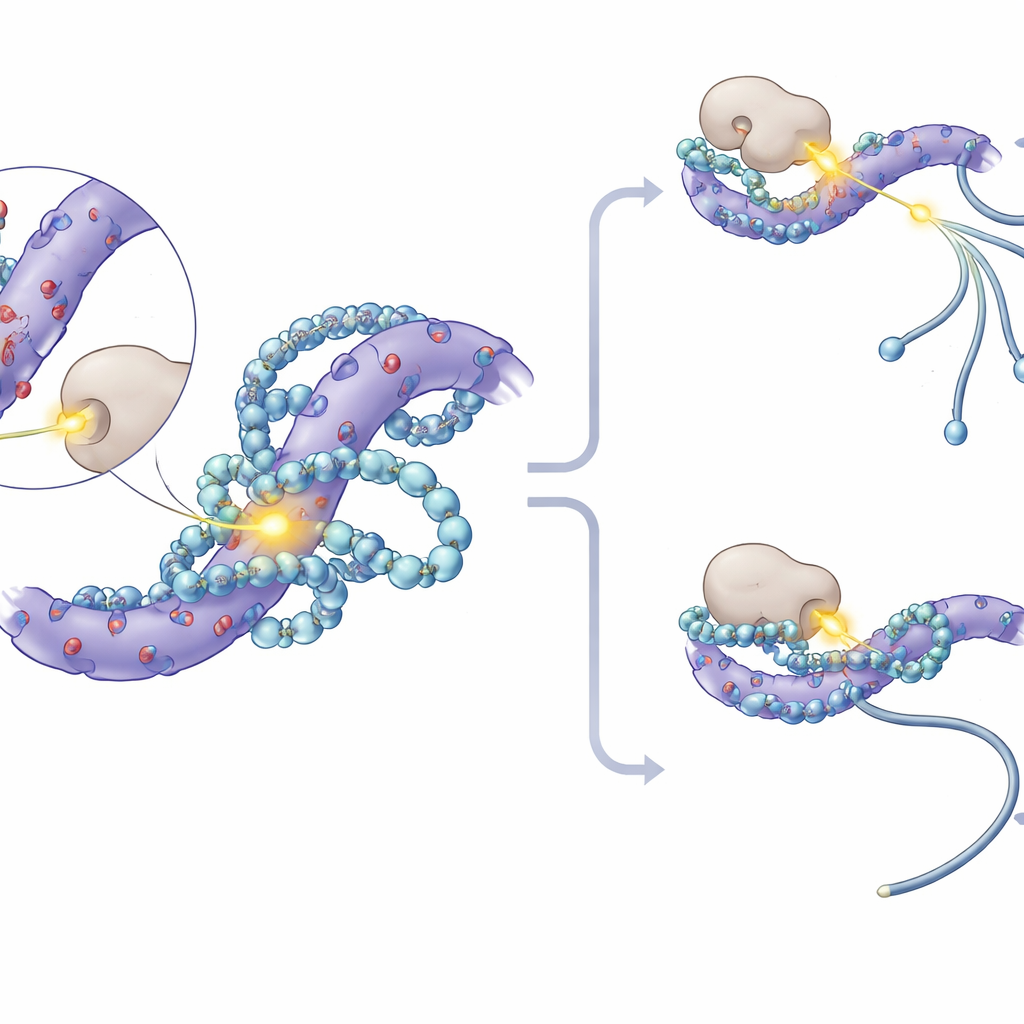
Uma molécula desenhada que separa papéis
O estudo também apresenta um fármaco do tipo poliamina, BENSpm, que é mais fortemente carregado positivamente, mas simultaneamente inibe a produção celular de poliaminas. BENSpm ligou-se fortemente às manchas ácidas do SF3 e bloqueou a ação de quinases, assim como as poliaminas naturais, mas não restaurou o crescimento celular quando as poliaminas reais estavam escassas. Isso permitiu aos autores separar as funções clássicas das poliaminas (suporte ao crescimento e ao metabolismo) do papel recém-definido de blindagem. Em células-tronco embrionárias de camundongo, a depleção de poliaminas empurrou as células na direção da perda do marcador de "stemness" Nanog e alterou seu panorama de splicing. BENSpm restaurou tanto o perfil de splicing quanto a expressão de Nanog apesar da supressão contínua da síntese normal de poliaminas, indicando que a blindagem metabólica é um requisito chave para manter a identidade de células-tronco.
Por que essa descoberta importa
Em termos cotidianos, este trabalho mostra que poliaminas atuam como pequenas luvas protetoras ao redor de partes sensíveis de proteínas-chave do splicing. Quando as luvas estão colocadas, as quinases não conseguem agarrar e marcar facilmente esses sítios, e a edição de RNA da célula segue seu curso. Quando as poliaminas estão baixas, as luvas saem, a fosforilação aumenta e os padrões de splicing mudam, com consequências tanto para células cancerosas quanto para células-tronco. Ao definir esse mecanismo de "blindagem metabólica" e ao fornecer uma molécula-ferramenta que o imita seletivamente, o estudo abre caminho para novas formas de ajustar a leitura dos genes sem alterar o DNA em si, potencialmente inspirando futuras terapias que atinjam o splicing no câncer e na medicina regenerativa.
Citação: Zabala-Letona, A., Pujana-Vaquerizo, M., Martinez-Laosa, B. et al. Polyamine-dependent metabolic shielding regulates alternative splicing. Nature 651, 819–828 (2026). https://doi.org/10.1038/s41586-025-09965-1
Palavras-chave: poliaminas, splicing alternativo, processamento de RNA, sinalização metabólica, regulação de células-tronco