Clear Sky Science · pt
Genômica funcional com resolução temporal usando deep learning revela controle hierárquico global da autofagia
Como as Células Se Reciclam — e Sabem Quando Parar
Nossas células sobrevivem a períodos de escassez reciclando suas próprias partes por meio de um processo chamado autofagia — literalmente, “auto‑comer”. Pouca reciclagem faz com que componentes danificados se acumulem; demais, e a célula se canibaliza. Este estudo aborda uma pergunta aparentemente simples, mas com grandes implicações para envelhecimento e doença: como uma célula viva liga e desliga a autofagia nos momentos certos conforme os níveis de nutrientes sobem e descem?
Acompanhando Milhares de Células Durante um Ciclo de Abundância a Fome
Para investigar isso, os pesquisadores usaram a levedura de padeiro como modelo e observaram quase seis mil linhagens mutantes diferentes enquanto passavam por privação e recuperação de nutrientes. Cada linhagem de levedura carregava marcadores fluorescentes que sinalizavam estruturas envolvidas na autofagia, permitindo a um microscópio de alta potência capturar imagens a cada hora enquanto os nutrientes eram removidos e depois restaurados. Em vez de classificar manualmente essas imagens, a equipe treinou algoritmos de deep learning para reconhecer quando uma célula estava em estado autofágico, com base inteiramente em recursos de imagem em vez do julgamento humano. Isso produziu curvas temporais precisas da atividade autofágica para quase todo o genoma de levedura, revelando quão rápido e quão intensamente cada mutante respondia às mudanças de nutrientes. 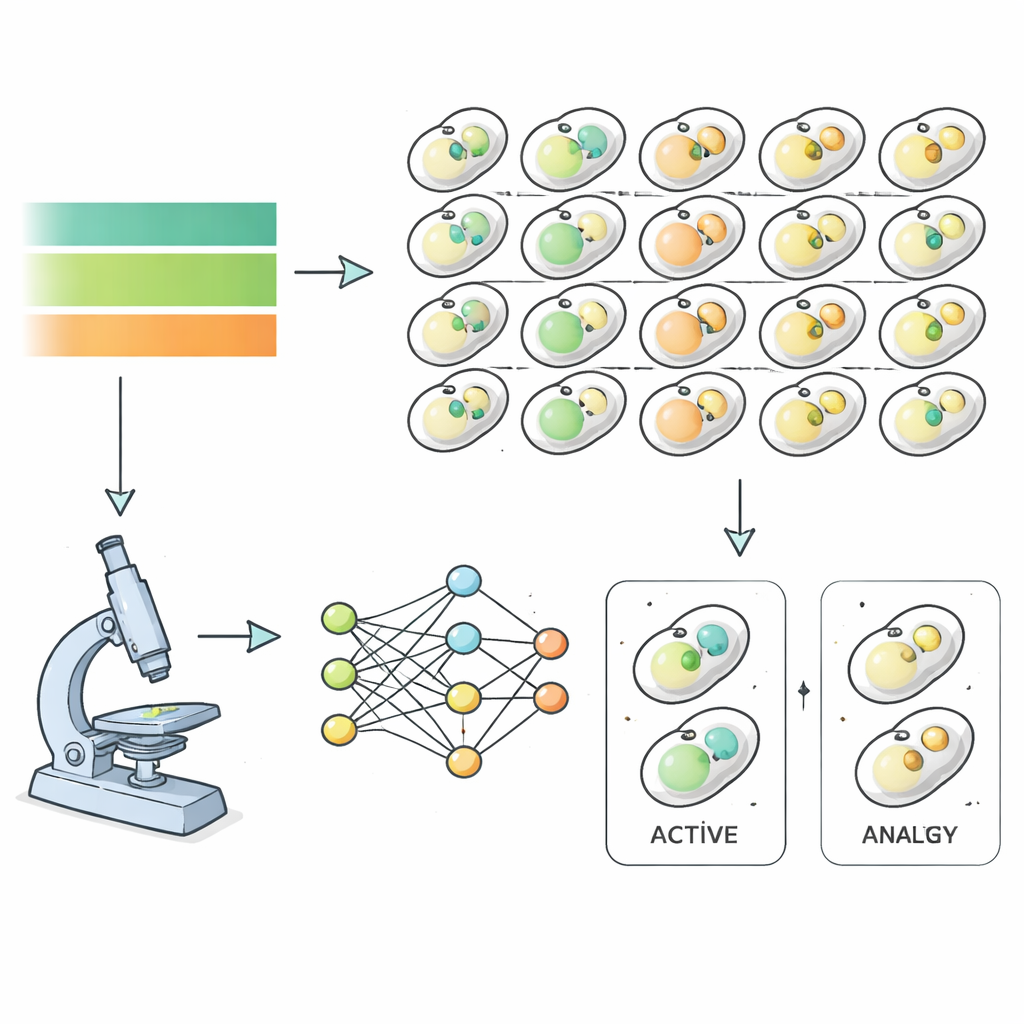
Seis Maneiras Distintas pelas Quais as Células Lidam Mal com a Reciclagem
Ajustando matematicamente essas curvas temporais, os autores extrairam “impressões digitais cinéticas” detalhadas para cada mutante — quão rápido a autofagia ligava, quanto tempo permanecia elevada e quão abruptamente se desligava. Agrupar essas assinaturas revelou seis tipos amplos de comportamento. Alguns mutantes eram “ultrassensíveis”, respondendo muito rapidamente à fome e ao retorno de nutrientes. Outros eram “hipossensíveis”, reagindo de forma lenta. Um grupo “hiperativo” mostrou reciclagem basal anormalmente alta, enquanto vários grupos apresentaram diferentes graus de incapacidade de montar uma resposta adequada. Importante: genes centrais já conhecidos da autofagia caíram nas classes mais severas, validando que o método captura biologia genuína em vez de ruído de medição.
Mapeando uma Hierarquia de Controle sobre a Autofagia
A autofagia não ocorre isoladamente; ela está integrada às redes regulatórias mais amplas da célula. A equipe sobrepôs seus perfis dinâmicos a grandes mapas de interações genéticas e proteicas em levedura. Genes cuja perda causava defeitos acentuados na autofagia tendiam a ficar próximos à conhecida “máquina central” da autofagia nesses mapas, enquanto mutantes mais sutis estavam mais distantes, consistente com um controle mais indireto. Ao examinar quais processos celulares eram enriquecidos em cada classe comportamental, eles descobriram que a ativação desencadeada pela fome é fortemente moldada por vias que lidam com RNA, produção de proteínas e metabolismo de energia, enquanto o desligamento da autofagia após o retorno de nutrientes depende mais do tráfego e fusão de membranas que eliminam os vesículos de reciclagem.
Aproximando‑se de Como os Vesículos se Formam e São Eliminados
A autofagia prossegue por duas etapas principais: construir vesículas carregadas de carga e então fundi‑las com o compartimento de reciclagem da célula para degradação. Para dissecar essas etapas, os pesquisadores exploraram o “espaço latente” dentro de sua rede neural — a representação comprimida que ela usa para distinguir imagens. Projetando essa representação interna em um mapa bidimensional, eles puderam ver populações celulares moverem‑se de uma região sem vesículas, por uma com muitas vesículas livres, e finalmente para uma região onde os vesículos tinham sido removidos. Usando comparações estatísticas contra mutantes de referência presos em diferentes estágios, quantificaram para cada gene se ele afetava principalmente a formação de vesículas, a eliminação de vesículas ou ambos. Essa análise mostrou que o controle da formação de vesículas é altamente sensível aos níveis de nitrogênio ao longo do tempo, ao passo que a maquinaria de eliminação se comporta de forma mais estável e frequentemente é o principal limitador do fluxo total de reciclagem. 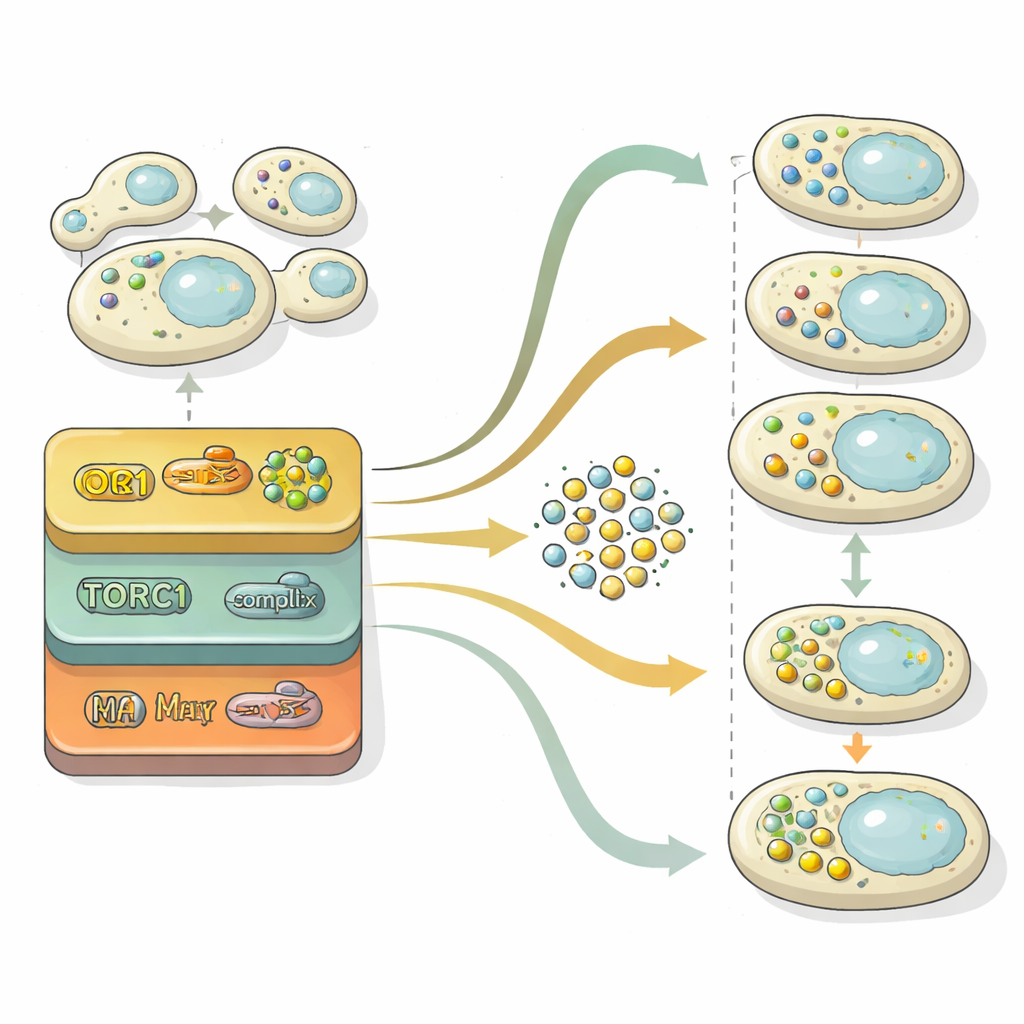
Um Freio Oculto na Reciclagem: a Via Retrógrada
Uma das descobertas mais marcantes envolveu a chamada via retrógrada (RTG), que transmite sinais das mitocôndrias para o núcleo. Células de levedura sem componentes RTG produziram autophagosomas em excesso mesmo quando os nutrientes eram abundantes e tiveram dificuldade em eliminá‑los quando os nutrientes retornaram. Experimentos de acompanhamento detalhados mostraram que essa via controla a expressão de genes-chave da autofagia, especialmente o iniciador mestre ATG1, em grande parte independentemente do conhecido sensor de nutrientes TORC1, alvo de drogas como rapamicina. Na prática, a sinalização RTG atua como um freio variável no tempo que previne autofagia descontrolada em condições ricas e ajuda a terminar a resposta quando as condições melhoram.
Por Que Isso Importa para Saúde e Terapia
No conjunto, este trabalho fornece um mapa genômico e com resolução temporal de como as células ajustam a autofagia diante de mudanças nutricionais. Revela que ativação e desligamento não são imagens espelhadas: muitos mais genes influenciam como a reciclagem começa do que como ela para, e o equilíbrio de longo prazo depende fortemente da eliminação de vesículas e de freios transcricionais como a via RTG. Para o leitor geral, a conclusão principal é que o autocanibalismo celular está sob controle estratificado e hierárquico, e que agora podemos mapear essas camadas com alta precisão. Essa visão em nível de sistemas pode, eventualmente, orientar terapias mais sutis que ajustem a autofagia em fases específicas — estimulando a reciclagem benéfica sem desencadear os efeitos nocivos da autodegradação crônica e descontrolada.
Citação: Chica, N., Andersen, A.N., Orellana-Muñoz, S. et al. Time-resolved functional genomics using deep learning reveals global hierarchical control of autophagy. Nat Cell Biol 28, 465–479 (2026). https://doi.org/10.1038/s41556-025-01837-0
Palavras-chave: autofagia, deep learning, genética de levedura, sensoriamento de nutrientes, reciclagem celular