Clear Sky Science · pt
Inferência baseada em simulação da dinâmica de migração celular em ambientes espaciais complexos
Como células imunes encontram o caminho através de tecidos lotados
Nossas células imunes frequentemente precisam se espremer por tecidos densos e parecidos com labirintos para alcançar locais de infecção ou linfonodos. Este estudo faz uma pergunta aparentemente simples, mas com grandes implicações: como essas células navegam em ambientes tão congestionados e como podemos inferir de forma confiável seus comportamentos a partir de dados microscópicos ruidosos? Ao combinar "labirintos" de laboratório precisamente projetados com simulações computacionais avançadas e ferramentas modernas de aprendizado de máquina, os autores mostram uma nova maneira de decodificar as regras que guiam o movimento celular em arredores complexos.
Construindo um labirinto em miniatura para células imunes
Para investigar como o ambiente molda o movimento, os pesquisadores se concentraram em células dendríticas — sentinelas imunes que precisam viajar de tecidos periféricos até linfonodos, guiadas por atrativos químicos chamados quimiocinas. Eles construíram um chip microfabricado: uma "floresta de pilares" plana composta por postes regularmente espaçados feitos de borracha de silicone (PDMS), com brechas estreitas de 10 micrômetros que imitam os espaços apertados dos tecidos reais. Um lado do chip foi carregado com dezenas de milhares de células dendríticas; o lado oposto continha uma fonte da quimiocina CCL19, que cria um gradiente estável através dos pilares. Usando microscopia time‑lapse, acompanharam os núcleos de células individuais a cada 30 segundos enquanto elas tentavam se mover em direção à fonte de quimiocina. 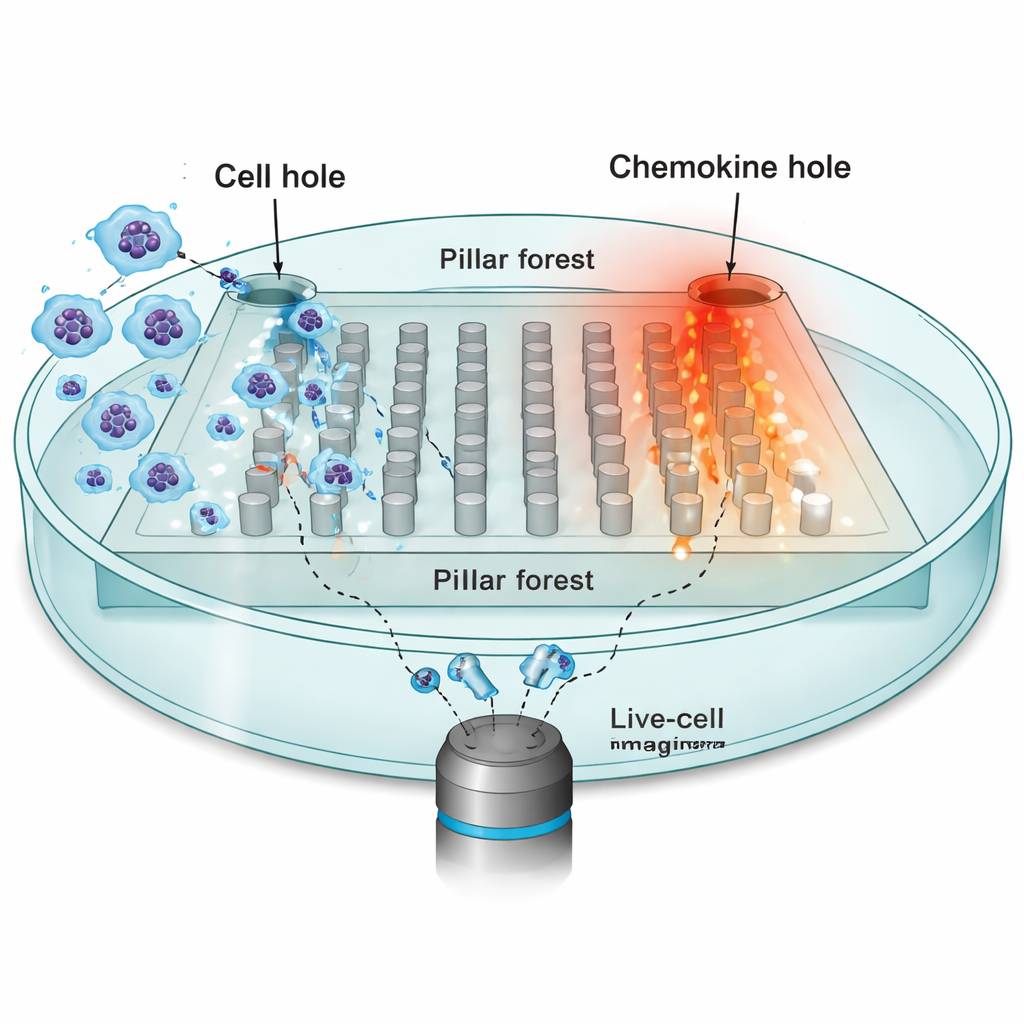
Transformando biologia em um experimento virtual
Para entender essa diversidade, a equipe construiu um modelo computacional detalhado de migração celular usando um arcabouço conhecido como modelo de Potts celular. Em vez de tratar a célula como um ponto simples, essa abordagem representa cada célula como uma mancha estendida em uma grade, permitindo que ela mude de forma, se esprema entre pilares e responda a sinais químicos. O modelo inclui quatro ingredientes-chave: quão fortemente uma célula é atraída pelo gradiente de quimiocina (mdir), quanto ela tende a persistir na direção atual de movimento (mrand), com que frequência ela se reorienta (capturado por uma taxa λ) e seu tamanho efetivo (a). Ajustando esses parâmetros e executando simulações, o modelo produz trajetórias sintéticas que podem ser comparadas diretamente com os percursos registrados na floresta de pilares.
Por que medidas escolhidas à mão são insuficientes
Tradicionalmente, pesquisadores resumem esses dados de movimento com um punhado de estatísticas familiares — quão longe uma célula percorre (deslocamento), quão rápido ela se move (velocidade) e como sua direção muda ao longo do tempo (ângulos de curva). Os autores primeiro usaram essas medidas manualmente elaboradas dentro de uma técnica chamada computação bayesiana aproximada (ABC), que busca conjuntos de parâmetros que façam as trajetórias simuladas se assemelharem às experimentais. Eles descobriram que, embora esses resumos capturem tendências gerais, eles deixam de fora grande parte da estrutura fina dos dados. Como resultado, alguns parâmetros do modelo, especialmente os que governam a persistência aleatória e o tempo de reorientação, permaneceram pouco restritos ou até viésados. Além disso, o ABC exigiu centenas de milhares de simulações e muitas horas de tempo de computação para alcançar ajustes aceitáveis.
Deixar redes neurais aprenderem o que importa
Para superar essas limitações, o estudo recorreu a uma família mais recente de métodos chamada estimação neural de posterior (NPE). Aqui, uma rede neural é treinada diretamente em muitos pares de dados simulados e parâmetros subjacentes. Uma parte da rede aprende automaticamente seu próprio conjunto compacto de "características resumo" a partir de coleções inteiras de trajetórias celulares; outra parte aprende como essas características se mapeiam de volta para valores prováveis de parâmetros. Crucialmente, essas características aprendidas são otimizadas explicitamente para a inferência precisa de parâmetros, não para interpretabilidade humana. Os autores então reutilizaram os resumos aprendidos dentro de uma estrutura ABC, criando um pipeline híbrido que combina a robustez do ABC com a flexibilidade das redes neurais. 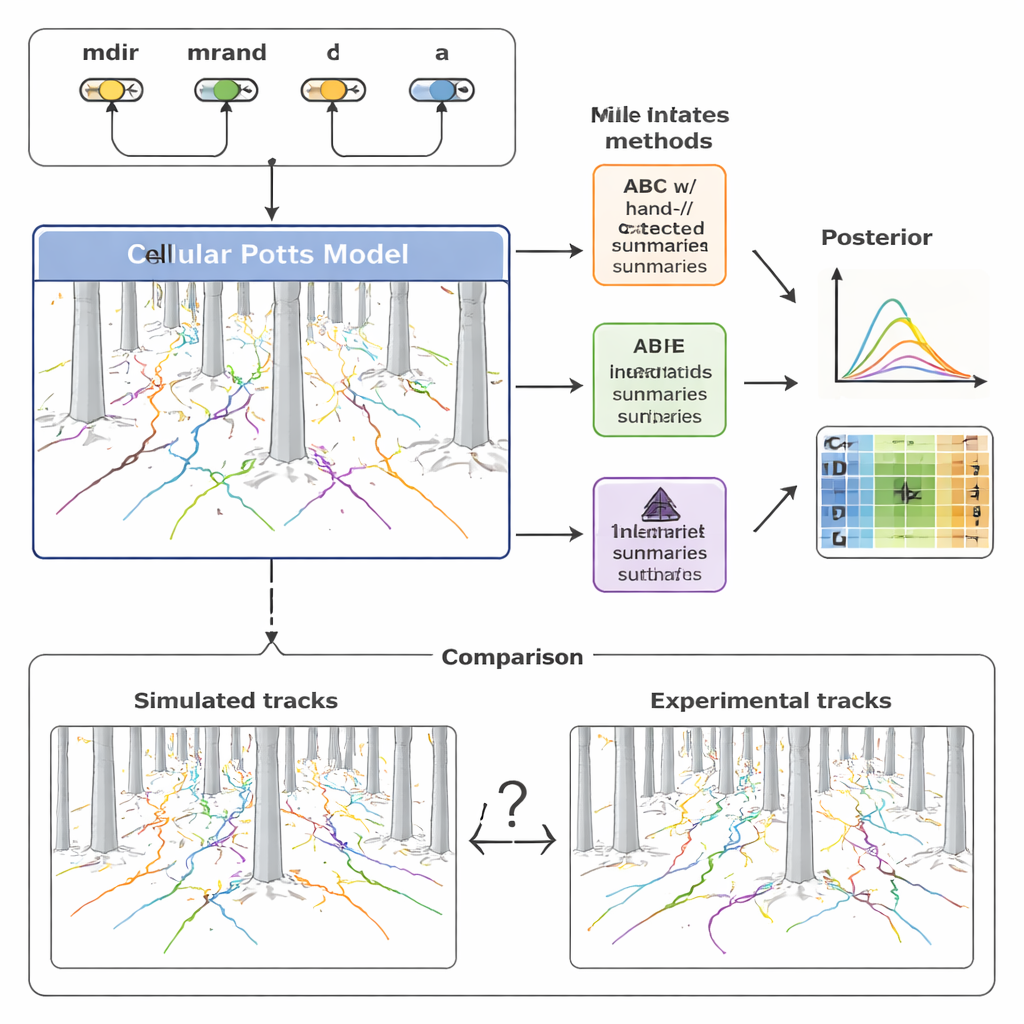
O que a nova abordagem revela sobre a navegação celular
Com esse modelo calibrado, os pesquisadores exploraram como sinais de quimiocina e obstáculos físicos moldam conjuntamente a migração. O tamanho celular inferido sugeriu que células dendríticas efetivamente encolhem e se deformam para passar pelas brechas de 10 micrômetros, consistente com sua flexibilidade conhecida. Simulações indicaram que o movimento persistente aleatório é um dos principais motores de quão amplamente as células se espalham, mesmo sem orientação por quimiocina, e que a floresta de pilares pode aprisionar células quando fortes sinais direcionais e persistência atuam em conjunto. Surpreendentemente, o modelo prevê que um sinal de quimiocina ativo apenas brevemente no início pode, em alguns casos, ajudar mais células a alcançar o alvo do que um sinal constante, porque a atração prolongada pode manter as células circulando dentro dos obstáculos em vez de fazê‑las escapar.
Por que isso importa para a biologia e a modelagem
Para não especialistas, a mensagem principal é dupla. Primeiro, a migração de células imunes em tecidos não se resume a seguir uma trilha química; ela emerge de uma interação sutil entre sinais orientadores, as próprias tendências de movimento das células e a disposição física do entorno. Segundo, extrair essas regras a partir de dados de imagem requer deixar o computador aprender quais padrões nos dados são mais informativos, em vez de depender exclusivamente de medidas simples projetadas pelo humano. Ao integrar experimentos microengenheirados, simulações que resolvem forma e inferência baseada em redes neurais, este trabalho oferece um modelo poderoso para estudar como células de muitos tipos se movem por ambientes complexos, com aplicações potenciais que vão desde entender a vigilância imune até projetar melhores terapias contra o câncer.
Citação: Arruda, J., Alamoudi, E., Mueller, R. et al. Simulation-based inference of cell migration dynamics in complex spatial environments. npj Syst Biol Appl 12, 20 (2026). https://doi.org/10.1038/s41540-026-00648-9
Palavras-chave: migração celular, células dendríticas, gradientes de quimiocinas, inferência baseada em simulação, florestas de pilares microfluídicas