Clear Sky Science · pt
Estudo multi-ômico em larga escala revela interações hospedeiro–microbioma que impulsionam o desenvolvimento radicular e a aquisição de nitrogênio
Como micróbios do solo amigáveis podem ajudar a alimentar o mundo
A agricultura moderna depende fortemente de fertilizantes nitrogenados para alimentar uma população crescente, mas isso traz altos custos ambientais, desde a poluição da água até emissões de gases de efeito estufa. Este estudo mostra que as plantas cultivadas não são passivas no solo: suas raízes se comunicam ativamente com os micróbios ao redor. Ao decodificar essa conversa oculta em canola, os autores revelam como uma bactéria específica que vive nas raízes ajuda as plantas a desenvolver mais raízes e a captar mais nitrogênio, sugerindo culturas futuras que precisarão de muito menos fertilizante.
Raízes, vizinhos e nutrição vegetal
As raízes das plantas ficam em uma faixa estreita do solo chamada rizosfera, uma zona movimentada onde raízes e micróbios trocam constantemente substâncias químicas. Esses vizinhos microscópicos podem impulsionar o crescimento das plantas, defender contra doenças e ajudar as plantas a lidar com solos pobres. Ainda assim, em culturas como a canola, os cientistas não sabiam totalmente como os próprios genes da planta moldam quais micróbios se reúnem ao redor das raízes, ou como isso, por sua vez, afeta nutrientes-chave como o nitrogênio. Entender essas conexões poderia permitir que melhoristas selecionassem variedades que naturalmente atraem os micróbios mais úteis.
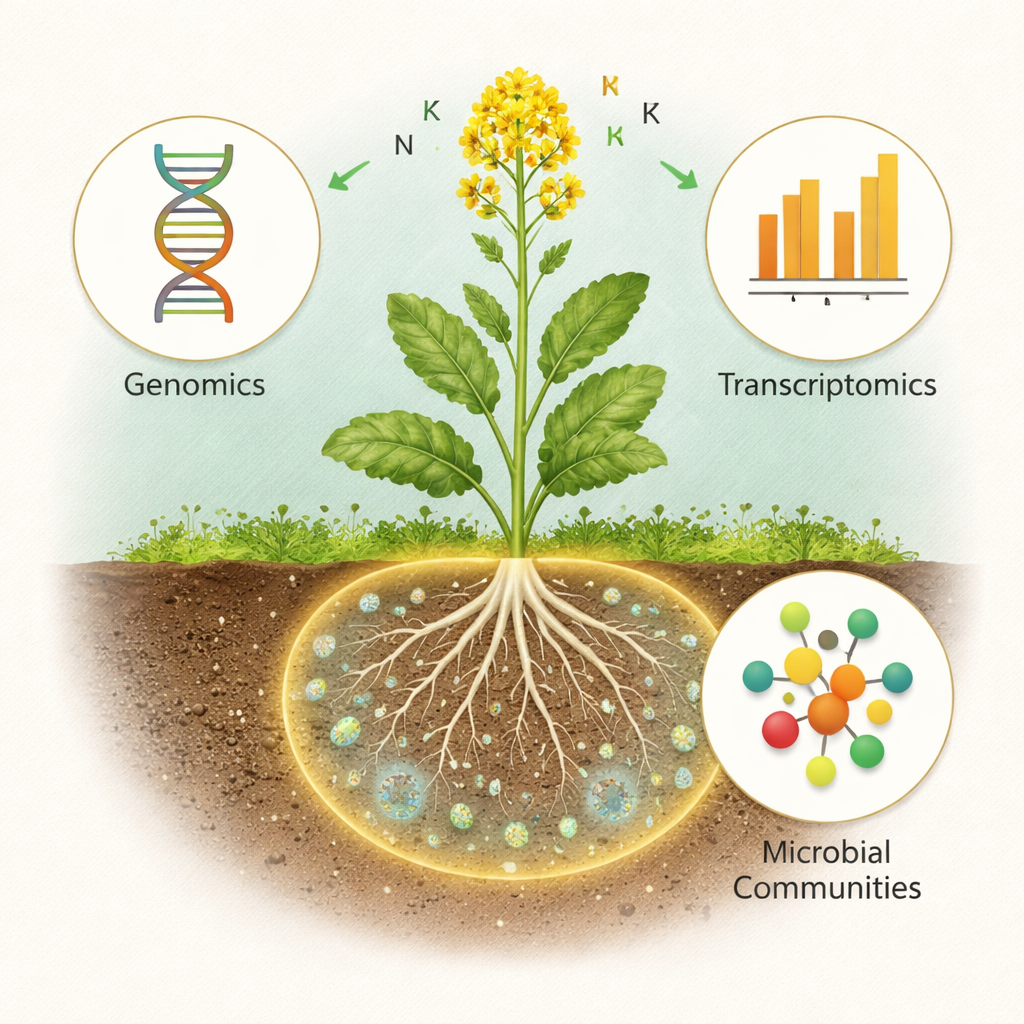
Um olhar multi-ângulo em larga escala sobre a canola
A equipe de pesquisa plantou 175 variedades geneticamente distintas de canola em dois locais de campo muito diferentes na China. Em cada parcela, coletaram três tipos de dados: quais espécies bacterianas viviam no solo aderido às raízes, quais genes nas raízes estavam ativados ou desativados, e quanto de 12 nutrientes minerais, incluindo nitrogênio, acabou nos ramos aéreos. Juntas, essas medições “multi-ômicas” criaram 1.341 conjuntos de dados pareados, permitindo aos cientistas alinhar lado a lado o DNA da planta, a atividade gênica radicular e as comunidades microbianas. Em seguida, usaram modelos estatísticos para ver o quanto cada camada podia prever as outras.
Quando a atividade gênica diz quem são os vizinhos
A análise mostrou que o padrão de genes ativados nas raízes fez um trabalho melhor ao prever quais bactérias apareciam ao redor delas do que a sequência de DNA subjacente por si só. Em outras palavras, o que a raiz está fazendo agora importa mais para seus hóspedes microbianos do que seu código genético estático. Quando os pesquisadores combinaram informações sobre a atividade gênica radicular com a mistura de bactérias, conseguiram explicar até cerca de metade das diferenças naturais nos níveis de nitrogênio entre as plantas. Isso sugere que o microbioma está profundamente entrelaçado com a eficiência com que uma planta absorve nutrientes essenciais.
Destaque para uma bactéria útil
Entre centenas de tipos bacterianos, um grupo chamado Sphingopyxis destacou-se repetidamente. Sua abundância ao redor das raízes esteve fortemente ligada a regiões específicas do genoma da canola e a clusters de genes radiculares envolvidos no processamento de compostos de nitrogênio e carbono. A equipe isolou uma cepa de Sphingopyxis das raízes de canola, sequenciou seu genoma e testou seus efeitos em experimentos controlados em vasos. Embora a bactéria não pudesse fixar nitrogênio atmosférico por conta própria, as plantas inoculadas com ela desenvolveram mais raízes laterais, acumularam mais nitrogênio e produziram maior biomassa aérea, especialmente em solo com baixo teor de nitrogênio.
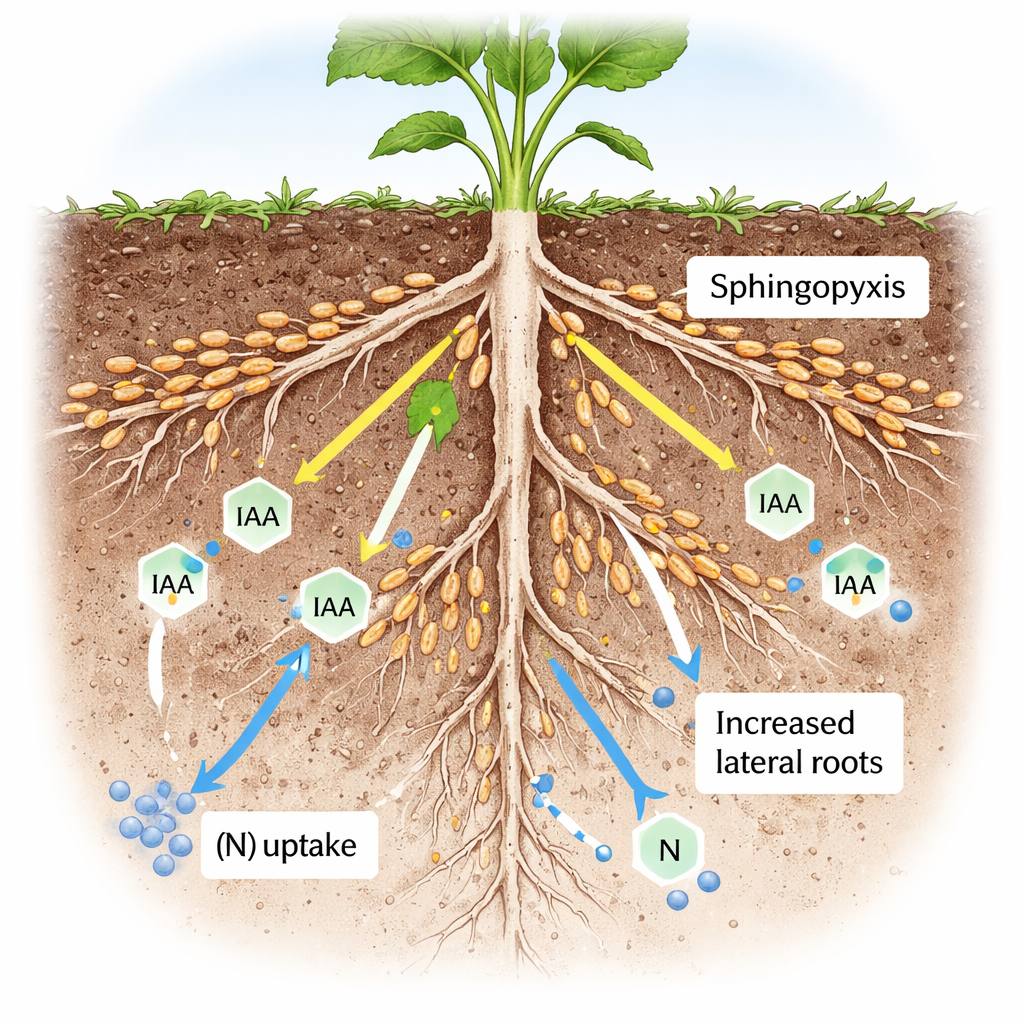
Como um microbe molda raízes de dentro
Aprofundando-se, os cientistas examinaram a química das raízes colonizadas por Sphingopyxis. Eles encontraram mudanças em muitas pequenas moléculas, incluindo aquelas ligadas ao hormônio vegetal auxina, um regulador mestre do ramificação radicular. Em testes de laboratório, a bactéria produziu auxina quando fornecida com blocos de construção simples. Microscopia usando plantas repórter fluorescentes mostrou que Sphingopyxis alterou a sinalização de auxina em ramos radiculares em desenvolvimento. Plantas com versões normais de dois genes específicos responderam fortemente à bactéria, crescendo mais raízes e biomassa. Plantas mutantes sem esses genes perderam grande parte do benefício de crescimento, ligando os efeitos de Sphingopyxis diretamente ao próprio sistema de controle genético da planta.
De parcerias ocultas a cultivos mais inteligentes
No conjunto, o estudo revela que plantas de canola usam seus genes não apenas para construir raízes, mas também para recrutar bactérias específicas que ajudam essas raízes a explorar o solo e capturar nitrogênio de forma mais eficaz. Para leigos, a mensagem-chave é que o melhoramento de culturas no futuro pode não se concentrar apenas na planta, mas em equipes planta–microbio ajustadas para trabalharem juntas. Ao selecionar variedades que atraem parceiros benéficos como Sphingopyxis, os agricultores poderiam um dia cultivar culturas de alto rendimento com menos fertilizante, reduzindo custos e danos ambientais enquanto mantêm colheitas fortes.
Citação: Li, N., Li, G., Huang, X. et al. Large-scale multi-omics unveils host–microbiome interactions driving root development and nitrogen acquisition. Nat. Plants 12, 319–336 (2026). https://doi.org/10.1038/s41477-025-02210-7
Palavras-chave: microbioma de plantas, desenvolvimento radicular, absorção de nitrogênio, canola, bactérias benéficas