Clear Sky Science · pt
A N-acetiltransferase B associada ao ribossomo coordena a proteostase global e a autofagia em plantas ao criar Ac/N-degrons
Como as plantas mantêm o equilíbrio de suas proteínas
Cada célula de uma planta está repleta de proteínas que devem ser constantemente sintetizadas, reparadas e removidas. Quando esse ato de equilíbrio falha, o crescimento desacelera e o estresse pode se tornar letal. Este estudo revela como uma pequena marca química colocada no início de muitas proteínas ajuda as plantas a decidir quais proteínas reciclar rapidamente e com que intensidade ativar um processo interno de limpeza chamado autofagia. Entender esse sistema de controle explica como as plantas sobrevivem por longos períodos sem luz ou nutrientes e pode, no futuro, ajudar a criar culturas que suportem melhor condições adversas.
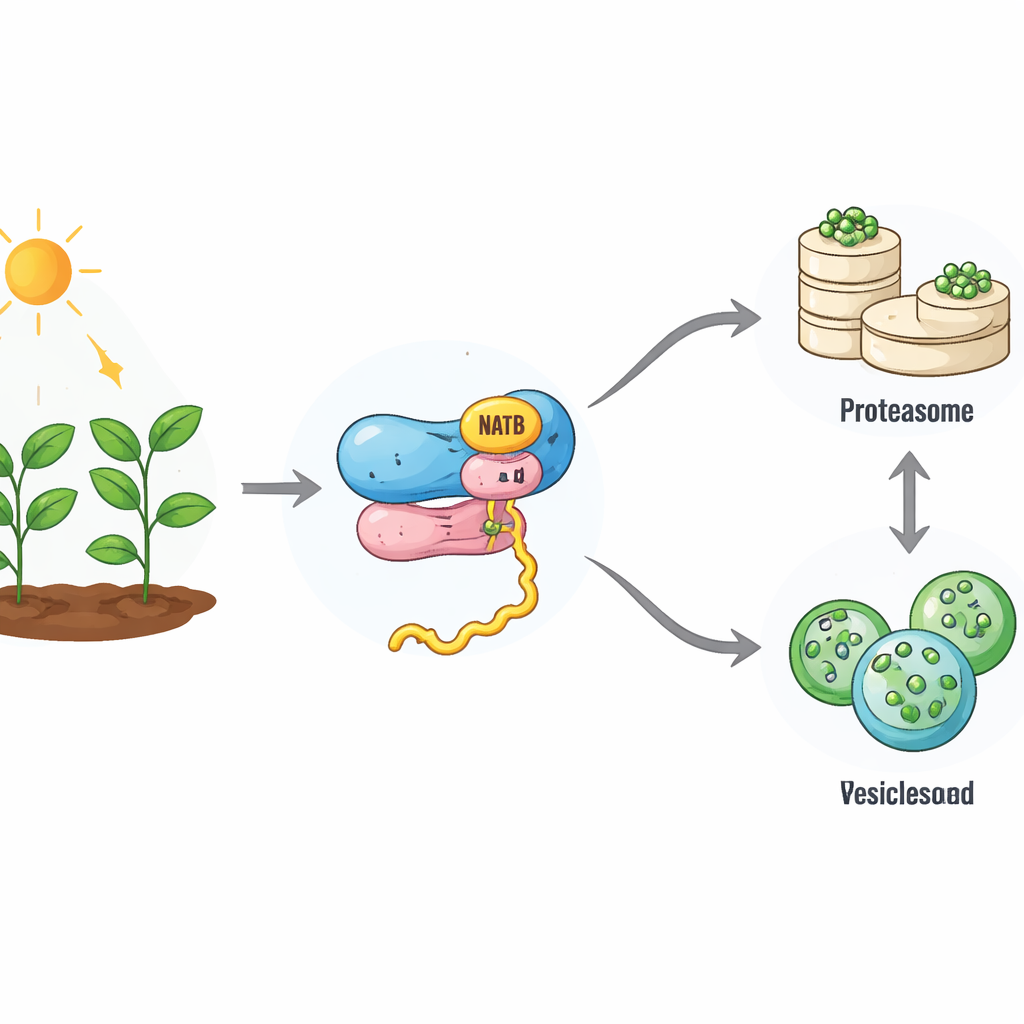
Uma pequena marca com grandes consequências
À medida que novas proteínas são produzidas nos ribossomos, elas podem receber um “tampão” químico em sua extremidade inicial. Em plantas, um complexo enzimático ligado ao ribossomo chamado NatB adiciona esse tampão a cerca de um quinto de todas as proteínas. Até agora, os cientistas não compreendiam totalmente o que essa marca generalizada significa para o destino dessas proteínas. Ao usar edição gênica por CRISPR para desligar a parte catalítica do NatB em Arabidopsis, os autores criaram plantas que em grande parte carecem dessa modificação nos alvos habituais do NatB. Surpreendentemente, essas plantas eram atrofiadas, mas sobreviveram, ao contrário de animais deficientes em NatB, sugerindo que células vegetais podem compensar parcialmente a perda. Ainda assim, muitas proteínas que normalmente carregam a marca NatB ficaram apenas parcialmente ou nada modificadas, oferecendo uma janela para entender como esse sistema funciona.
Turnover proteico mais lento e uma mudança no sistema de reciclagem celular
Quando a equipe mediu com que rapidez as proteínas são degradadas, constatou que plantas deficientes em NatB apresentam uma maquinaria de reciclagem celular mais lenta. A principal via de destruição de proteínas, o sistema ubiquitina–proteassoma, funcionou com menos eficiência: sua atividade diminuiu e proteínas direcionadas a essa via exibiram menos das habituais marcas de “destrua-me”. Ao mesmo tempo, a taxa geral de produção de novas proteínas também caiu. Levantamentos detalhados de proteínas mostraram que muitas proteínas dependentes do NatB tornaram-se mais estáveis e se acumularam na célula, indicando que a marca do NatB normalmente ajuda a converter algumas proteínas em componentes de curta duração. Ainda assim, nem todos os alvos do NatB se comportaram dessa forma, apontando para um efeito mais seletivo moldado pela sequência e contexto de cada proteína.
A autofagia entra em cena como plano de contingência
O estudo revelou que, à medida que a via do proteassoma desacelera, outra via de reciclagem aumenta sua atividade. Esse segundo sistema, a autofagia, envolve porções da célula em bolhas de membrana que são encaminhadas a um compartimento onde o conteúdo é degradado e reutilizado. Plantas deficientes em NatB mostraram níveis mais altos de proteínas centrais da autofagia e um fluxo maior de material por essa via, especialmente durante o escuro, quando a energia é escassa. Plantas sem NatB sobreviveram muito mais tempo em períodos prolongados de escuridão ou sob privação de nitrogênio e enxofre do que plantas normais, mas essa vantagem desapareceu quando genes de autofagia foram desativados. Isso indica que a autofagia reforçada ajuda a compensar o enfraquecimento do sistema do proteassoma, evitando o colapso da economia proteica da célula.
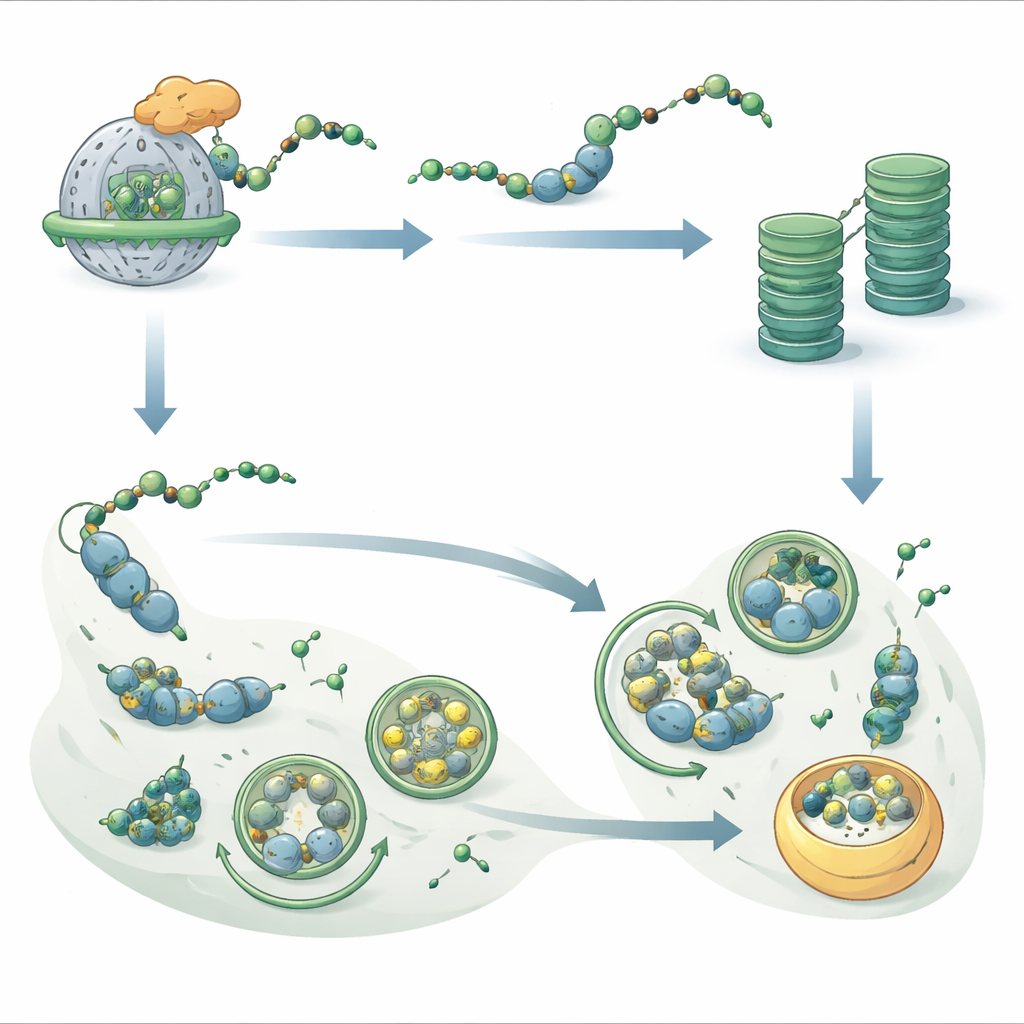
Um sensor chave de energia no centro da mudança
Para entender o que desloca o equilíbrio do uso do proteassoma para a autofagia, os autores focaram em um complexo sensor de energia chamado SnRK1. Duas subunidades intimamente relacionadas, KIN10 e KIN11, começam com sequências que as tornam prováveis clientes do NatB. Os pesquisadores demonstraram que o NatB pode marcar essas proteínas diretamente em ensaios de tubo de ensaio. Em plantas sem NatB, apenas KIN11 se acumulou fortemente, e sua forma ativa fosforilada foi mais abundante. O acompanhamento cuidadoso da degradação proteica revelou que quando KIN11 carrega a marca do NatB, ela é mais prontamente sinalizada para destruição pelo proteassoma, enquanto KIN11 sem marca persiste. Plantas que careciam tanto de NatB quanto de KIN11 perderam sua resistência extra ao estresse por escuridão, enquanto plantas modificadas para superproduzir apenas KIN11 tornaram-se mais tolerantes a períodos prolongados de escuridão. Essas descobertas apontam KIN11 como um mensageiro crucial que, quando estabilizado, empurra a célula a favorecer a autofagia e a conservação de energia.
O que isso significa para a sobrevivência das plantas
Em termos simples, o NatB escreve uma marca removível de “usar e descartar” em proteínas específicas, incluindo o sensor de energia KIN11. Quando o NatB está ativo, KIN11 é mantido sob controle, o turnover proteico via proteassoma é rápido e as plantas crescem rapidamente em condições favoráveis. Quando a atividade do NatB é perdida ou reduzida, KIN11 escapa da destruição rápida, a autofagia é aumentada e as plantas entram em um modo de sobrevivência que conserva recursos e lida melhor com longos períodos de escuridão ou nutrição pobre. Este trabalho revela o NatB como um coordenador central entre dois grandes sistemas de reciclagem nas células vegetais e explica como uma marca química sutil no começo de uma proteína pode inclinar a balança entre crescimento e resistência.
Citação: Gong, X., Pożoga, M., Boyer, JB. et al. The ribosome-associated N-terminal acetyltransferase B coordinates global proteostasis and autophagy in plants by creating Ac/N-degrons. Nat Commun 17, 3116 (2026). https://doi.org/10.1038/s41467-026-71208-2
Palavras-chave: controle de qualidade de proteínas, autofagia, tolerância ao estresse em plantas, modificação pós-traducional, degradação de proteínas