Clear Sky Science · pt
TONSL suprime duplicações em tandem dependentes da polimerase theta por meio de reparo guiado pela cromatina
Quando o DNA Faz Cópias Extras Perigosas
Cada célula precisa copiar seu DNA com precisão extraordinária, mas nossos genomas ainda são alvo de danos que podem rearranjar cromossomos. Uma alteração especialmente importante é a “duplicação em tandem”, em que um trecho de DNA é copiado e colado logo ao lado de sua localização original. Essas cópias extras podem favorecer a evolução ao fornecer novo material gênico, mas no câncer costumam impulsionar o crescimento descontrolado. Este estudo revela como uma proteína chamada TONSL ajuda as células a evitar essas duplicações arriscadas, mostrando uma salvaguarda oculta que parece ser compartilhada por animais e plantas. 
Cópias Extras: Úteis para a Evolução, Arriscadas para a Saúde
Grandes repetições de DNA consecutivas, conhecidas como duplicações em tandem, estão entre as mudanças estruturais mais comuns em genomas complexos. Elas podem dobrar genes inteiros, às vezes permitindo que novas funções evoluam ao longo de escalas de tempo extensas. Ainda assim, ao examinar tecidos saudáveis, os cientistas encontram pouquíssimas duplicações em tandem recentes, o que sugere que as células as previnem ativamente. Em muitos cânceres, porém, essas duplicações são abundantes, remodelando o genoma em grande escala. O mistério era como células normais normalmente reparam quebras de DNA sem criar acidentalmente segmentos copiados tão grandes.
Encontrando um Guardião Genômico Oculto
Para buscar protetores naturais contra esses eventos de duplicação, os pesquisadores recorreram ao minúsculo verme redondo Caenorhabditis elegans, que pode ser criado e sequenciado em grande número. Ao reanalisar uma coleção de cerca de 2.000 linhagens de vermes mutagenizados, eles identificaram um punhado com números inesperadamente altos de duplicações em tandem. Um fio condutor entre essas linhagens era o dano em um único gene, chamado tnsl-1, que codifica a proteína TONSL. Quando a equipe intencionalmente nocauteou esse gene e propagou os vermes por muitas gerações, seus genomas acumularam duplicações em tandem a um ritmo constante, aproximadamente uma por geração, espalhadas por todos os cromossomos. Surpreendentemente, os animais permaneceram em grande parte saudáveis, revelando que um genoma pode acumular silenciosamente muitas duplicações grandes sem colapsar imediatamente.
Células Rápidas Fazem Duplicações Pequenas, Células Lentas Fazem as Grandes
Uma inspeção mais próxima mostrou que as novas duplicações surgiram em dois intervalos principais de tamanho: um grupo em torno de dezenas de milhares de pares de bases e outro em torno de algumas centenas de milhares. A equipe suspeitou que o ritmo da divisão celular poderia moldar o tamanho de uma duplicação. Embriões de verme se dividem muito rápido, com ciclos celulares durando cerca de 20 minutos, enquanto as células germinativas que dão origem a óvulos e espermatozoides se dividem muito mais lentamente. Usando cruzamentos genéticos cuidadosamente desenhados e sequenciamento do genoma completo dos descendentes, os pesquisadores conseguiram cronometrar quando as duplicações surgiram. Eles descobriram que duplicações pequenas se formaram durante divisões embrionárias rápidas e iniciais, enquanto as grandes se originaram mais tarde, na linhagem germinativa de ciclo lento. Isso apontou para um modelo em que o tempo disponível para reparo e cópia do DNA determina até onde um processo de cópia impulsionado por quebras pode avançar antes de ser interrompido.
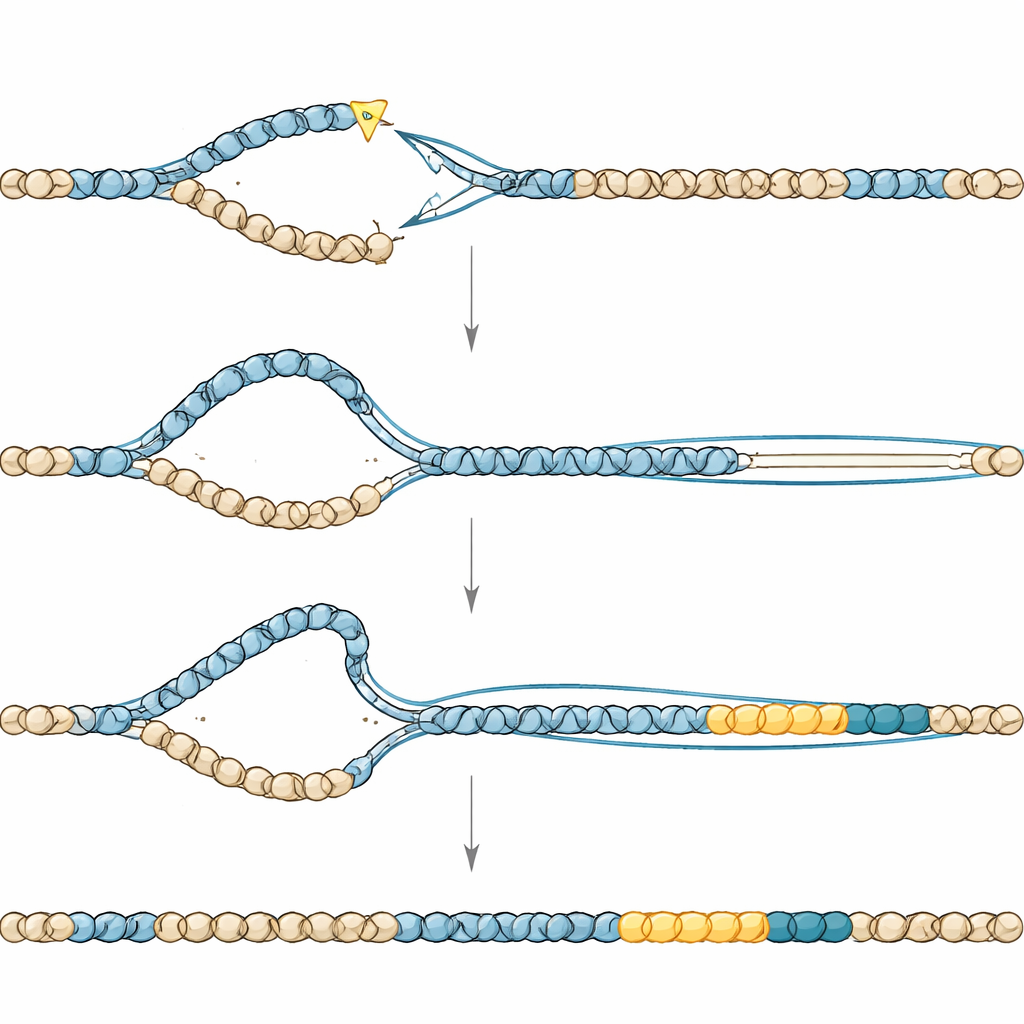
Como o Maquinário de Reparo Defeituoso Constrói Duplicações
As junções onde os segmentos duplicados se uniam ao DNA original traziam as impressões digitais de uma via de reparo especializada e propensa a erros chamada junção de extremidades mediada pela polimerase theta. Quando a enzima-chave dessa via foi desativada, as duplicações praticamente desapareceram, mas os vermes pagaram um preço alto em fertilidade, implicando que essa mesma via também é necessária para resgatar cromossomos quebrados quando TONSL está ausente. Outros experimentos apontaram para um segundo ator, um processo semelhante à “replicação induzida por quebras”, no qual uma extremidade de DNA quebrada usa um molde intacto para copiar longos trechos de sequência. A remoção de uma helicase que promove essa cópia de longa distância reduziu o tamanho das duplicações sem impedi-las, reforçando a ideia de que síntese de DNA prolongada e mal controlada está por trás desses eventos.
A Cromatina como Diretora Silenciosa do Reparo
Sabese que TONSL se liga a marcas químicas específicas nas proteínas de empacotamento do DNA recém-replicado, sugerindo que ajuda a reconstruir a cromatina — a estrutura que envolve e organiza o DNA — logo após a cópia. Os autores introduziram uma alteração sutil na proteína do verme que enfraquece essa ligação à cromatina. Vermes portadores dessa troca de um único aminoácido ainda formaram duplicações, mas em número e tamanho menores, indicando que a aderência de TONSL à cromatina recém-formada restringe diretamente a síntese de DNA descontrolada em locais de reparo. Na sua ausência, intermediários de reparo podem se estender demais antes de serem finalmente costurados pela via de junção propensa a erros, deixando para trás um bloco duplicado em vez de um conserto limpo.
Uma Defesa Compartilhada de Vermes a Plantas
Para testar se esse papel protetor é conservado em outras espécies, a equipe examinou um mutante da planta modelo Arabidopsis thaliana que carecia da proteína relacionada TONSOKU. Após apenas algumas gerações, essas plantas acumularam um número notável de grandes duplicações em tandem, somando aproximadamente um aumento de um por cento no tamanho do genoma por geração — uma mudança enorme em escalas evolutivas. As junções do DNA novamente apresentaram os curtos solapamentos e inserções característicos da mesma via de reparo propensa a erros, sugerindo que vermes e plantas utilizam um sistema guiado pela cromatina profundamente conservado para afastar quebras associadas à replicação de resultados propensos a duplicações.
O Que Isso Significa para o Câncer e a Estabilidade Genômica
Em termos simples, este trabalho mostra que TONSL e seu equivalente em plantas atuam como controladores de qualidade que ficam no cruzamento entre a cópia do DNA e o reparo. Ao ajudar a reconstruir a cromatina corretamente após uma quebra, eles mantêm os processos de reparo curtos e organizados, impedindo que longos trechos de DNA sejam copiados duas vezes seguidas. Sem esse controle, as células ainda reparan as quebras, mas o fazem estendendo demais a síntese e depois reatravessando o DNA de forma grosseira, deixando duplicações em tandem. Como padrões de duplicação semelhantes são observados em vários cânceres humanos, incluindo tumores com defeitos em fatores associados à replicação, entender o papel de TONSL pode, eventualmente, ajudar a explicar por que certos cânceres adquirem genomas tão profundamente remodelados e sugerir novas maneiras de prever ou influenciar como seu DNA evoluirá sob terapia.
Citação: van Schendel, R., Romeijn, R., Kralemann, L.E.M. et al. TONSL suppresses polymerase theta-dependent tandem duplications through chromatin-guided repair. Nat Commun 17, 2875 (2026). https://doi.org/10.1038/s41467-026-70905-2
Palavras-chave: estabilidade genômica, duplicações em tandem, reparo de DNA, cromatina, TONSL