Clear Sky Science · pt
SMART: agregação multiómica espacial usando redes neurais gráficas e aprendizado métrico
Vendo Tecidos como Mapas de Vizinhança
Nossos corpos são formados por vizinhanças celulares dinâmicas, onde genes, proteínas e a organização do DNA atuam juntos em locais precisos. Novos microscópios e ferramentas de sequenciamento conseguem agora ler muitas dessas camadas moleculares diretamente em cortes finos de tecido, mas transformar esse fluxo de dados espaciais e multicamadas em imagens claras sobre como os órgãos estão organizados é um enorme desafio computacional. Este estudo apresenta o SMART, um método computacional que ajuda cientistas a fundir esses sinais complexos em mapas detalhados de onde diferentes comunidades celulares vivem e como estão dispostas.
Por que Mapear Vizinhanças Celulares é Difícil
Tecnologias modernas de “multiómica espacial” podem medir vários tipos de informação molecular ao mesmo tempo — como RNA, proteínas de superfície celular e quão acessível está o cromatina — mantendo a posição exata de cada medida em um corte de tecido. Cada tipo, ou “ômica”, oferece uma visão diferente do comportamento celular, mas são dados ruidosos, de alta dimensionalidade e que não se alinham naturalmente entre si. Além disso, células do mesmo tipo nem sempre ficam agrupadas; podem aparecer como ilhas dispersas ao longo de um órgão. Ferramentas existentes frequentemente ignoram o arranjo espacial, simplificam demais como as diferentes ômicas se relacionam ou têm dificuldade em escalar para os conjuntos de dados muito grandes que os novos instrumentos podem gerar.
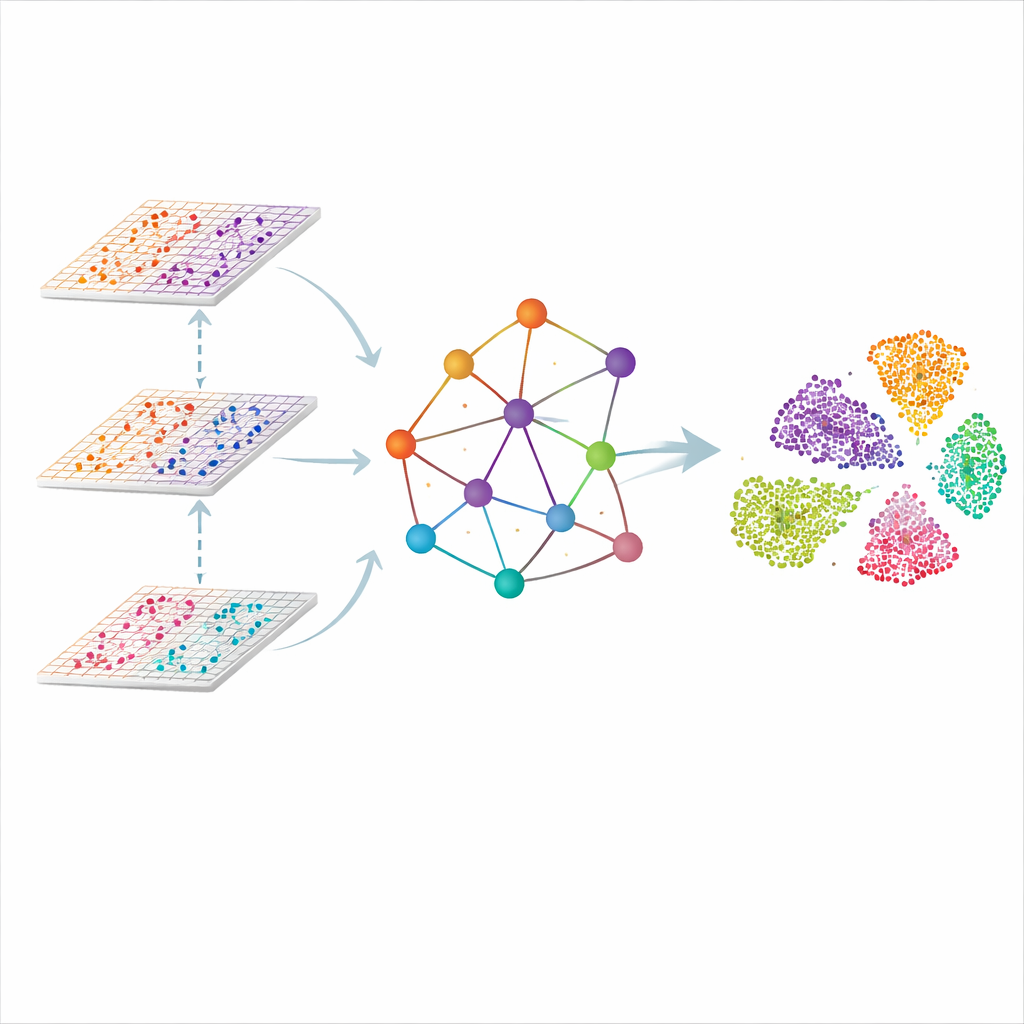
Um Grafo do Tecido, Não Apenas uma Lista de Células
O SMART aborda o problema tratando cada ponto de medição no tecido como um nó em uma rede. Pontos próximos são conectados para formar um grafo espacial, e os perfis moleculares de cada ômica são primeiro comprimidos em um conjunto menor de características coordenadas que capturam padrões gerais em vez de genes individuais. Um tipo de rede neural projetada para grafos então propaga informação ao longo das arestas, permitindo que cada ponto “escute” seus vizinhos enquanto mantém registro de como cada ômica contribui. O resultado é uma representação compartilhada e de baixa dimensionalidade na qual regiões semelhantes do tecido — como camadas distintas do cérebro ou zonas de um linfonodo — naturalmente se agrupam.
Ensinando ao Modelo o Que Deve Ser Similar
Seguir apenas os vizinhos físicos não é suficiente, porque células do mesmo tipo podem estar distantes. O SMART adiciona um segundo ingrediente emprestado de sistemas de reconhecimento facial: aprendizado métrico com tripletas. Para cada ponto, o método encontra automaticamente outro ponto com padrões moleculares muito semelhantes (um “positivo”) e um que é claramente diferente (um “negativo”). Em seguida, ajusta a representação interna para que positivos sejam puxados para mais perto e negativos empurrados para longe, mesmo que estejam distantes no corte tecidual. Essa disputa é executada junto com uma etapa de reconstrução que força o SMART a preservar os detalhes-chave de cada camada ômica, balanceando continuidade espacial com especificidade molecular.
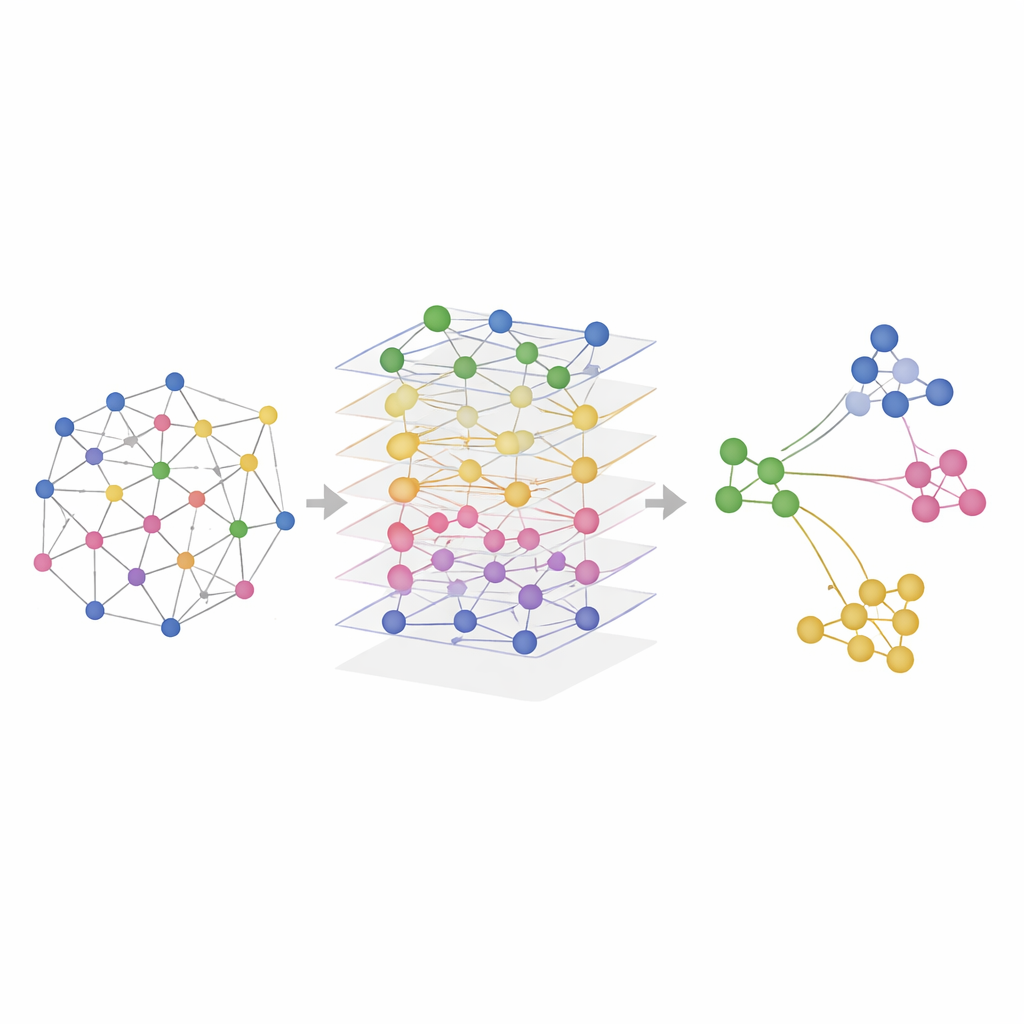
Testando o SMART em Tecidos Reais
Os pesquisadores testaram o SMART em dados simulados e em experimentos reais que mediram combinações de RNA, proteínas e acessibilidade de cromatina em cérebros de camundongo, baços de camundongo, linfonodos humanos e tonsilas. Em simulações controladas onde as regiões espaciais verdadeiras eram conhecidas, o SMART recuperou com maior precisão os padrões reais e manteve as relações presentes em cada camada ômica. Em conjuntos de dados reais, o SMART identificou de forma consistente estruturas anatômicas finas — como regiões cerebrais específicas ou zonas de células imunes em órgãos linfoides — com maior nitidez do que métodos concorrentes, ao mesmo tempo em que mantinha exigências computacionais baixas. Uma versão relacionada, chamada SMART‑MS, estende as mesmas ideias por múltiplas seções de tecido, alinhando cortes do mesmo órgão e corrigindo diferenças técnicas entre experimentos.
Mapas Rápidos para a Próxima Onda da Biologia Espacial
Em termos simples, o SMART é um motor de mapeamento para a próxima geração de atlas moleculares. Ao combinar modelagem em estilo de rede do arranjo tecidual com um senso embutido do que deve contar como “semelhante”, ele pode transformar coleções vastas e desordenadas de medidas multiómicas espaciais em mapas coerentes das vizinhanças dos órgãos. Isso permite que pesquisadores identifiquem mais facilmente onde determinados tipos celulares e microambientes residem, como eles mudam durante o desenvolvimento ou na doença, e como novas tecnologias experimentais se encaixam. À medida que os dados espaciais continuam a crescer em tamanho e complexidade, ferramentas como SMART e SMART‑MS serão fundamentais para transformar medições brutas em insight biológico.
Citação: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Palavras-chave: multiómica espacial, redes neurais gráficas, microambiente tecidual, integração de dados, biologia de célula única