Clear Sky Science · pt
Um único aglomerado de moléculas da RNA Polimerase II está associado de forma estável a genes ativos
Como as células ligam genes em explosões poderosas
Cada célula do seu corpo precisa decidir quais genes usar e quando, frequentemente ativando-os em rajadas curtas e intensas. Durante décadas, cientistas suspeitaram que as enzimas responsáveis por ler o DNA se reúnem em pequenos “pontos quentes” dentro do núcleo para potencializar esse processo, mas o funcionamento desses aglomerados tem sido controverso. Este estudo investiga embriões vivos da mosca-das-frutas com microscópios avançados e mostra que cada gene ativo está acompanhado por um único aglomerado estável da enzima que converte DNA em RNA, e que esses aglomerados se comportam mais como locais de trabalho congestionados do que como gotículas exóticas de matéria “separada por fase”.
Pequenas máquinas que leem o genoma
A enzima no centro desta história é a RNA Polimerase II, uma máquina molecular que desliza ao longo do DNA e copia genes em RNA, o primeiro passo para fabricar proteínas. Trabalhos anteriores pintaram imagens conflitantes: alguns experimentos sugeriam que moléculas de polimerase se agrupam em grandes “fábricas” duradouras que atendem vários genes ao mesmo tempo, enquanto outros viam apenas ajuntamentos efêmeros de poucas moléculas. Os autores se concentraram em um momento dramático do desenvolvimento precoce da mosca: a ativação do genoma zigótico, quando um embrião silencioso subitamente liga milhares de seus próprios genes. Essa onda natural de atividade forneceu um cenário ideal para observar em tempo real como as polimerases se movimentam, se agregam e interagem com os genes.
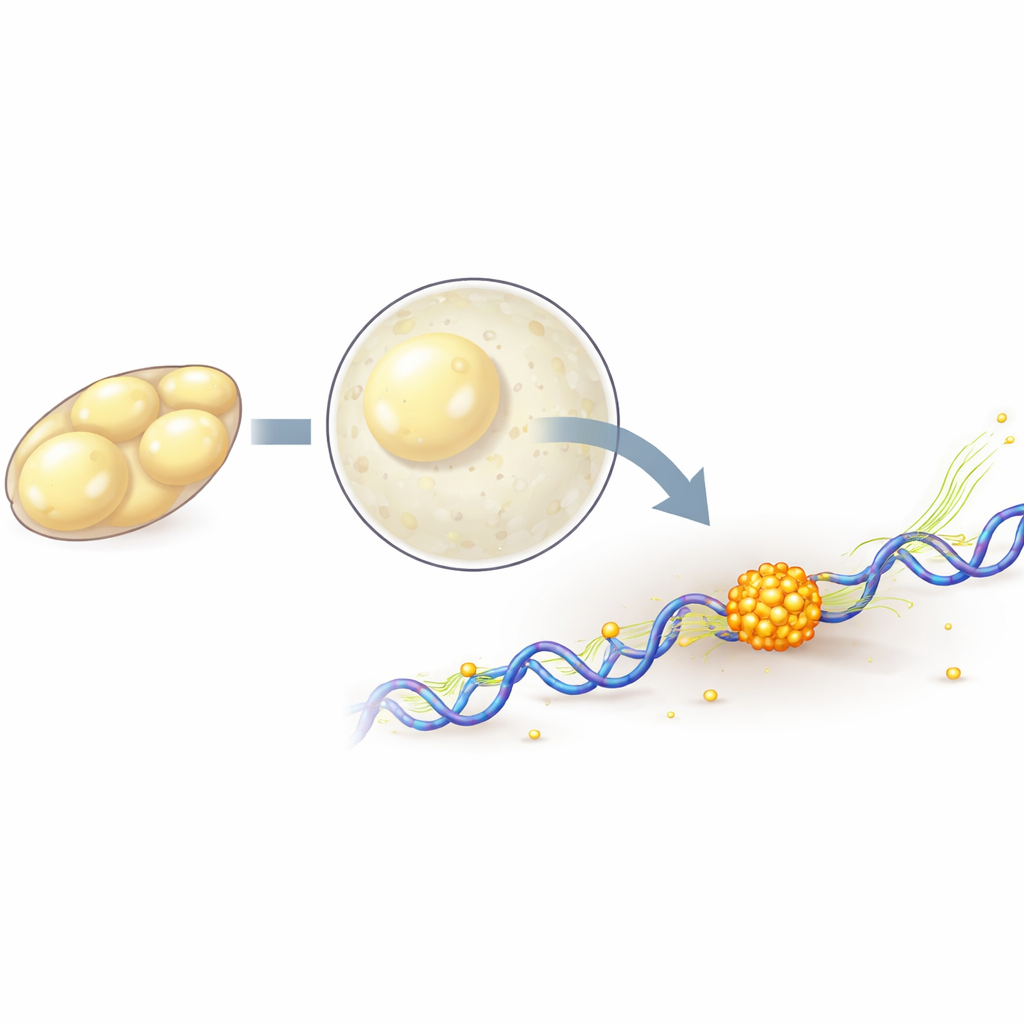
Observando moléculas únicas em um embrião vivo
Para seguir moléculas individuais de polimerase, a equipe marcou geneticamente um de seus componentes centrais com proteínas fluorescentes e usou microscopia de luz em lâmina reticulada (lattice light-sheet) e rastreamento de molécula única para registrar seus movimentos em 3D com alta velocidade e iluminação suave. Eles descobriram que, à medida que o embrião entra em sua fase principal de ativação, mais moléculas de polimerase ficam fortemente ligadas ao DNA, compatível com a ativação de mais genes. Bloqueando brevemente diferentes etapas do ciclo de transcrição com fármacos, puderam separar moléculas que estão apenas iniciando em um gene daquelas que estão ativamente se movendo ao longo dele. Essa análise mostrou que a formação de aglomerados depende dos passos iniciais de ativação gênica, enquanto a cópia ativa ao longo do gene tende a enfraquecer e encurtar os aglomerados.
Aglomerados que mudam de caráter conforme o desenvolvimento se desenrola
Imagens de núcleos inteiros ao longo do tempo revelaram dezenas de pequenos aglomerados de polimerase muito antes da onda de ativação em todo o genoma, com seu número e espaçamento mudando conforme as divisões nucleares diminuem. No início do desenvolvimento, muitos aglomerados persistem por quase tanto tempo quanto o intervalo entre divisões celulares, sugerindo que são dominados por polimerases em um estado inicial “preparado” que frequentemente falha em produzir moléculas completas de RNA. Mais tarde, quando a transcrição aumenta, os aglomerados tornam-se mais dinâmicos: suas durações deixam de acompanhar simplesmente o ciclo celular, e sua composição interna desloca-se em direção a polimerases que estão realmente elongando ao longo dos genes. Outras medições de como as moléculas se movem dentro e fora dos aglomerados indicam que, perto de genes ativos, as polimerases estão mais confinadas e são mais propensas a retornar aos mesmos sítios, apoiando a ideia de uma zona de trabalho localmente ocupada em vez de uma gotícula líquida frouxa.
Um aglomerado, um gene durante uma rajada
Para ligar aglomerados diretamente à produção gênica, os pesquisadores observaram genes repórter específicos que brilham onde novo RNA está sendo produzido, enquanto rastreavam simultaneamente a polimerase. Para vários genes diferentes, eles viram consistentemente apenas um aglomerado de polimerase em cada cópia ativa do gene durante uma rajada de transcrição. A intensidade do aglomerado aumentava e diminuía em sincronia com a quantidade de RNA nascente e, quando cópias irmãs duplicadas do gene podiam ser resolvidas, cada uma apresentava seu próprio aglomerado distinto em vez de compartilharem um único. Simulações por computador, ajustadas para corresponder às condições de imagem, mostraram que genes com forte recrutamento de polimerase formam aglomerados visíveis, enquanto genes mais fracos podem ainda recrutar polimerase, mas permanecerem muito tênues para serem detectados, explicando por que apenas uma minoria dos genes ativos mostra aglomerados claros no microscópio.
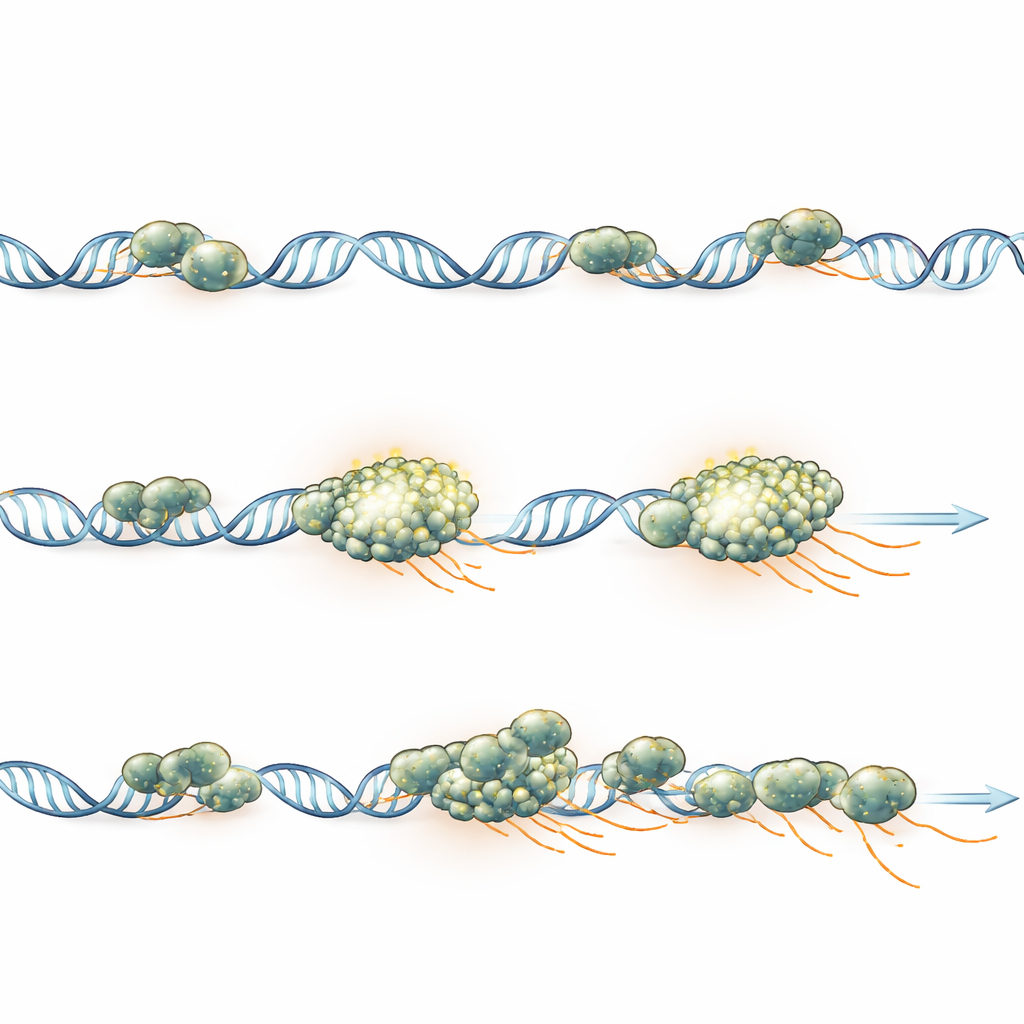
O que isso significa para o controle gênico
Este trabalho argumenta que, nesses embriões, os aglomerados de polimerase refletem principalmente quantas enzimas estão ativamente engajadas em um único gene, e não uma “fábrica” separada ou uma gotícula especial que precise se formar para permitir a transcrição. Um aglomerado aparece quando muitas polimerases são carregadas em rápida sucessão, permanece associada de forma estável a esse gene durante uma rajada de atividade e gradualmente se dispersa à medida que as polimerases terminam a cópia e partem. Para um leitor leigo, a mensagem principal é que a comutação gênica é organizada por centros focados, gene a gene: cada gene ativo reúne temporariamente sua própria equipe de máquinas de cópia, e o tamanho e a duração dessa equipe refletem diretamente o quão fortemente o gene está ativado.
Citação: Mukherjee, A., Kapoor, M., Shankta, K. et al. A single cluster of RNA Polymerase II molecules is stably associated with active genes. Nat Commun 17, 2580 (2026). https://doi.org/10.1038/s41467-026-70775-8
Palavras-chave: Agrupamento de RNA polimerase II, ativação do genoma zigótico, explosões de transcrição, regulação gênica em embriões, imagens de molécula única